peptides
spectra
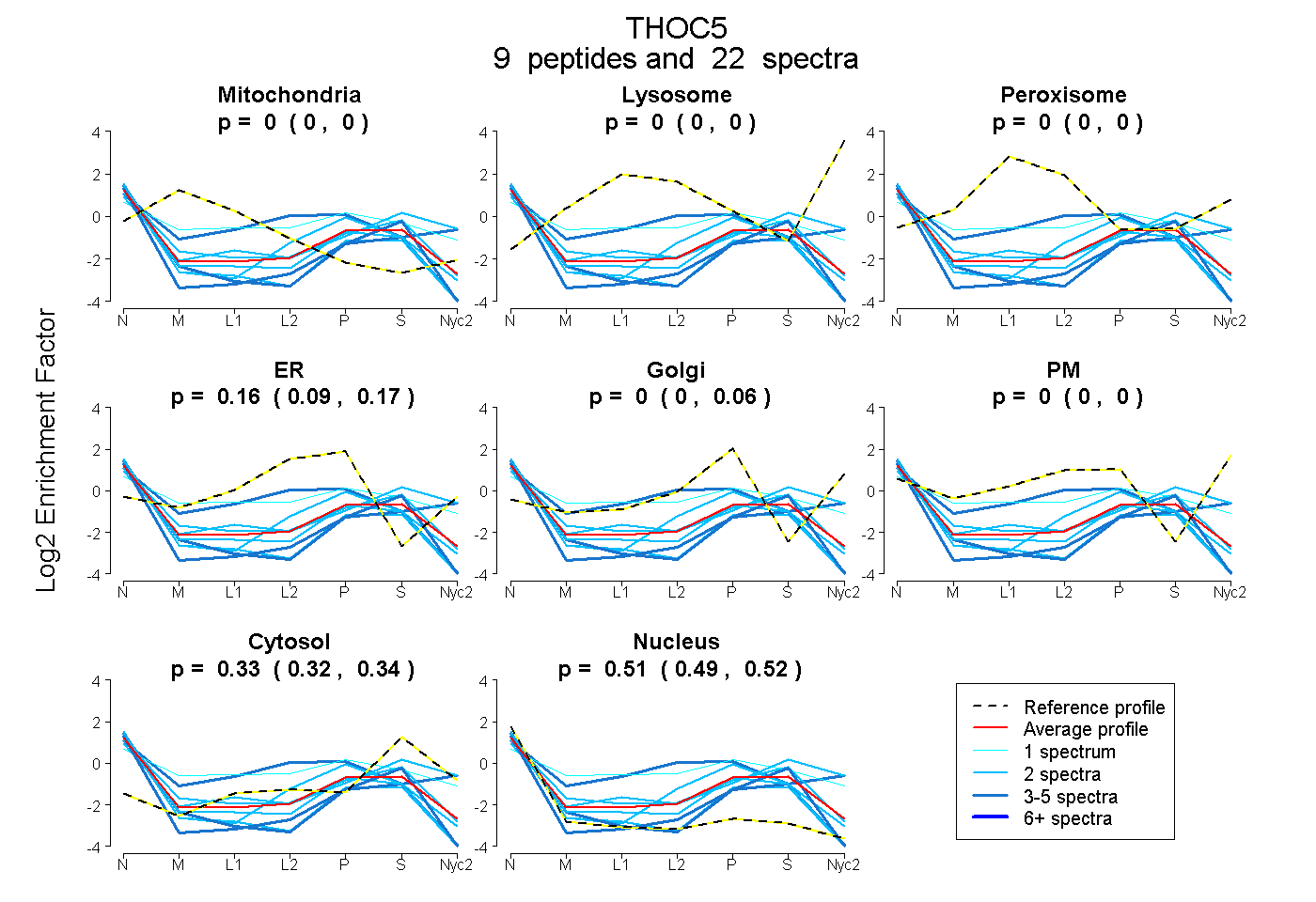
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.090 | 0.173
0.000 | 0.062
0.000 | 0.000
0.315 | 0.343
0.487 | 0.525
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.159 0.090 | 0.173 |
0.000 0.000 | 0.062 |
0.000 0.000 | 0.000 |
0.332 0.315 | 0.343 |
0.509 0.487 | 0.525 |
| 2 spectra, AMESEVNVCYR | 0.028 | 0.000 | 0.000 | 0.123 | 0.000 | 0.000 | 0.402 | 0.447 | ||
| 3 spectra, VGILTLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.316 | 0.684 | ||
| 4 spectra, AEITMGDPHQQTLAR | 0.000 | 0.000 | 0.119 | 0.152 | 0.000 | 0.330 | 0.181 | 0.218 | ||
| 2 spectra, HPLSVLLDLK | 0.000 | 0.000 | 0.000 | 0.237 | 0.000 | 0.000 | 0.216 | 0.547 | ||
| 2 spectra, TNSNDDNIR | 0.000 | 0.000 | 0.000 | 0.104 | 0.000 | 0.000 | 0.213 | 0.684 | ||
| 1 spectrum, LMAEIQDLK | 0.096 | 0.000 | 0.103 | 0.209 | 0.000 | 0.139 | 0.319 | 0.134 | ||
| 2 spectra, LDWELEQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.213 | 0.787 | ||
| 4 spectra, LGGLHFPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.224 | 0.776 | ||
| 2 spectra, TPNPANQYQFDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.200 | 0.535 | 0.266 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
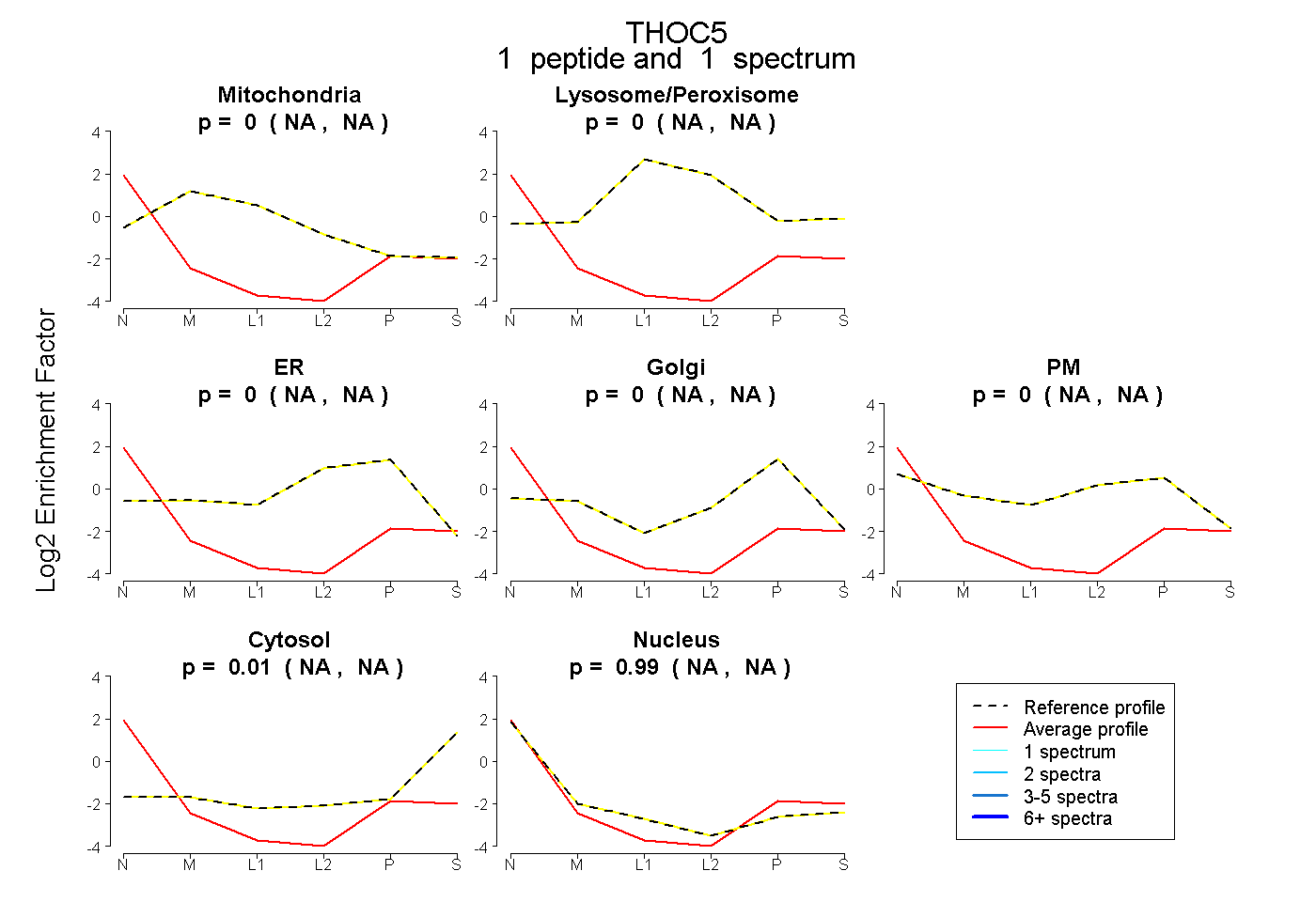 |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.005 NA | NA |
0.000 NA | NA |
0.009 NA | NA |
0.986 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptide |
3 spectra |
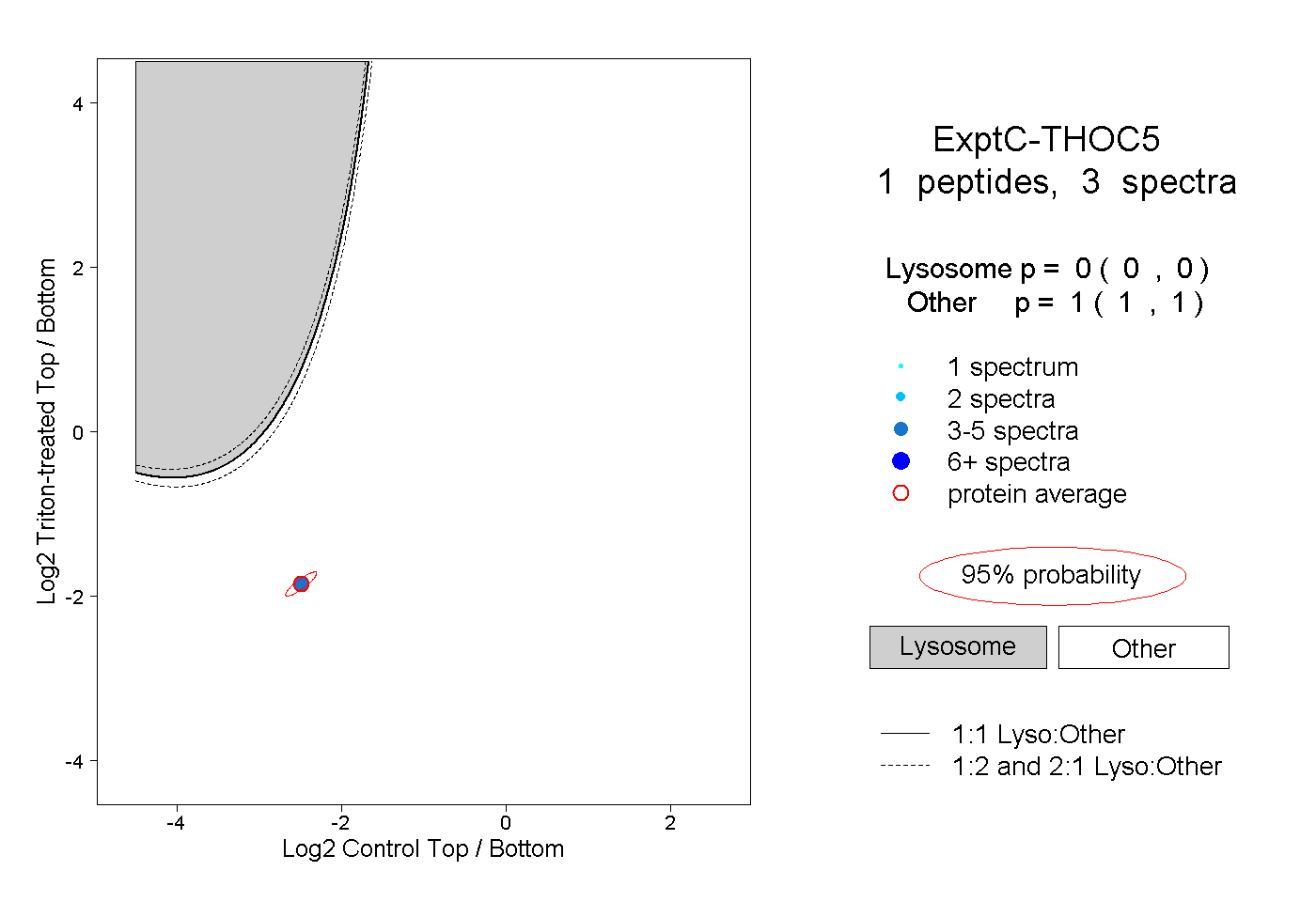 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |