peptides
spectra
0.000 | 0.000
0.033 | 0.096
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.898 | 0.959
0.000 | 0.000
0.000 | 0.000
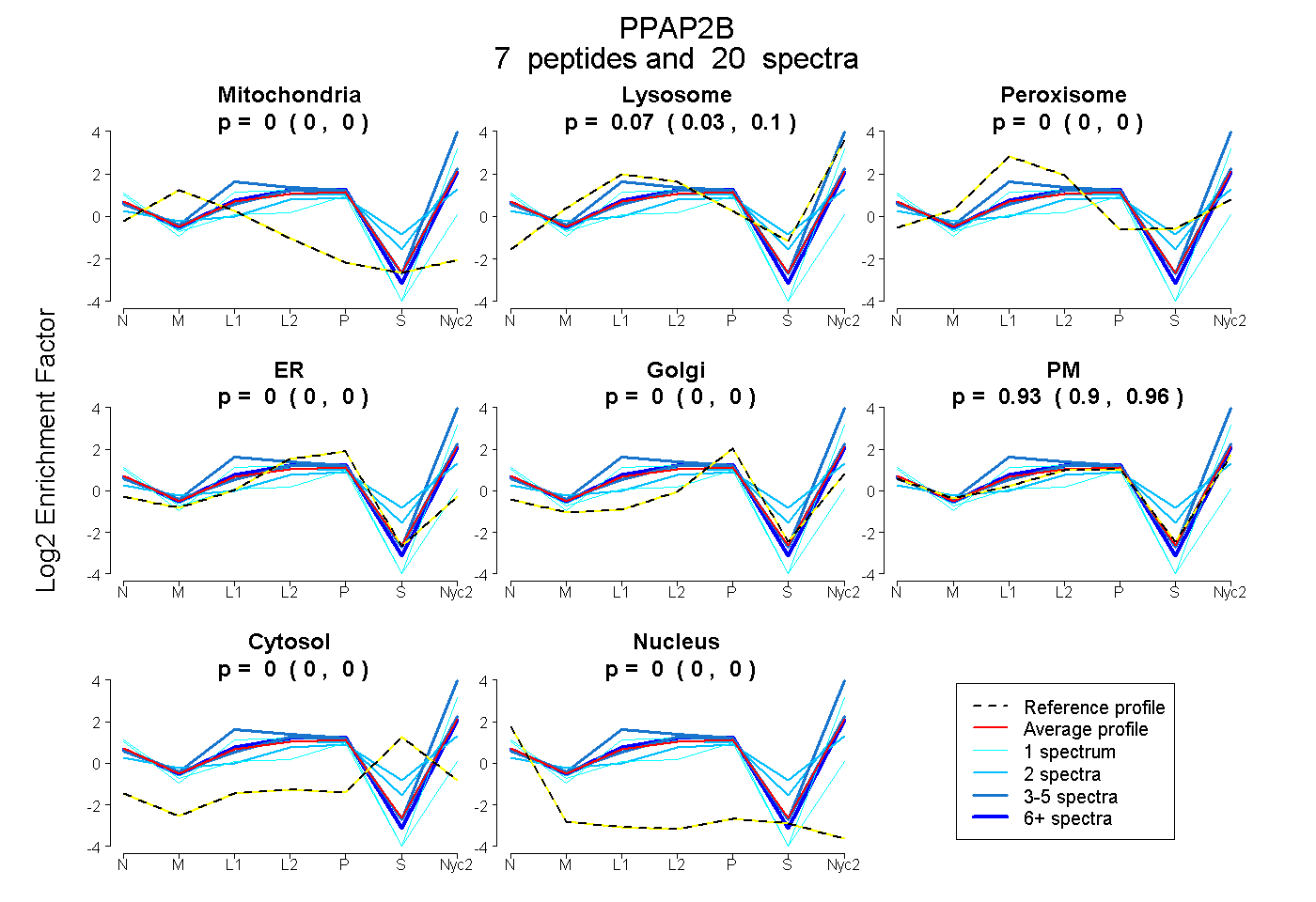
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
20 spectra |
 |
0.000 0.000 | 0.000 |
0.070 0.033 | 0.096 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.930 0.898 | 0.959 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 4 spectra, TTLSLPAPAIR | 0.000 | 0.082 | 0.000 | 0.000 | 0.000 | 0.918 | 0.000 | 0.000 | ||
| 7 spectra, EILSPVDIMDR | 0.000 | 0.032 | 0.000 | 0.000 | 0.000 | 0.968 | 0.000 | 0.000 | ||
| 2 spectra, NGGSPALNNNPR | 0.000 | 0.064 | 0.085 | 0.000 | 0.011 | 0.655 | 0.185 | 0.000 | ||
| 2 spectra, AIVPESK | 0.000 | 0.085 | 0.089 | 0.000 | 0.000 | 0.787 | 0.038 | 0.000 | ||
| 1 spectrum, STIQNPYVAALYK | 0.000 | 0.068 | 0.000 | 0.000 | 0.000 | 0.932 | 0.000 | 0.000 | ||
| 1 spectrum, QVGCFLFGCAISQSFTDIAK | 0.018 | 0.000 | 0.000 | 0.292 | 0.000 | 0.528 | 0.000 | 0.162 | ||
| 3 spectra, GFYCNDESIK | 0.000 | 0.447 | 0.000 | 0.000 | 0.000 | 0.553 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
2 spectra |
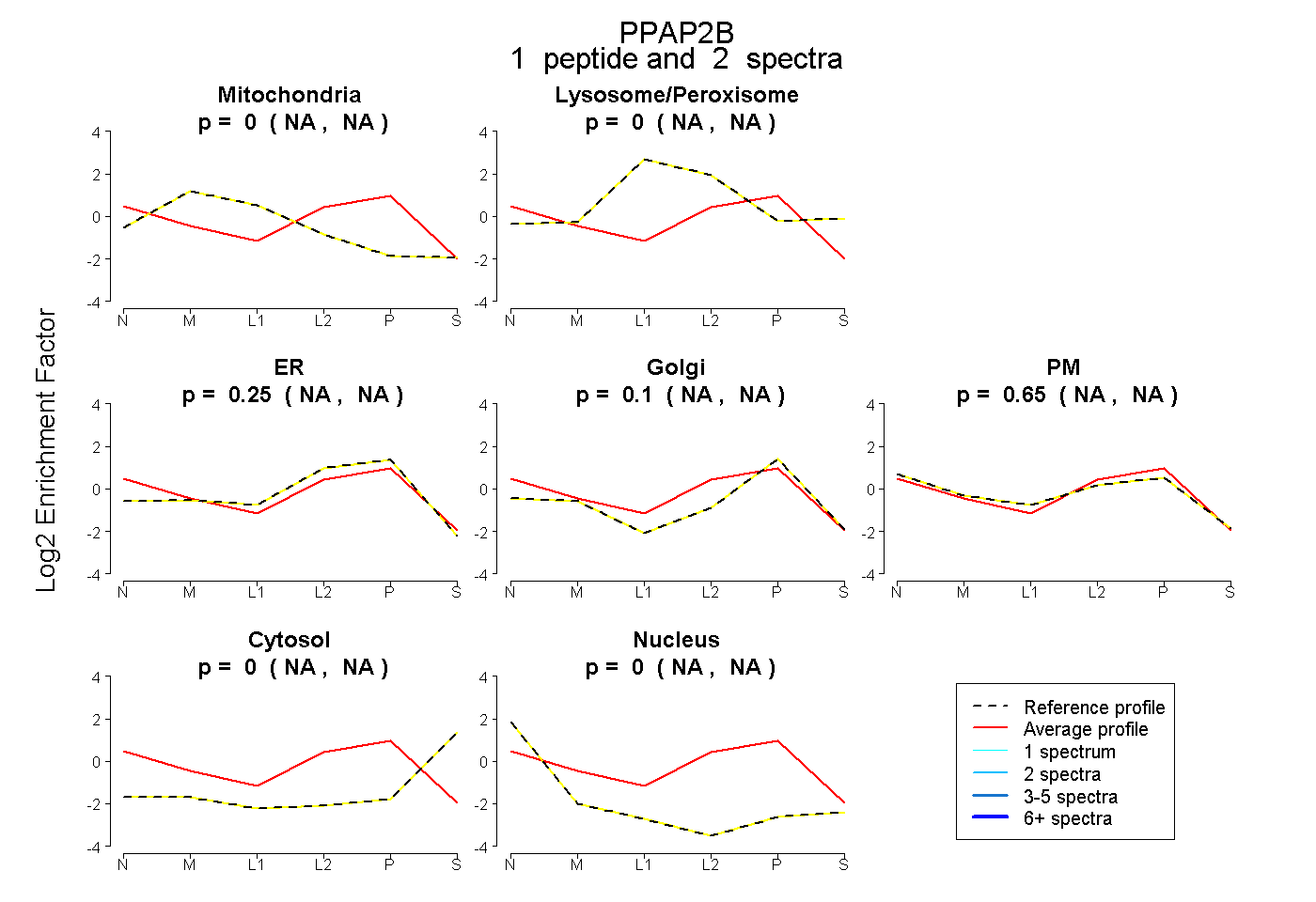 |
0.000 NA | NA |
0.000 NA | NA |
0.248 NA | NA |
0.103 NA | NA |
0.649 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
30 spectra |
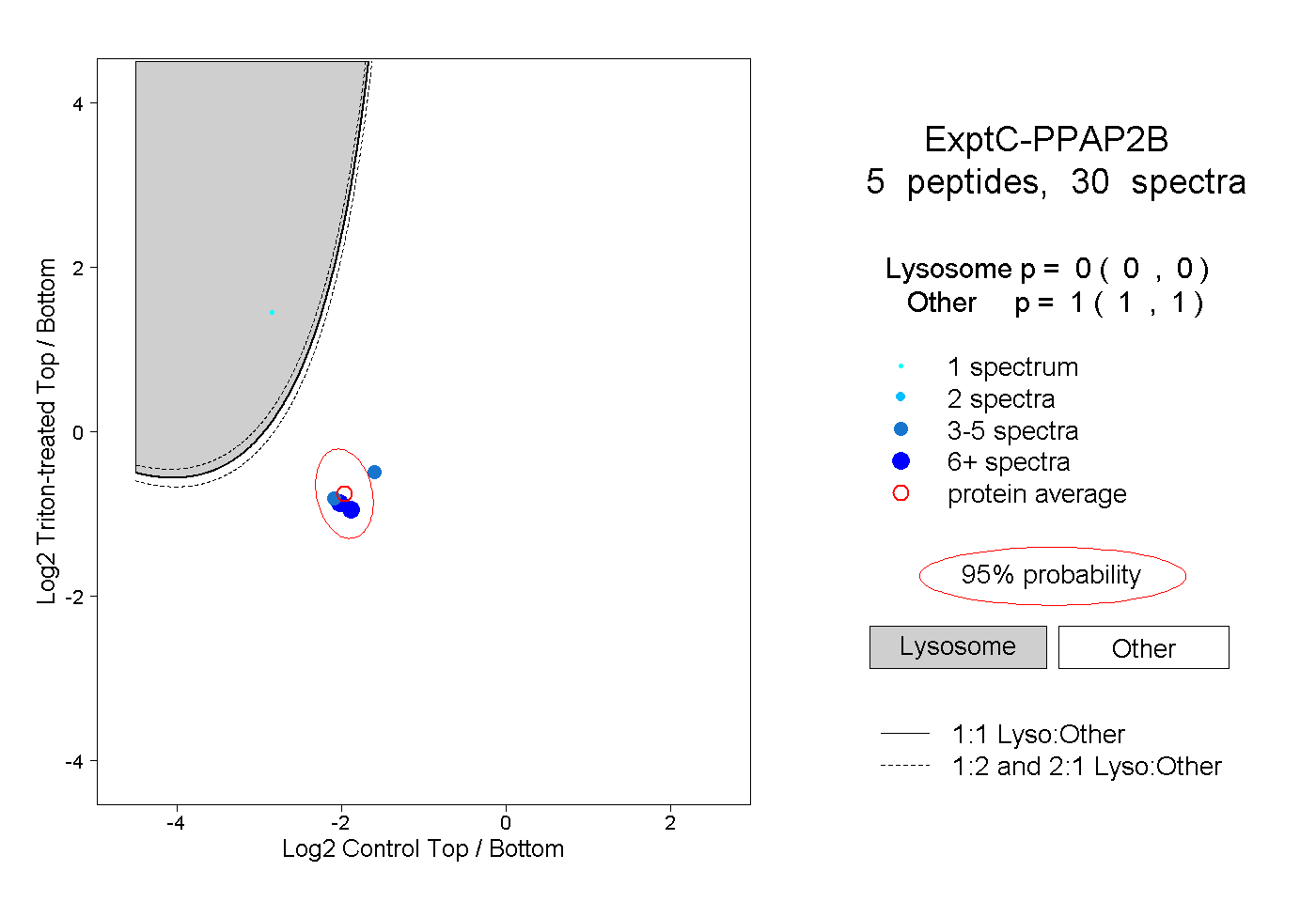 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
6 spectra |
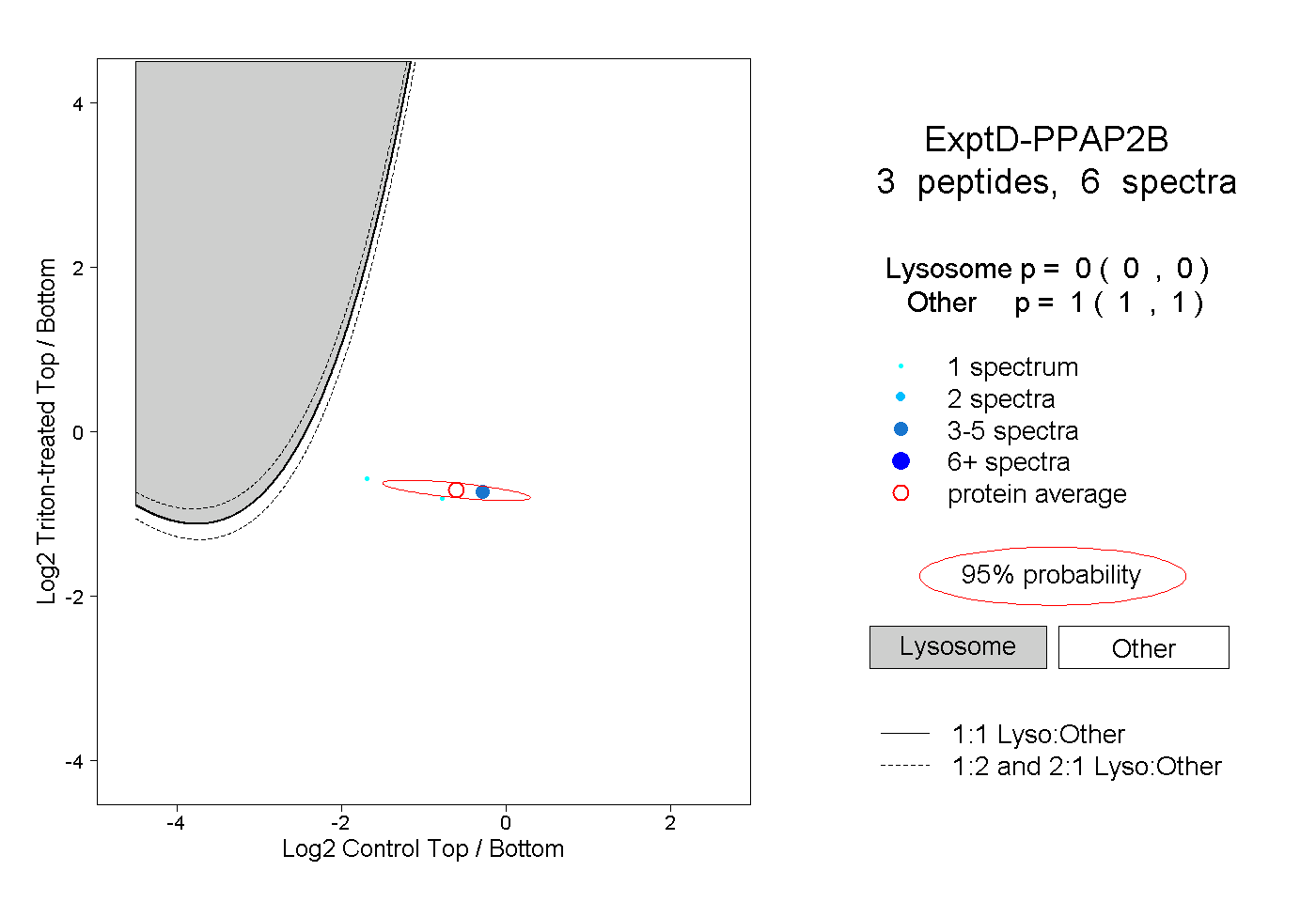 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |