peptides
spectra
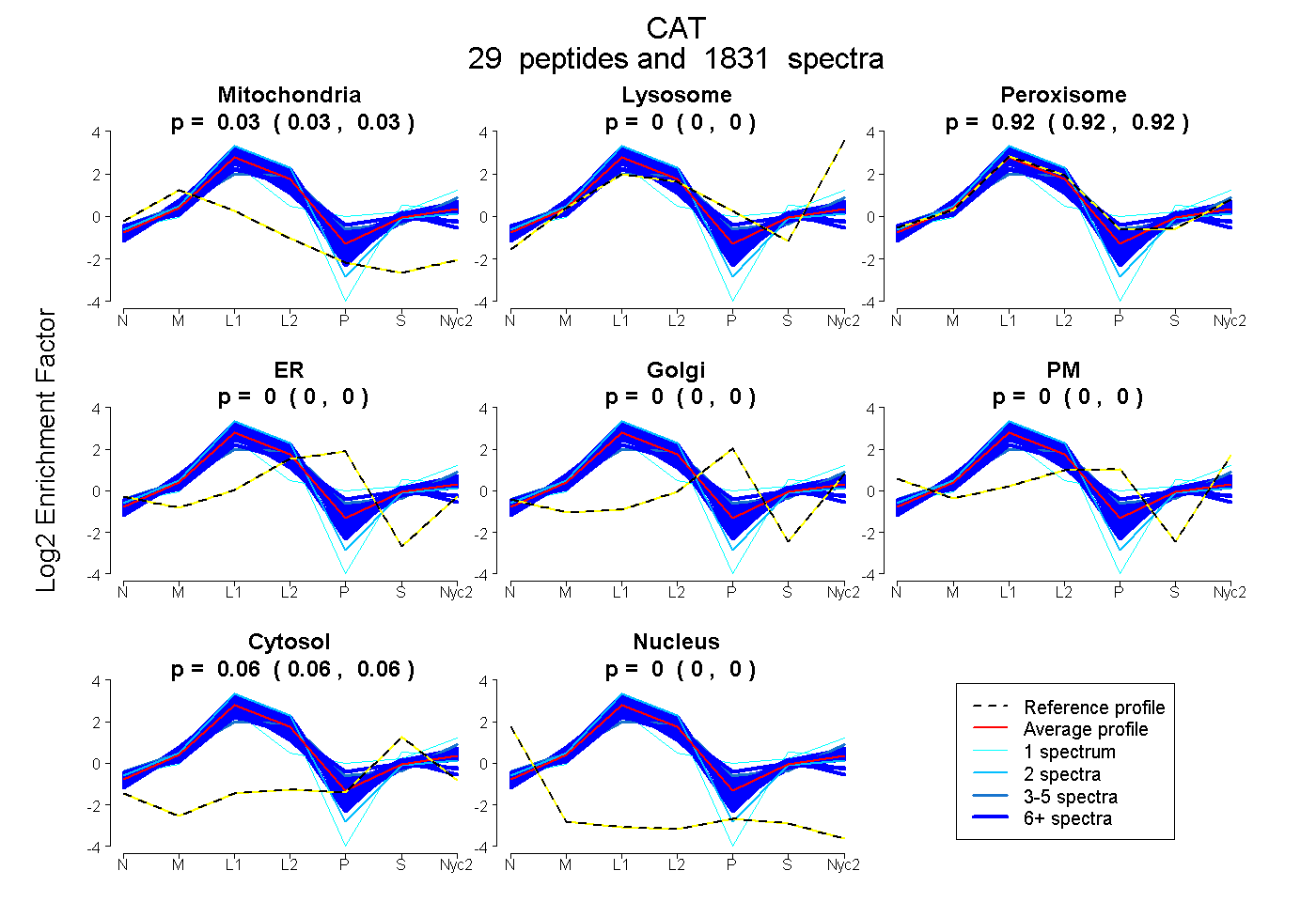
0.025 | 0.026
0.000 | 0.000
0.918 | 0.918
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.056 | 0.057
0.000 | 0.000
peptides
spectra
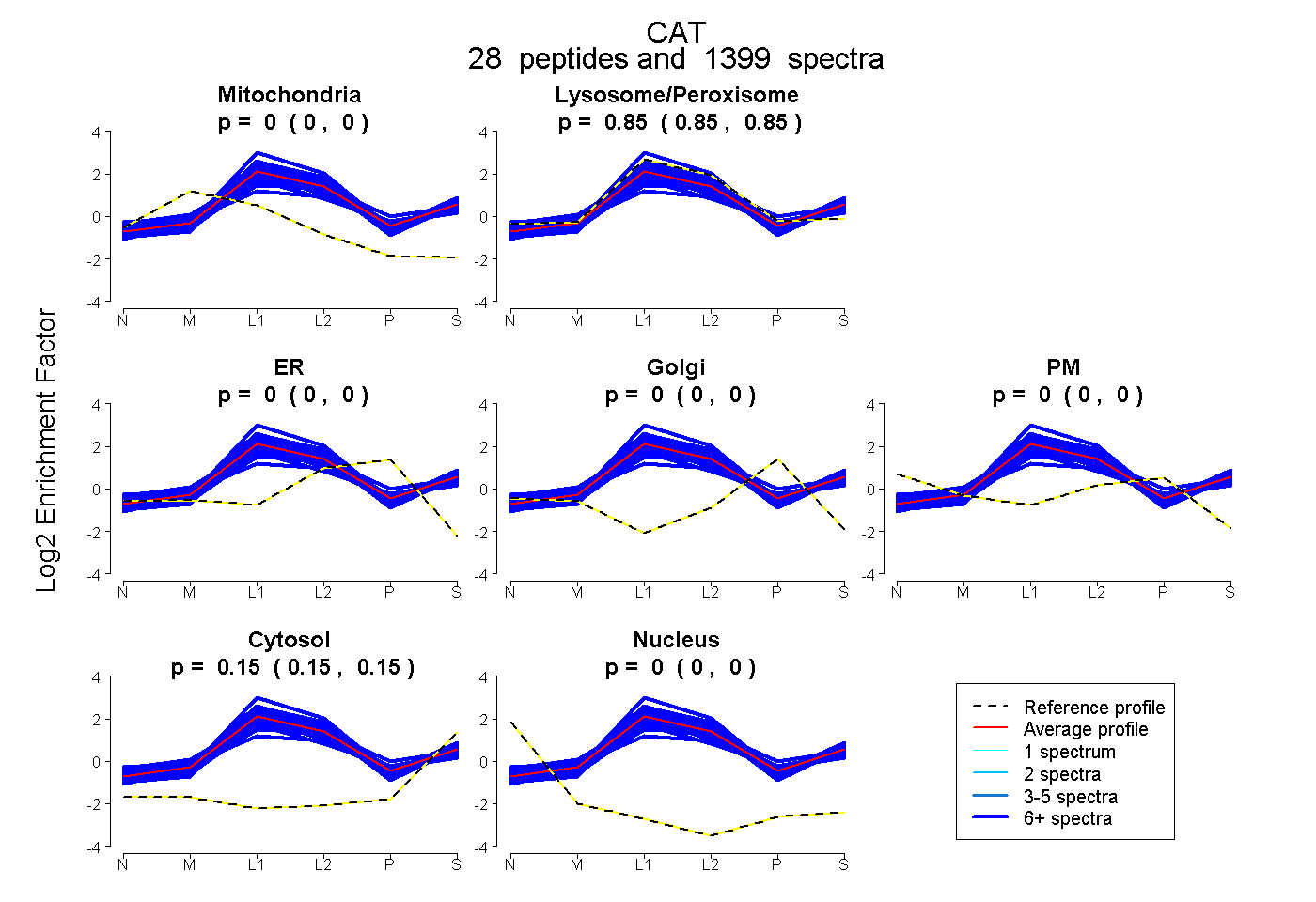
0.000 | 0.000
0.854 | 0.855
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.145 | 0.146
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
1831 spectra |
 |
0.026 0.025 | 0.026 |
0.000 0.000 | 0.000 |
0.918 0.918 | 0.918 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.056 0.056 | 0.057 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
1399 spectra |
 |
0.000 0.000 | 0.000 |
0.854 0.854 | 0.855 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.146 0.145 | 0.146 |
0.000 0.000 | 0.000 |
| 35 spectra, LCENIANHLK | 0.000 | 0.886 | 0.000 | 0.000 | 0.000 | 0.114 | 0.000 | |||
| 9 spectra, NAIHTYVQAGSHIAAK | 0.000 | 0.720 | 0.000 | 0.035 | 0.000 | 0.244 | 0.000 | |||
| 28 spectra, DAMLFPSFIHSQK | 0.000 | 0.768 | 0.000 | 0.000 | 0.000 | 0.232 | 0.000 | |||
| 3 spectra, DYPLIPVGK | 0.000 | 0.823 | 0.000 | 0.048 | 0.000 | 0.129 | 0.000 | |||
| 6 spectra, DPASDQMK | 0.000 | 0.802 | 0.000 | 0.000 | 0.000 | 0.198 | 0.000 | |||
| 16 spectra, LVNANGEAVYCK | 0.000 | 0.823 | 0.000 | 0.000 | 0.000 | 0.177 | 0.000 | |||
| 7 spectra, HMNGYGSHTFK | 0.000 | 0.808 | 0.000 | 0.000 | 0.000 | 0.192 | 0.000 | |||
| 381 spectra, GAGAFGYFEVTHDITR | 0.017 | 0.816 | 0.000 | 0.000 | 0.000 | 0.166 | 0.000 | |||
| 86 spectra, VANYQR | 0.000 | 0.919 | 0.000 | 0.000 | 0.000 | 0.081 | 0.000 | |||
| 128 spectra, GPLLVQDVVFTDEMAHFDR | 0.000 | 0.777 | 0.000 | 0.000 | 0.000 | 0.223 | 0.000 | |||
| 3 spectra, APQKPDVLTTGGGNPIGDK | 0.000 | 0.853 | 0.000 | 0.000 | 0.000 | 0.147 | 0.000 | |||
| 68 spectra, LFAYPDTHR | 0.016 | 0.827 | 0.000 | 0.003 | 0.000 | 0.154 | 0.000 | |||
| 7 spectra, VQALLDQYNSQKPK | 0.038 | 0.860 | 0.000 | 0.000 | 0.000 | 0.102 | 0.000 | |||
| 9 spectra, LGPNYLQIPVNCPYR | 0.000 | 0.891 | 0.000 | 0.000 | 0.000 | 0.109 | 0.000 | |||
| 77 spectra, TPIAVR | 0.000 | 0.979 | 0.000 | 0.000 | 0.000 | 0.021 | 0.000 | |||
| 20 spectra, GIPDGHR | 0.095 | 0.785 | 0.000 | 0.014 | 0.000 | 0.106 | 0.000 | |||
| 30 spectra, VFEHIGK | 0.000 | 0.908 | 0.000 | 0.000 | 0.000 | 0.092 | 0.000 | |||
| 12 spectra, FSTVAGESGSADTVR | 0.000 | 0.851 | 0.000 | 0.000 | 0.000 | 0.149 | 0.000 | |||
| 8 spectra, NPQTHLK | 0.000 | 0.806 | 0.027 | 0.000 | 0.000 | 0.167 | 0.000 | |||
| 48 spectra, LAQEDPDYGLR | 0.000 | 0.864 | 0.000 | 0.000 | 0.000 | 0.136 | 0.000 | |||
| 16 spectra, FNSANEDNVTQVR | 0.000 | 0.882 | 0.000 | 0.000 | 0.000 | 0.118 | 0.000 | |||
| 15 spectra, TDQGIK | 0.000 | 0.924 | 0.000 | 0.000 | 0.000 | 0.076 | 0.000 | |||
| 87 spectra, VLNEEER | 0.000 | 0.915 | 0.000 | 0.000 | 0.000 | 0.085 | 0.000 | |||
| 87 spectra, NFTDVHPDYGAR | 0.044 | 0.758 | 0.000 | 0.044 | 0.001 | 0.153 | 0.000 | |||
| 78 spectra, NLPVEEAGR | 0.000 | 0.904 | 0.000 | 0.000 | 0.000 | 0.096 | 0.000 | |||
| 35 spectra, LNIMTAGPR | 0.000 | 0.795 | 0.000 | 0.000 | 0.000 | 0.205 | 0.000 | |||
| 24 spectra, EAETFPFNPFDLTK | 0.000 | 0.857 | 0.000 | 0.000 | 0.000 | 0.143 | 0.000 | |||
| 76 spectra, DAQLFIQR | 0.000 | 0.885 | 0.000 | 0.000 | 0.000 | 0.115 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
7216 spectra |
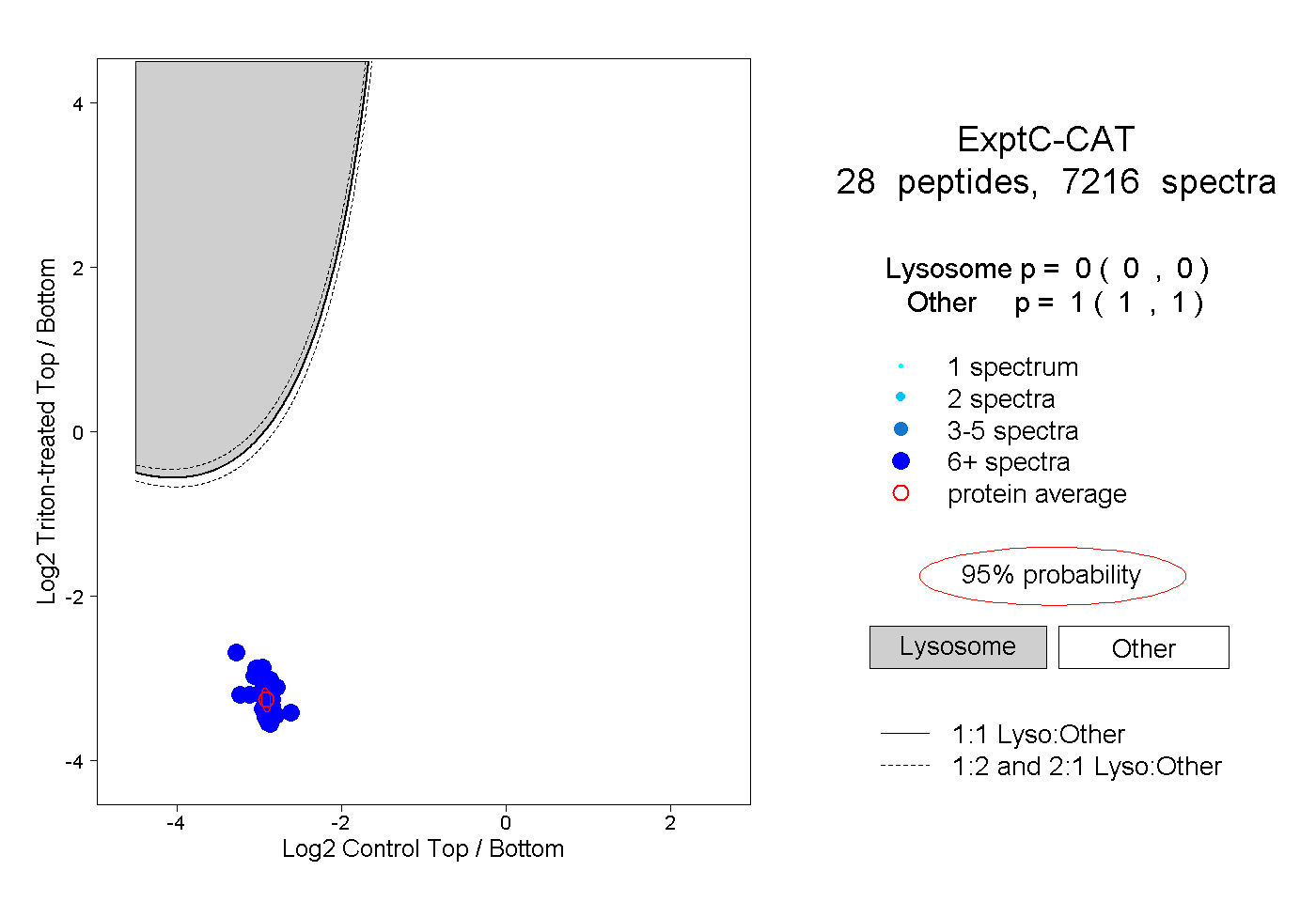 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
695 spectra |
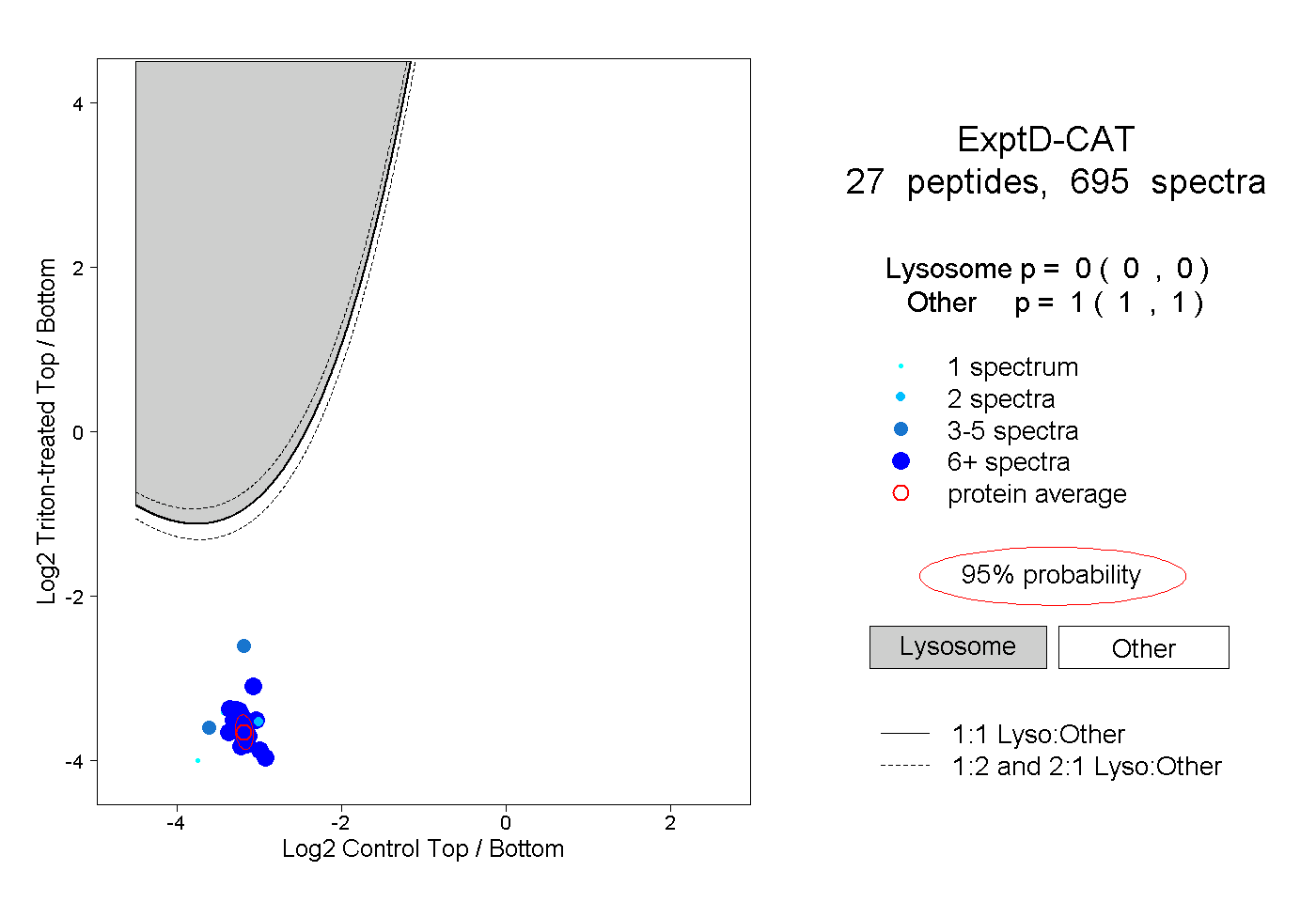 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |