peptides
spectra
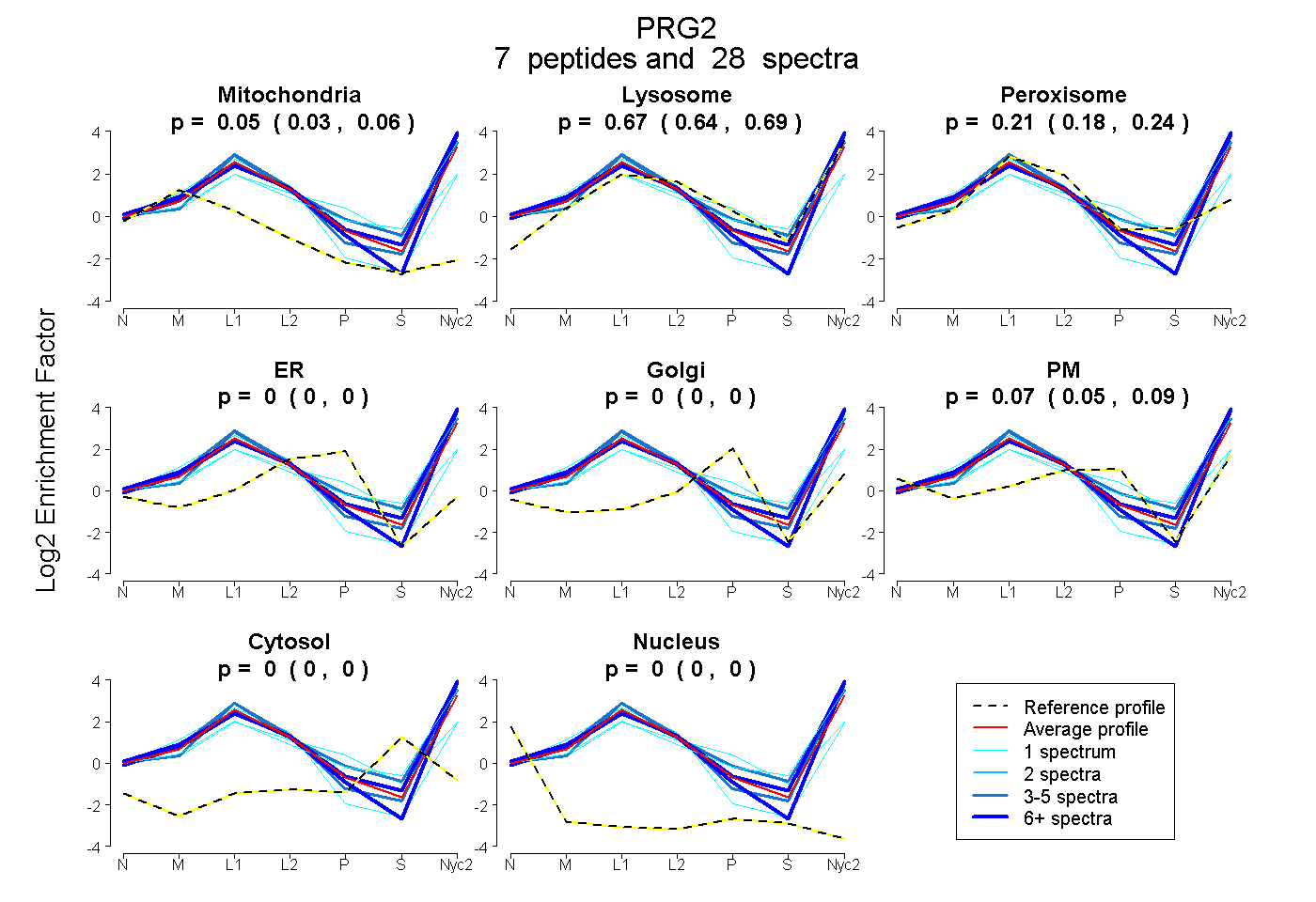
0.031 | 0.059
0.635 | 0.694
0.178 | 0.239
0.000 | 0.000
0.000 | 0.000
0.050 | 0.091
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
28 spectra |
 |
0.046 0.031 | 0.059 |
0.668 0.635 | 0.694 |
0.212 0.178 | 0.239 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.073 0.050 | 0.091 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 5 spectra, GTLASIHSFSVNFR | 0.000 | 0.708 | 0.260 | 0.000 | 0.000 | 0.032 | 0.000 | 0.000 | ||
| 4 spectra, GINQGQVWIGGR | 0.032 | 0.834 | 0.134 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 10 spectra, IVGWGR | 0.082 | 0.807 | 0.000 | 0.000 | 0.000 | 0.111 | 0.000 | 0.000 | ||
| 1 spectrum, CVTLCTR | 0.253 | 0.397 | 0.350 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, LVMQGR | 0.000 | 0.771 | 0.122 | 0.000 | 0.000 | 0.075 | 0.000 | 0.031 | ||
| 6 spectra, IQSFVR | 0.017 | 0.866 | 0.091 | 0.000 | 0.000 | 0.026 | 0.000 | 0.000 | ||
| 1 spectrum, AQLVCR | 0.000 | 0.234 | 0.417 | 0.000 | 0.000 | 0.350 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
12 spectra |
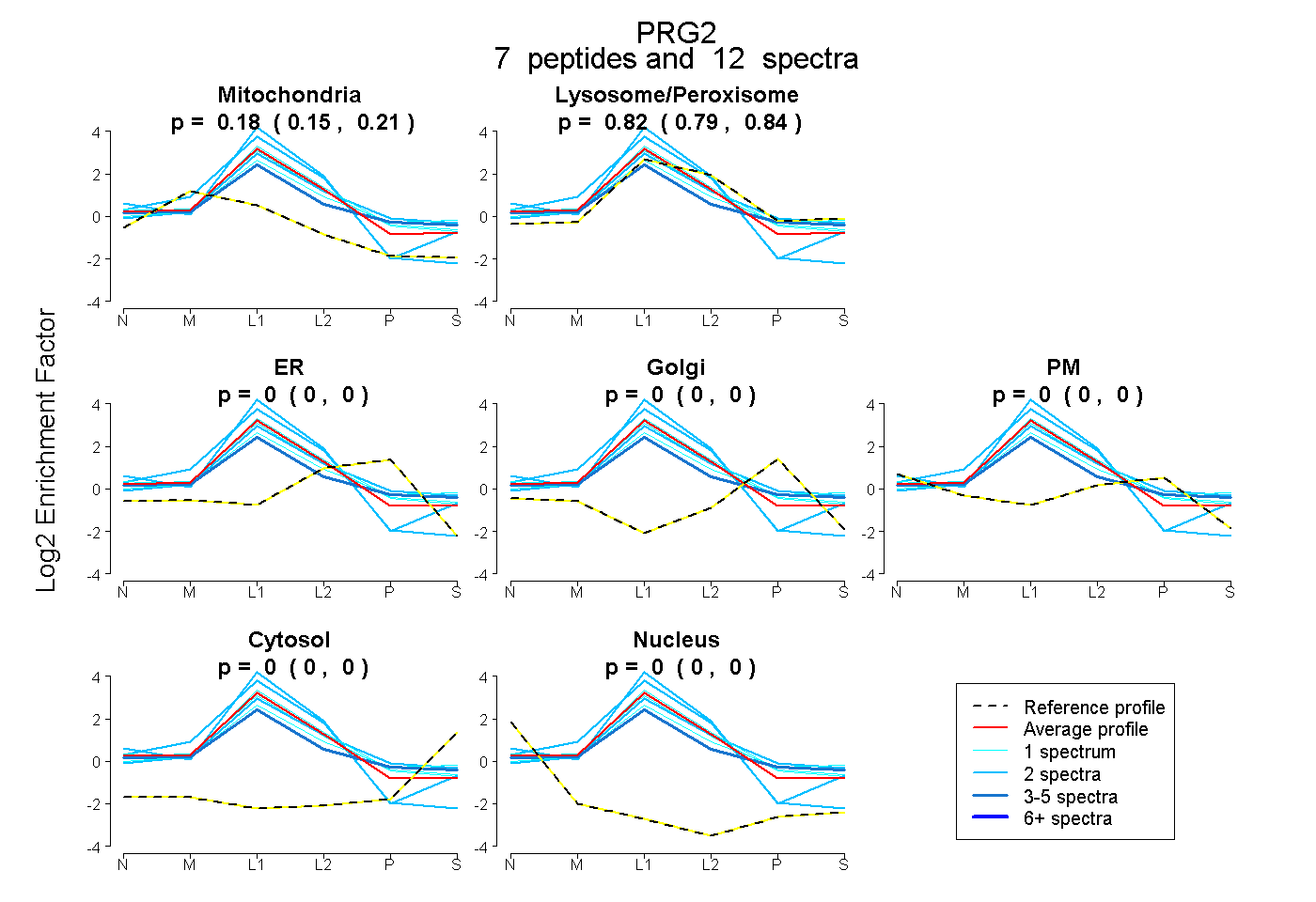 |
0.182 0.153 | 0.207 |
0.818 0.789 | 0.843 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
51 spectra |
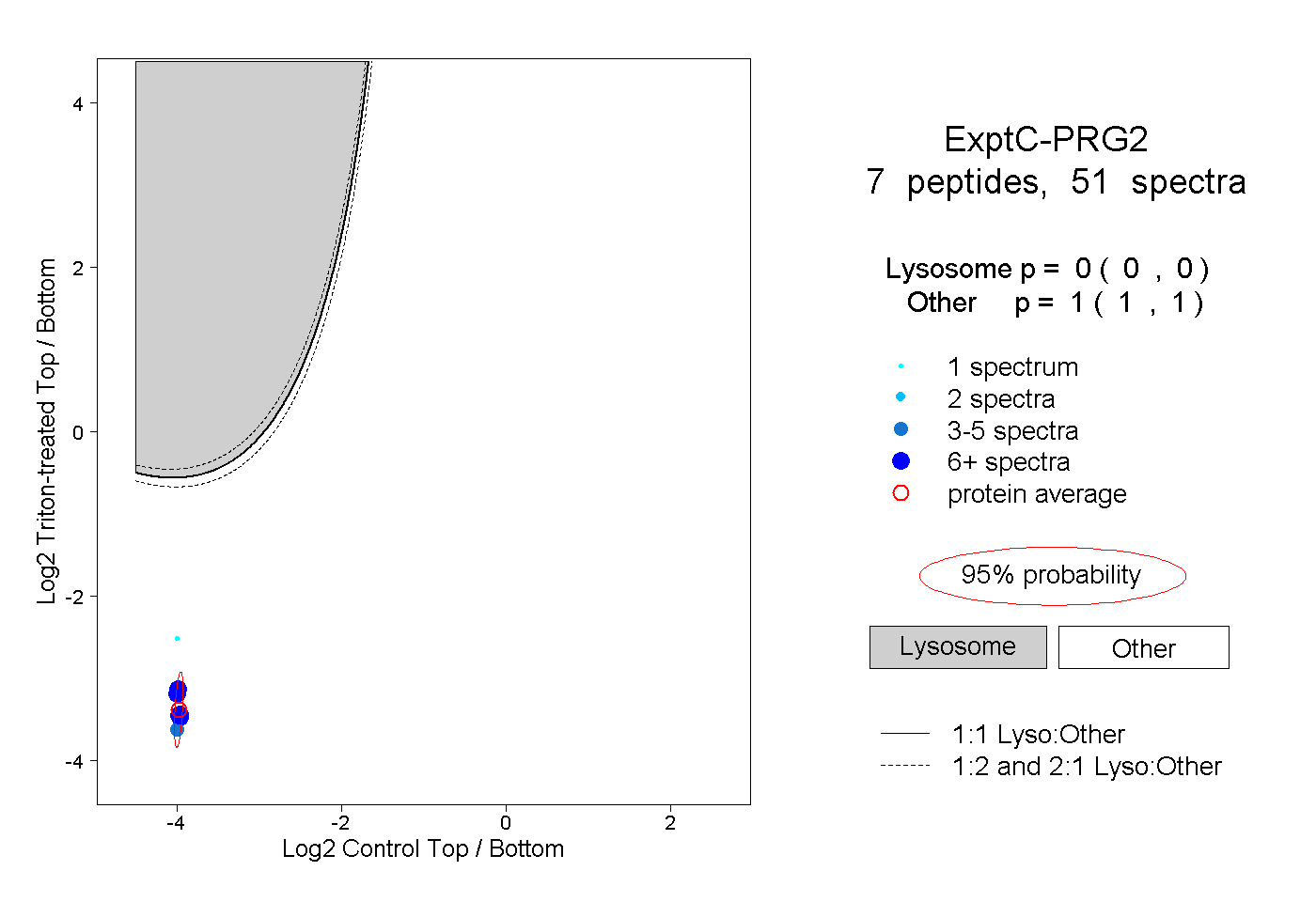 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
8 spectra |
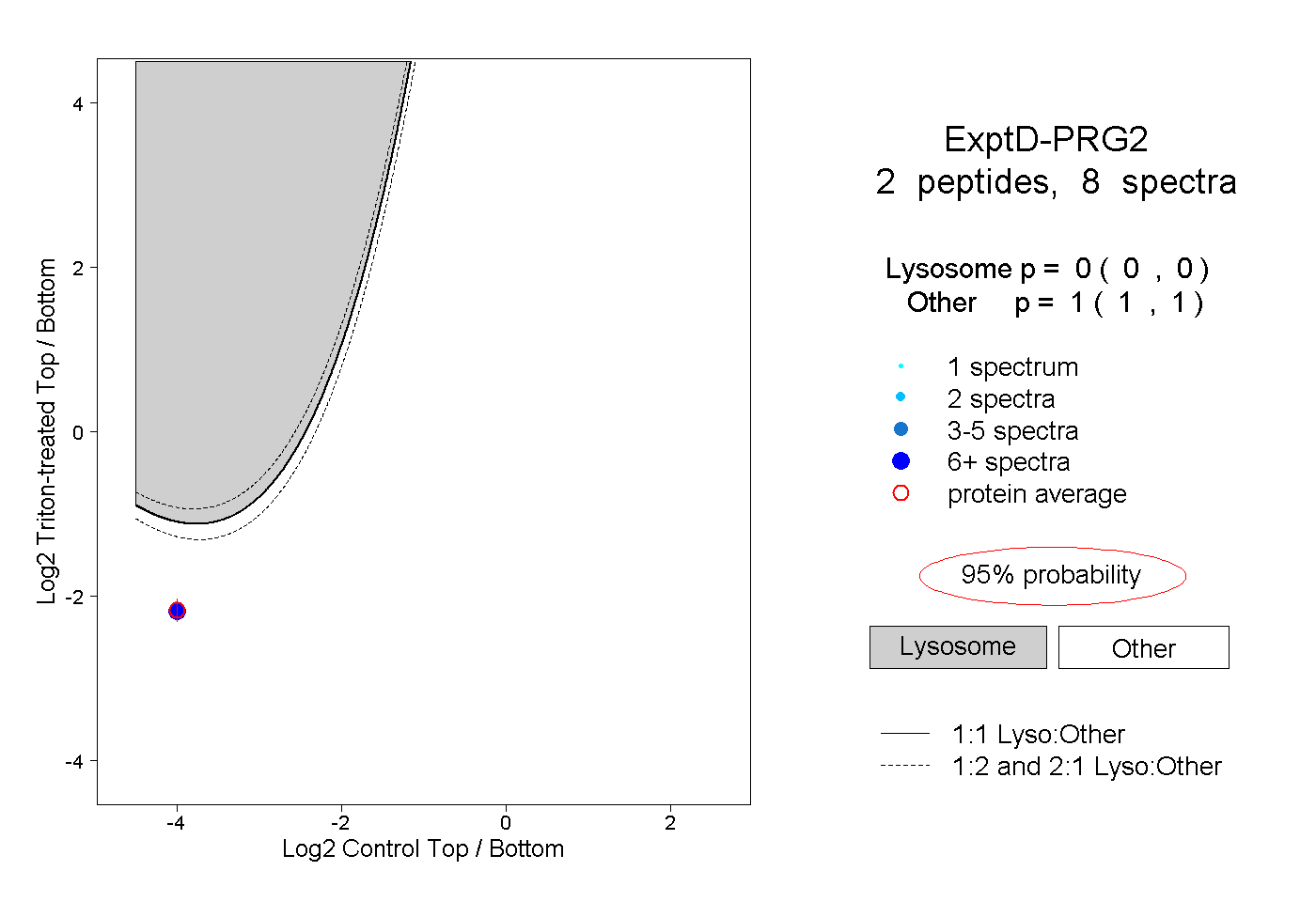 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |