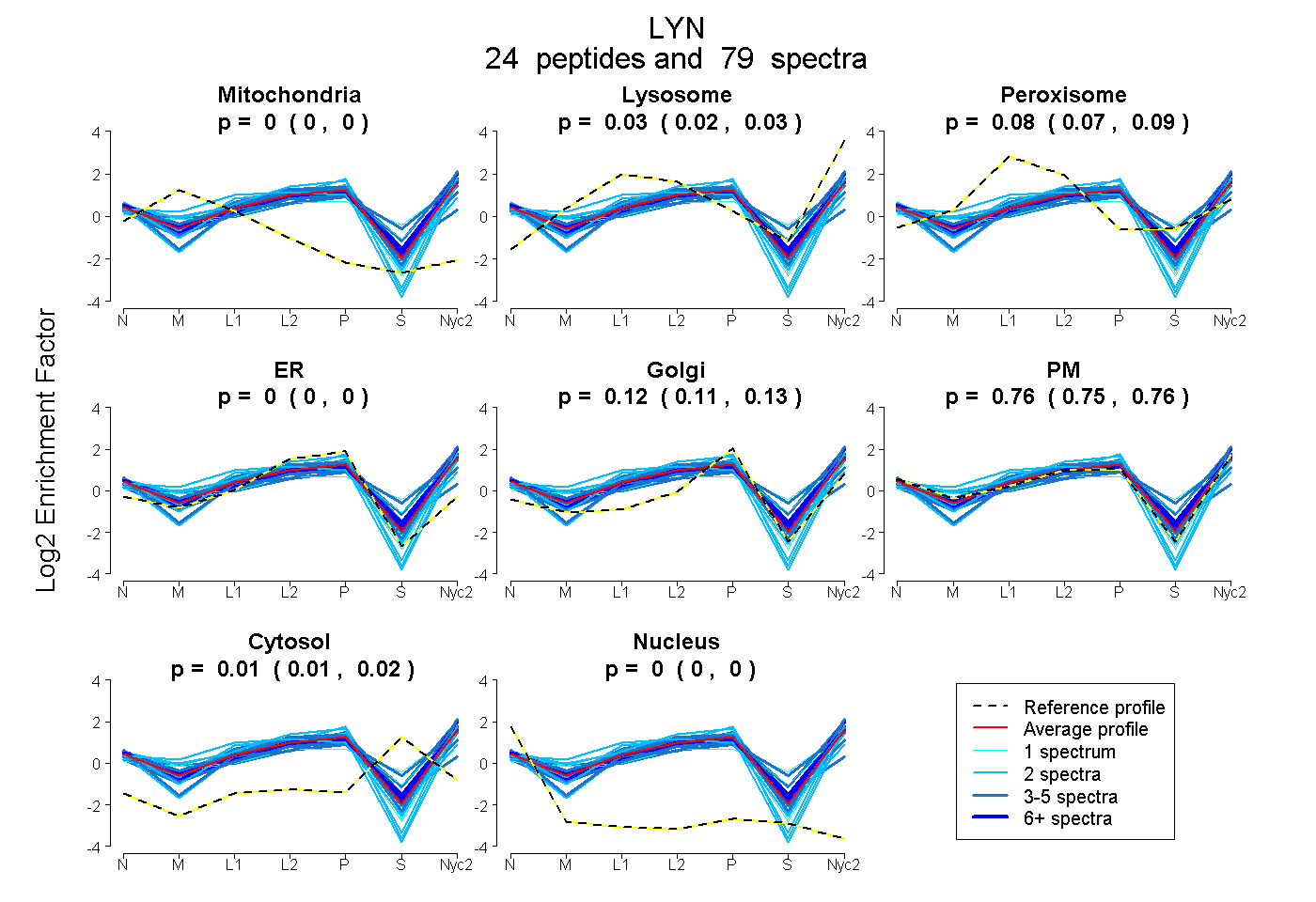
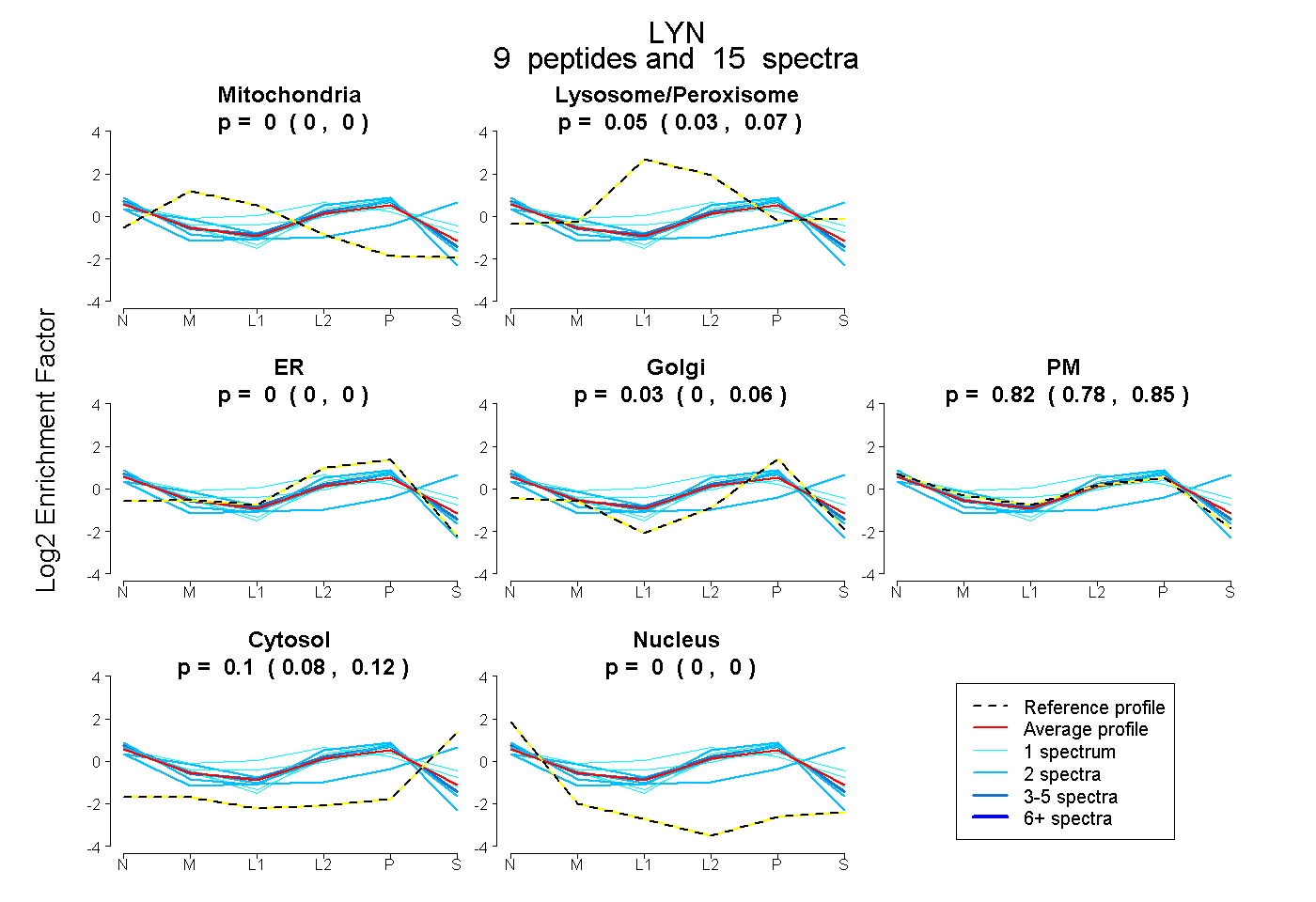
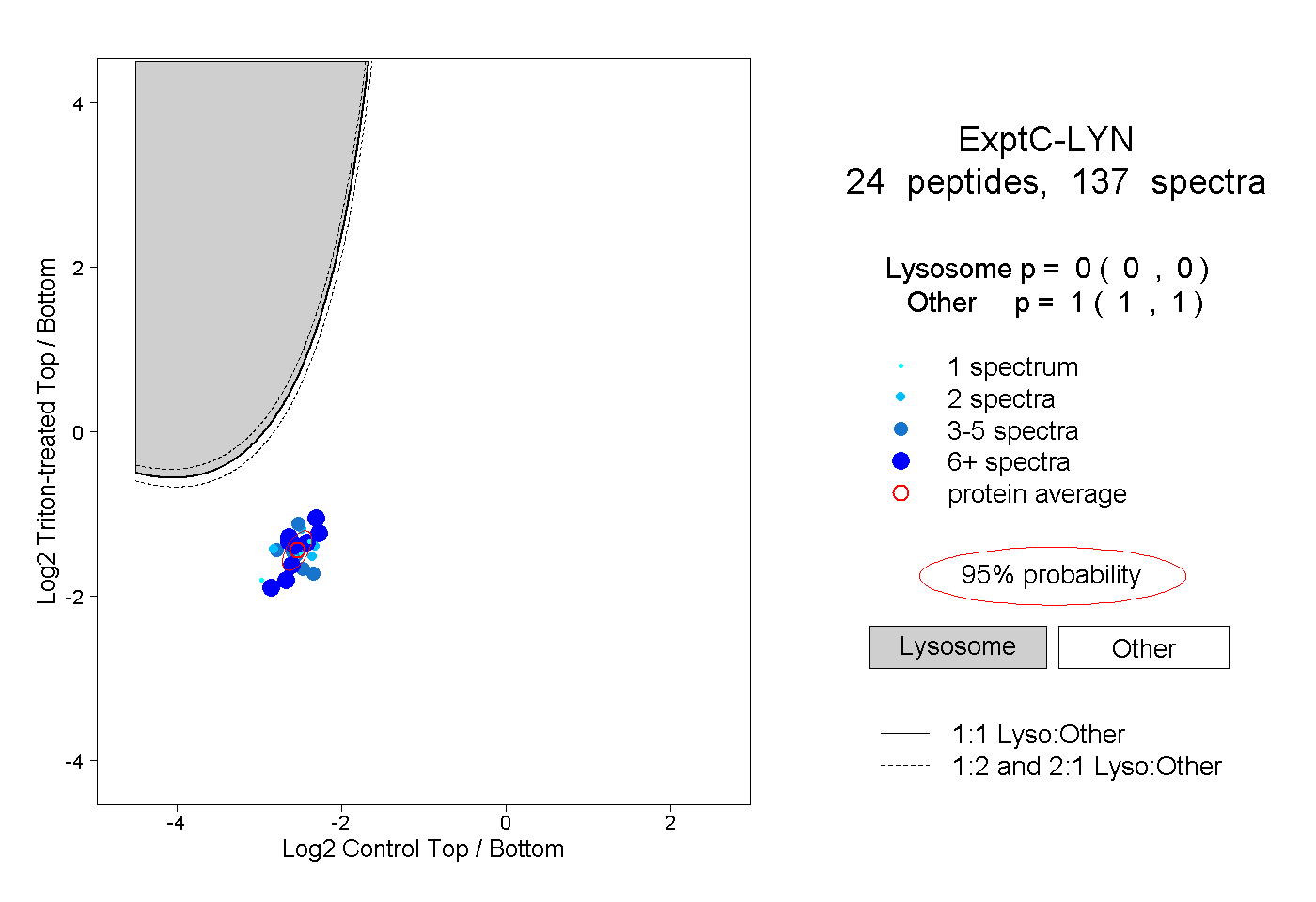
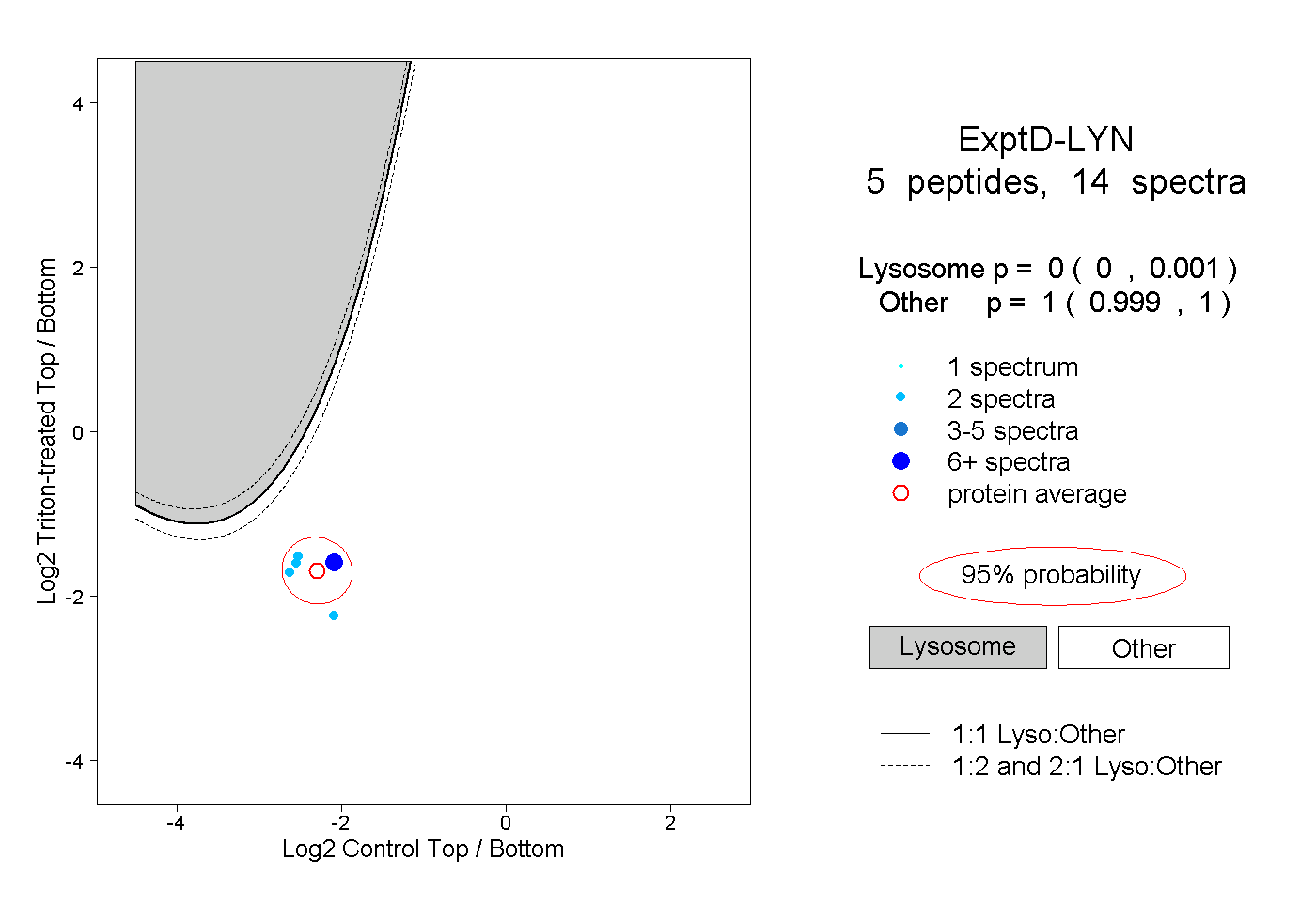
| 7 spectra, DPTSNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, MENCPDELYDIMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TIYVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, DNLNDDGVDMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, TLQHDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SLSSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, TNADVMTALSQGYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, DAWEIPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EGFIPSNYVAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, QLLAPGNSAGAFLIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 15 spectra, DYDPMHGDVIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, VLEEHGEWWK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SLDNGGYYISPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QQRPVPESQLLPGQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, LYAVVTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, GSFSLSVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, ITFPCISDMIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 20 spectra, GSLLDFLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EEPIYIITEFMAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, LADFGLAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SDEGSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, VIEDNEYTAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, IPYPGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VNTLETEEWFFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |