peptides
spectra
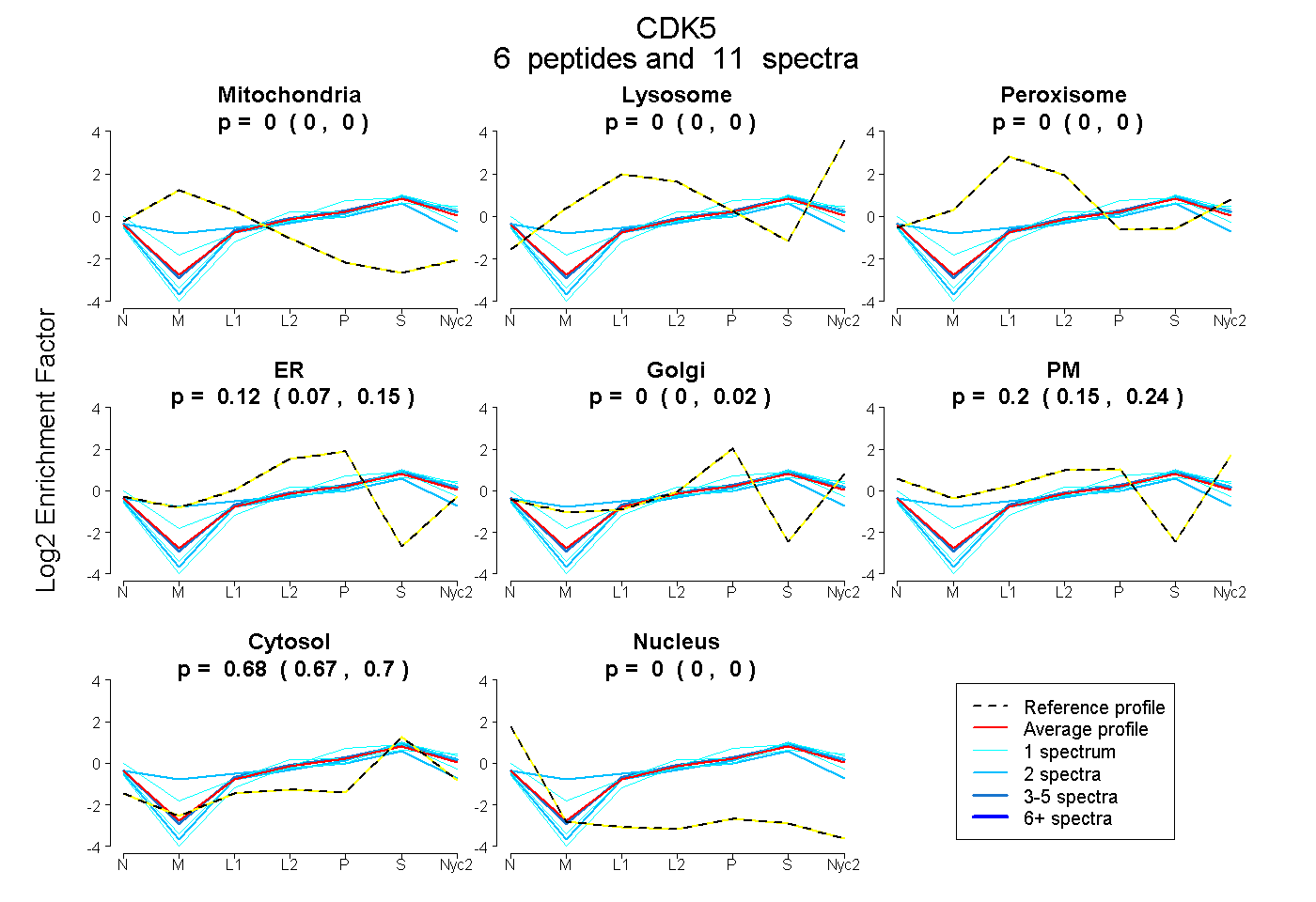
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.072 | 0.147
0.000 | 0.021
0.150 | 0.238
0.668 | 0.697
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
11 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.116 0.072 | 0.147 |
0.000 0.000 | 0.021 |
0.199 0.150 | 0.238 |
0.684 0.668 | 0.697 |
0.000 0.000 | 0.000 |
| 4 spectra, DLKPQNLLINR | 0.000 | 0.001 | 0.000 | 0.078 | 0.000 | 0.244 | 0.677 | 0.000 | ||
| 1 spectrum, LDDDDEGVPSSALR | 0.000 | 0.006 | 0.000 | 0.000 | 0.011 | 0.242 | 0.741 | 0.000 | ||
| 2 spectra, GLGFCHSR | 0.050 | 0.000 | 0.171 | 0.184 | 0.049 | 0.000 | 0.547 | 0.000 | ||
| 1 spectrum, YFDSCNGDLDPEIVK | 0.000 | 0.000 | 0.000 | 0.120 | 0.167 | 0.000 | 0.713 | 0.000 | ||
| 2 spectra, DLLQNLLK | 0.000 | 0.000 | 0.000 | 0.035 | 0.080 | 0.137 | 0.749 | 0.000 | ||
| 1 spectrum, LHDVLHSDK | 0.000 | 0.000 | 0.018 | 0.000 | 0.000 | 0.414 | 0.568 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
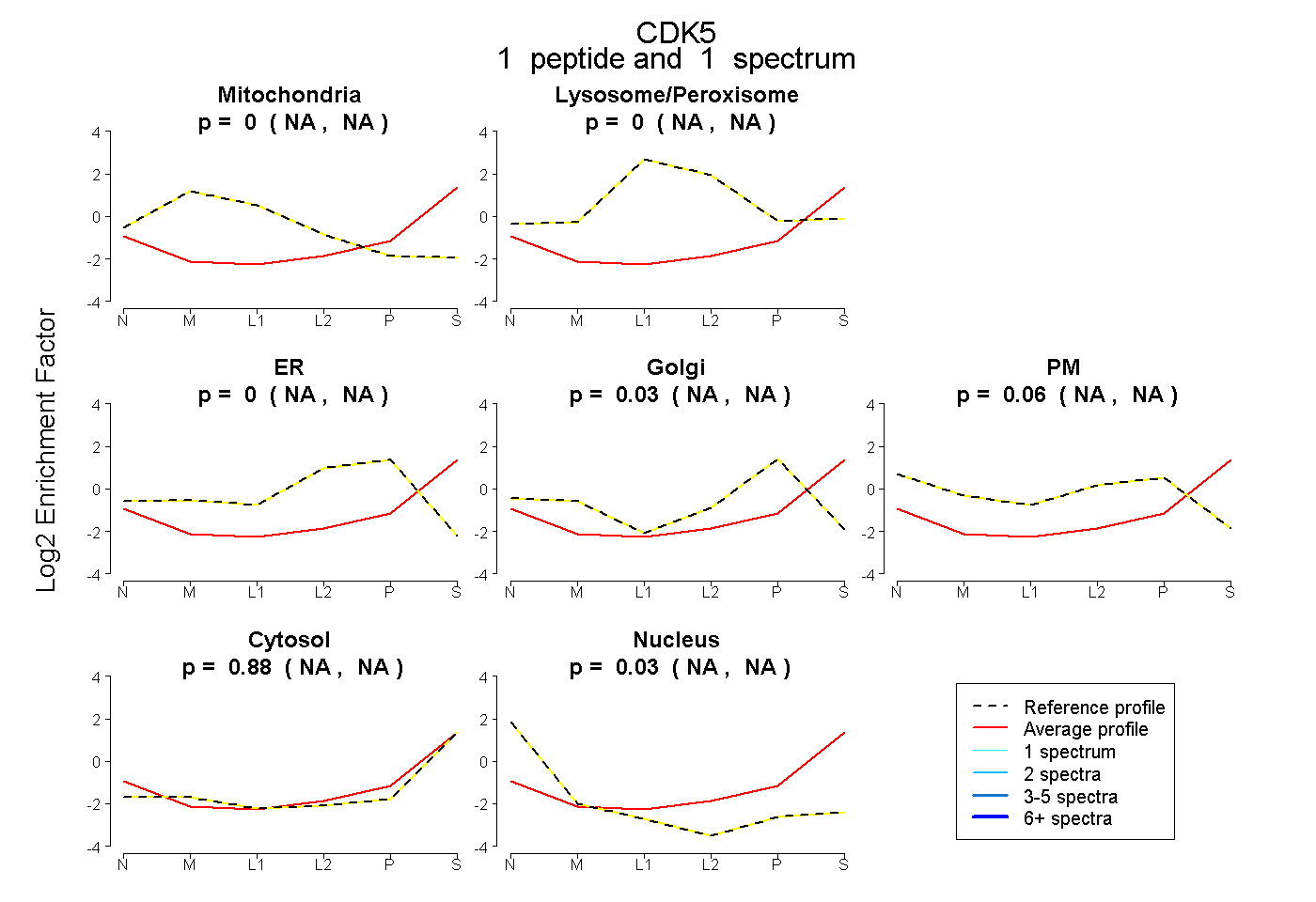 |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.030 NA | NA |
0.061 NA | NA |
0.880 NA | NA |
0.029 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
9 spectra |
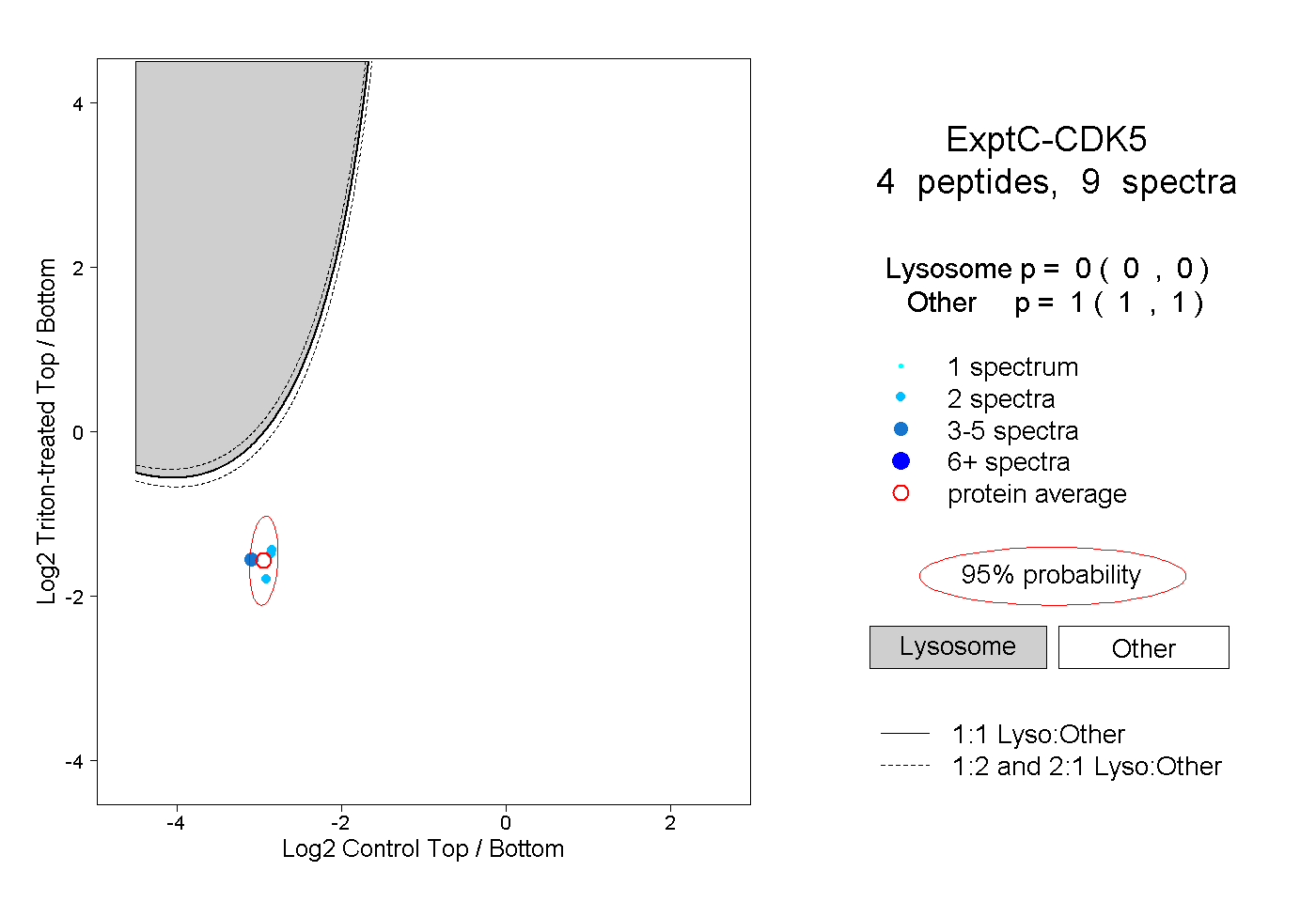 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |