peptides
spectra
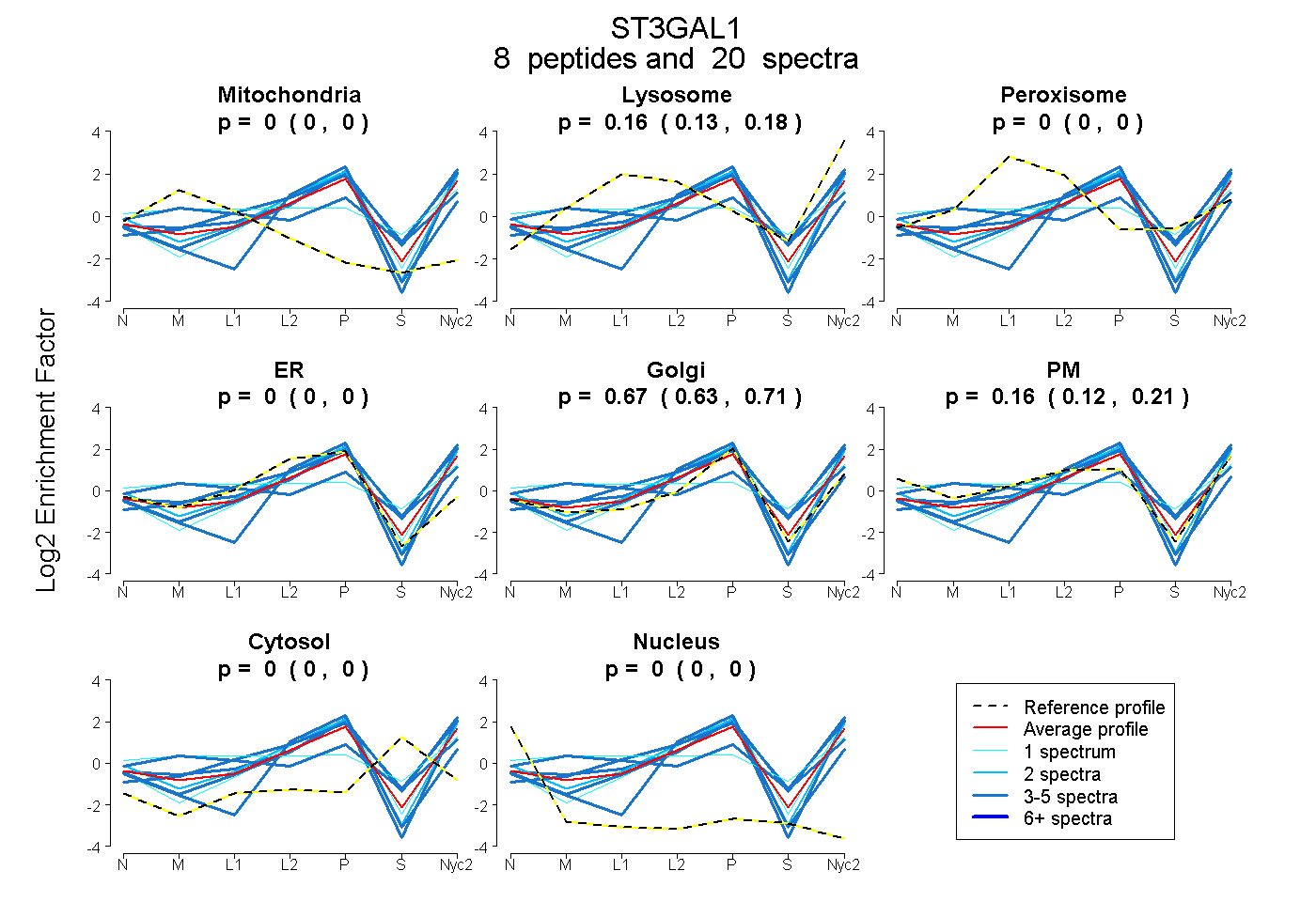
0.000 | 0.000
0.135 | 0.184
0.000 | 0.000
0.000 | 0.000
0.633 | 0.707
0.117 | 0.206
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
20 spectra |
 |
0.000 0.000 | 0.000 |
0.161 0.135 | 0.184 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.674 0.633 | 0.707 |
0.165 0.117 | 0.206 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, APTVGFEADVGSR | 0.000 | 0.134 | 0.000 | 0.000 | 0.821 | 0.046 | 0.000 | 0.000 | ||
| 3 spectra, SQPCTCR | 0.000 | 0.000 | 0.000 | 0.074 | 0.918 | 0.000 | 0.000 | 0.008 | ||
| 4 spectra, DSSYGPEIDSHDFVLR | 0.000 | 0.078 | 0.000 | 0.000 | 0.554 | 0.368 | 0.000 | 0.000 | ||
| 3 spectra, ILIYHPAFIK | 0.000 | 0.242 | 0.000 | 0.000 | 0.731 | 0.000 | 0.028 | 0.000 | ||
| 2 spectra, QMVLEFSENFR | 0.000 | 0.018 | 0.000 | 0.000 | 0.525 | 0.457 | 0.000 | 0.000 | ||
| 3 spectra, TMQPLLTAHNALMEEDTYR | 0.000 | 0.402 | 0.000 | 0.000 | 0.587 | 0.000 | 0.011 | 0.000 | ||
| 3 spectra, YVFDNWLQGHGR | 0.167 | 0.242 | 0.000 | 0.000 | 0.338 | 0.183 | 0.071 | 0.000 | ||
| 1 spectrum, TTHHLVYPESFR | 0.092 | 0.167 | 0.092 | 0.000 | 0.000 | 0.494 | 0.155 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
20 spectra |
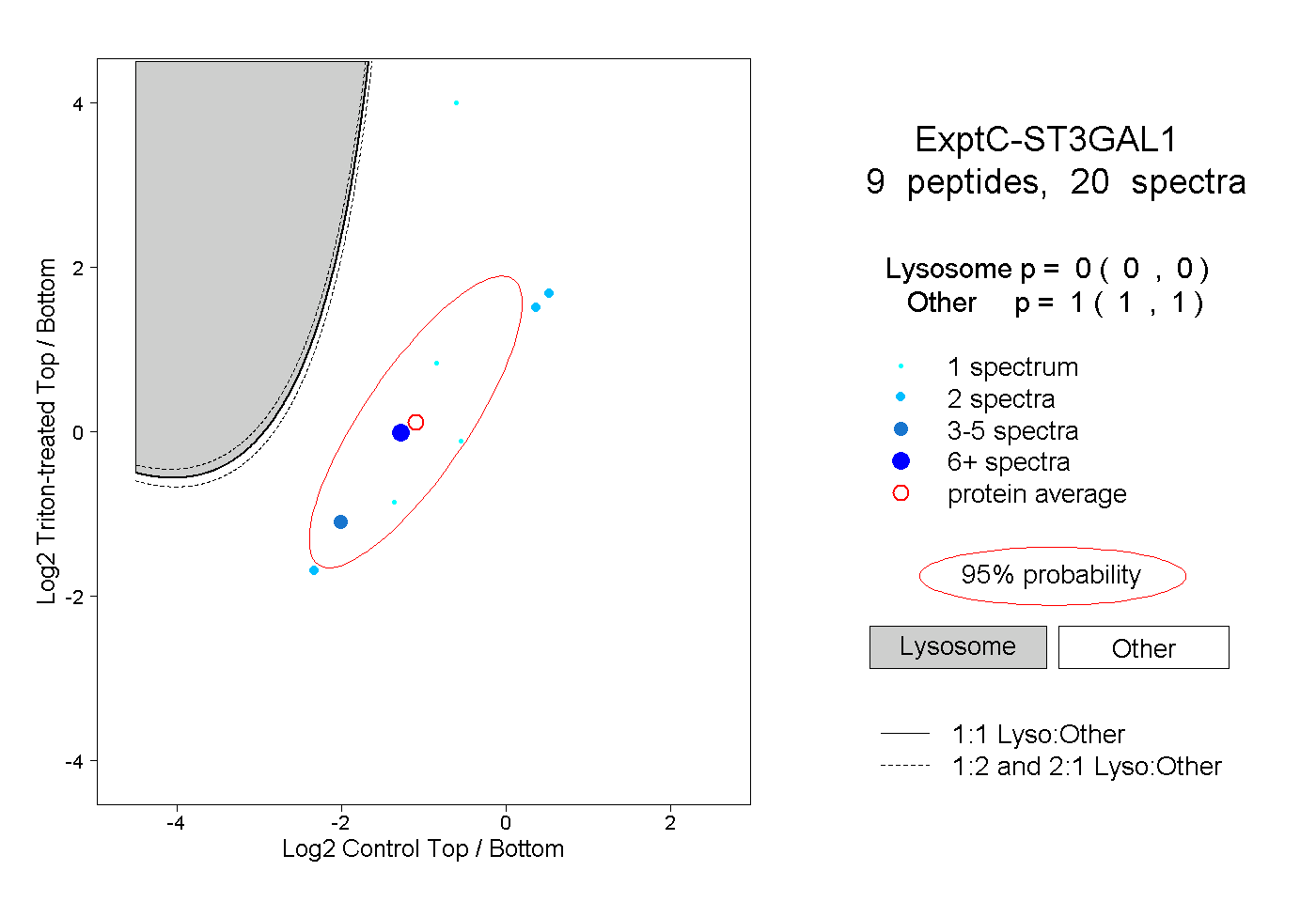 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
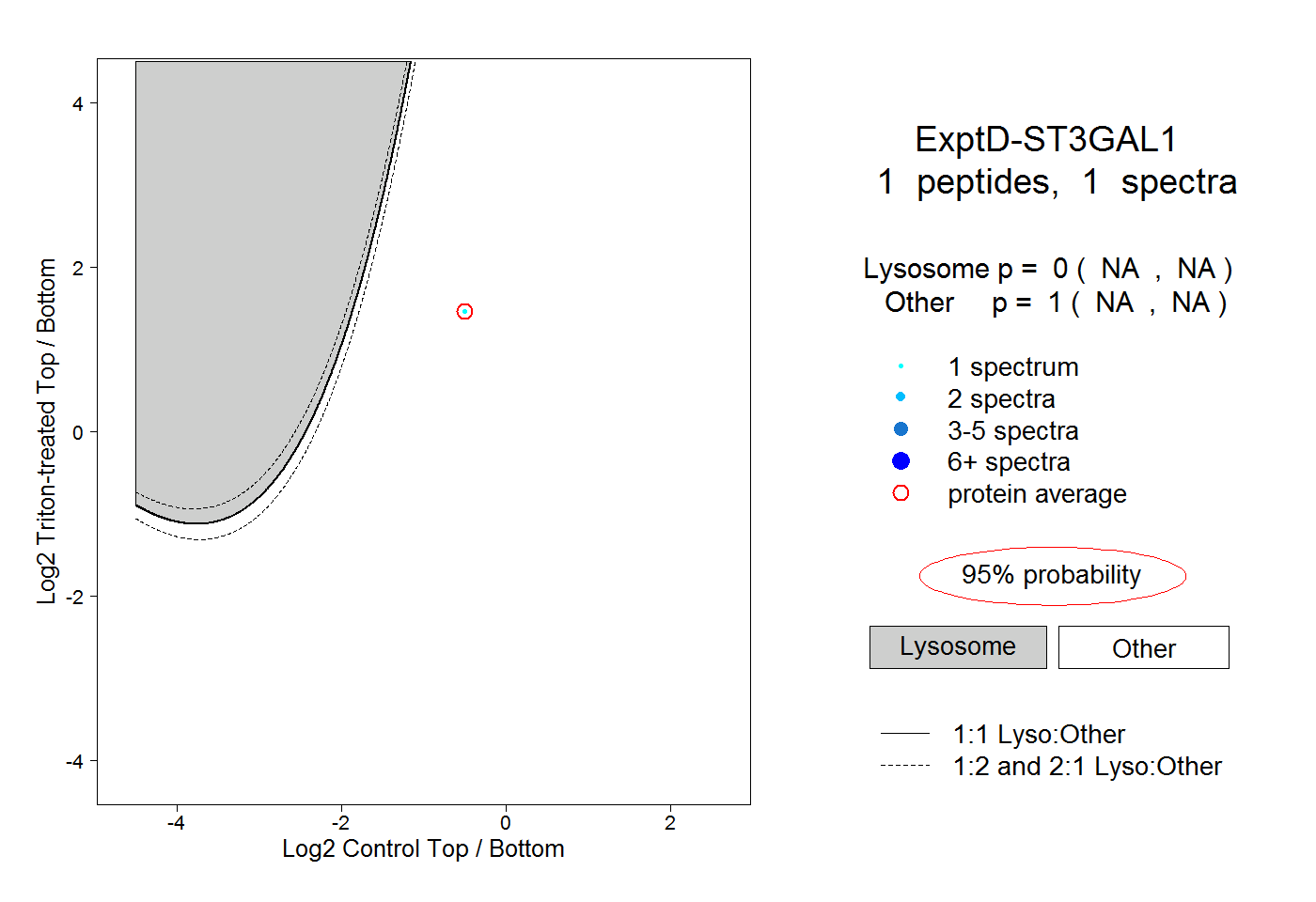 |
0.000 NA | NA |
1.000 NA | NA |