peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.887 | 0.893
0.000 | 0.000
0.000 | 0.000
0.106 | 0.113
0.000 | 0.000
peptides
spectra
0.000 | 0.000
0.147 | 0.168
0.756 | 0.786
0.000 | 0.000
0.057 | 0.079
0.000 | 0.000
0.000 | 0.000
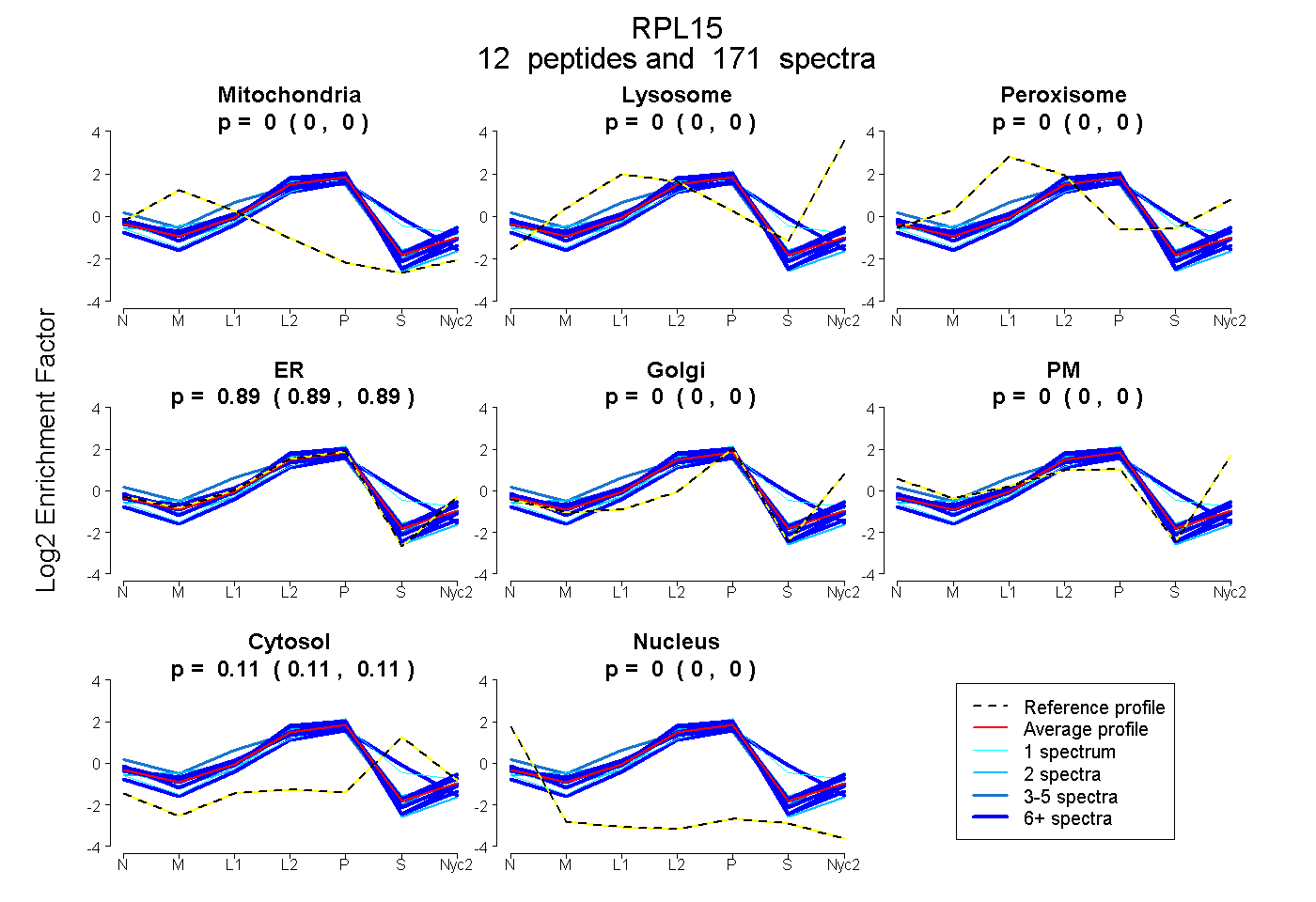
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
171 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.890 0.887 | 0.893 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.110 0.106 | 0.113 |
0.000 0.000 | 0.000 |
||
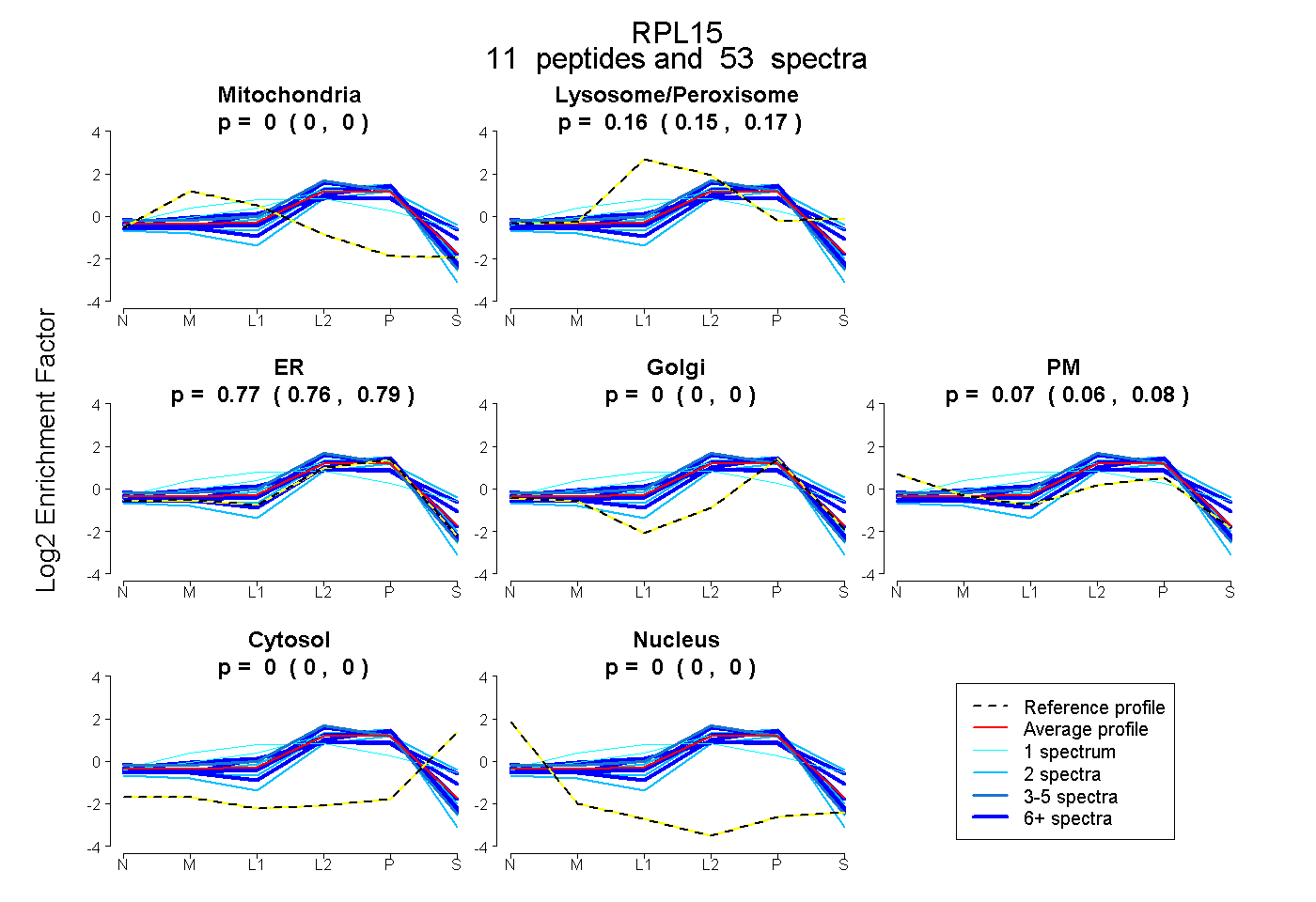
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
53 spectra |
 |
0.000 0.000 | 0.000 |
0.158 0.147 | 0.168 |
0.773 0.756 | 0.786 |
0.000 0.000 | 0.000 |
0.069 0.057 | 0.079 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, GATYGKPVHHGVNQLK | 0.000 | 0.043 | 0.957 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, NTLQLHR | 0.000 | 0.394 | 0.270 | 0.267 | 0.070 | 0.000 | 0.000 | |||
| 4 spectra, YIQELWR | 0.000 | 0.158 | 0.842 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, APRPTRPDK | 0.000 | 0.020 | 0.980 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, QGYVIYR | 0.000 | 0.060 | 0.940 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, QSLALHR | 0.034 | 0.173 | 0.792 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, VLNSYWVGEDSTYK | 0.119 | 0.571 | 0.000 | 0.310 | 0.000 | 0.000 | 0.000 | |||
| 12 spectra, SLQSVAEER | 0.000 | 0.000 | 0.975 | 0.025 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, FFEVILIDPFHK | 0.000 | 0.150 | 0.823 | 0.000 | 0.027 | 0.000 | 0.000 | |||
| 2 spectra, GLTSAGR | 0.000 | 0.037 | 0.729 | 0.000 | 0.000 | 0.234 | 0.000 | |||
| 6 spectra, QLSALHR | 0.000 | 0.440 | 0.191 | 0.325 | 0.000 | 0.044 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
180 spectra |
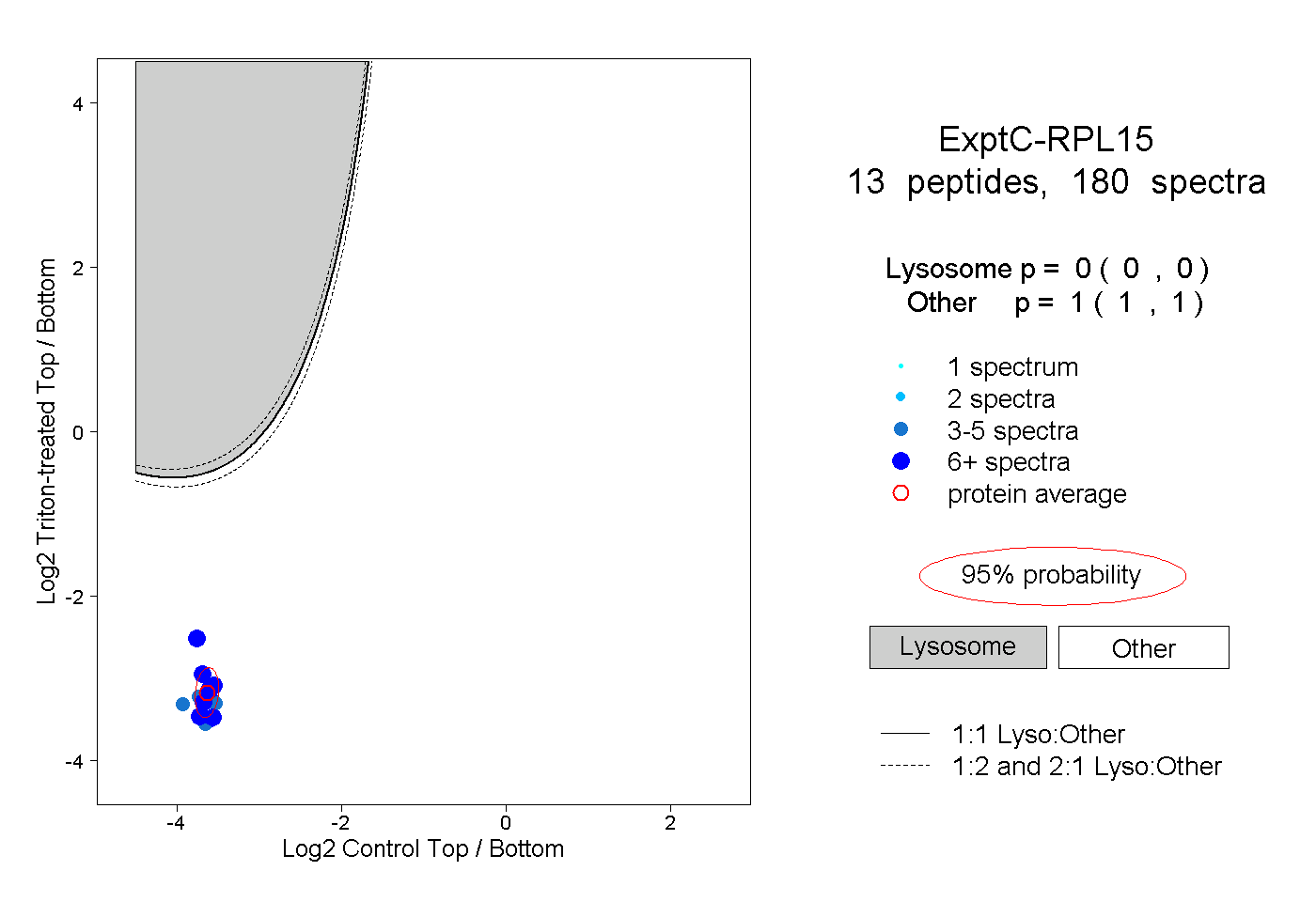 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
21 spectra |
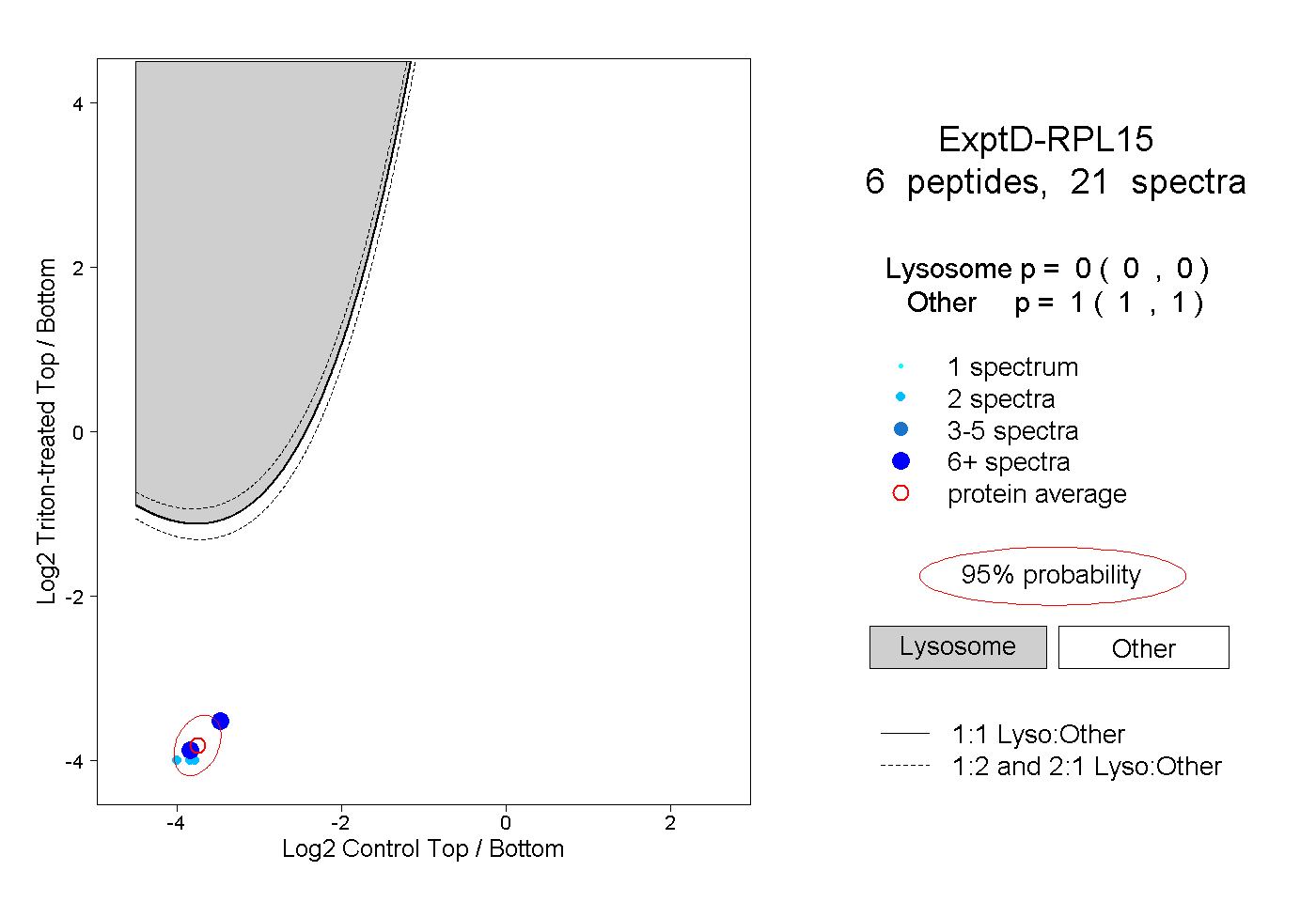 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |