peptides
spectra
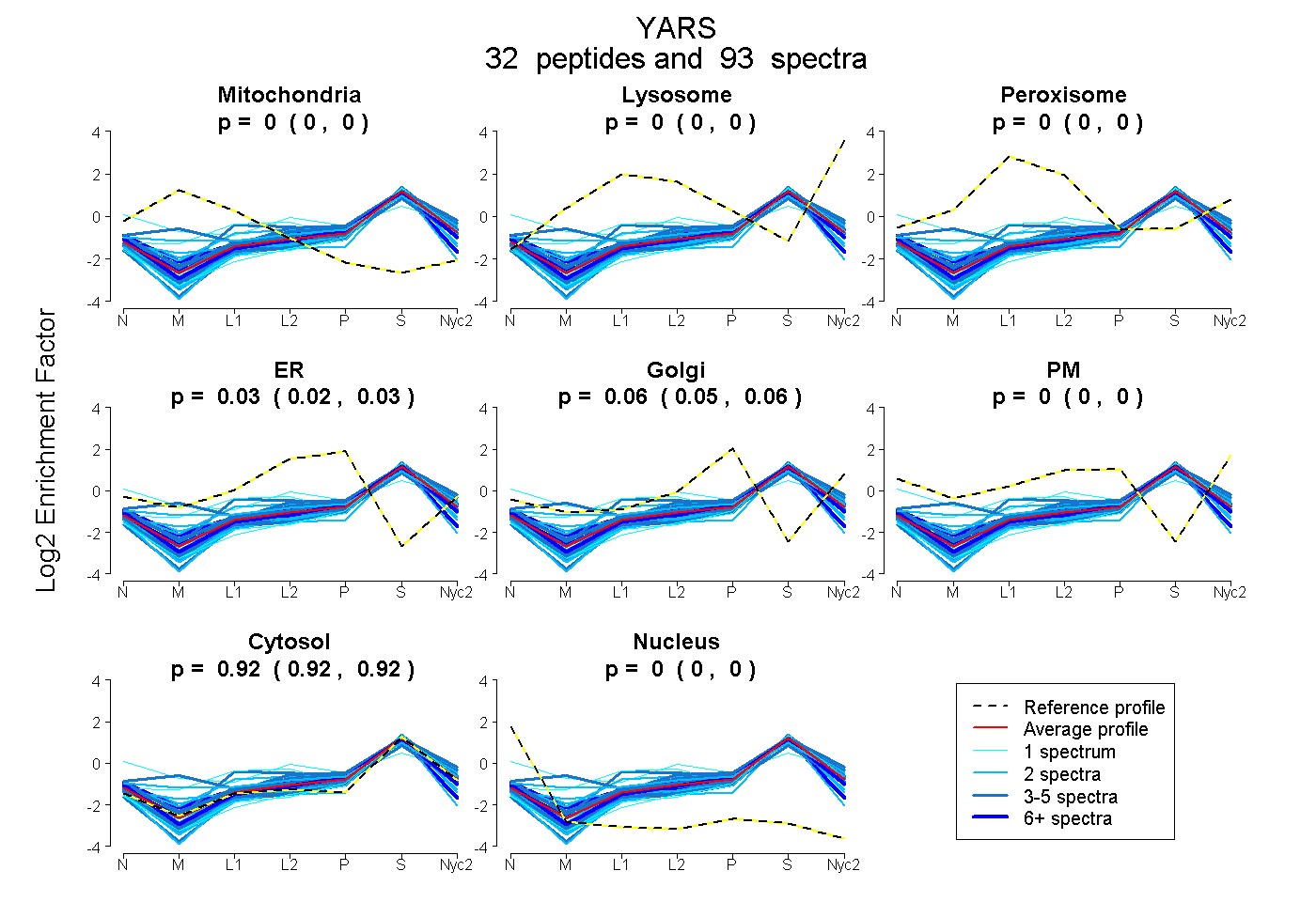
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.021 | 0.032
0.049 | 0.061
0.000 | 0.000
0.916 | 0.919
0.000 | 0.000
peptides
spectra
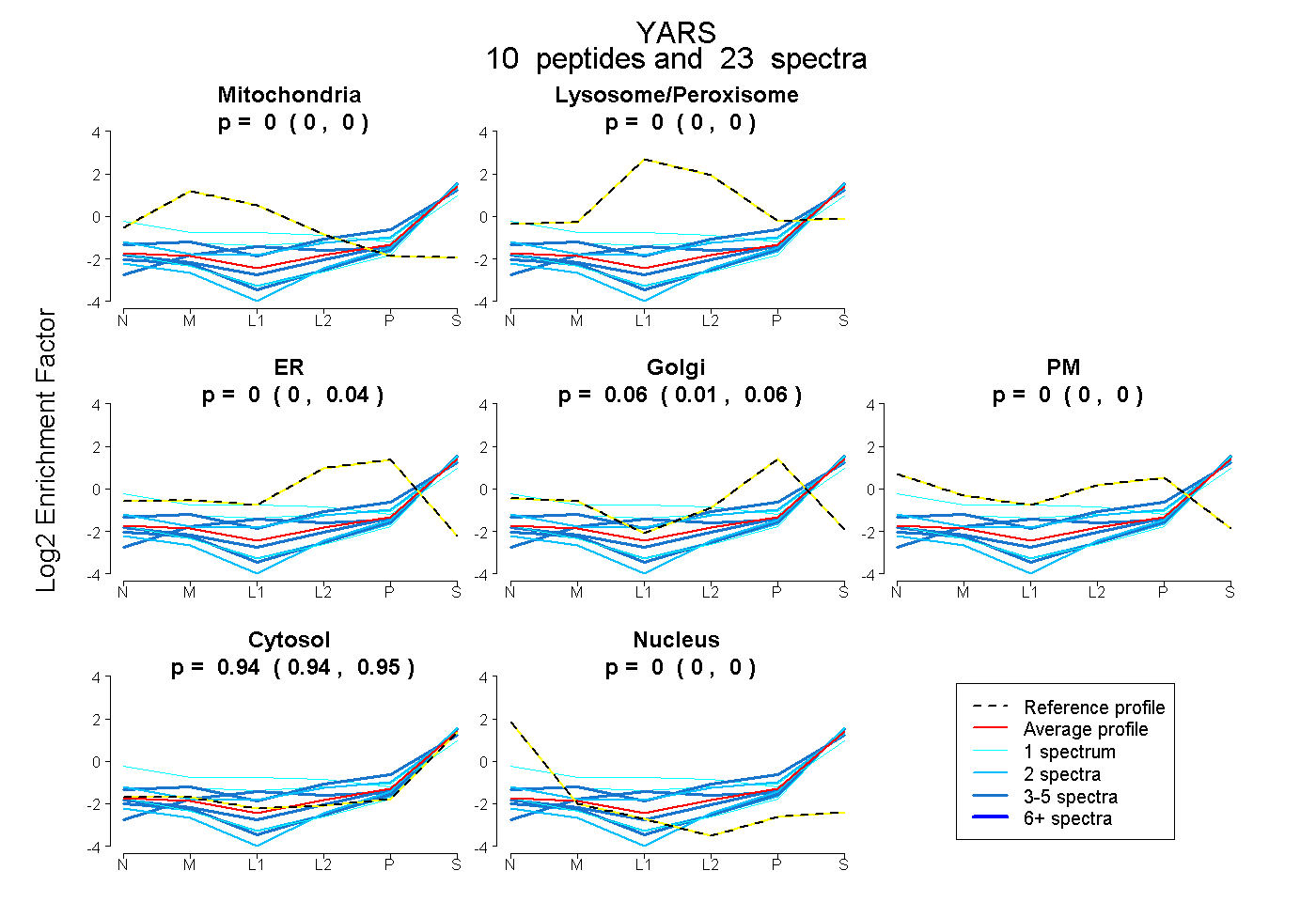
0.000 | 0.000
0.000 | 0.000
0.000 | 0.038
0.008 | 0.061
0.000 | 0.000
0.937 | 0.954
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
93 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.027 0.021 | 0.032 |
0.055 0.049 | 0.061 |
0.000 0.000 | 0.000 |
0.918 0.916 | 0.919 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
23 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.038 |
0.055 0.008 | 0.061 |
0.000 0.000 | 0.000 |
0.945 0.937 | 0.954 |
0.000 0.000 | 0.000 |
| 1 spectrum, TVVSGLVQFVPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.977 | 0.023 | |||
| 2 spectra, APWELLELR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 5 spectra, LHLITR | 0.000 | 0.092 | 0.000 | 0.000 | 0.000 | 0.908 | 0.000 | |||
| 1 spectrum, QVEPLDPPAGSAPGER | 0.000 | 0.307 | 0.000 | 0.000 | 0.061 | 0.552 | 0.081 | |||
| 2 spectra, SEFVILR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, VDAQFGGIDQR | 0.000 | 0.081 | 0.098 | 0.000 | 0.000 | 0.821 | 0.000 | |||
| 3 spectra, EYTLDVYR | 0.000 | 0.000 | 0.000 | 0.007 | 0.000 | 0.993 | 0.000 | |||
| 3 spectra, HVLFPLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, IFTFAEK | 0.000 | 0.190 | 0.000 | 0.047 | 0.000 | 0.763 | 0.000 | |||
| 3 spectra, SSEPEEIIPSR | 0.000 | 0.097 | 0.071 | 0.101 | 0.000 | 0.731 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
107 spectra |
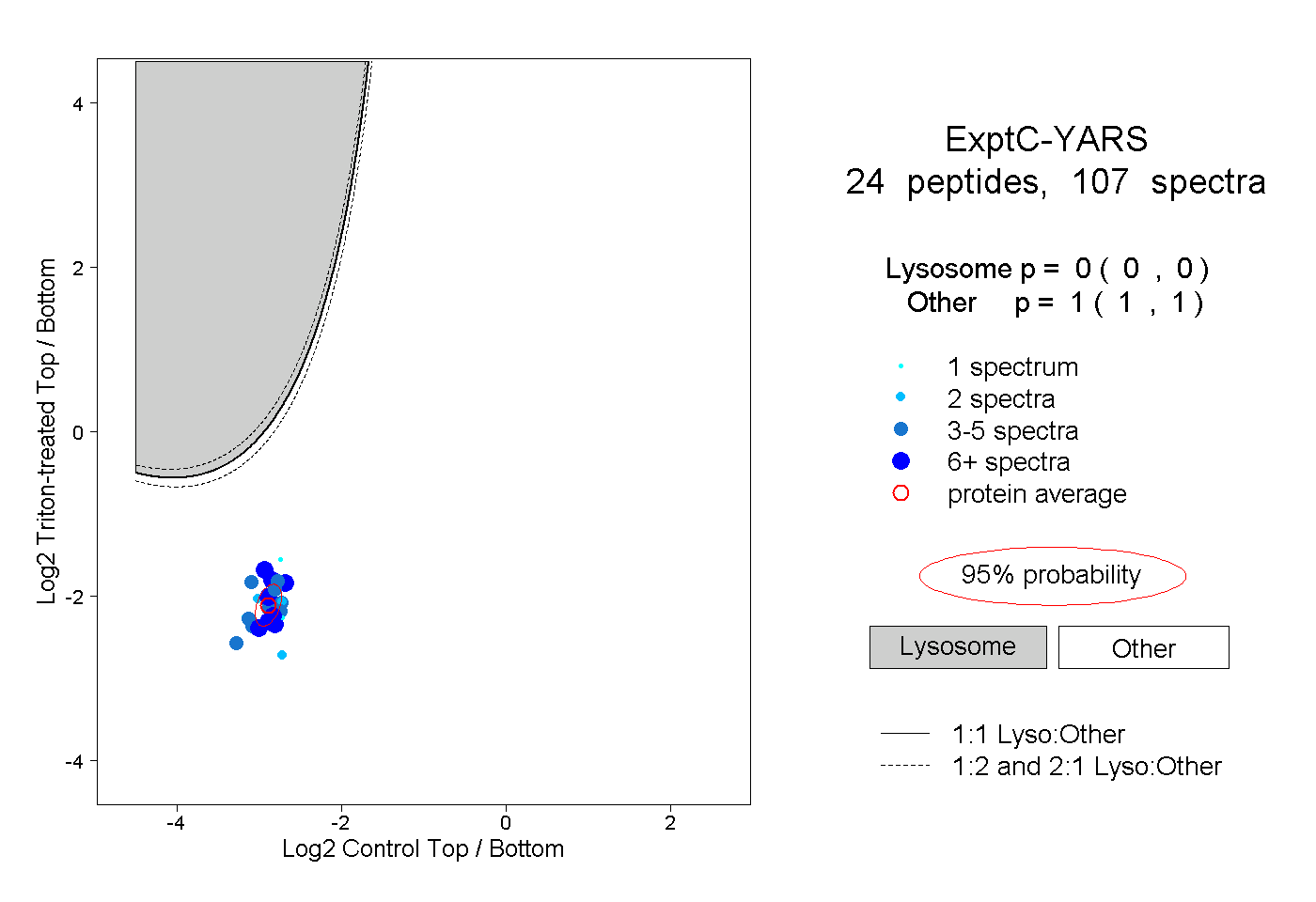 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
13 spectra |
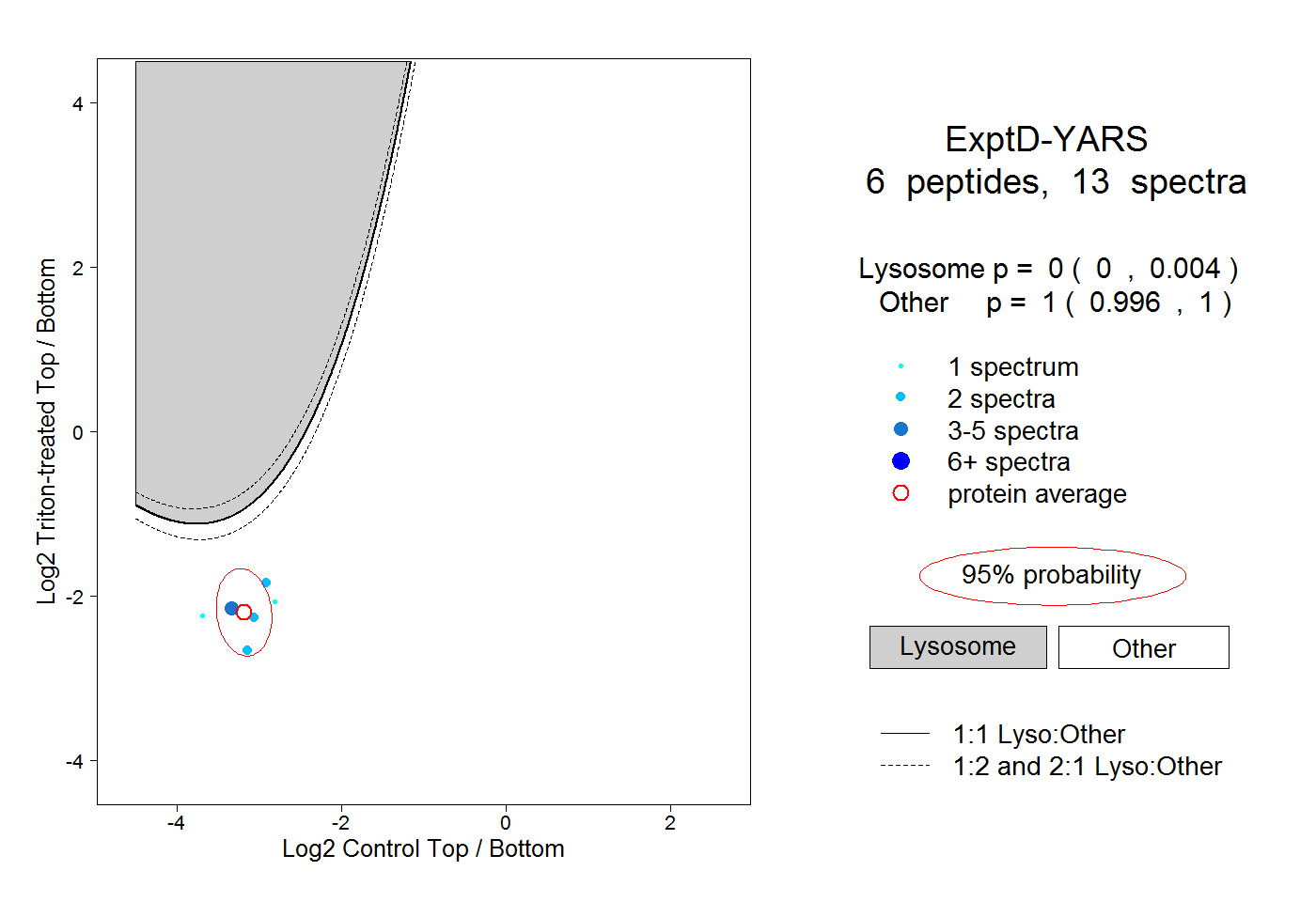 |
0.000 0.000 | 0.004 |
1.000 0.996 | 1.000 |