peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.373 | 0.399
0.018 | 0.041
0.051 | 0.073
0.515 | 0.523
0.000 | 0.000
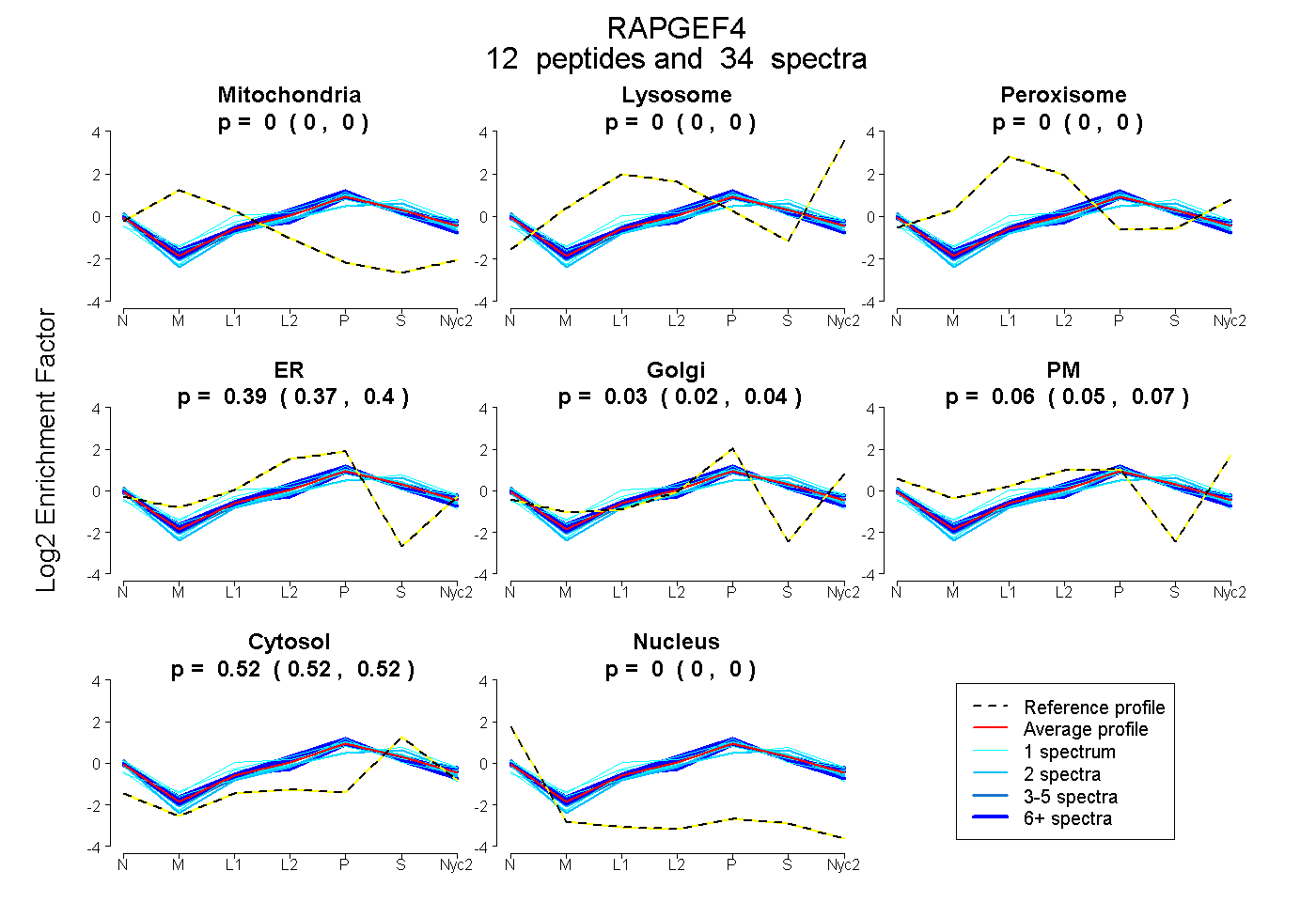
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
34 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.387 0.373 | 0.399 |
0.030 0.018 | 0.041 |
0.063 0.051 | 0.073 |
0.519 0.515 | 0.523 |
0.000 0.000 | 0.000 |
| 1 spectrum, VLLQQFNTGDER | 0.000 | 0.000 | 0.000 | 0.357 | 0.187 | 0.000 | 0.456 | 0.000 | ||
| 1 spectrum, TADDLEIIYDELLHIK | 0.000 | 0.000 | 0.071 | 0.158 | 0.111 | 0.049 | 0.611 | 0.000 | ||
| 2 spectra, GVVCTLHEGDDFGK | 0.000 | 0.000 | 0.000 | 0.251 | 0.000 | 0.139 | 0.610 | 0.000 | ||
| 2 spectra, TFLDNLVNFEK | 0.000 | 0.000 | 0.000 | 0.321 | 0.107 | 0.000 | 0.571 | 0.000 | ||
| 1 spectrum, EVISAVADK | 0.000 | 0.000 | 0.000 | 0.422 | 0.000 | 0.000 | 0.578 | 0.000 | ||
| 1 spectrum, VYCIDHTYTTIR | 0.000 | 0.000 | 0.150 | 0.270 | 0.152 | 0.000 | 0.428 | 0.000 | ||
| 1 spectrum, VPVAASVK | 0.000 | 0.000 | 0.143 | 0.278 | 0.021 | 0.130 | 0.429 | 0.000 | ||
| 6 spectra, LFACPR | 0.000 | 0.000 | 0.000 | 0.513 | 0.002 | 0.000 | 0.486 | 0.000 | ||
| 6 spectra, MIANTAR | 0.000 | 0.000 | 0.000 | 0.397 | 0.064 | 0.079 | 0.460 | 0.000 | ||
| 3 spectra, ILEHFLETIR | 0.000 | 0.000 | 0.000 | 0.442 | 0.018 | 0.053 | 0.486 | 0.000 | ||
| 2 spectra, LEPPLIPFMPLLIK | 0.000 | 0.000 | 0.000 | 0.411 | 0.069 | 0.030 | 0.490 | 0.000 | ||
| 8 spectra, GSDEVLFK | 0.000 | 0.000 | 0.059 | 0.233 | 0.209 | 0.000 | 0.499 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
3 spectra |
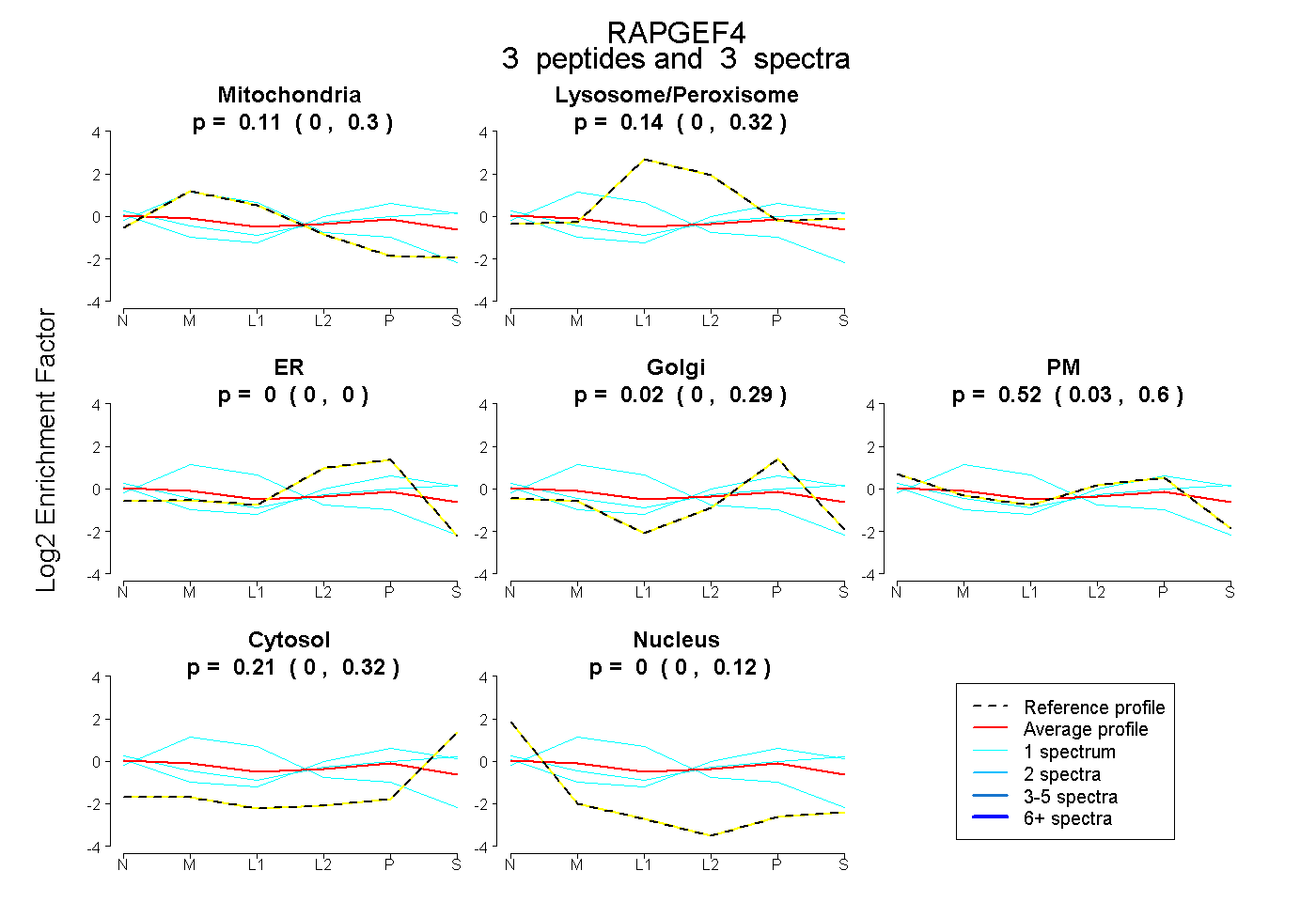 |
0.107 0.000 | 0.296 |
0.141 0.000 | 0.319 |
0.000 0.000 | 0.000 |
0.022 0.000 | 0.291 |
0.516 0.031 | 0.597 |
0.215 0.000 | 0.320 |
0.000 0.000 | 0.120 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
22 spectra |
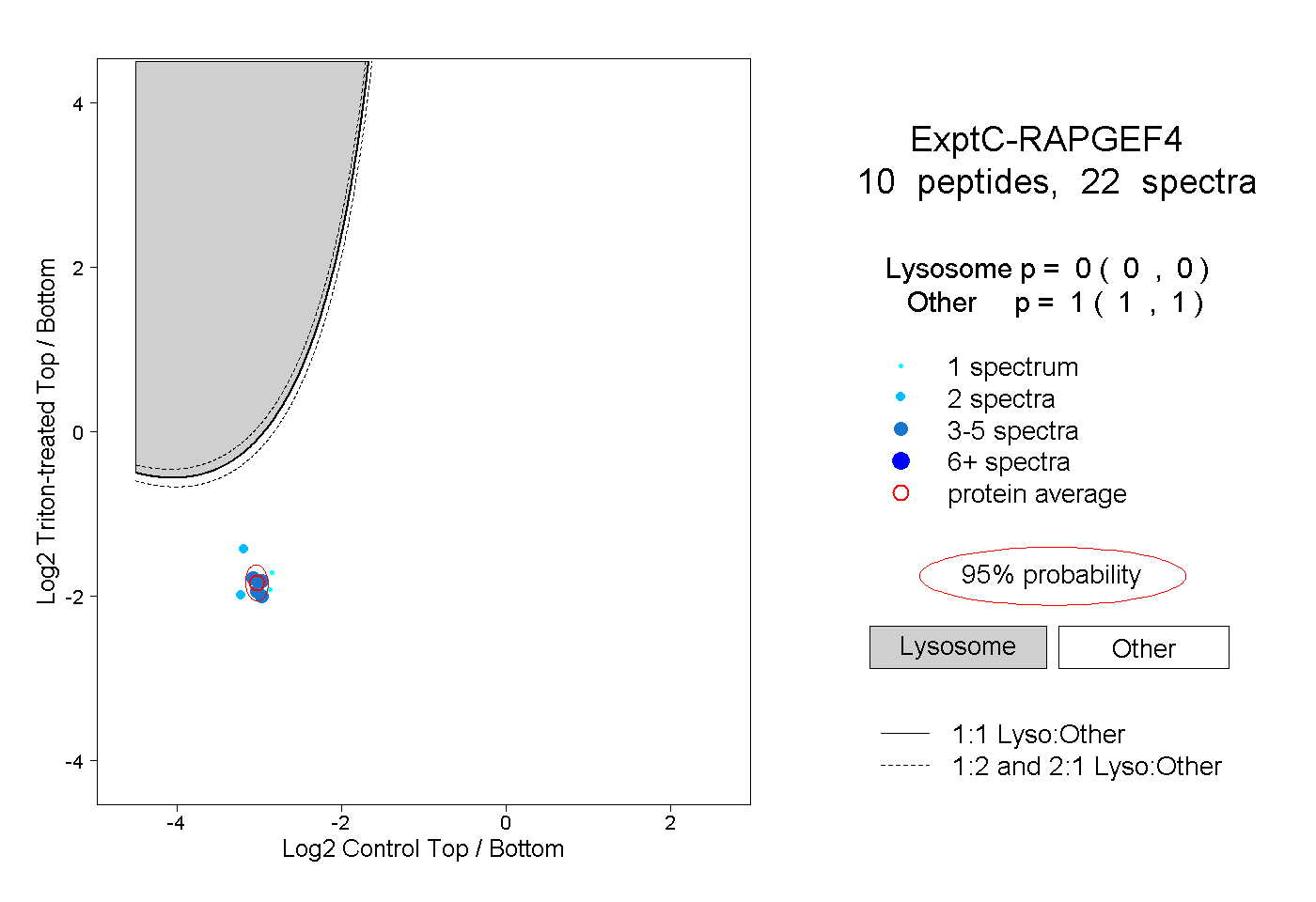 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |