peptides
spectra
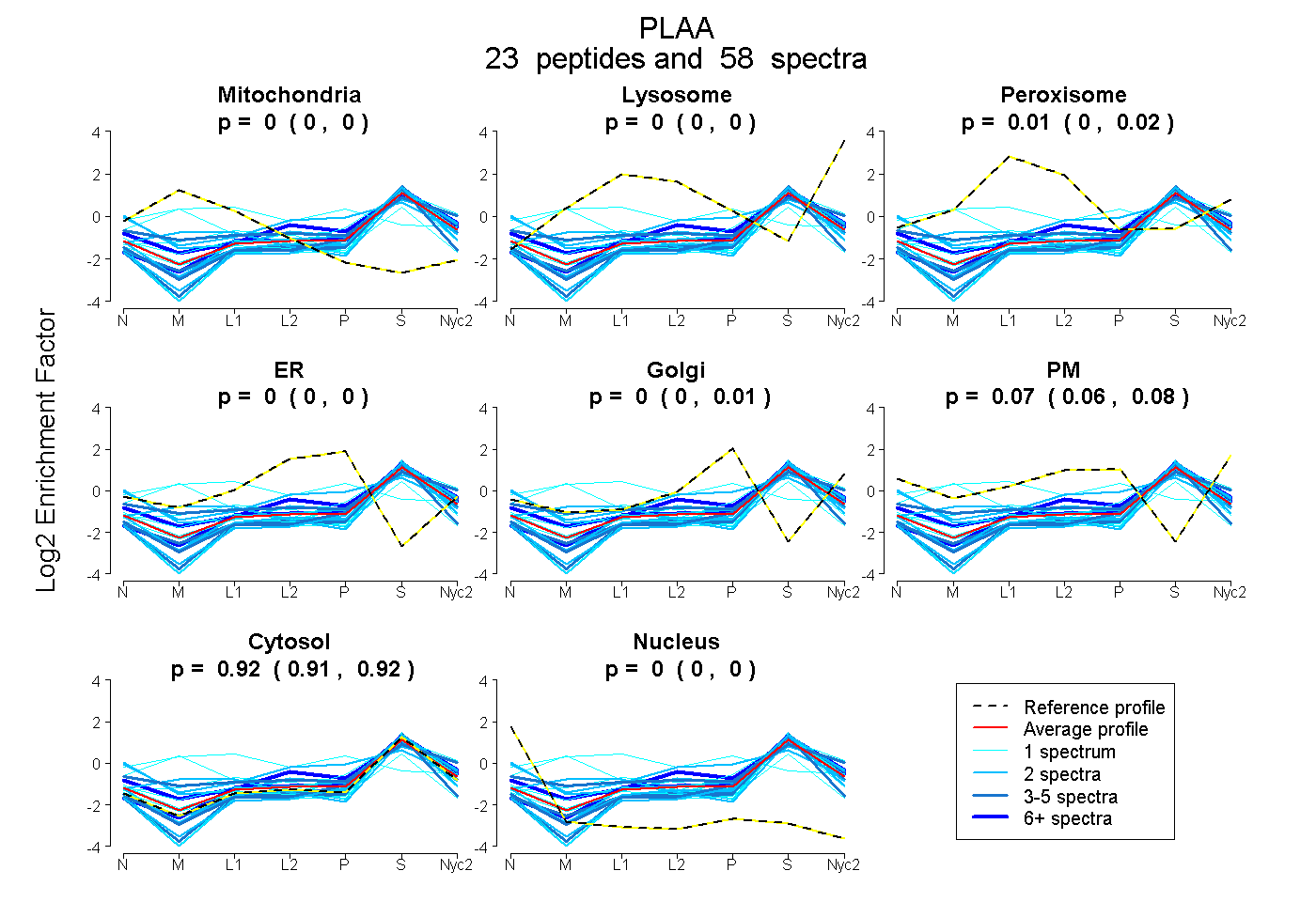
0.000 | 0.002
0.000 | 0.002
0.003 | 0.017
0.000 | 0.000
0.000 | 0.008
0.057 | 0.076
0.912 | 0.922
0.000 | 0.000
peptides
spectra
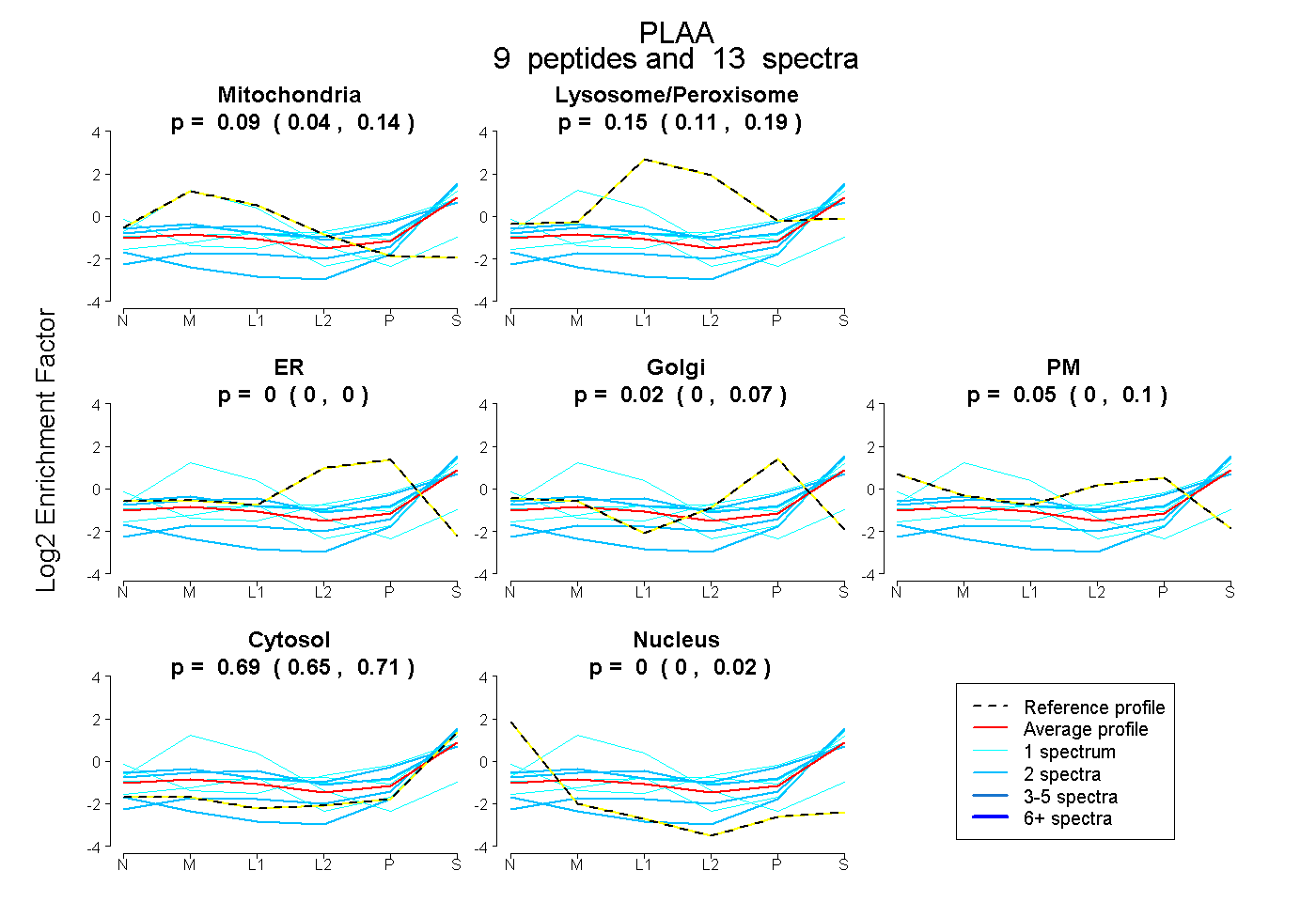
0.038 | 0.137
0.113 | 0.185
0.000 | 0.000
0.000 | 0.073
0.000 | 0.099
0.652 | 0.711
0.000 | 0.018
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
58 spectra |
 |
0.000 0.000 | 0.002 |
0.000 0.000 | 0.002 |
0.010 0.003 | 0.017 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.008 |
0.072 0.057 | 0.076 |
0.918 0.912 | 0.922 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
13 spectra |
 |
0.093 0.038 | 0.137 |
0.149 0.113 | 0.185 |
0.000 0.000 | 0.000 |
0.022 0.000 | 0.073 |
0.049 0.000 | 0.099 |
0.687 0.652 | 0.711 |
0.000 0.000 | 0.018 |
| 2 spectra, EHLNEPGTR | 0.000 | 0.043 | 0.000 | 0.000 | 0.000 | 0.957 | 0.000 | |||
| 1 spectrum, LWAPDSPNR | 0.000 | 0.086 | 0.000 | 0.005 | 0.358 | 0.550 | 0.000 | |||
| 1 spectrum, LILNLL | 0.854 | 0.000 | 0.000 | 0.000 | 0.000 | 0.146 | 0.000 | |||
| 1 spectrum, ILPEQGLMLTGSADK | 0.000 | 0.300 | 0.000 | 0.000 | 0.039 | 0.661 | 0.000 | |||
| 1 spectrum, GQTLGLGNTSFSDPFTGGGR | 0.073 | 0.196 | 0.000 | 0.000 | 0.157 | 0.574 | 0.000 | |||
| 2 spectra, TFCNCFVSQAGQK | 0.010 | 0.242 | 0.000 | 0.161 | 0.108 | 0.478 | 0.000 | |||
| 2 spectra, DFVTTAEDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.957 | 0.043 | |||
| 1 spectrum, GKPANQLLALR | 0.072 | 0.099 | 0.000 | 0.000 | 0.000 | 0.829 | 0.000 | |||
| 2 spectra, LSCSLPGHELDVR | 0.083 | 0.281 | 0.000 | 0.050 | 0.025 | 0.561 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
61 spectra |
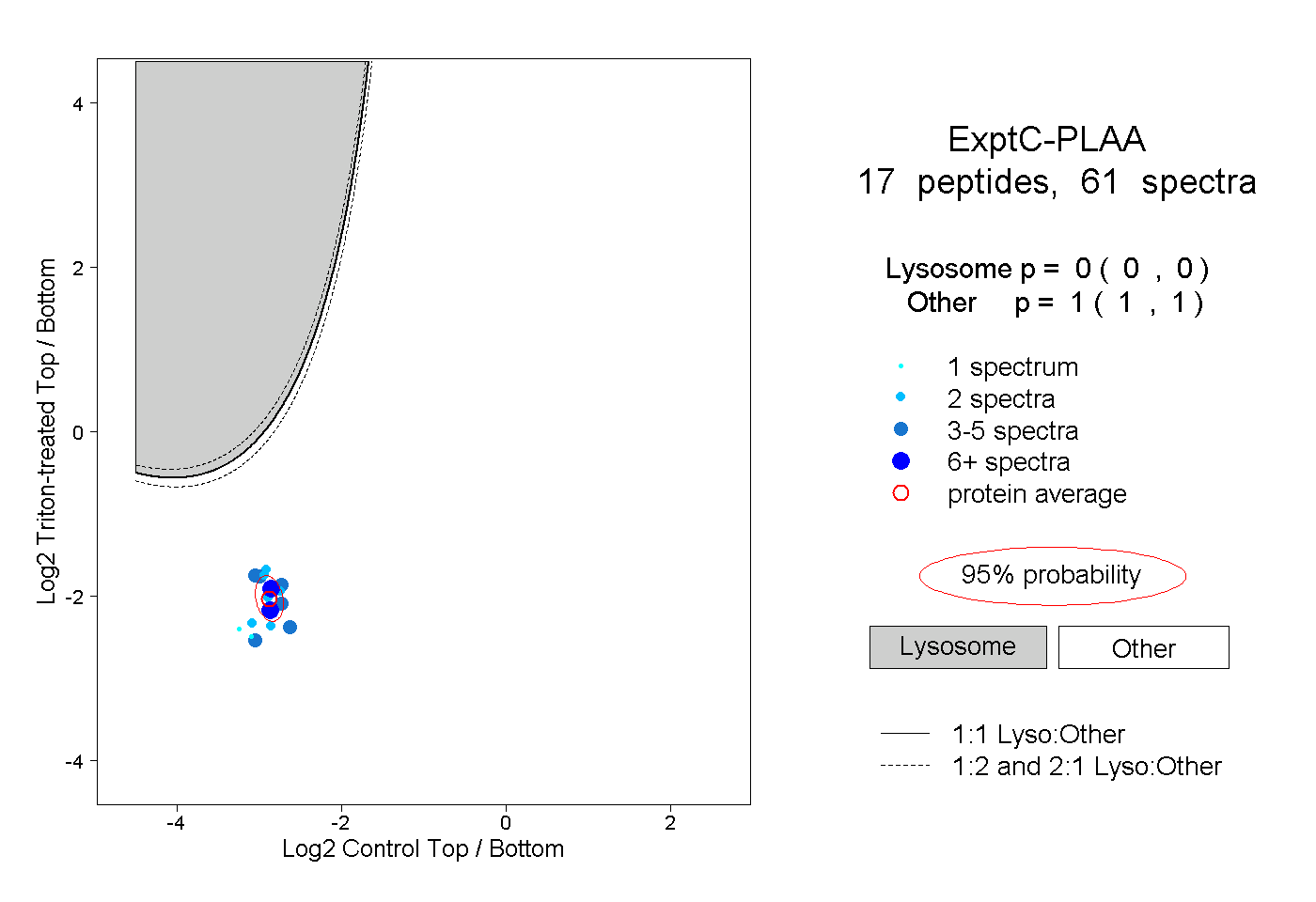 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
7 spectra |
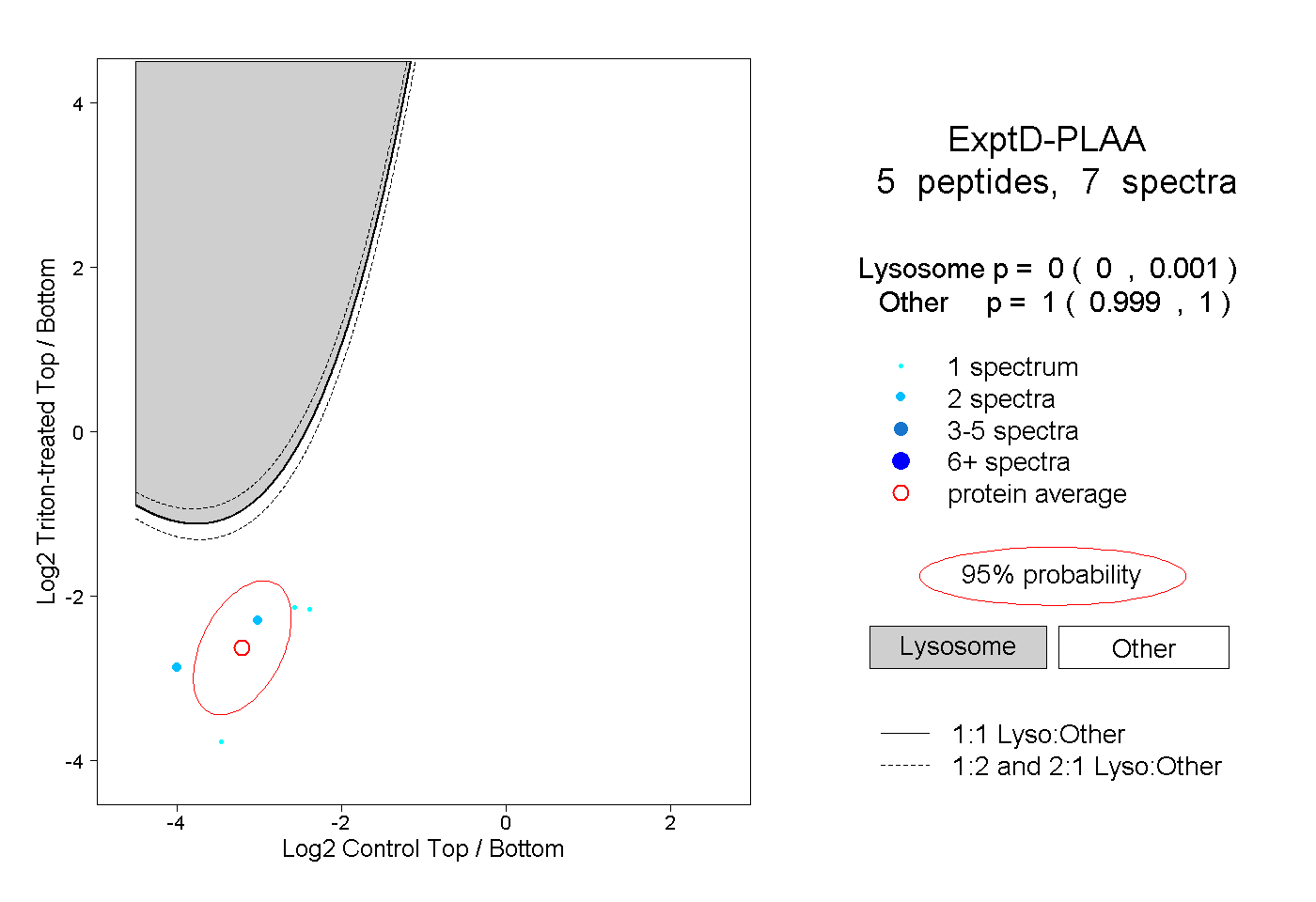 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |