peptides
spectra
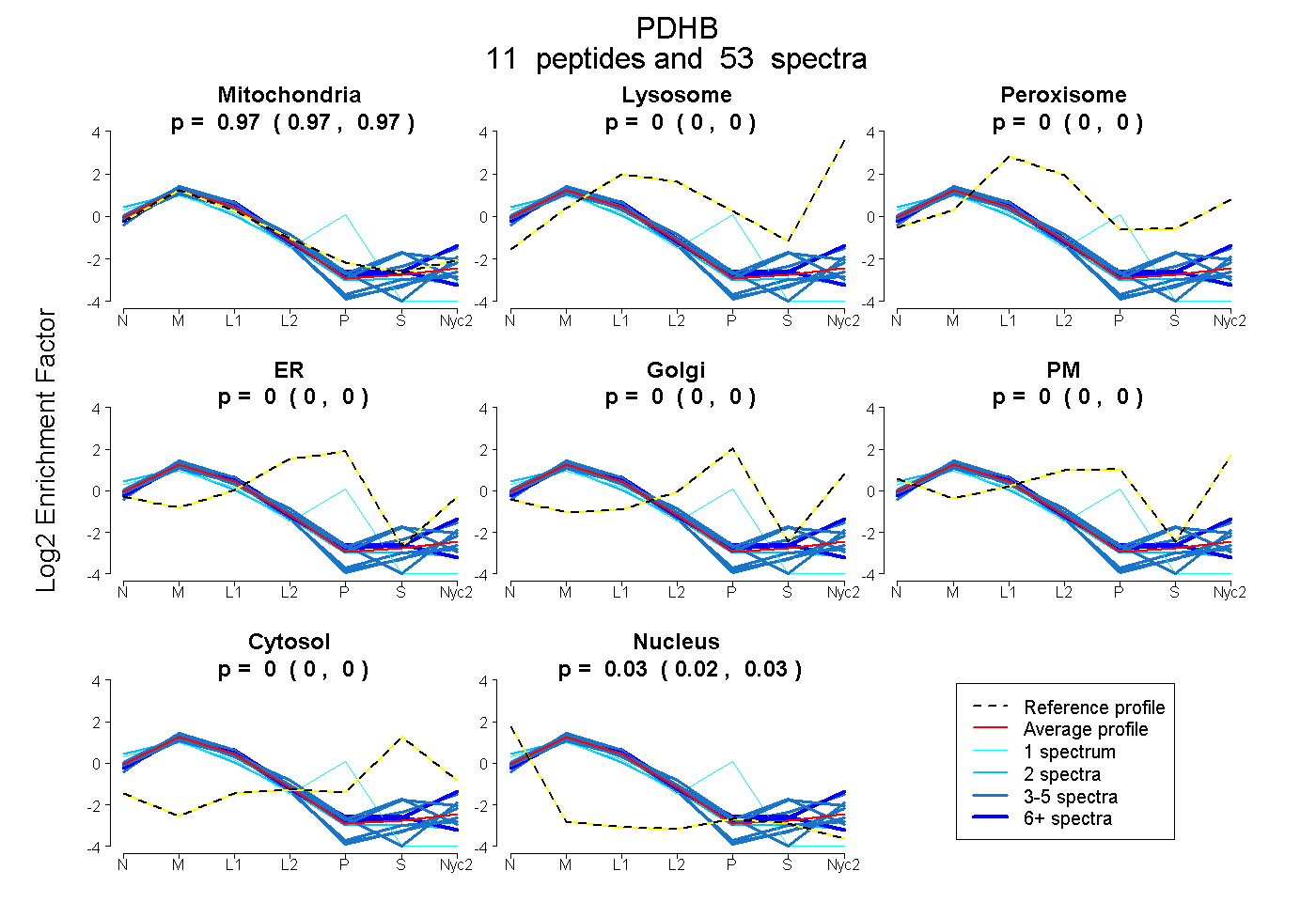
0.968 | 0.975
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.025 | 0.031
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
53 spectra |
 |
0.972 0.968 | 0.975 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.028 0.025 | 0.031 |
| 3 spectra, VTGADVPMPYAK | 0.911 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.089 | 0.000 | ||
| 4 spectra, IMEGPAFNFLDAPAVR | 0.984 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.016 | ||
| 14 spectra, EGIECEVINLR | 0.961 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.039 | ||
| 3 spectra, ILEDNSIPQVK | 0.958 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.042 | ||
| 5 spectra, TIRPMDIEAIEASVMK | 0.990 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.010 | ||
| 2 spectra, DFLIPIGK | 0.852 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.148 | ||
| 5 spectra, EAINQGMDEELER | 0.962 | 0.017 | 0.000 | 0.000 | 0.000 | 0.000 | 0.021 | 0.000 | ||
| 1 spectrum, TNHLVTVEGGWPQFGVGAEICAR | 0.669 | 0.000 | 0.000 | 0.173 | 0.000 | 0.000 | 0.000 | 0.158 | ||
| 4 spectra, VVSPWNSEDAK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, VFLLGEEVAQYDGAYK | 0.925 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.049 | 0.026 | ||
| 7 spectra, TYYMSAGLQPVPIVFR | 0.951 | 0.045 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.005 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
27 spectra |
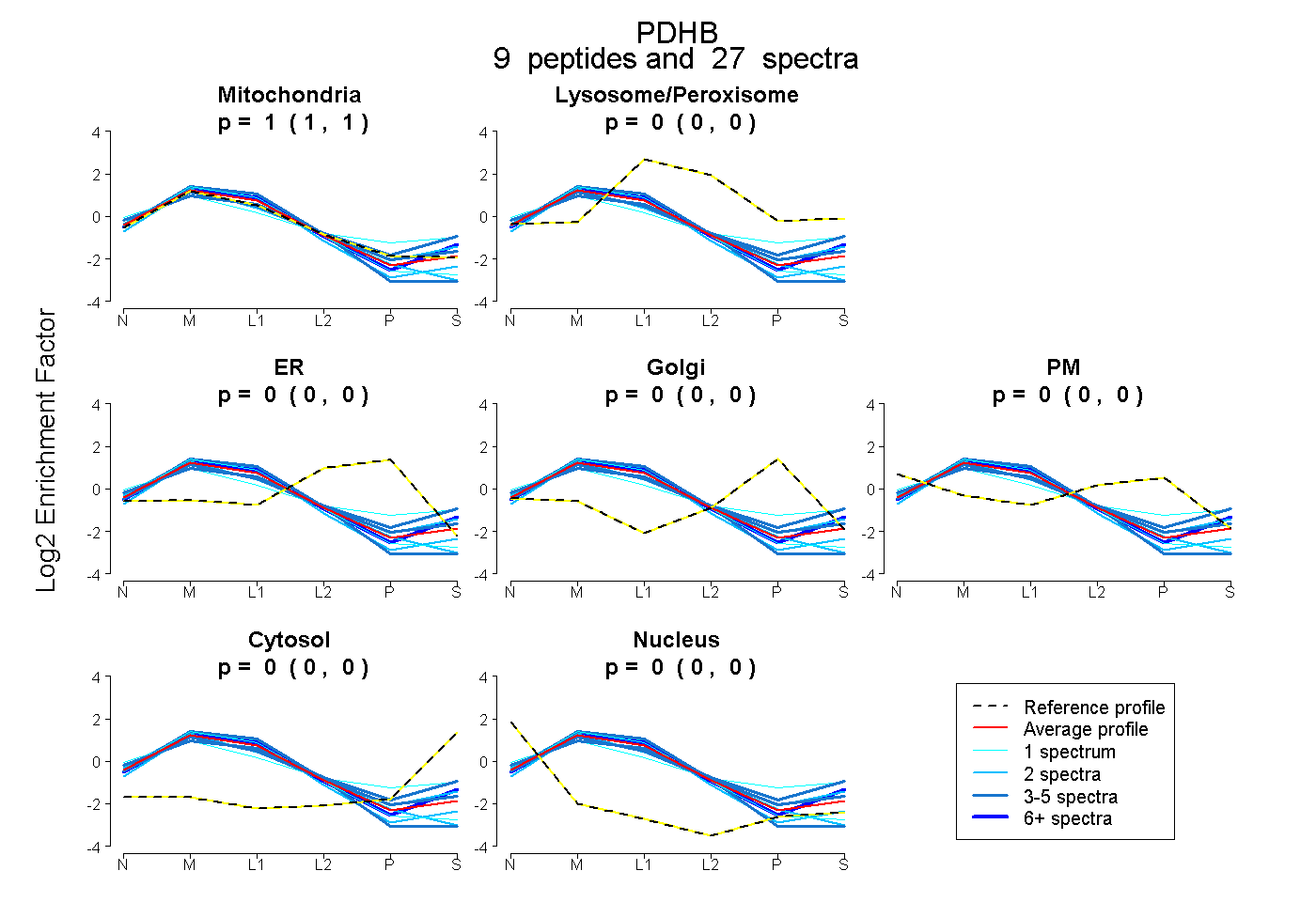 |
1.000 0.995 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.004 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
161 spectra |
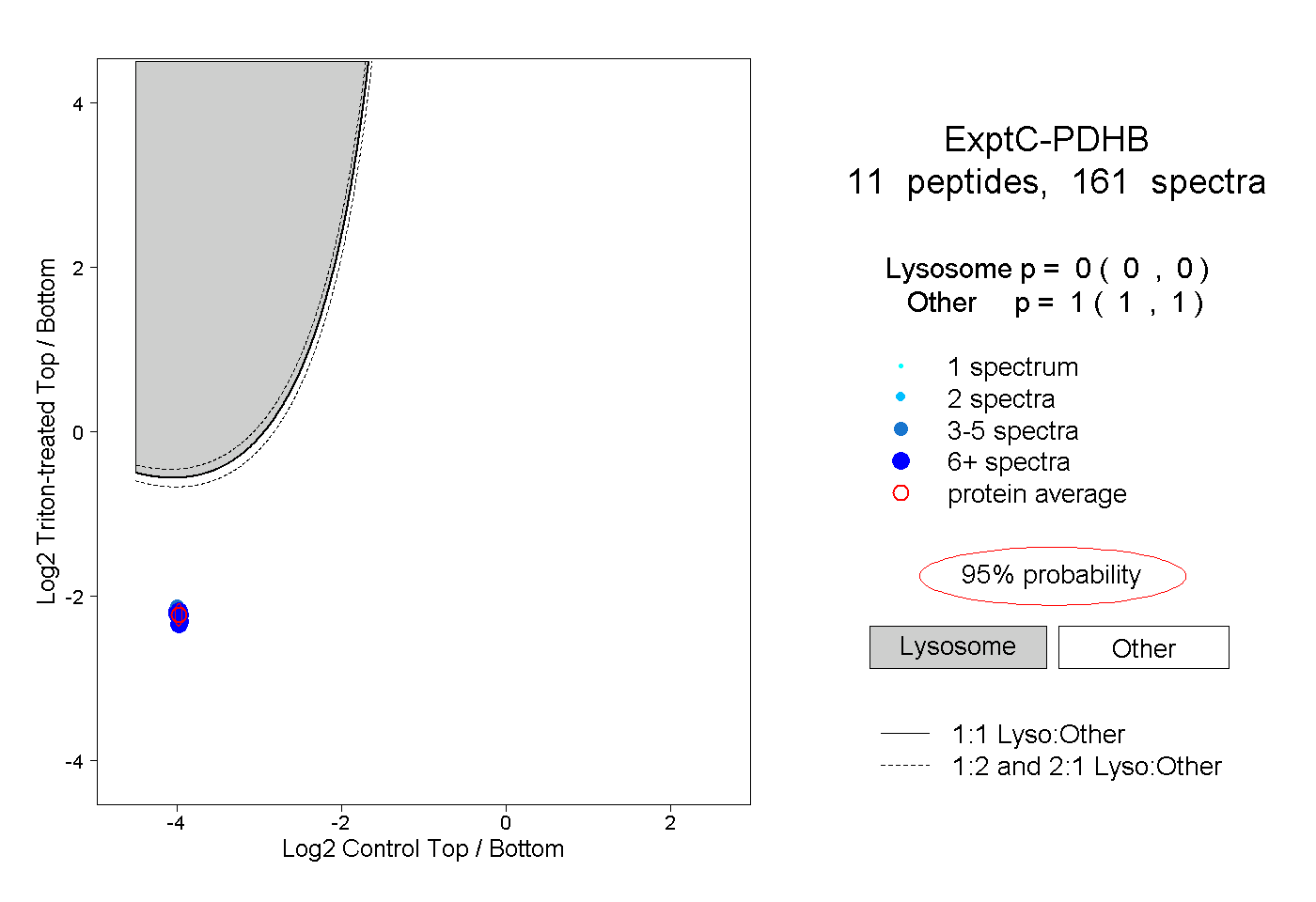 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
13 spectra |
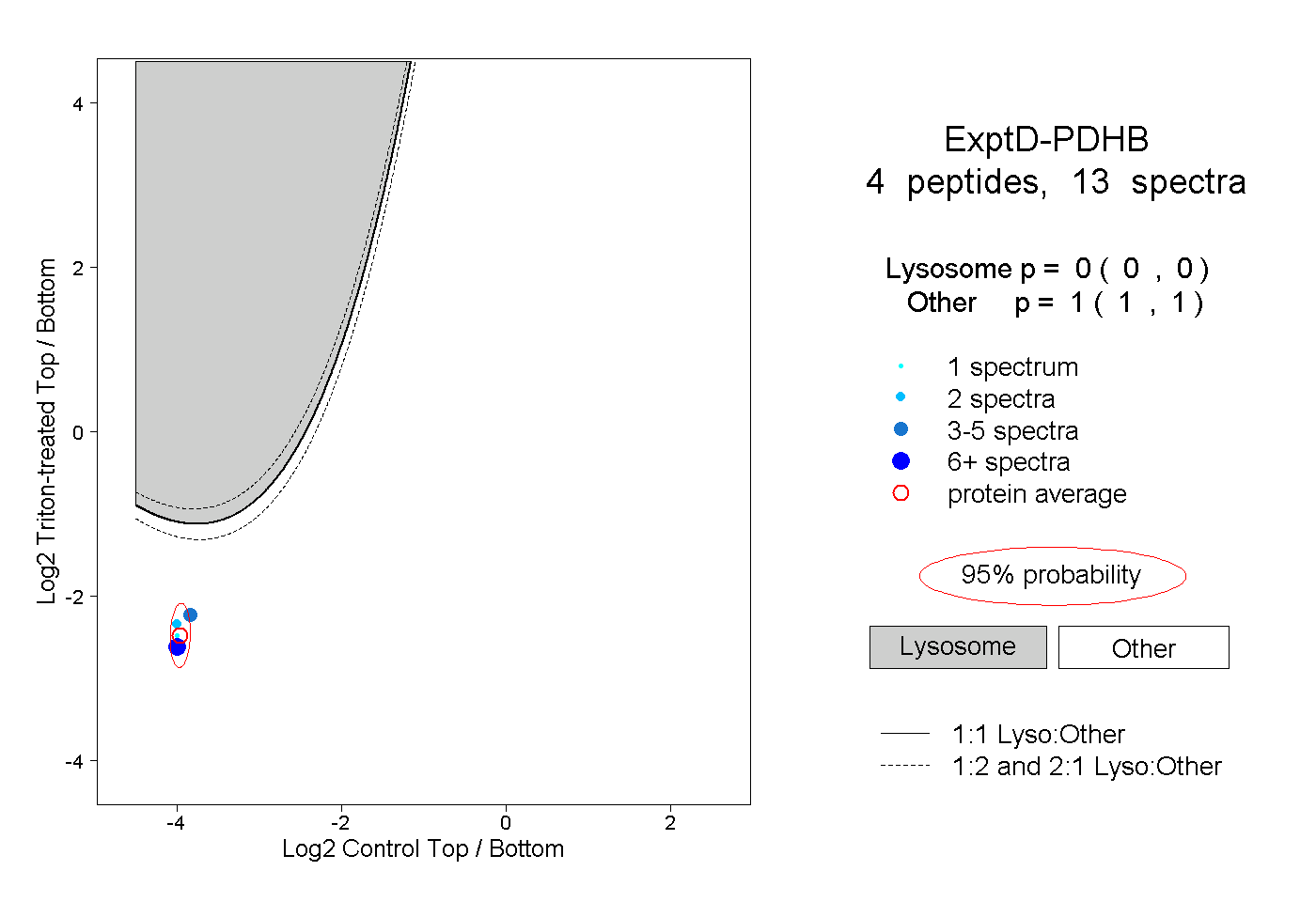 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |