peptides
spectra
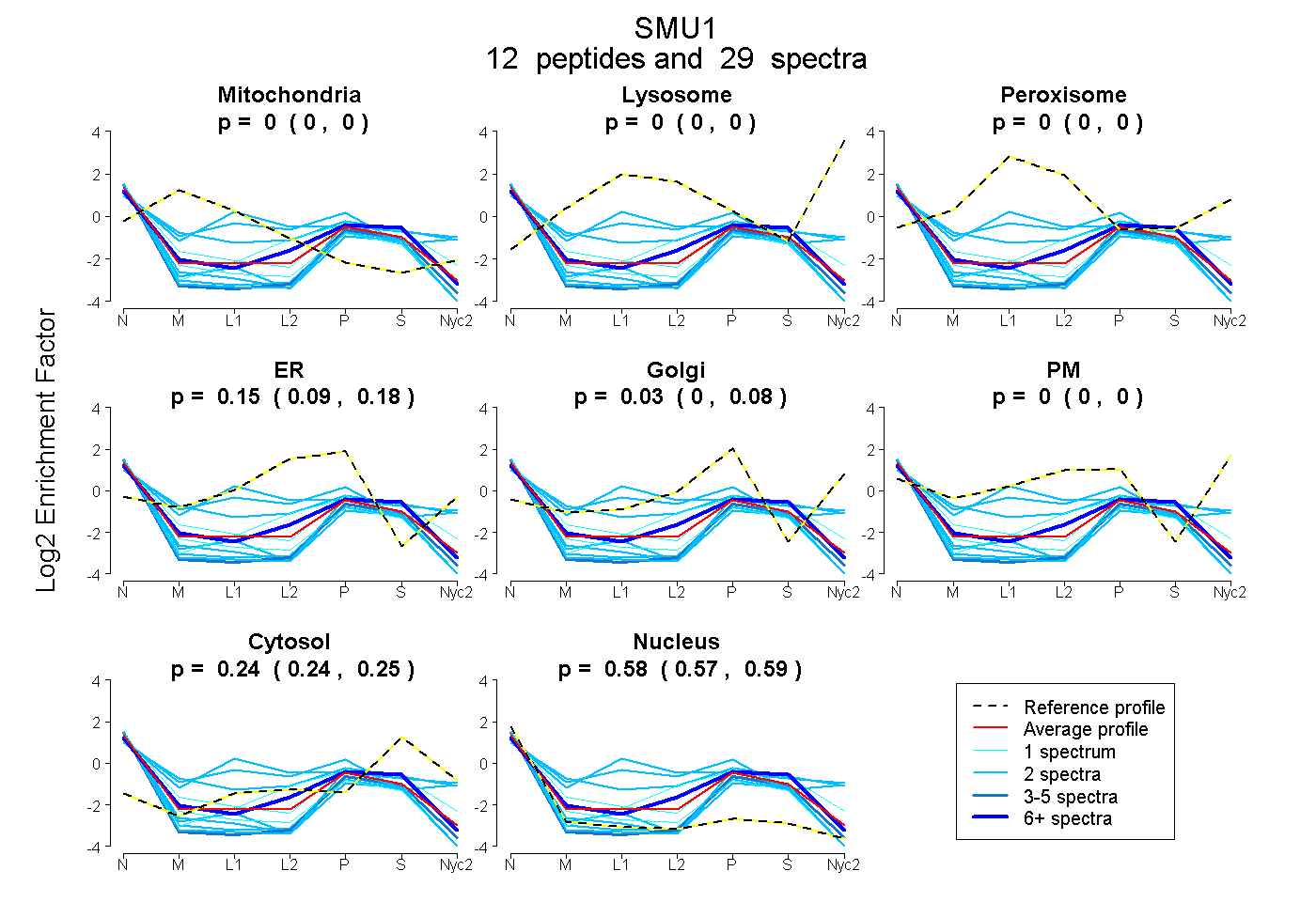
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.093 | 0.181
0.000 | 0.080
0.000 | 0.000
0.235 | 0.249
0.567 | 0.590
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
29 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.149 0.093 | 0.181 |
0.028 0.000 | 0.080 |
0.000 0.000 | 0.000 |
0.244 0.235 | 0.249 |
0.580 0.567 | 0.590 |
| 2 spectra, EGGDFVCCALSPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.018 | 0.000 | 0.183 | 0.799 | ||
| 1 spectrum, SHVECAR | 0.000 | 0.000 | 0.000 | 0.223 | 0.000 | 0.000 | 0.329 | 0.448 | ||
| 4 spectra, LIMQYLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.014 | 0.000 | 0.230 | 0.756 | ||
| 1 spectrum, QTDPMIMLK | 0.000 | 0.000 | 0.000 | 0.191 | 0.000 | 0.000 | 0.174 | 0.635 | ||
| 2 spectra, ELGAAR | 0.113 | 0.000 | 0.000 | 0.000 | 0.054 | 0.308 | 0.294 | 0.233 | ||
| 1 spectrum, QTQPER | 0.000 | 0.000 | 0.000 | 0.073 | 0.000 | 0.000 | 0.168 | 0.759 | ||
| 2 spectra, NPEHFVVCNR | 0.000 | 0.000 | 0.290 | 0.065 | 0.241 | 0.048 | 0.025 | 0.332 | ||
| 2 spectra, DSSQILSASFDQTIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.001 | 0.000 | 0.223 | 0.776 | ||
| 2 spectra, TTECSNTFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.031 | 0.000 | 0.181 | 0.788 | ||
| 8 spectra, YIHLENLLAR | 0.000 | 0.000 | 0.000 | 0.177 | 0.000 | 0.000 | 0.302 | 0.520 | ||
| 2 spectra, DTEMLATGAQDGK | 0.000 | 0.000 | 0.385 | 0.012 | 0.000 | 0.155 | 0.131 | 0.317 | ||
| 2 spectra, IQSGQCLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.034 | 0.000 | 0.188 | 0.778 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
5 spectra |
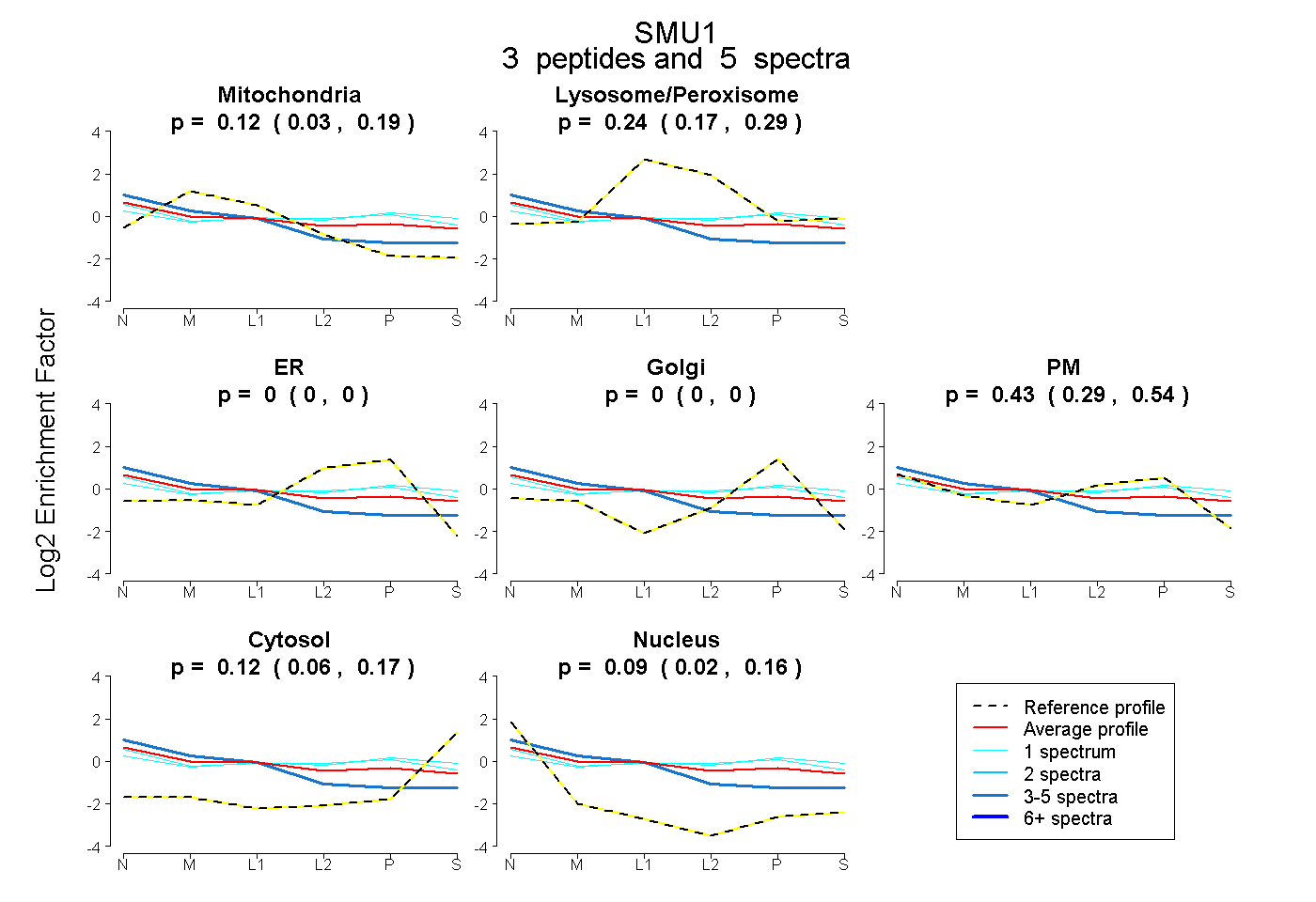 |
0.121 0.032 | 0.191 |
0.236 0.169 | 0.290 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.427 0.292 | 0.541 |
0.122 0.065 | 0.170 |
0.094 0.019 | 0.156 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
2 spectra |
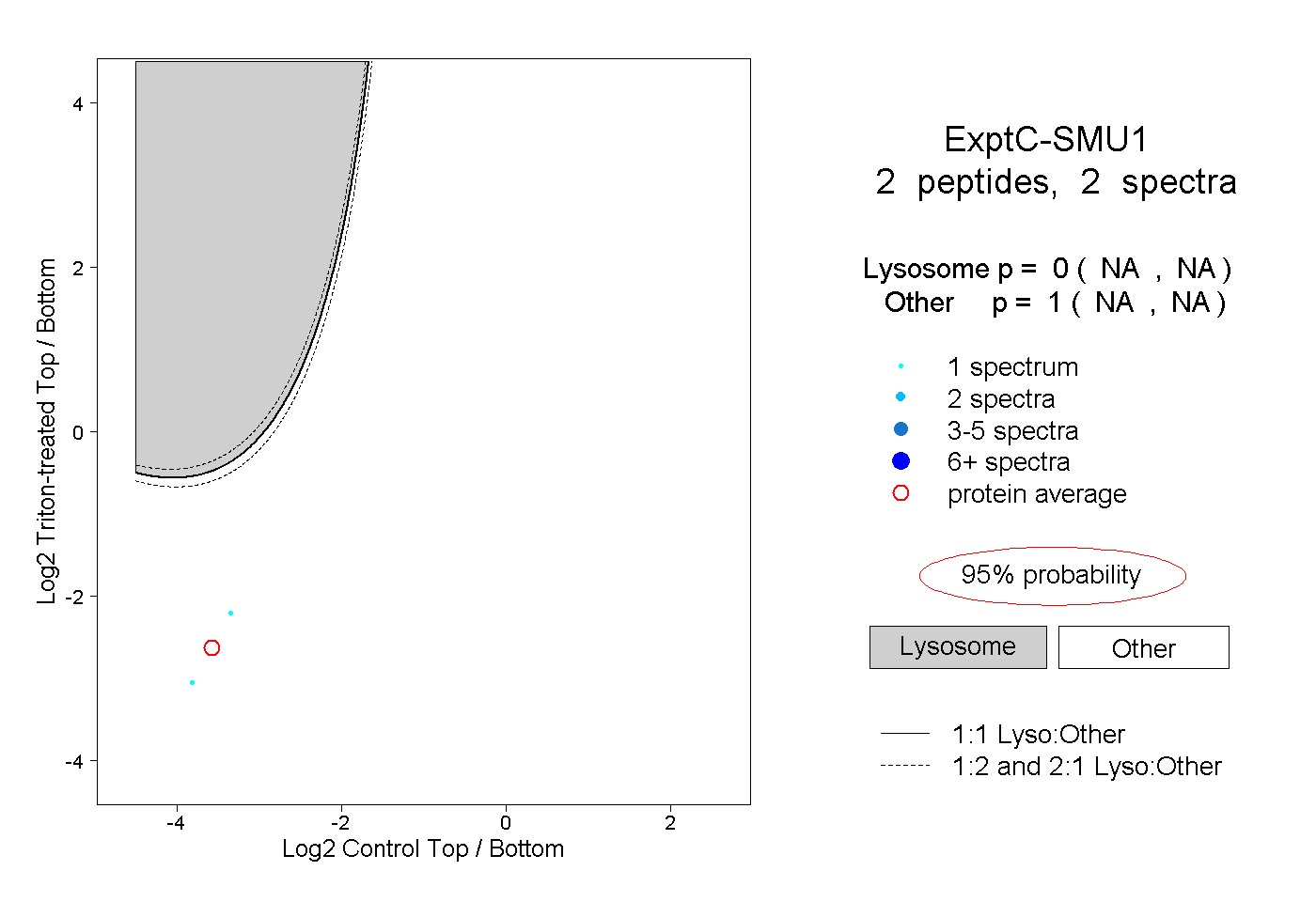 |
0.000 NA | NA |
1.000 NA | NA |