peptides
spectra
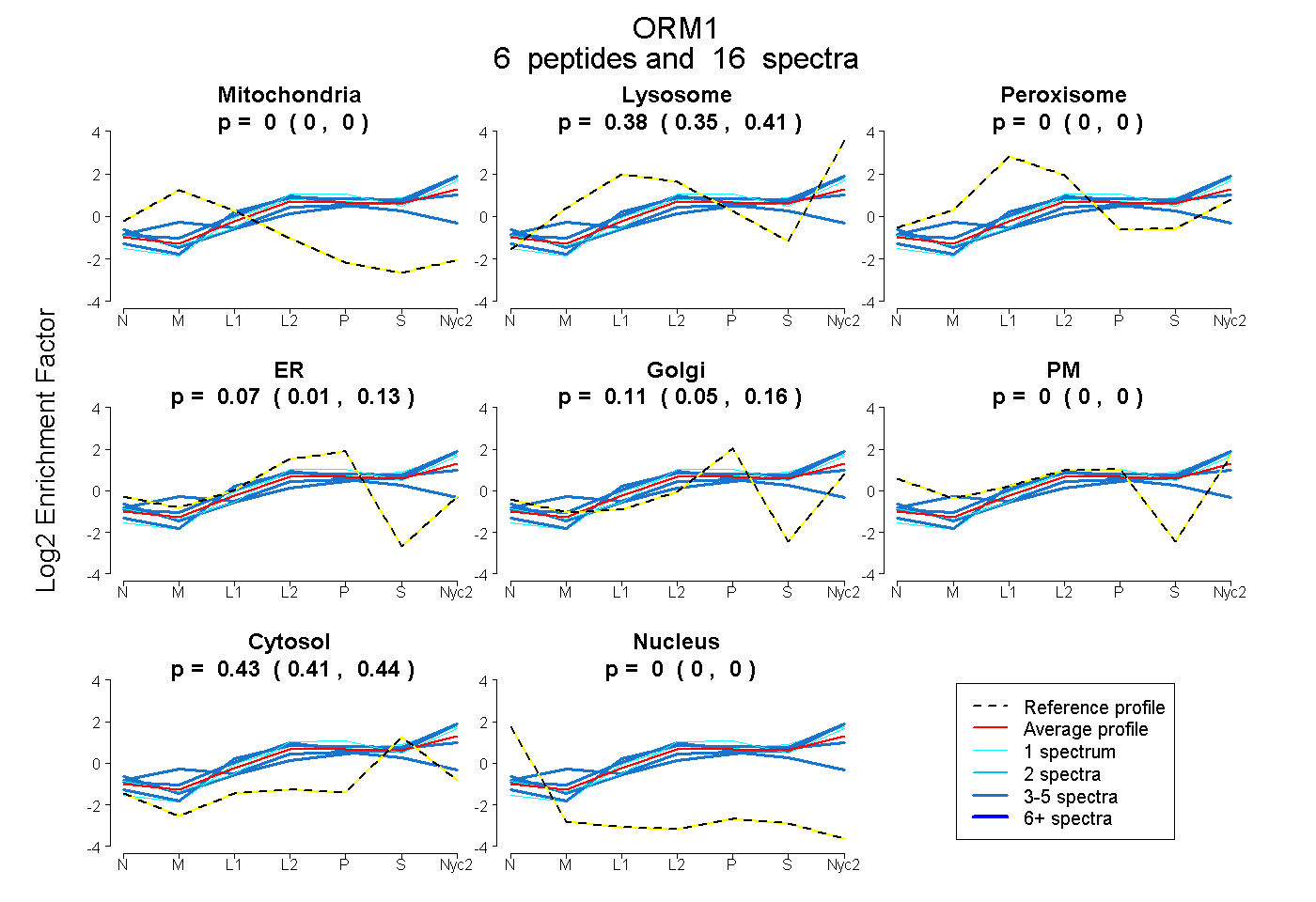
0.000 | 0.000
0.353 | 0.405
0.000 | 0.000
0.007 | 0.130
0.055 | 0.158
0.000 | 0.000
0.414 | 0.444
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
16 spectra |
 |
0.000 0.000 | 0.000 |
0.382 0.353 | 0.405 |
0.000 0.000 | 0.000 |
0.075 0.007 | 0.130 |
0.113 0.055 | 0.158 |
0.000 0.000 | 0.000 |
0.430 0.414 | 0.444 |
0.000 0.000 | 0.000 |
| 4 spectra, KPDLSPELR | 0.000 | 0.495 | 0.000 | 0.000 | 0.093 | 0.000 | 0.412 | 0.000 | ||
| 1 spectrum, DVGMDESEIVFVDWTK | 0.000 | 0.467 | 0.000 | 0.000 | 0.072 | 0.000 | 0.461 | 0.000 | ||
| 3 spectra, IFQQAVK | 0.000 | 0.499 | 0.000 | 0.006 | 0.095 | 0.031 | 0.369 | 0.000 | ||
| 3 spectra, CAGAVK | 0.000 | 0.240 | 0.000 | 0.000 | 0.134 | 0.113 | 0.513 | 0.000 | ||
| 1 spectrum, WFYMGAAFR | 0.000 | 0.380 | 0.000 | 0.017 | 0.253 | 0.000 | 0.350 | 0.000 | ||
| 4 spectra, QQLELEK | 0.000 | 0.000 | 0.232 | 0.234 | 0.125 | 0.000 | 0.409 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
4 spectra |
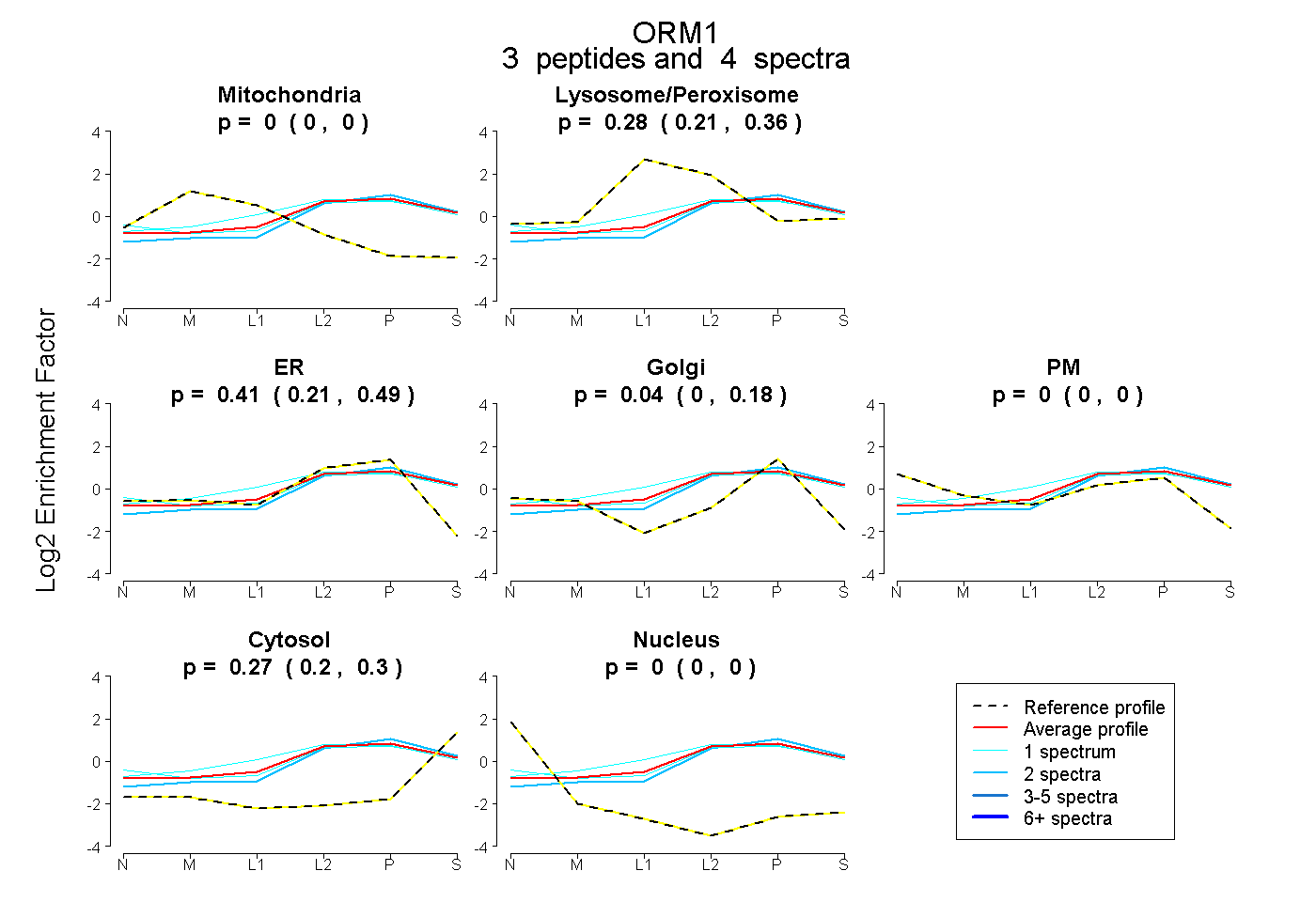 |
0.000 0.000 | 0.000 |
0.277 0.211 | 0.363 |
0.413 0.212 | 0.487 |
0.042 0.000 | 0.176 |
0.000 0.000 | 0.000 |
0.268 0.205 | 0.297 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
111 spectra |
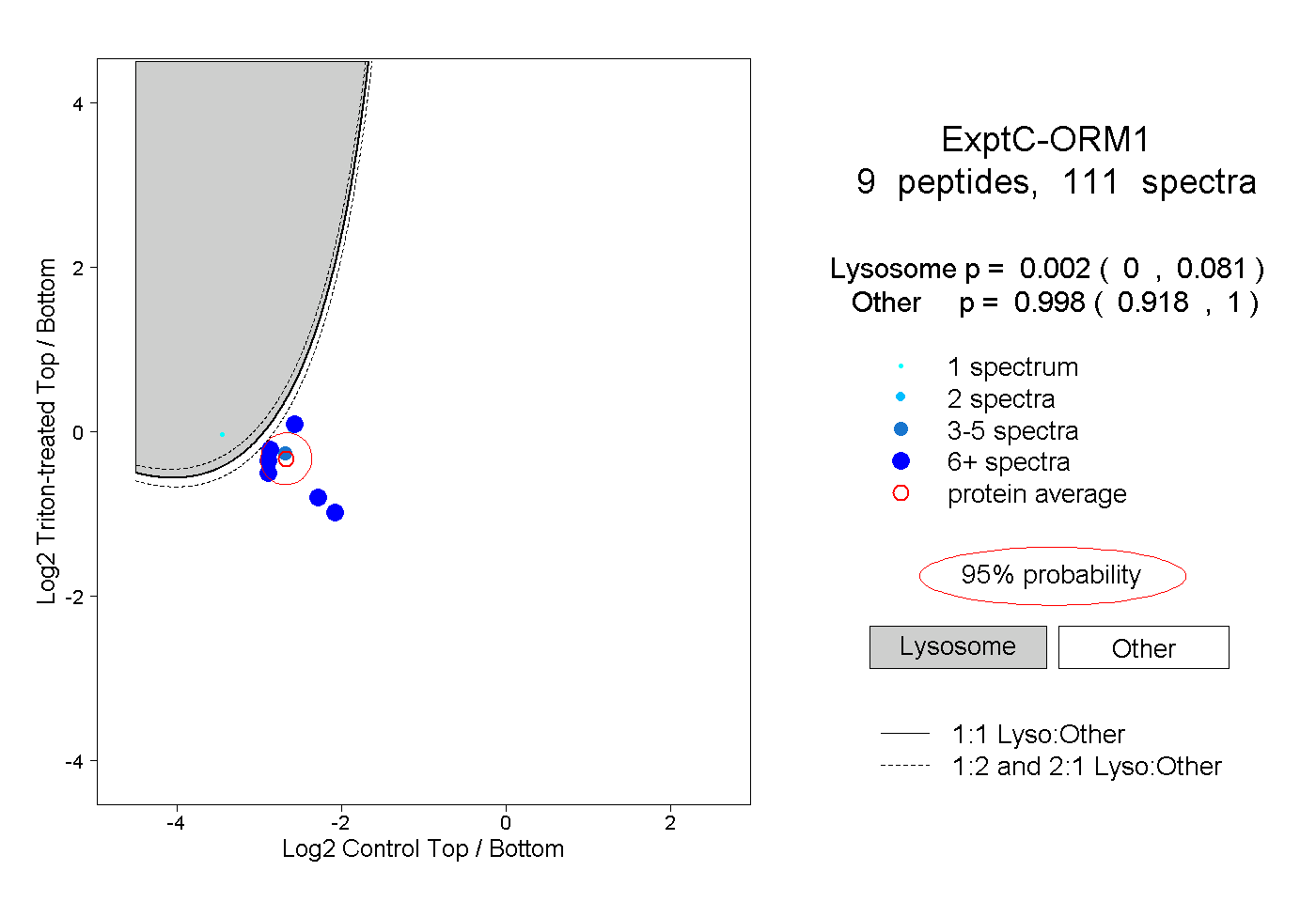 |
0.002 0.000 | 0.081 |
0.998 0.918 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
6 spectra |
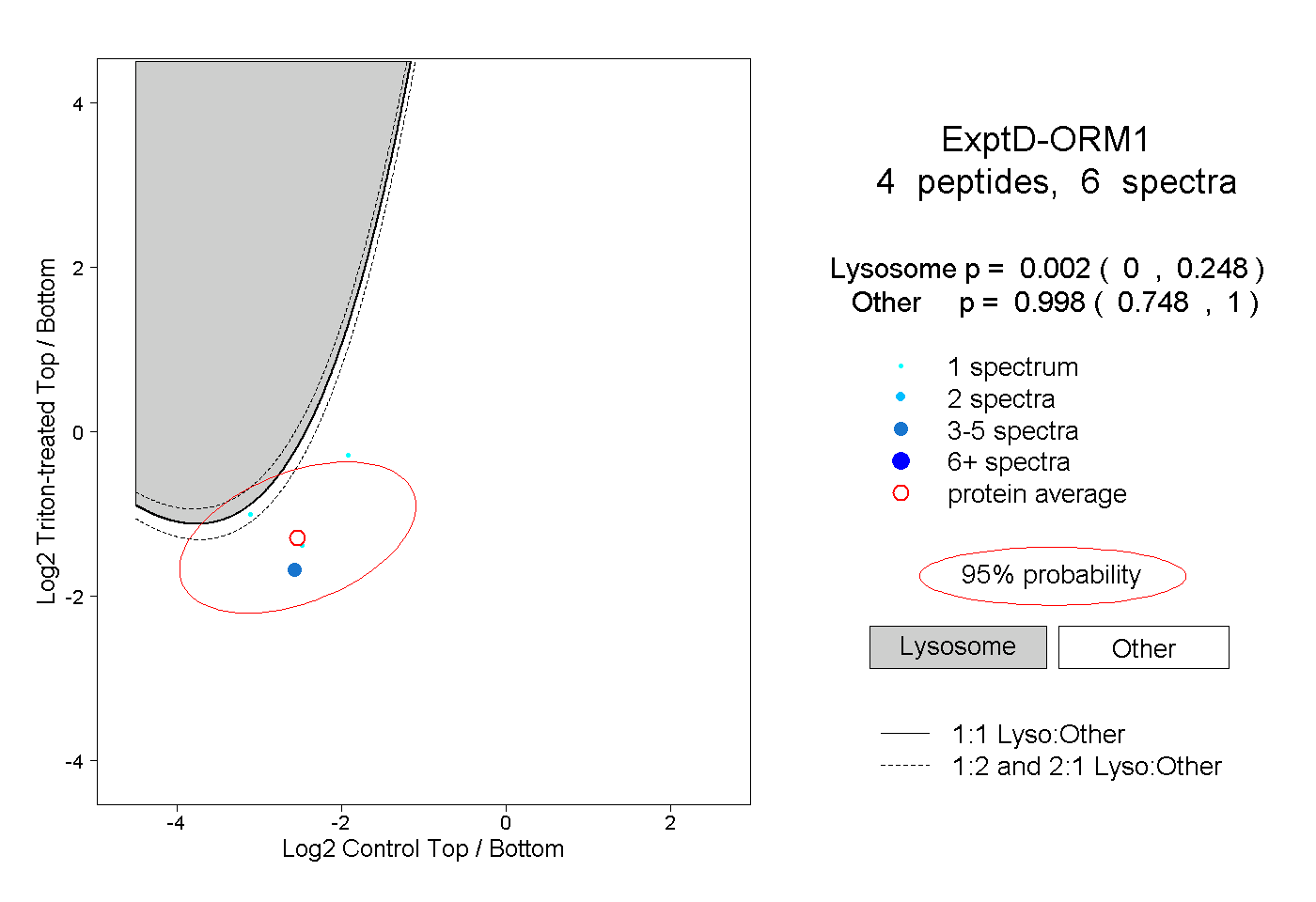 |
0.002 0.000 | 0.248 |
0.998 0.748 | 1.000 |