peptides
spectra
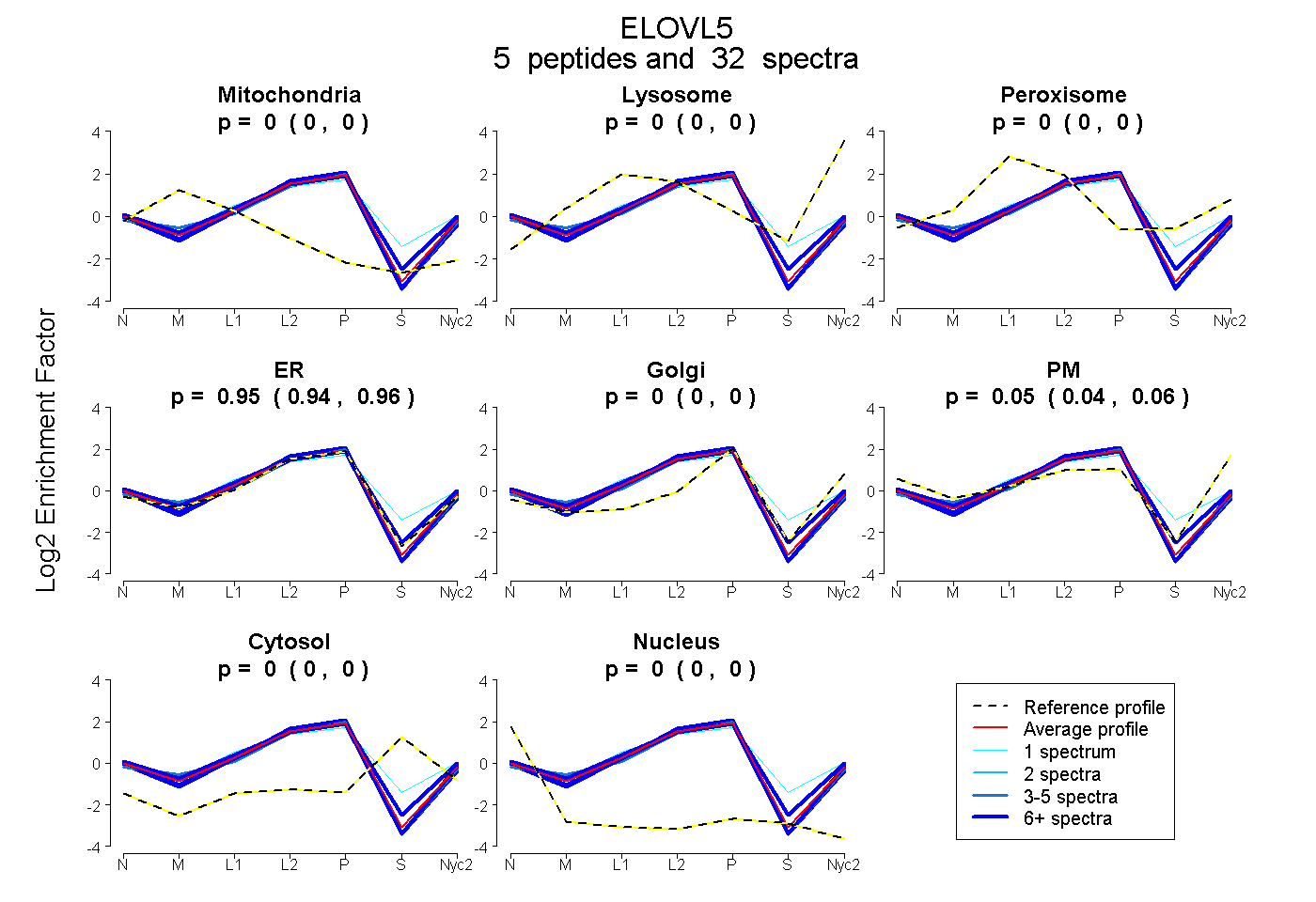
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.938 | 0.960
0.000 | 0.000
0.038 | 0.059
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
32 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.950 0.938 | 0.960 |
0.000 0.000 | 0.000 |
0.050 0.038 | 0.059 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 9 spectra, YNFFCQGTR | 0.000 | 0.000 | 0.000 | 0.918 | 0.000 | 0.082 | 0.000 | 0.000 | ||
| 1 spectrum, QPFSCR | 0.000 | 0.000 | 0.208 | 0.656 | 0.081 | 0.000 | 0.055 | 0.000 | ||
| 8 spectra, SAGESDMK | 0.000 | 0.000 | 0.000 | 0.854 | 0.000 | 0.139 | 0.006 | 0.000 | ||
| 4 spectra, MEHFDASLSTYFR | 0.022 | 0.000 | 0.000 | 0.975 | 0.000 | 0.003 | 0.000 | 0.000 | ||
| 10 spectra, ALLGPR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
10 spectra |
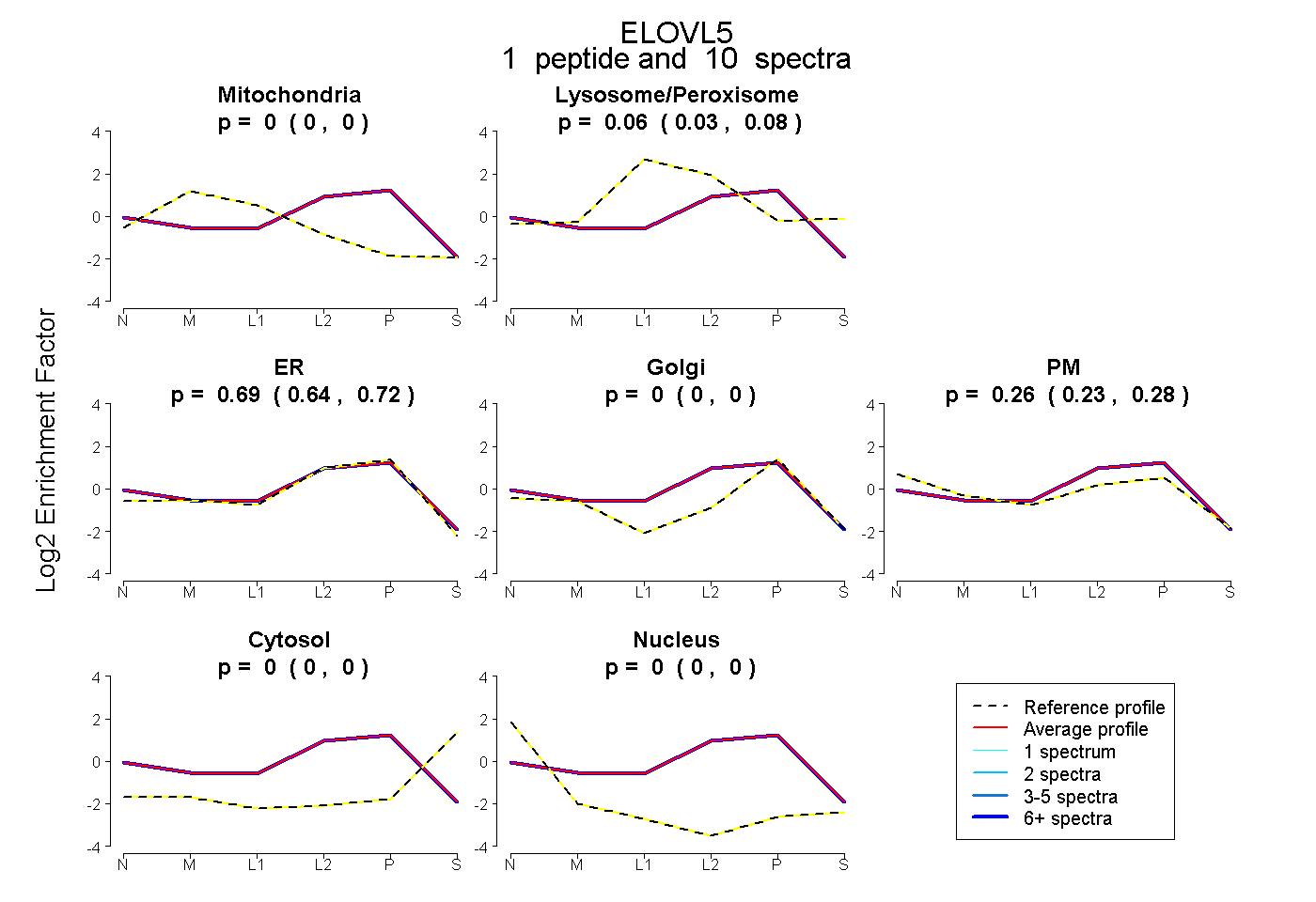 |
0.000 0.000 | 0.000 |
0.056 0.030 | 0.077 |
0.685 0.640 | 0.717 |
0.000 0.000 | 0.000 |
0.259 0.232 | 0.279 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
38 spectra |
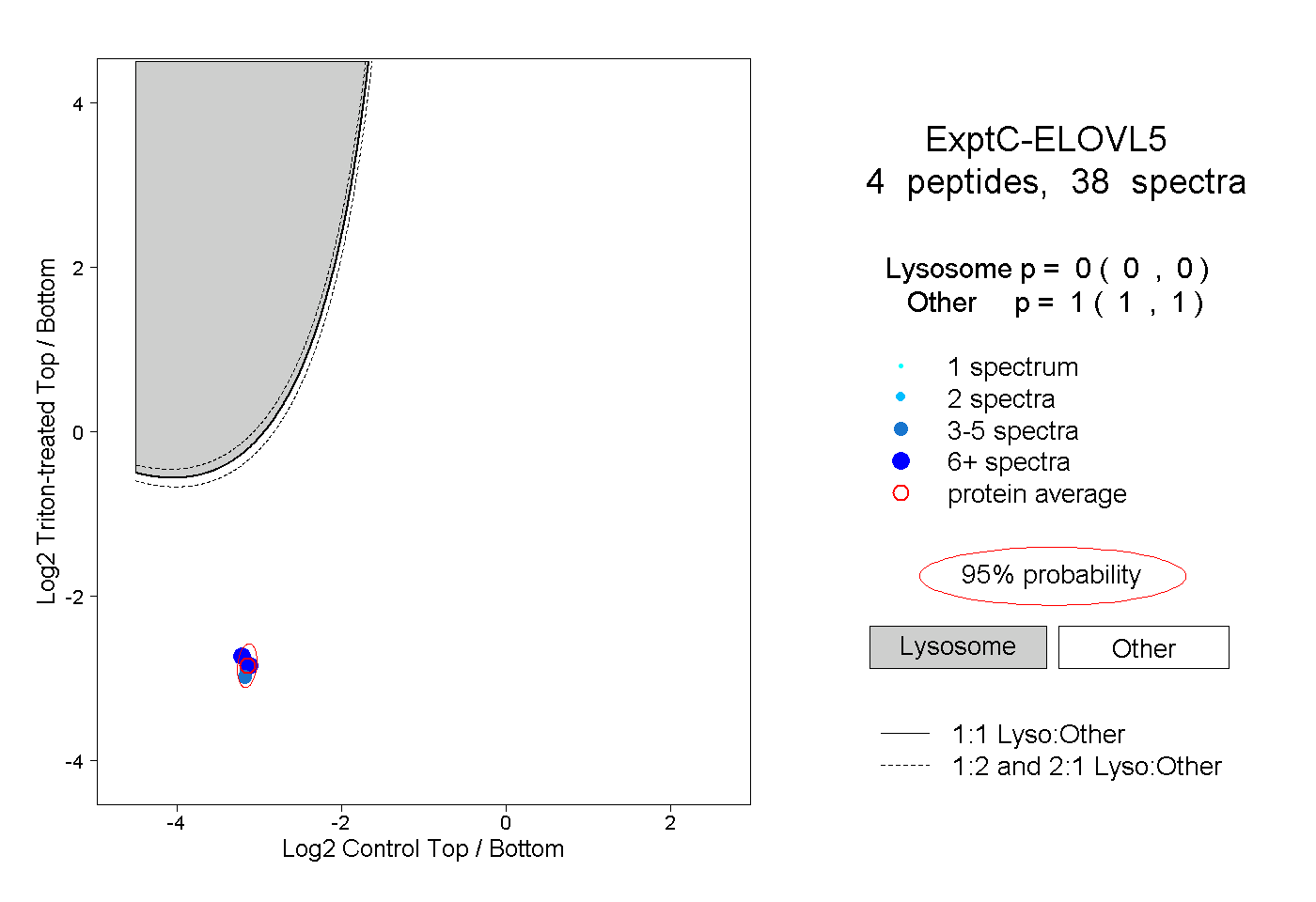 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
9 spectra |
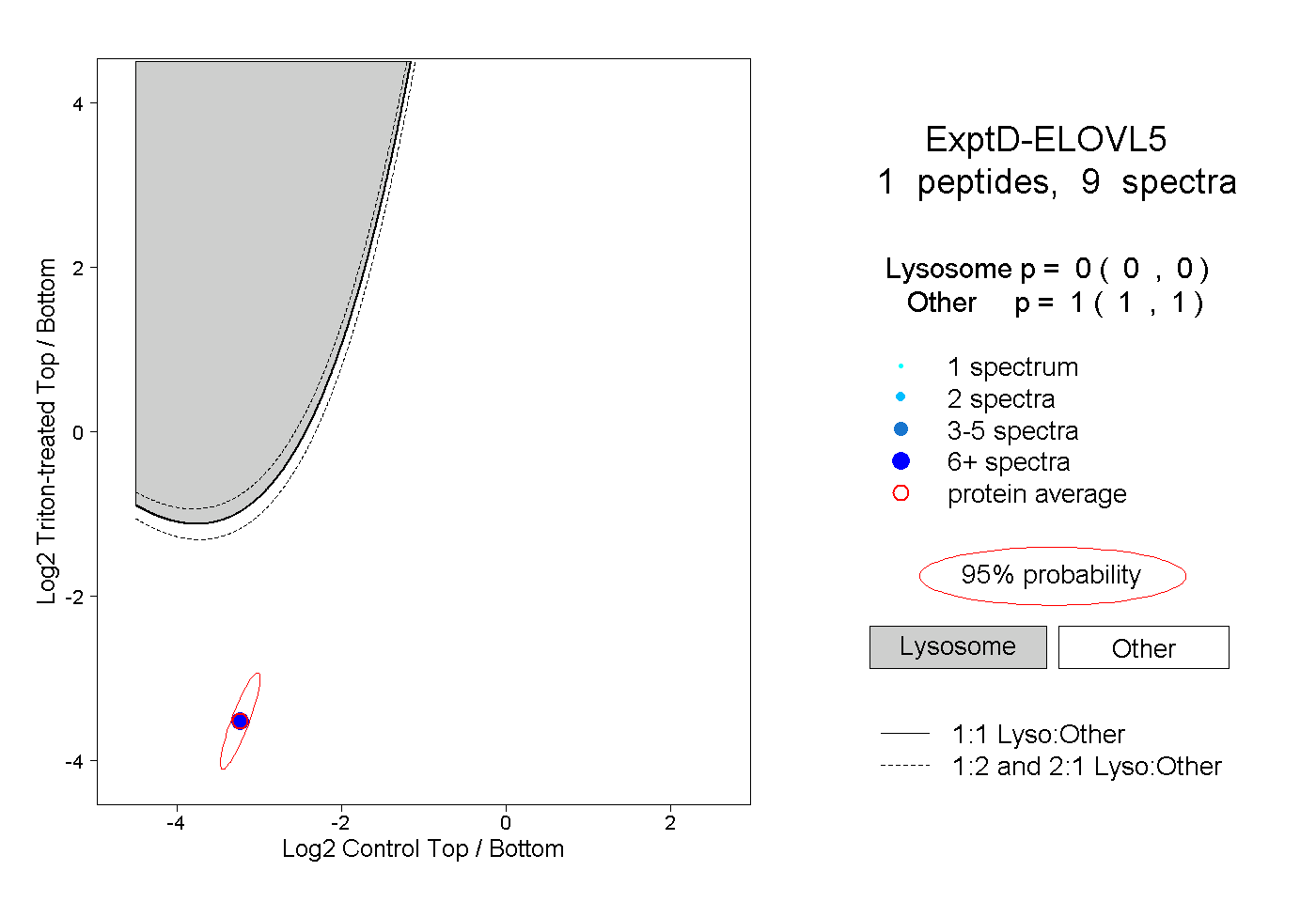 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |