peptides
spectra
0.000 | 0.002
0.000 | 0.000
0.012 | 0.018
0.804 | 0.809
0.000 | 0.000
0.000 | 0.000
0.176 | 0.179
0.000 | 0.000
peptides
spectra
0.000 | 0.000
0.221 | 0.242
0.632 | 0.674
0.017 | 0.063
0.005 | 0.036
0.043 | 0.055
0.000 | 0.000
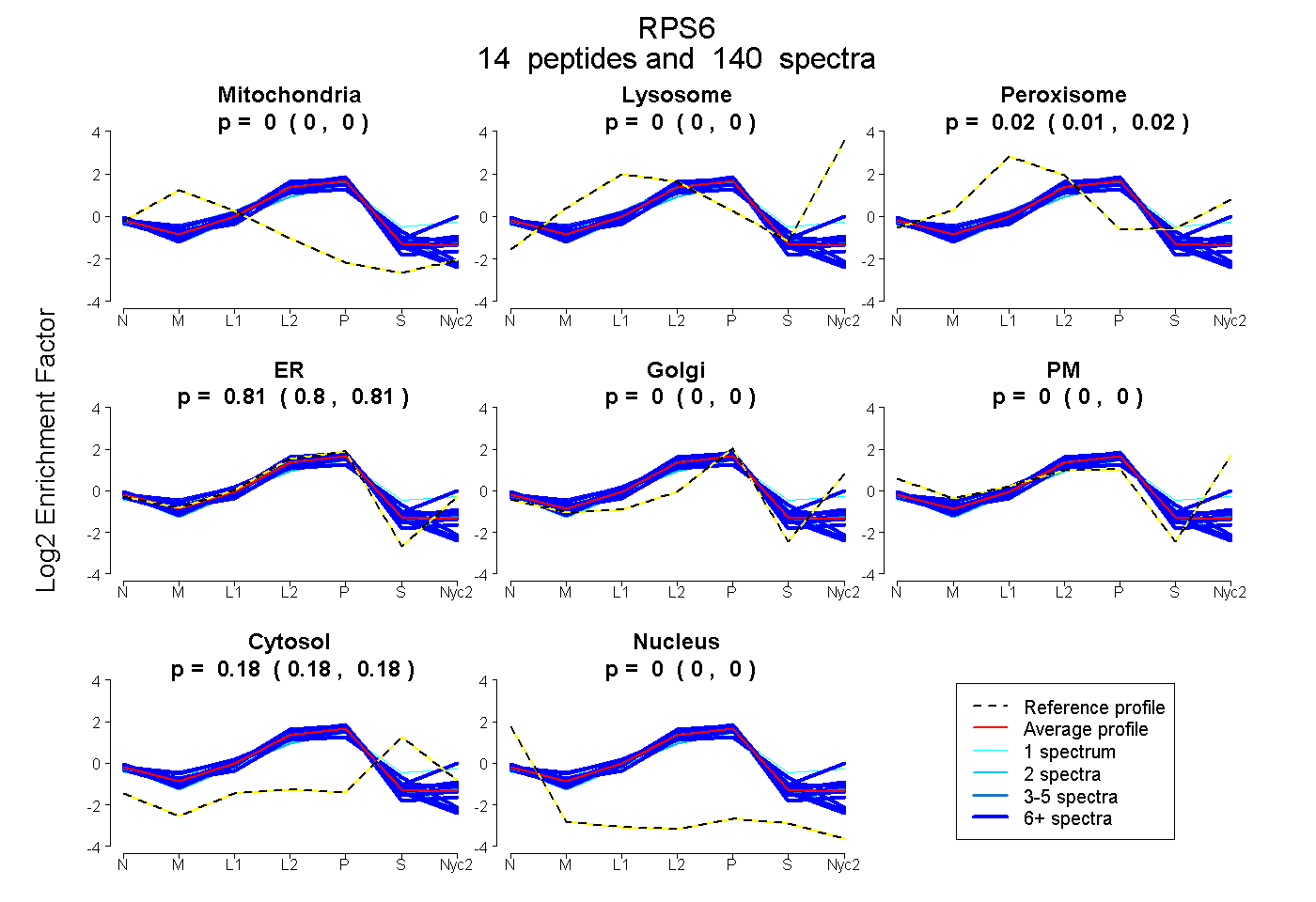
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
140 spectra |
 |
0.000 0.000 | 0.002 |
0.000 0.000 | 0.000 |
0.016 0.012 | 0.018 |
0.807 0.804 | 0.809 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.178 0.176 | 0.179 |
0.000 0.000 | 0.000 |
||
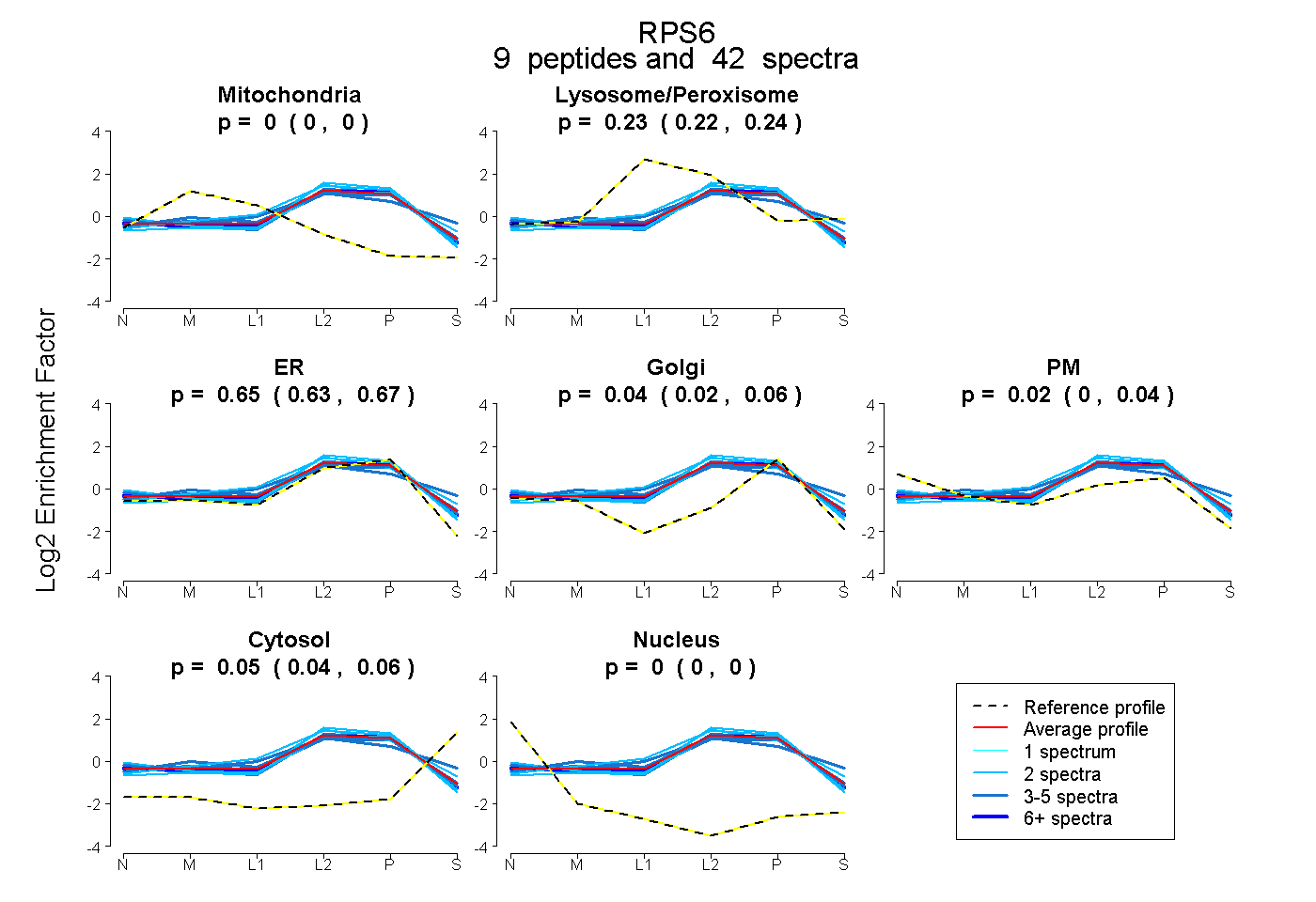
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
42 spectra |
 |
0.000 0.000 | 0.000 |
0.232 0.221 | 0.242 |
0.655 0.632 | 0.674 |
0.042 0.017 | 0.063 |
0.022 0.005 | 0.036 |
0.049 0.043 | 0.055 |
0.000 0.000 | 0.000 |
| 18 spectra, LIEVDDER | 0.000 | 0.226 | 0.618 | 0.110 | 0.030 | 0.016 | 0.000 | |||
| 5 spectra, LFNLSK | 0.000 | 0.154 | 0.758 | 0.000 | 0.032 | 0.056 | 0.000 | |||
| 2 spectra, TFYEK | 0.000 | 0.263 | 0.737 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, DIPGLTDTTVPR | 0.000 | 0.268 | 0.509 | 0.180 | 0.000 | 0.043 | 0.000 | |||
| 2 spectra, GHSCYRPR | 0.000 | 0.271 | 0.630 | 0.000 | 0.019 | 0.079 | 0.000 | |||
| 2 spectra, QEQIAK | 0.000 | 0.142 | 0.605 | 0.000 | 0.228 | 0.024 | 0.000 | |||
| 3 spectra, QGVLTHGR | 0.000 | 0.292 | 0.503 | 0.196 | 0.000 | 0.010 | 0.000 | |||
| 4 spectra, LNISFPATGCQK | 0.000 | 0.409 | 0.253 | 0.146 | 0.102 | 0.090 | 0.000 | |||
| 2 spectra, MATEVAADALGEEWK | 0.000 | 0.154 | 0.811 | 0.000 | 0.000 | 0.035 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
256 spectra |
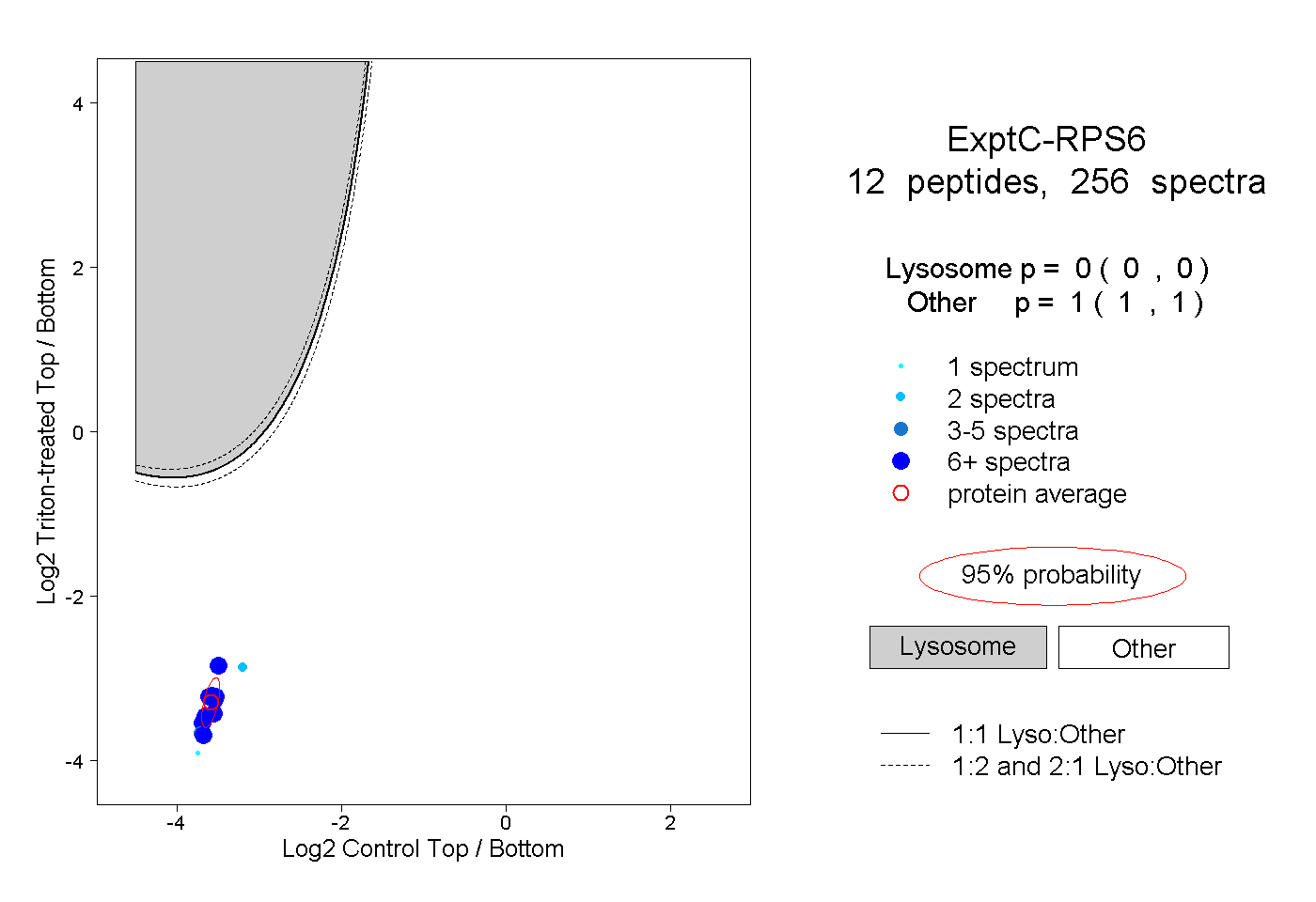 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
24 spectra |
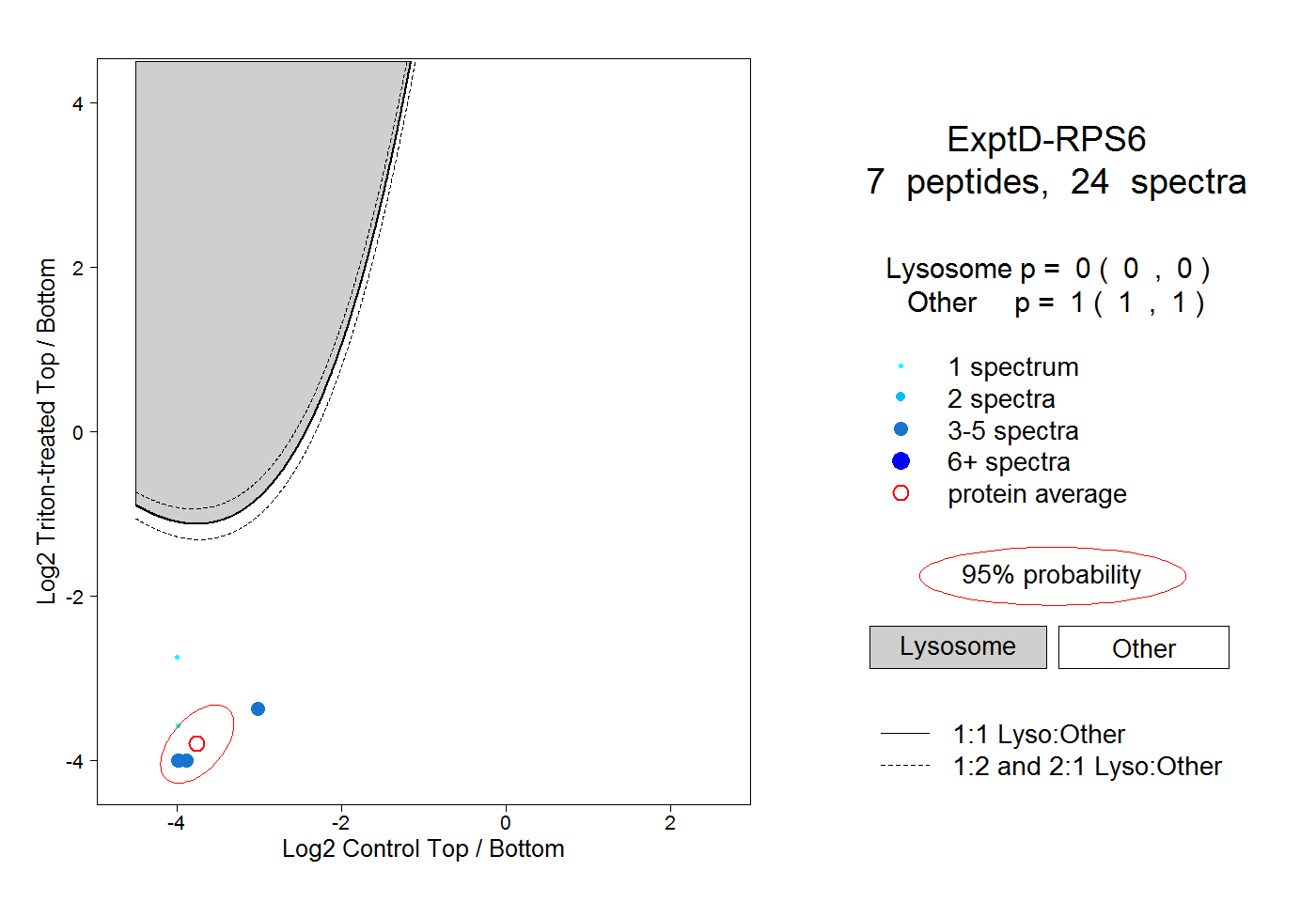 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |