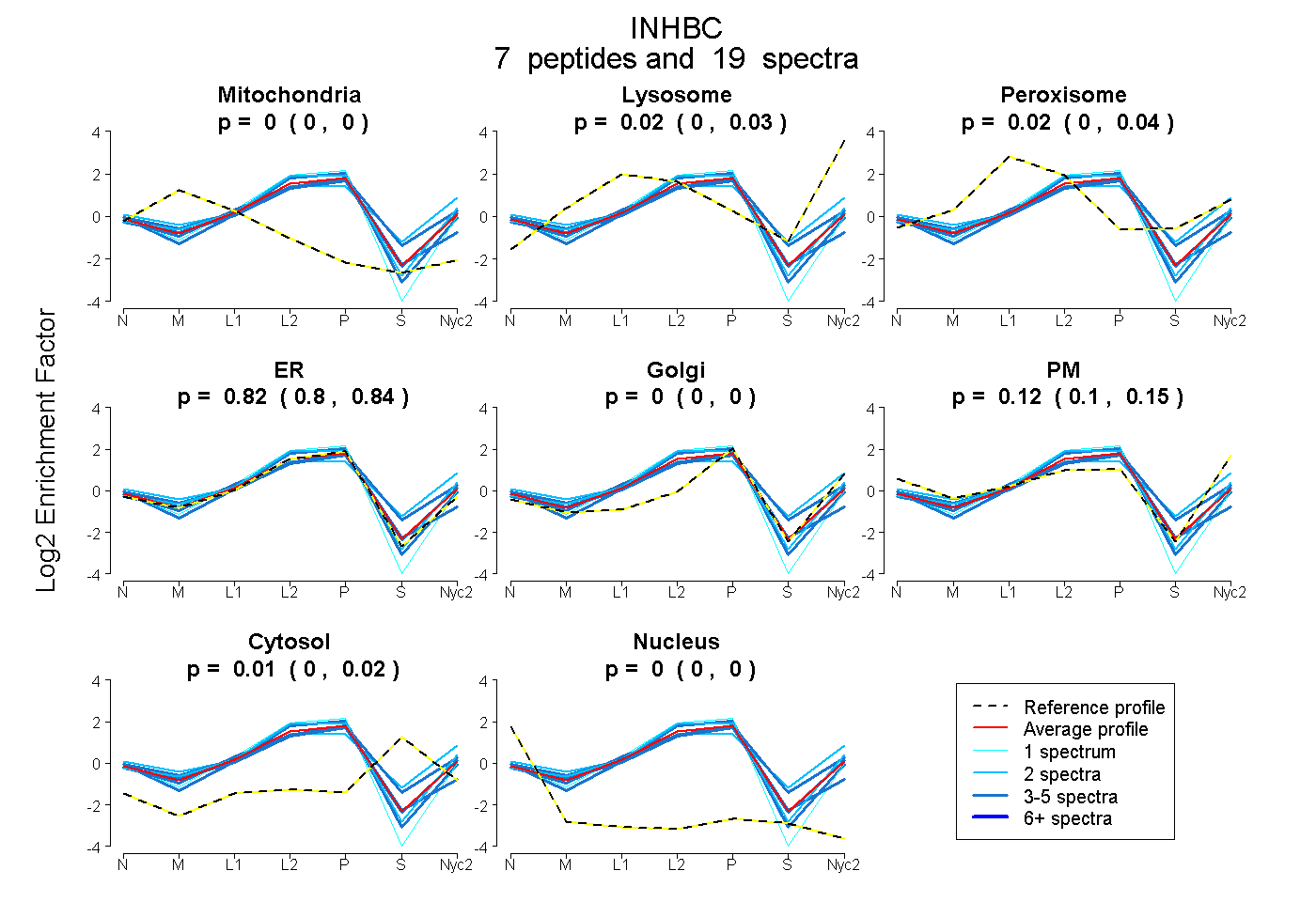
peptides
spectra
0.000 | 0.000
0.000 | 0.034
0.004 | 0.041
0.795 | 0.842
0.000 | 0.000
0.099 | 0.145
0.000 | 0.024
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
19 spectra |
 |
0.000 0.000 | 0.000 |
0.016 0.000 | 0.034 |
0.025 0.004 | 0.041 |
0.821 0.795 | 0.842 |
0.000 0.000 | 0.000 |
0.125 0.099 | 0.145 |
0.013 0.000 | 0.024 |
0.000 0.000 | 0.000 |
| 2 spectra, TTGGVEVLQTR | 0.000 | 0.062 | 0.000 | 0.823 | 0.000 | 0.115 | 0.000 | 0.000 | ||
| 3 spectra, ANTDAGTAR | 0.000 | 0.000 | 0.000 | 0.992 | 0.000 | 0.008 | 0.000 | 0.000 | ||
| 4 spectra, GINCQGLSR | 0.033 | 0.000 | 0.000 | 0.915 | 0.000 | 0.000 | 0.045 | 0.007 | ||
| 2 spectra, AETLLEHDQR | 0.000 | 0.081 | 0.085 | 0.370 | 0.000 | 0.369 | 0.095 | 0.000 | ||
| 3 spectra, RPLSLLYYDR | 0.000 | 0.062 | 0.111 | 0.630 | 0.118 | 0.000 | 0.079 | 0.000 | ||
| 4 spectra, GSCCVPTSR | 0.006 | 0.000 | 0.057 | 0.687 | 0.083 | 0.167 | 0.000 | 0.000 | ||
| 1 spectrum, ELLLDLAK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
2 spectra |
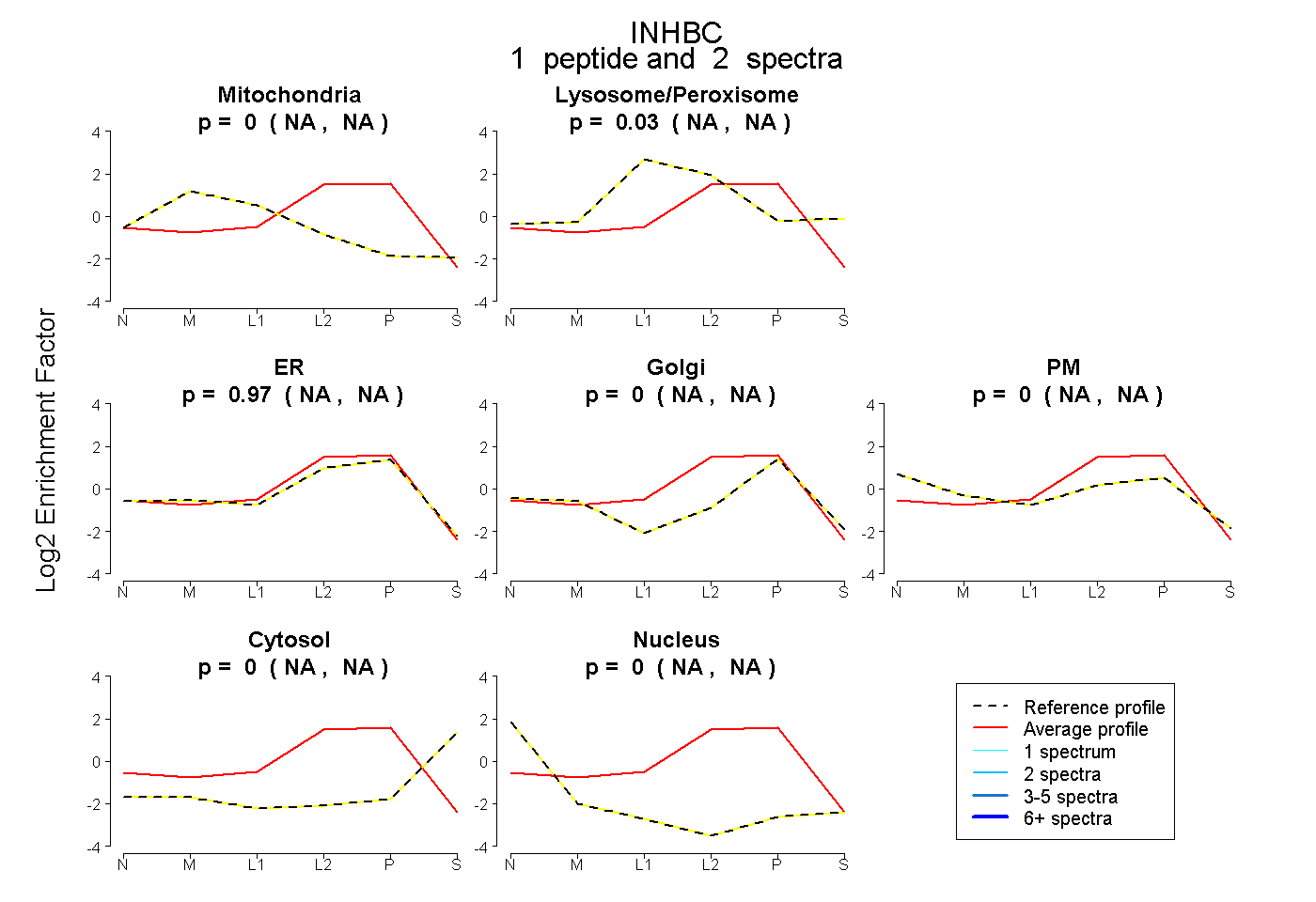 |
0.000 NA | NA |
0.033 NA | NA |
0.967 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
21 spectra |
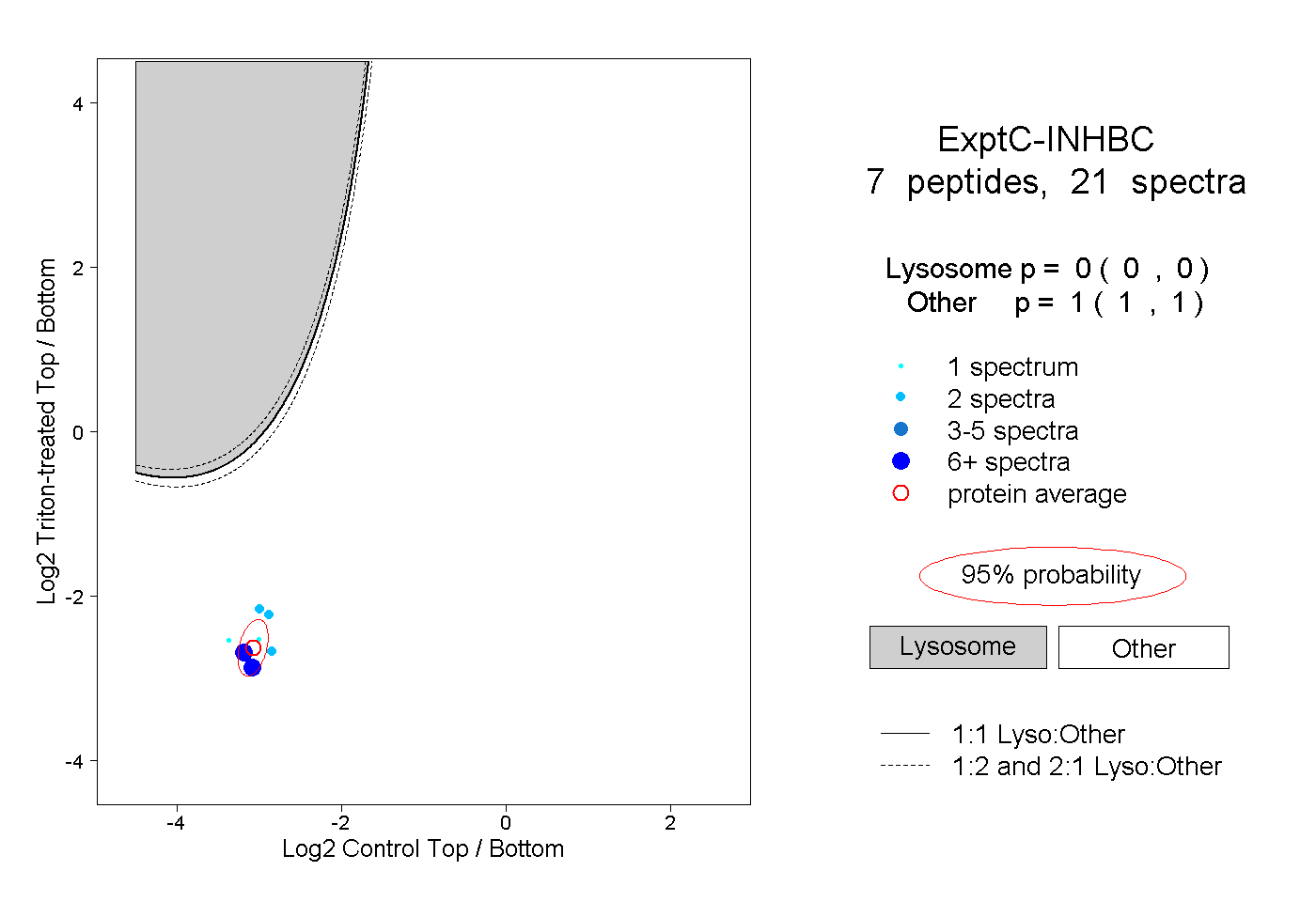 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
5 spectra |
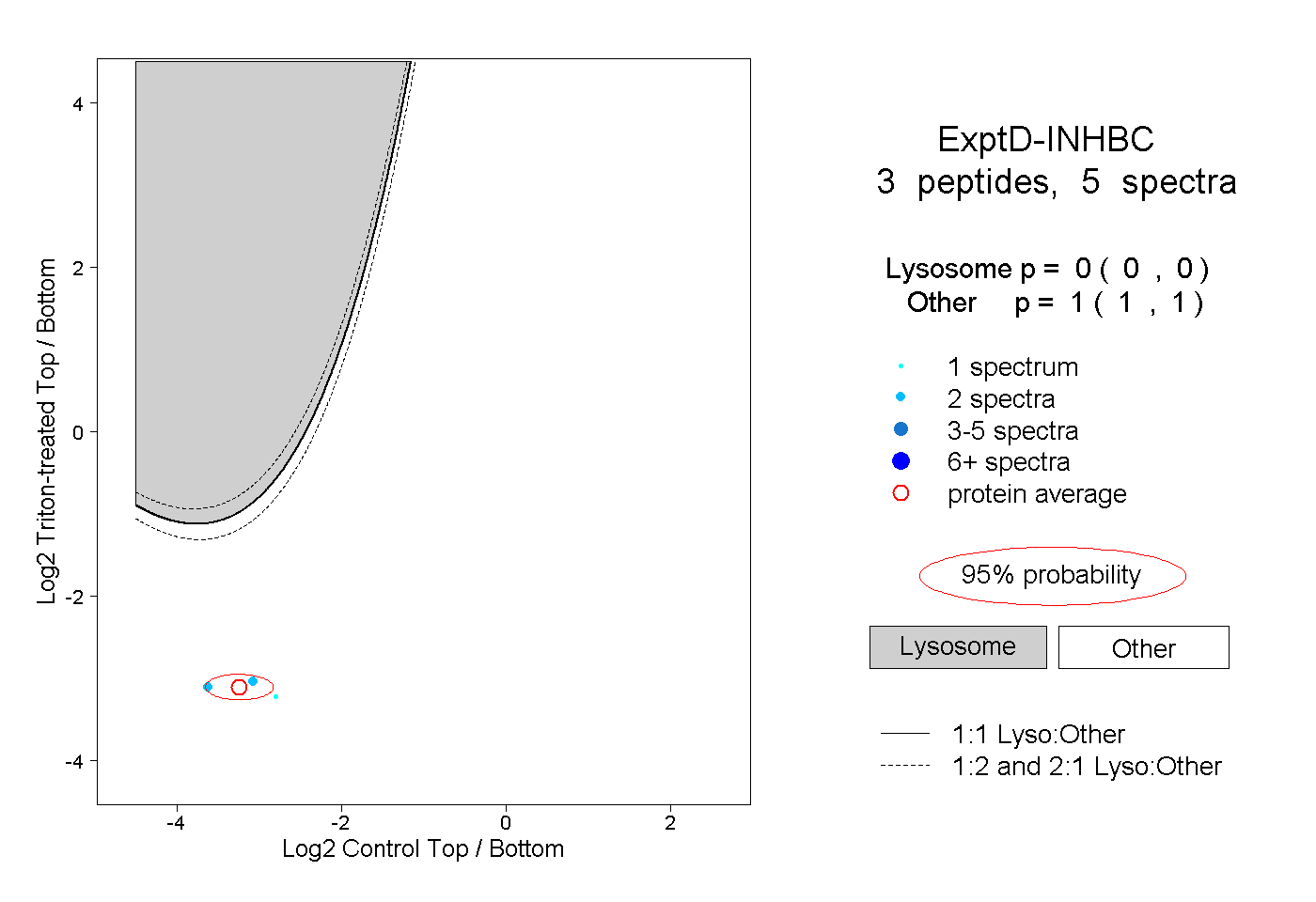 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |