peptides
spectra
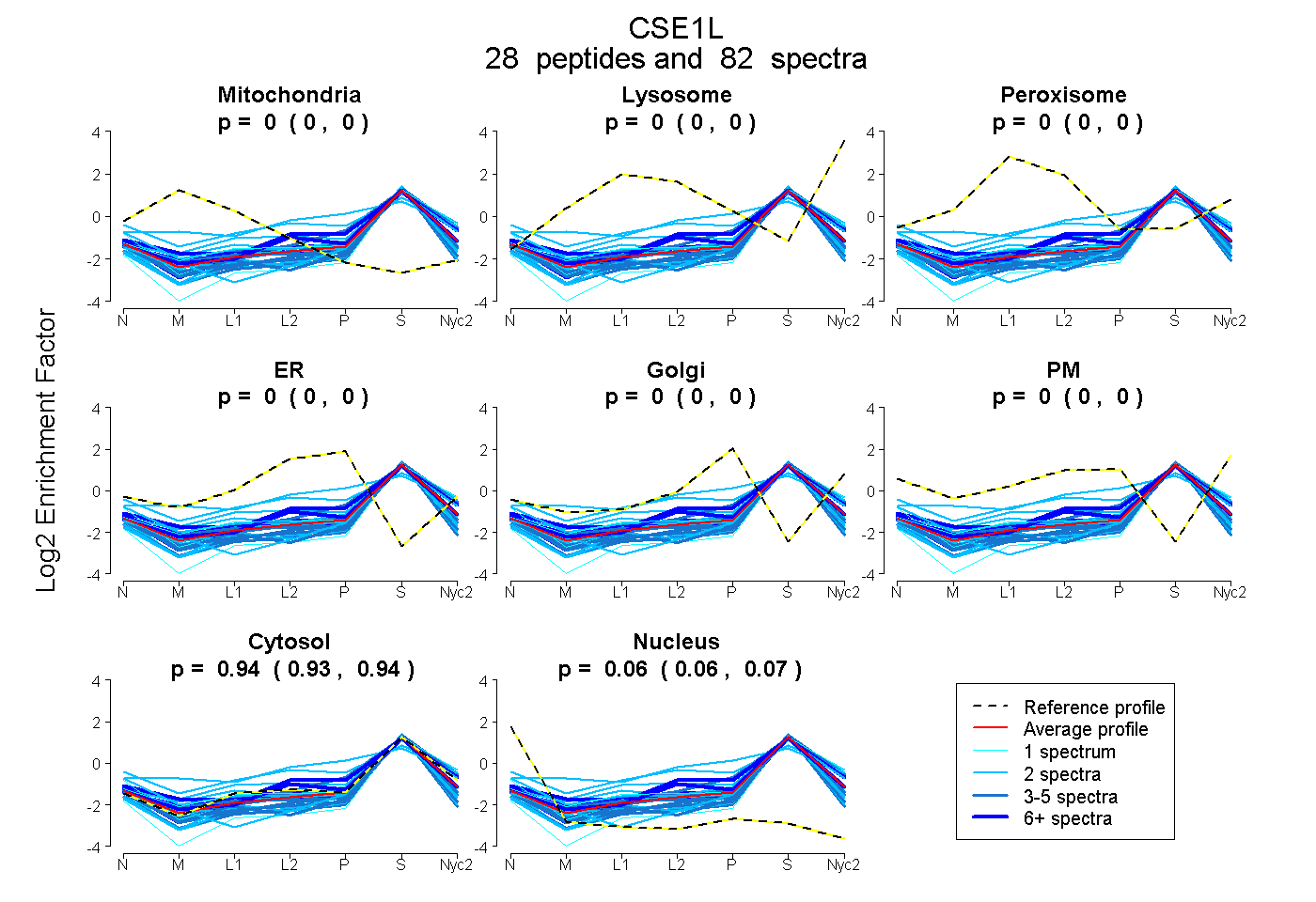
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.934 | 0.937
0.062 | 0.066
peptides
spectra
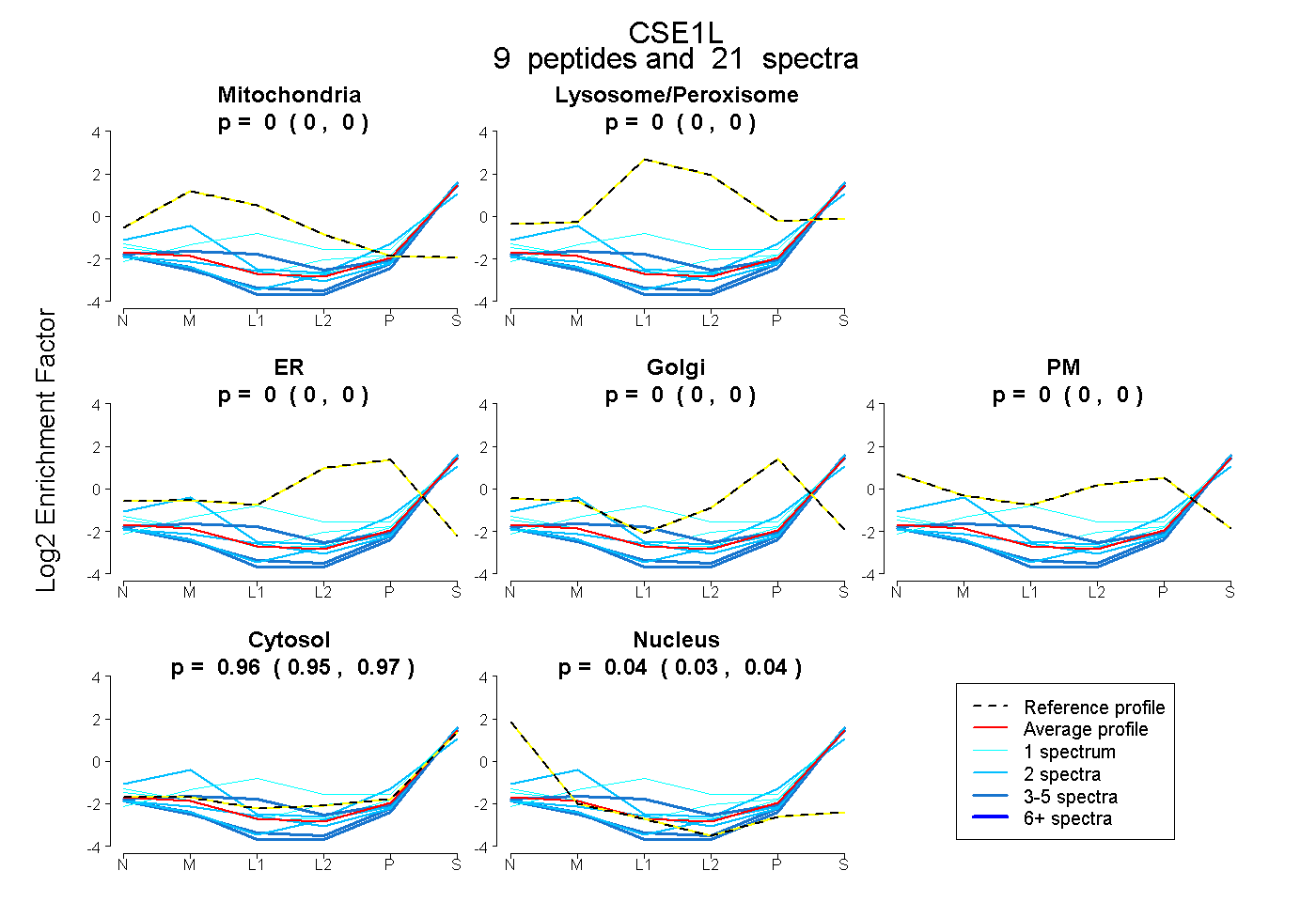
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.954 | 0.969
0.030 | 0.044
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
82 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.936 0.934 | 0.937 |
0.064 0.062 | 0.066 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
21 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.962 0.954 | 0.969 |
0.038 0.030 | 0.044 |
| 2 spectra, EYDPVGQTVNNPR | 0.050 | 0.000 | 0.000 | 0.093 | 0.000 | 0.800 | 0.057 | |||
| 1 spectrum, SQICDNAALYAQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.920 | 0.080 | |||
| 1 spectrum, SNELWTEIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.977 | 0.023 | |||
| 4 spectra, DLEGSDIDTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.940 | 0.060 | |||
| 3 spectra, LLQAFLER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.920 | 0.080 | |||
| 2 spectra, QLSDAISIVGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.977 | 0.023 | |||
| 5 spectra, YDEEFQR | 0.015 | 0.000 | 0.000 | 0.000 | 0.000 | 0.985 | 0.000 | |||
| 1 spectrum, VHLAQALHR | 0.000 | 0.187 | 0.000 | 0.000 | 0.000 | 0.813 | 0.000 | |||
| 2 spectra, TLDPDPAIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.977 | 0.023 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
32 spectra |
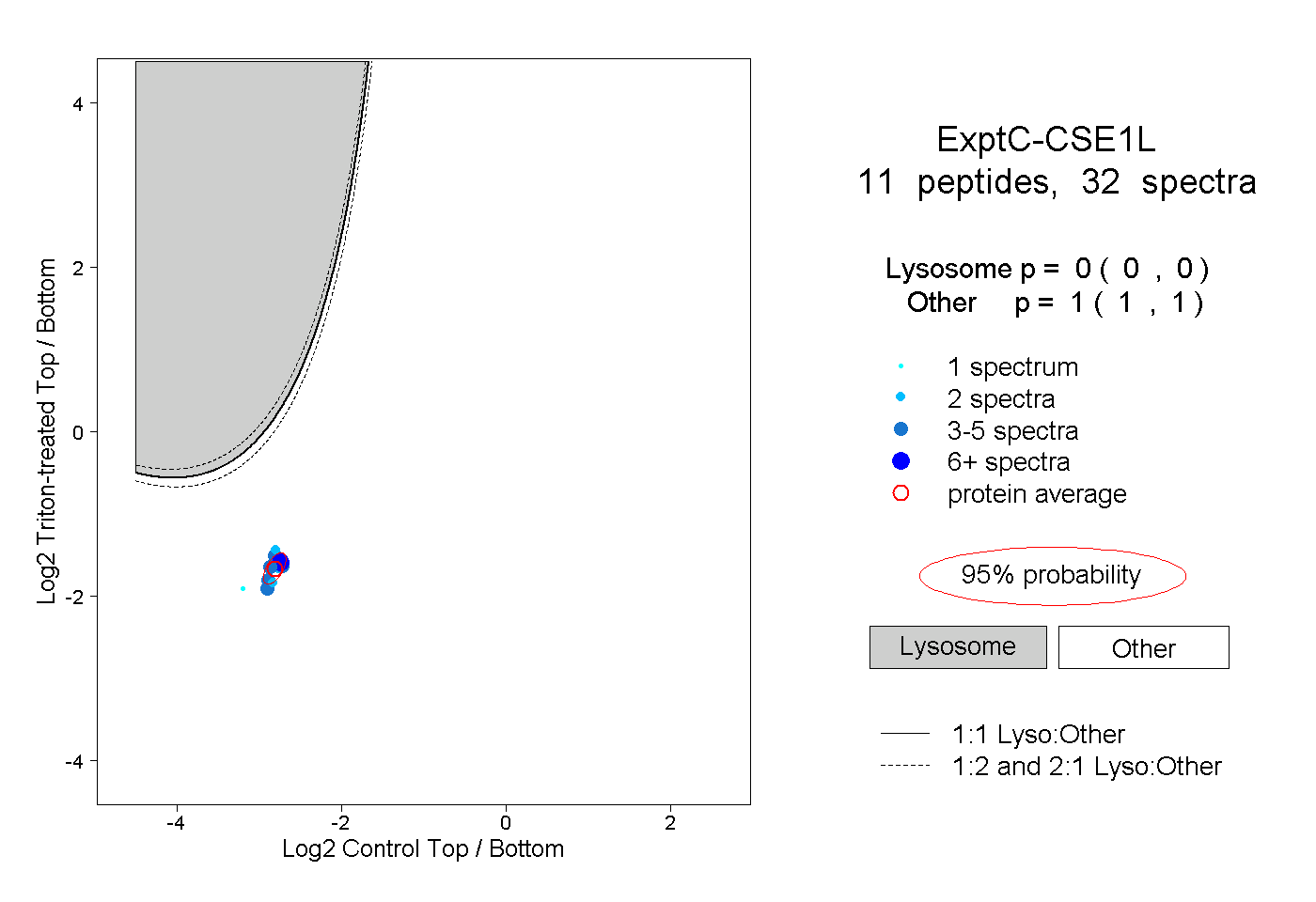 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
8 spectra |
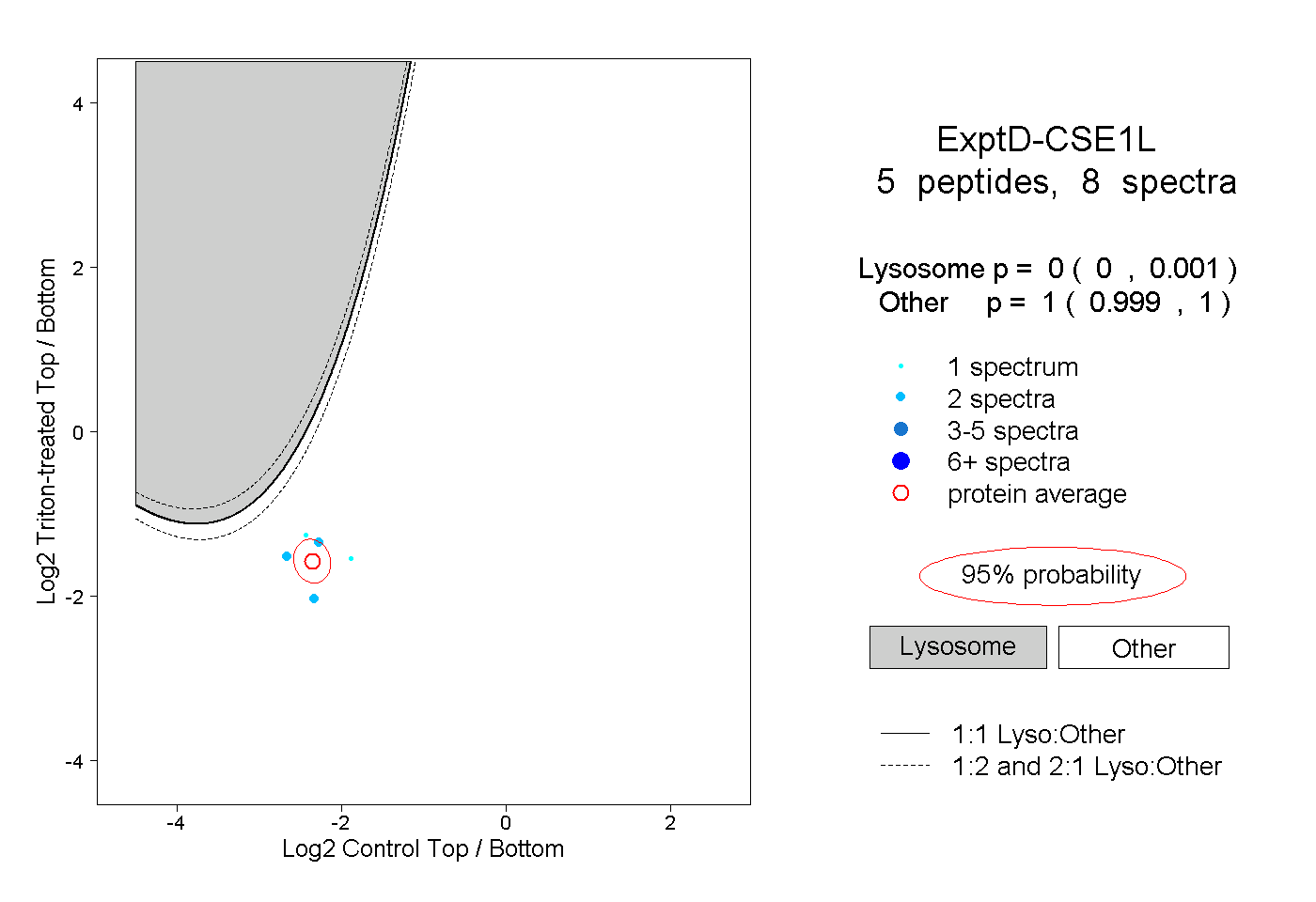 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |