peptides
spectra
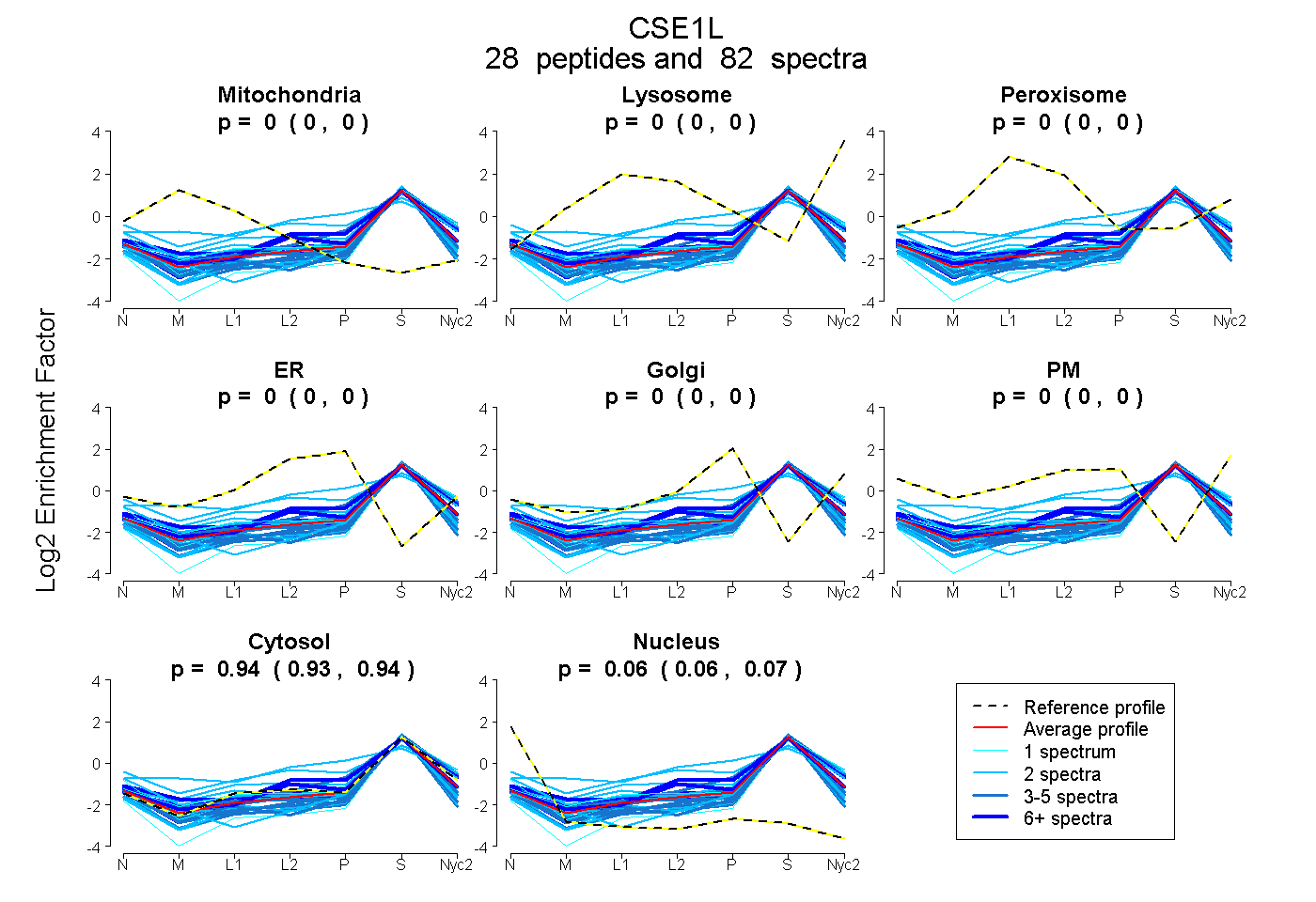
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.934 | 0.937
0.062 | 0.066
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
82 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.936 0.934 | 0.937 |
0.064 0.062 | 0.066 |
| 3 spectra, LSTACPGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.892 | 0.108 | ||
| 4 spectra, VIVPNMEFR | 0.010 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.934 | 0.056 | ||
| 2 spectra, SNNVNEFPVLK | 0.007 | 0.000 | 0.158 | 0.097 | 0.169 | 0.000 | 0.569 | 0.000 | ||
| 2 spectra, VCASVTFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.909 | 0.091 | ||
| 2 spectra, LLTECPAMMDTEYTK | 0.000 | 0.000 | 0.110 | 0.008 | 0.000 | 0.200 | 0.682 | 0.000 | ||
| 3 spectra, SNELWTEIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.835 | 0.165 | ||
| 2 spectra, ALTLPGSSENEYIMK | 0.083 | 0.016 | 0.000 | 0.000 | 0.000 | 0.000 | 0.901 | 0.000 | ||
| 2 spectra, ANIVHLMLSSPEQIQK | 0.018 | 0.084 | 0.038 | 0.000 | 0.000 | 0.023 | 0.837 | 0.000 | ||
| 7 spectra, DLEGSDIDTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.942 | 0.058 | ||
| 1 spectrum, YIMIFR | 0.004 | 0.049 | 0.000 | 0.000 | 0.000 | 0.000 | 0.941 | 0.006 | ||
| 3 spectra, QLSDAISIVGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.948 | 0.052 | ||
| 2 spectra, GSSTIATAAADK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.881 | 0.119 | ||
| 2 spectra, WPDLLTEMVNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.847 | 0.153 | ||
| 6 spectra, VHLAQALHR | 0.000 | 0.000 | 0.000 | 0.010 | 0.100 | 0.000 | 0.890 | 0.000 | ||
| 4 spectra, TLDPDPAIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.930 | 0.070 | ||
| 2 spectra, NPSVNWK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.906 | 0.094 | ||
| 2 spectra, LLAVSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.923 | 0.077 | ||
| 2 spectra, EYDPVGQTVNNPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.862 | 0.138 | ||
| 3 spectra, ICAVGITK | 0.000 | 0.000 | 0.000 | 0.018 | 0.000 | 0.000 | 0.941 | 0.041 | ||
| 4 spectra, IVEDEPNK | 0.000 | 0.000 | 0.000 | 0.000 | 0.014 | 0.015 | 0.962 | 0.010 | ||
| 4 spectra, IIIPEIQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.842 | 0.158 | ||
| 2 spectra, VSGNVEK | 0.009 | 0.000 | 0.000 | 0.000 | 0.000 | 0.062 | 0.880 | 0.050 | ||
| 1 spectrum, SQDNVIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.866 | 0.134 | ||
| 1 spectrum, IPGLLGVFQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.863 | 0.137 | ||
| 6 spectra, LLQAFLER | 0.076 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.914 | 0.010 | ||
| 6 spectra, YDEEFQR | 0.000 | 0.000 | 0.000 | 0.021 | 0.000 | 0.000 | 0.942 | 0.037 | ||
| 2 spectra, EDFPQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.965 | 0.035 | ||
| 2 spectra, NLFEDQNTLTSICEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.868 | 0.132 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
21 spectra |
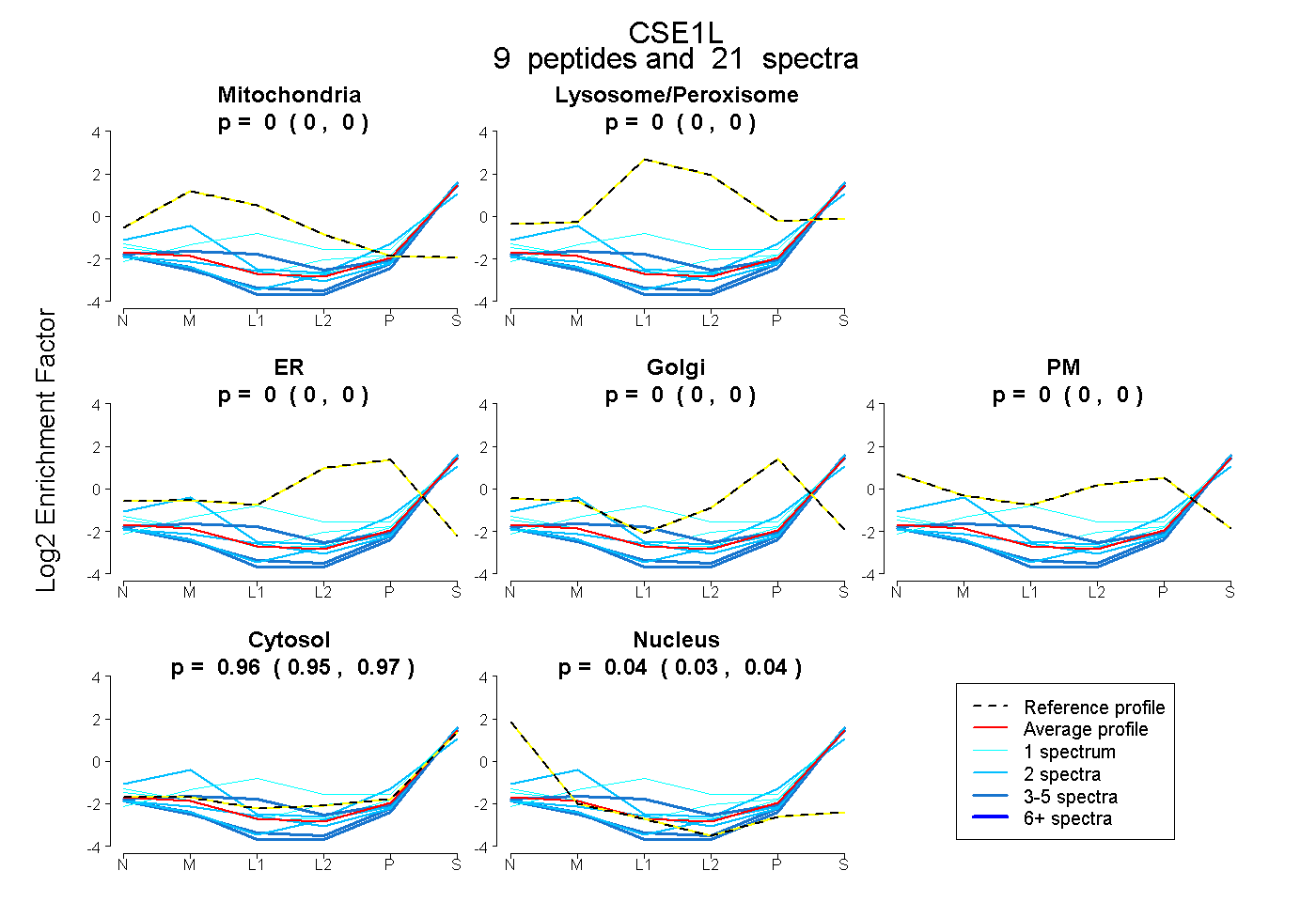 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.962 0.954 | 0.969 |
0.038 0.030 | 0.044 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
32 spectra |
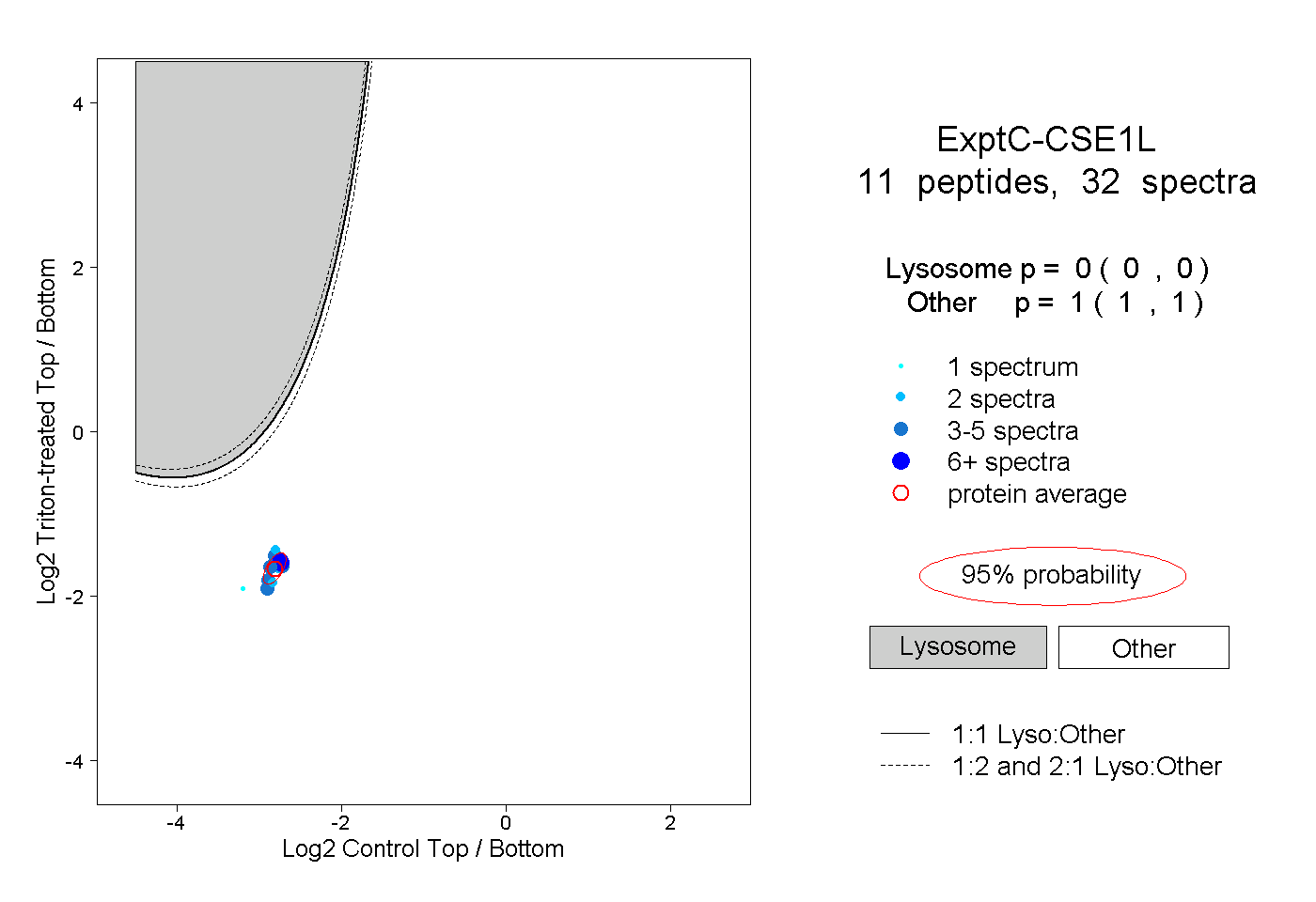 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
8 spectra |
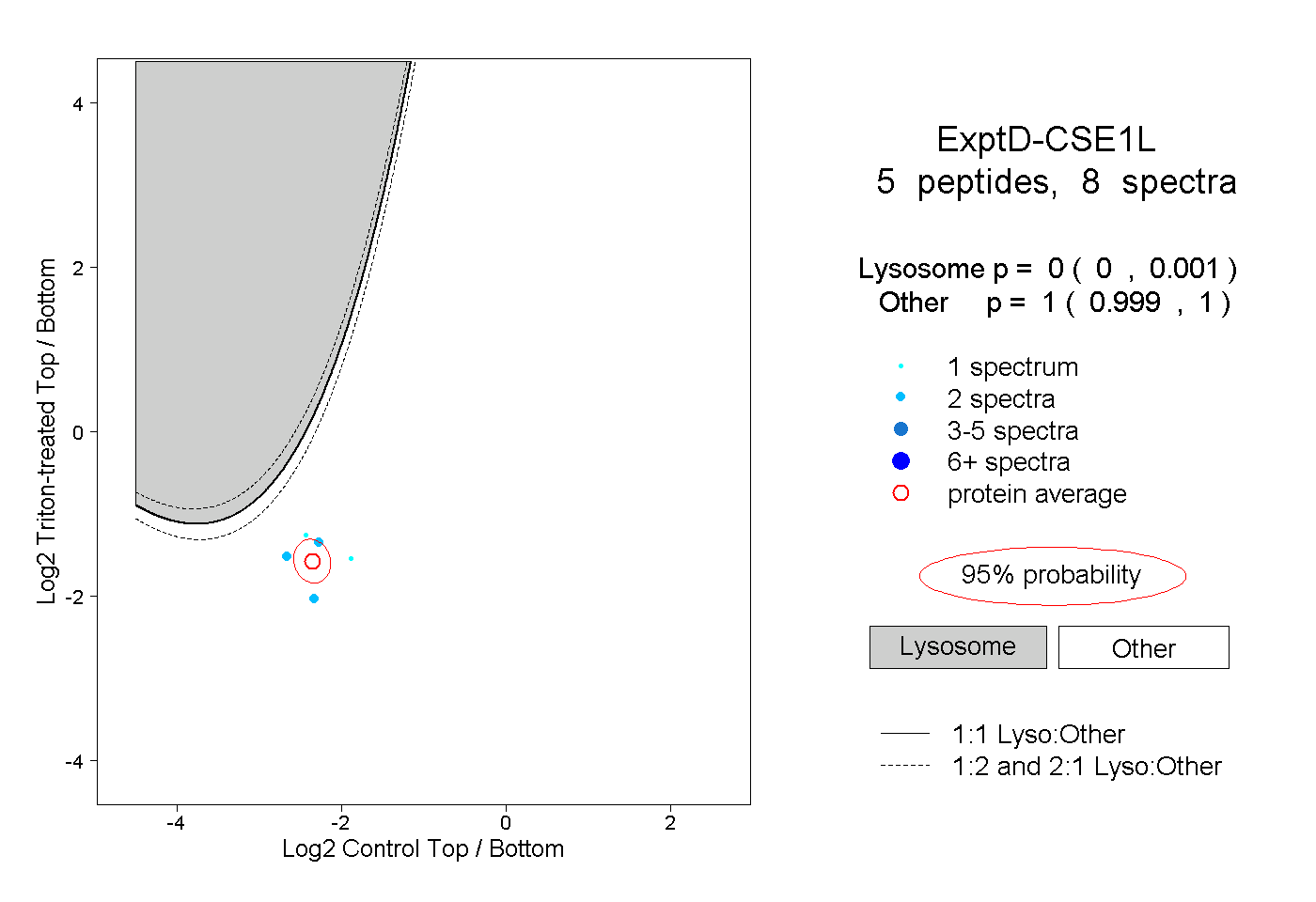 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |