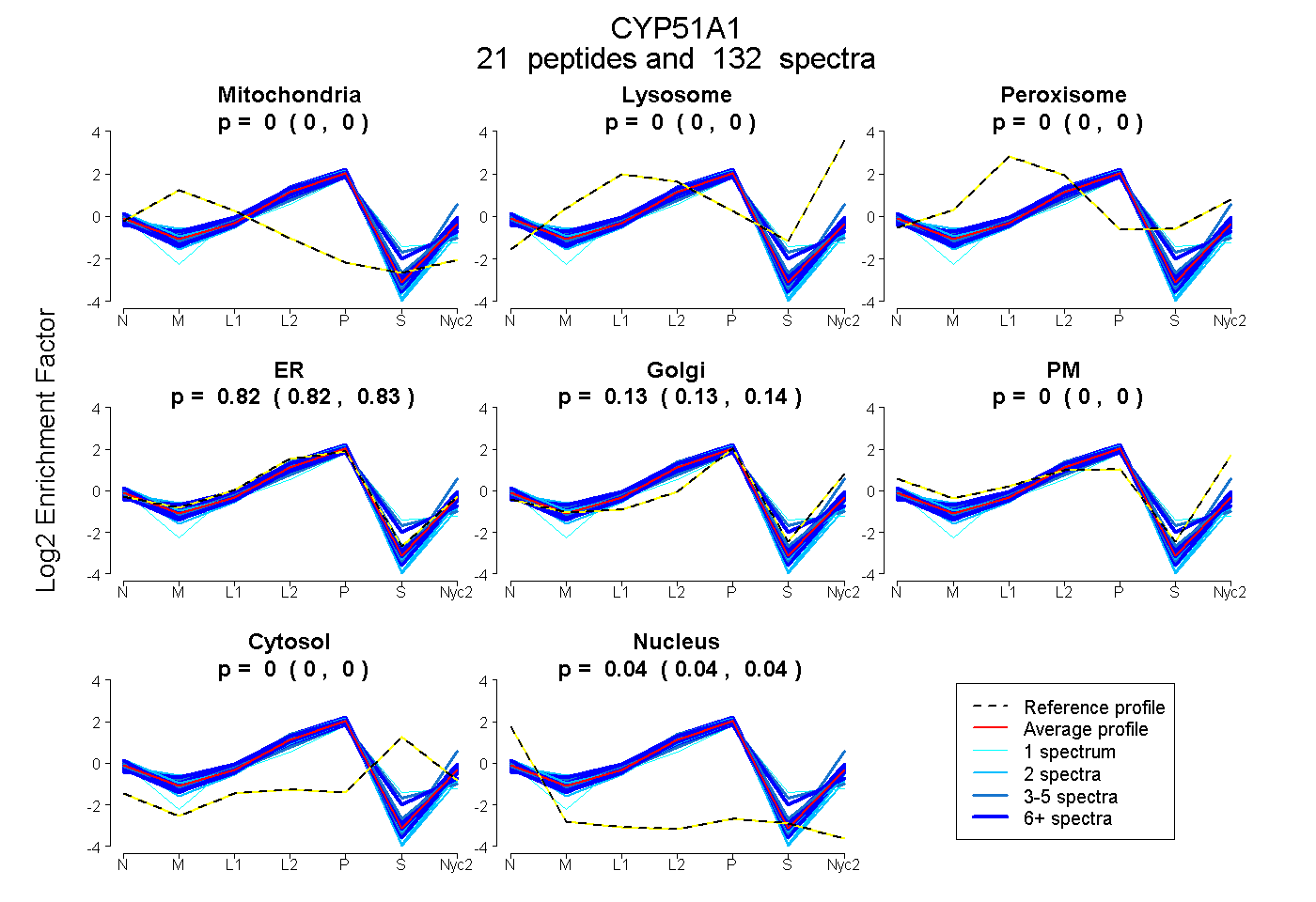
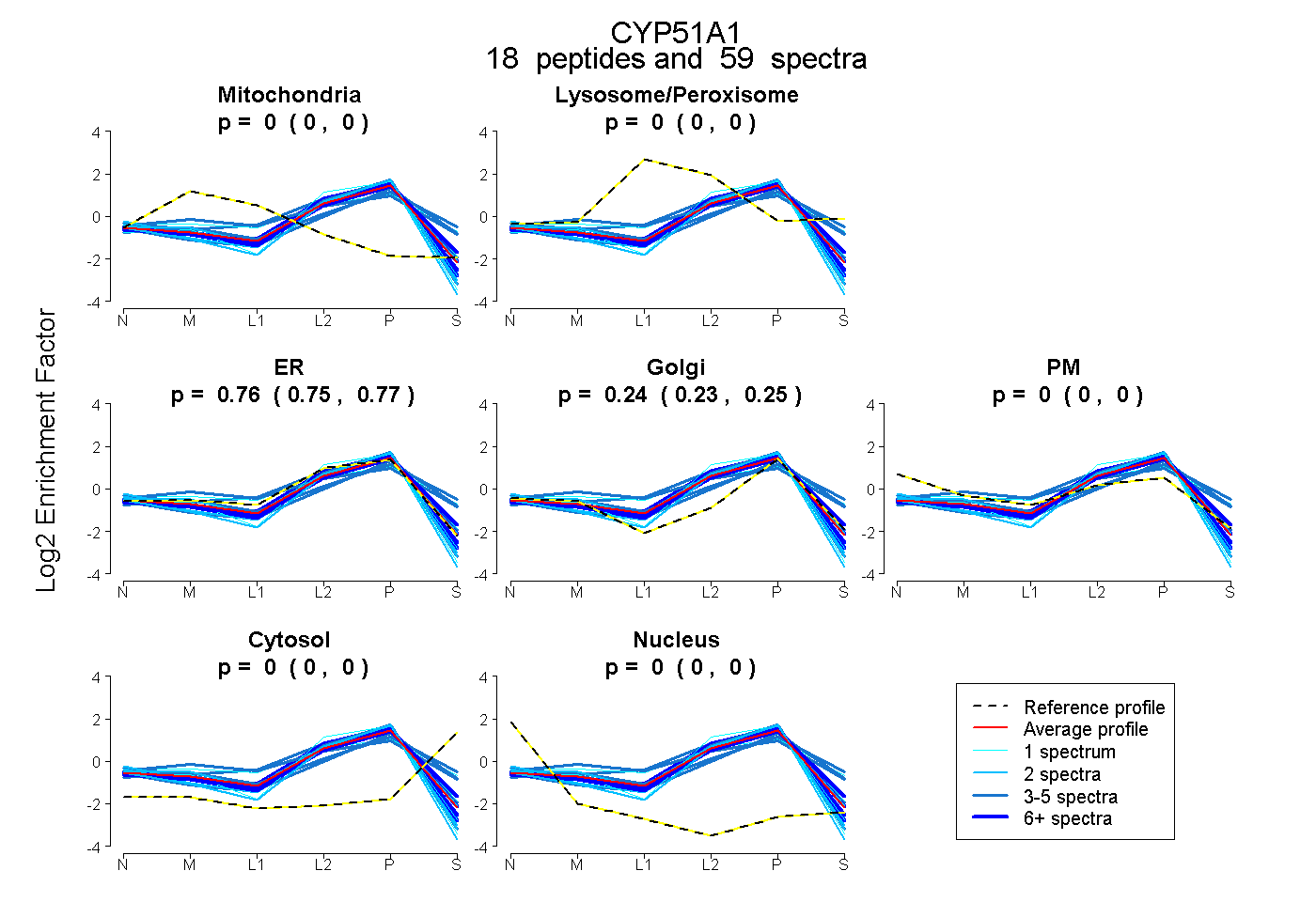
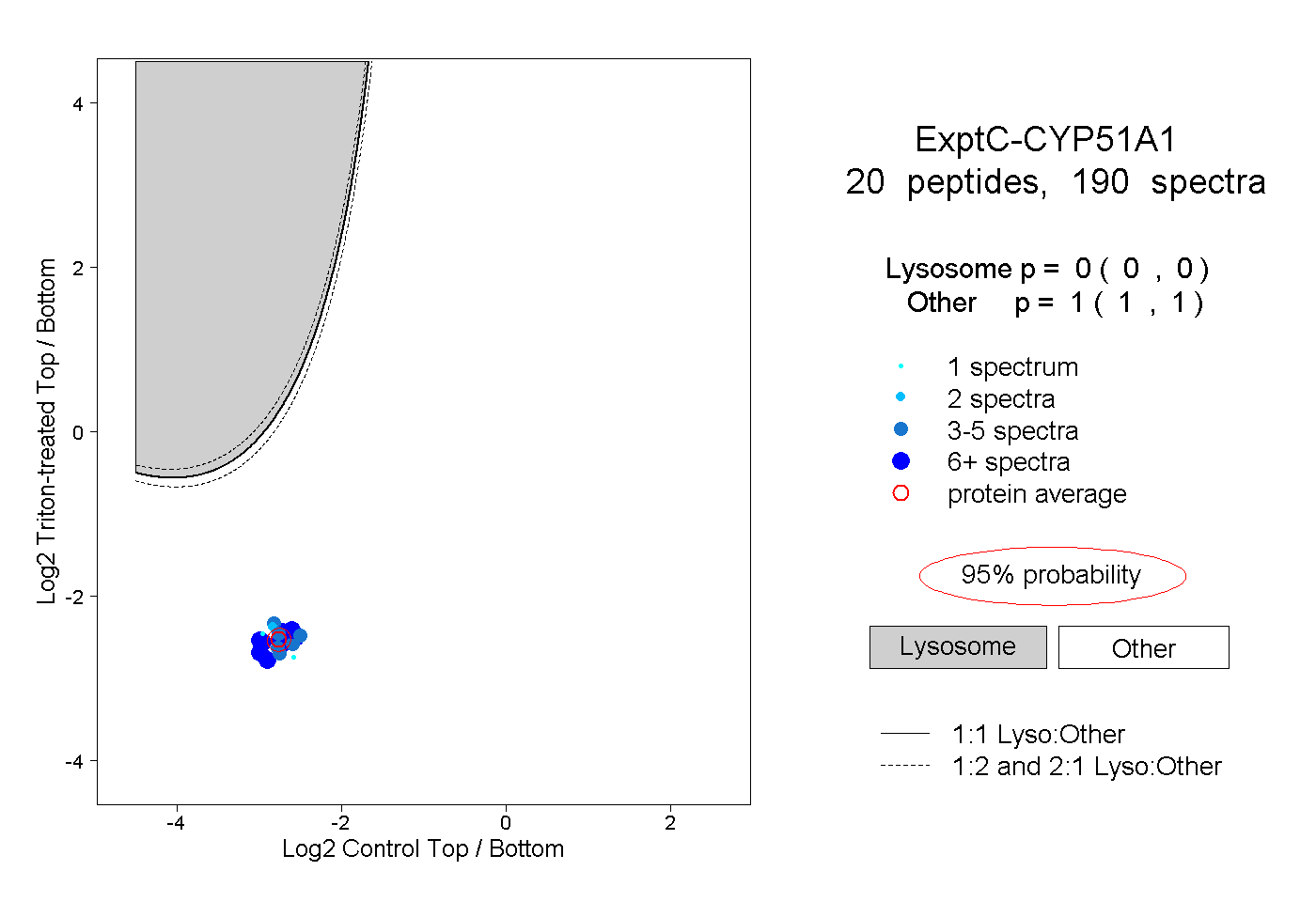
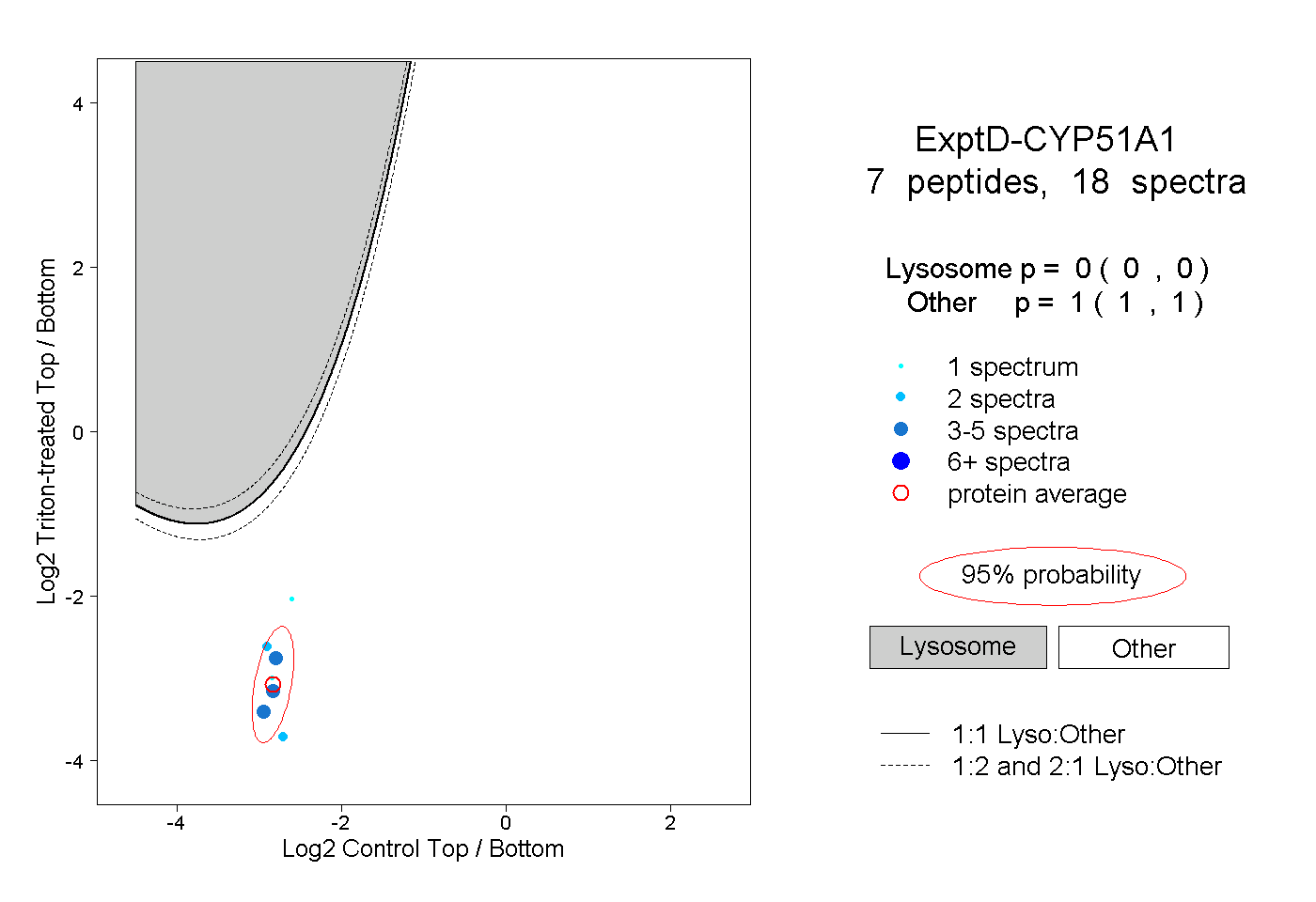
| 12 spectra, NEDLNAEEVYGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, CYLEQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, TIWSTMLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, LDFNPDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, CIGENFAYVQIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 17 spectra, DLNLLDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GVAYDVPNAVFLEQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, YLQDNPASGEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, TVCGEDLPPLTYEQLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 26 spectra, SQLNEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, DSWVER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, YGPVFSFTMVGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, QYVSIIEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 20 spectra, LTTPVFGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 15 spectra, DKPLQDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, SWGESGER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 17 spectra, FAYVPFGAGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, SGLNIAHFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, LAVGHMVQLPAGAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SPPYIYSPIPFLGHAIAFGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |