peptides
spectra
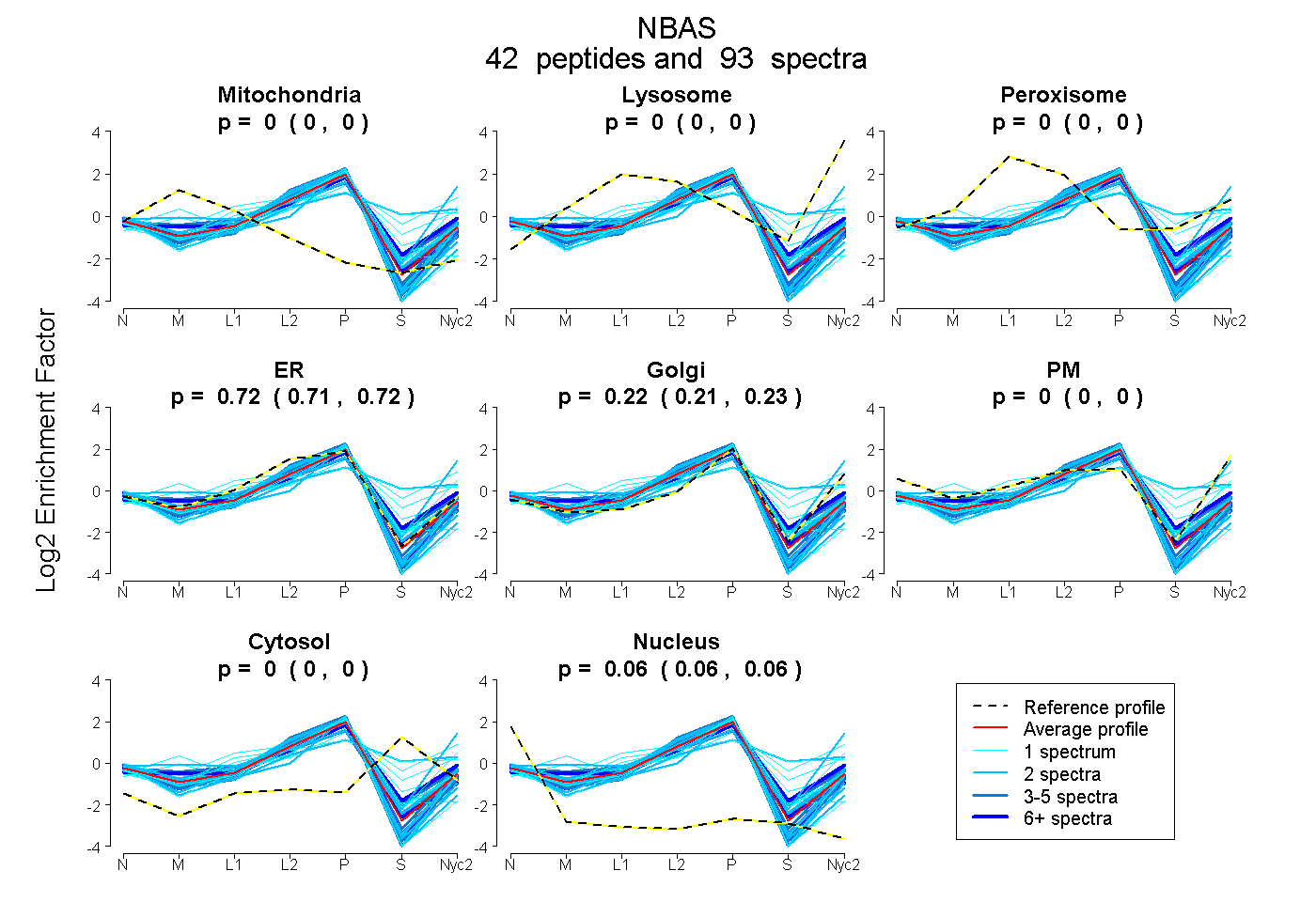
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.712 | 0.723
0.213 | 0.225
0.000 | 0.000
0.000 | 0.000
0.061 | 0.064
peptides
spectra
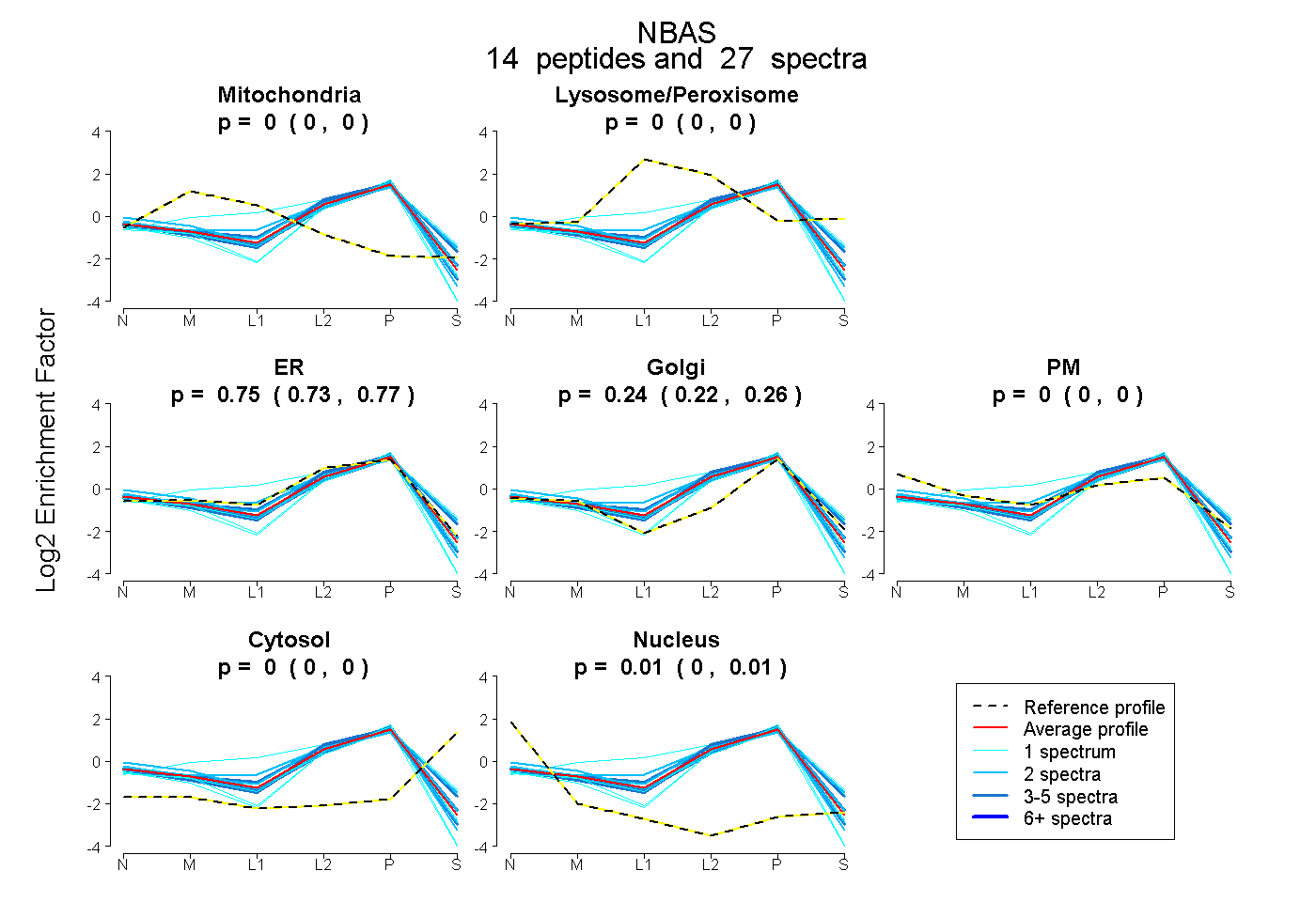
0.000 | 0.000
0.000 | 0.000
0.732 | 0.765
0.220 | 0.260
0.000 | 0.000
0.000 | 0.000
0.005 | 0.012
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
93 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.718 0.712 | 0.723 |
0.220 0.213 | 0.225 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.063 0.061 | 0.064 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
27 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.750 0.732 | 0.765 |
0.241 0.220 | 0.260 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.009 0.005 | 0.012 |
| 1 spectrum, HFIEKPR | 0.085 | 0.000 | 0.915 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, IGTVANDDLER | 0.000 | 0.000 | 0.711 | 0.286 | 0.000 | 0.000 | 0.003 | |||
| 3 spectra, LLPLQVR | 0.000 | 0.000 | 0.640 | 0.307 | 0.000 | 0.053 | 0.000 | |||
| 2 spectra, LLTFLDR | 0.000 | 0.000 | 0.948 | 0.008 | 0.000 | 0.000 | 0.043 | |||
| 1 spectrum, LSVEAR | 0.000 | 0.033 | 0.562 | 0.361 | 0.000 | 0.044 | 0.000 | |||
| 2 spectra, LGDEVLK | 0.000 | 0.000 | 0.686 | 0.285 | 0.014 | 0.000 | 0.015 | |||
| 3 spectra, LLGLAELLR | 0.000 | 0.000 | 0.924 | 0.041 | 0.000 | 0.000 | 0.035 | |||
| 1 spectrum, SLAYLRPLQGQDFGGAYR | 0.000 | 0.000 | 0.496 | 0.504 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, SQNIVLSAR | 0.000 | 0.000 | 0.655 | 0.245 | 0.000 | 0.100 | 0.000 | |||
| 2 spectra, TFSTALSALR | 0.000 | 0.000 | 0.756 | 0.136 | 0.064 | 0.000 | 0.043 | |||
| 2 spectra, STTPEELYQR | 0.000 | 0.000 | 0.692 | 0.296 | 0.000 | 0.000 | 0.012 | |||
| 2 spectra, LVNFSK | 0.000 | 0.188 | 0.466 | 0.346 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, ILSVSELLK | 0.000 | 0.000 | 0.534 | 0.466 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, LVTVMLTR | 0.000 | 0.000 | 0.756 | 0.244 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
79 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
8 spectra |
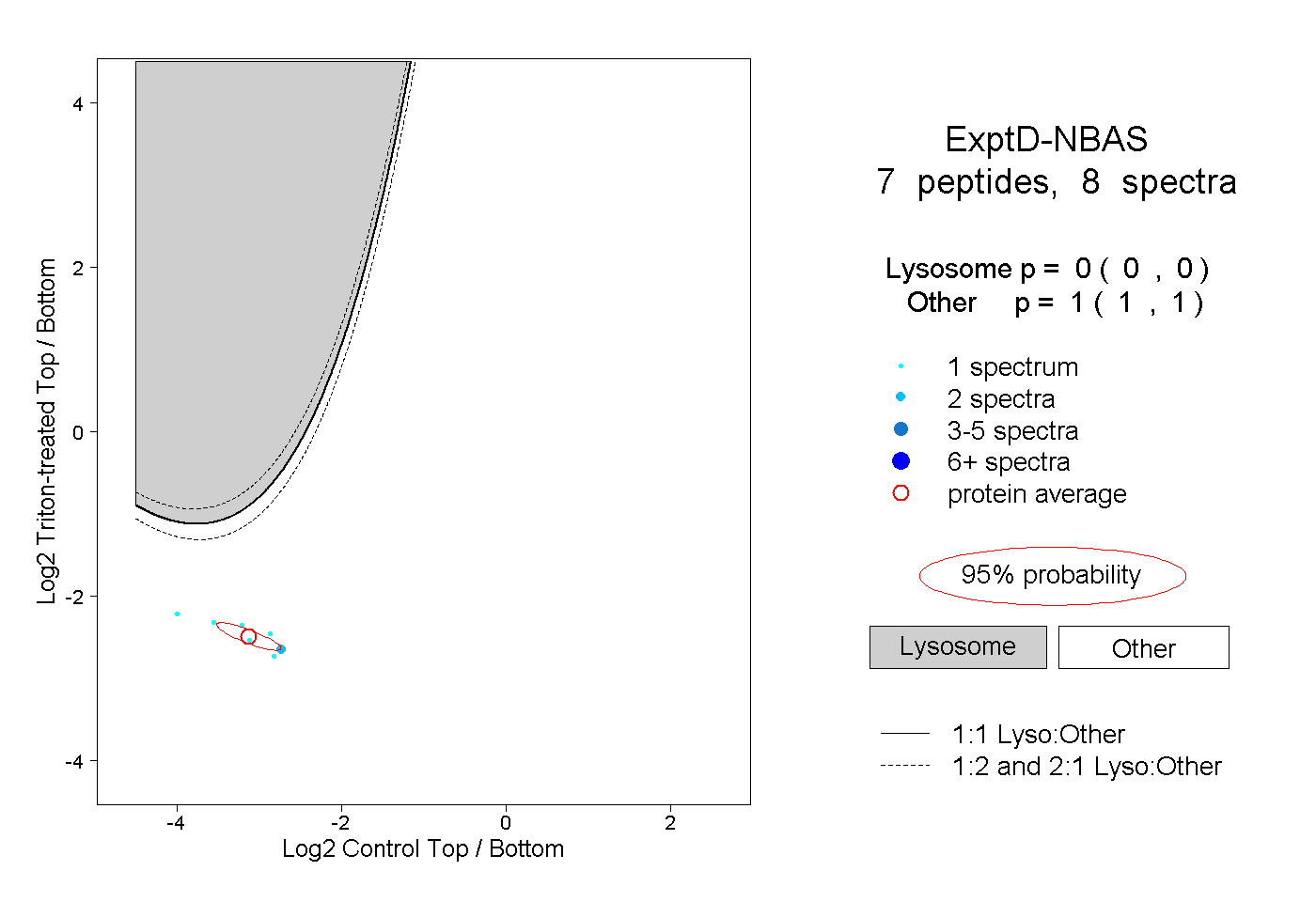 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |