peptides
spectra
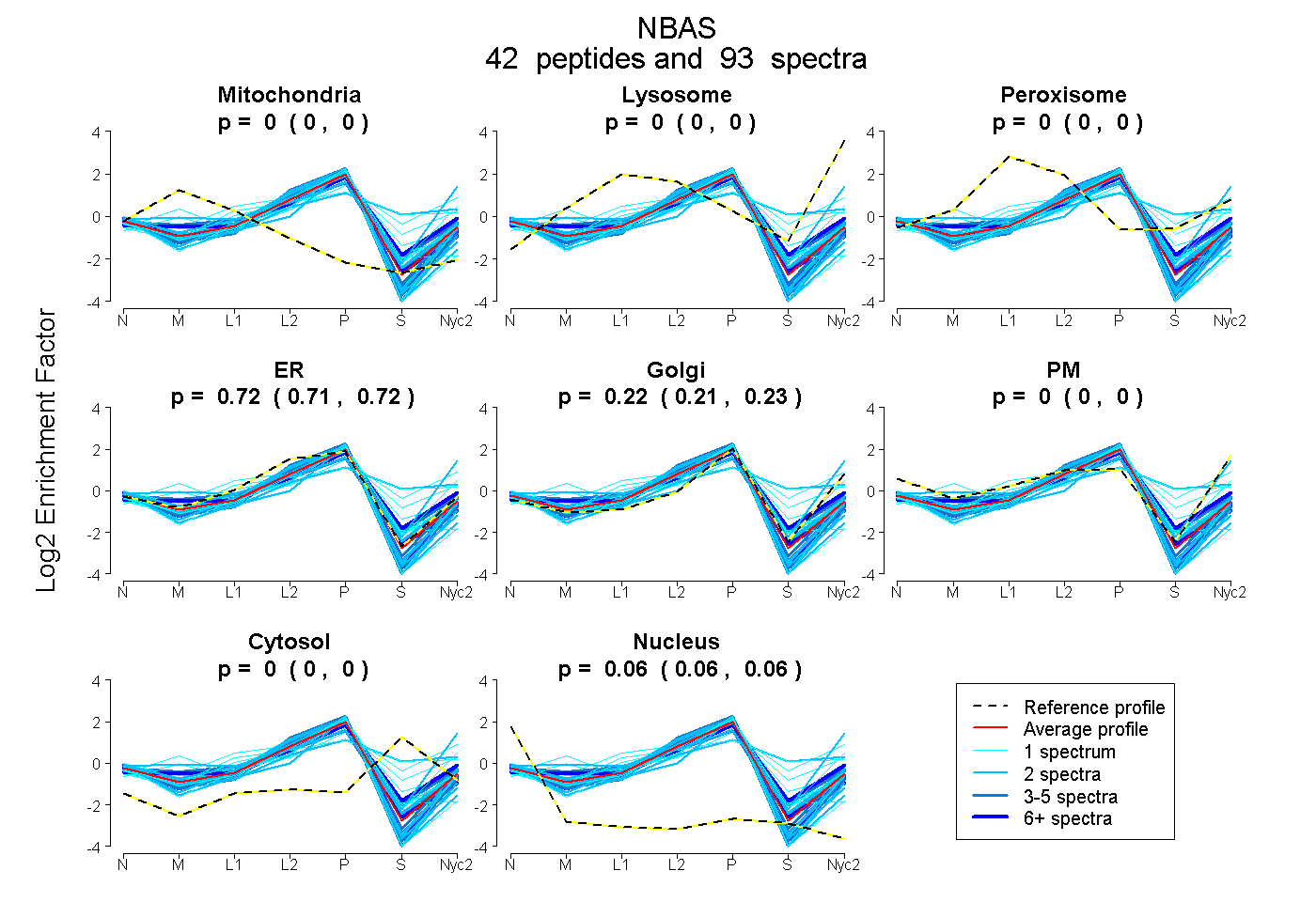
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.712 | 0.723
0.213 | 0.225
0.000 | 0.000
0.000 | 0.000
0.061 | 0.064
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
93 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.718 0.712 | 0.723 |
0.220 0.213 | 0.225 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.063 0.061 | 0.064 |
| 2 spectra, WNAEELAR | 0.182 | 0.000 | 0.000 | 0.638 | 0.180 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, SIDLVLAASR | 0.000 | 0.000 | 0.000 | 0.630 | 0.312 | 0.000 | 0.000 | 0.057 | ||
| 6 spectra, NSEQEVLQK | 0.027 | 0.000 | 0.021 | 0.487 | 0.384 | 0.000 | 0.082 | 0.000 | ||
| 2 spectra, QGLYLVTEMER | 0.000 | 0.000 | 0.000 | 0.695 | 0.258 | 0.000 | 0.011 | 0.036 | ||
| 4 spectra, IGTVANDDLER | 0.000 | 0.000 | 0.000 | 0.795 | 0.131 | 0.000 | 0.000 | 0.074 | ||
| 1 spectrum, LLPLQVR | 0.000 | 0.000 | 0.000 | 0.807 | 0.160 | 0.000 | 0.000 | 0.032 | ||
| 5 spectra, LLTFLDR | 0.000 | 0.000 | 0.000 | 0.754 | 0.204 | 0.000 | 0.000 | 0.042 | ||
| 1 spectrum, AQDIEHHAGQVDCALSLVR | 0.225 | 0.000 | 0.000 | 0.594 | 0.181 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, LNDQAVAMCLDGQPLR | 0.000 | 0.000 | 0.000 | 0.810 | 0.000 | 0.000 | 0.093 | 0.097 | ||
| 4 spectra, DHLLFLR | 0.000 | 0.000 | 0.000 | 0.772 | 0.142 | 0.000 | 0.086 | 0.000 | ||
| 1 spectrum, DDFTSIIGK | 0.101 | 0.000 | 0.000 | 0.449 | 0.308 | 0.000 | 0.141 | 0.000 | ||
| 2 spectra, VLSNTTTTTR | 0.000 | 0.000 | 0.000 | 0.603 | 0.231 | 0.000 | 0.000 | 0.166 | ||
| 1 spectrum, ELLQYGLK | 0.107 | 0.000 | 0.000 | 0.893 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, SLAYLRPLQGQDFGGAYR | 0.000 | 0.000 | 0.000 | 0.778 | 0.106 | 0.000 | 0.000 | 0.116 | ||
| 3 spectra, QVDVADTESEESR | 0.000 | 0.000 | 0.000 | 0.864 | 0.053 | 0.000 | 0.000 | 0.083 | ||
| 3 spectra, LLGLAELLR | 0.000 | 0.000 | 0.000 | 0.869 | 0.065 | 0.000 | 0.000 | 0.066 | ||
| 6 spectra, LGDEVLK | 0.000 | 0.000 | 0.000 | 0.781 | 0.114 | 0.000 | 0.000 | 0.105 | ||
| 2 spectra, SQNIVLSAR | 0.000 | 0.000 | 0.000 | 0.852 | 0.094 | 0.000 | 0.000 | 0.053 | ||
| 2 spectra, LVNFSK | 0.000 | 0.000 | 0.000 | 0.829 | 0.145 | 0.000 | 0.000 | 0.026 | ||
| 2 spectra, ASSCGLSAWR | 0.000 | 0.000 | 0.000 | 0.872 | 0.000 | 0.000 | 0.000 | 0.128 | ||
| 1 spectrum, GTDLEALVAIGK | 0.000 | 0.000 | 0.000 | 0.797 | 0.039 | 0.000 | 0.121 | 0.043 | ||
| 1 spectrum, ILSVSELLK | 0.000 | 0.000 | 0.000 | 0.750 | 0.190 | 0.000 | 0.000 | 0.060 | ||
| 2 spectra, YDAEFFK | 0.000 | 0.099 | 0.000 | 0.131 | 0.455 | 0.315 | 0.000 | 0.000 | ||
| 1 spectrum, QLHYYNER | 0.000 | 0.000 | 0.301 | 0.167 | 0.260 | 0.000 | 0.272 | 0.000 | ||
| 4 spectra, AQALHLFDTLK | 0.045 | 0.000 | 0.000 | 0.803 | 0.125 | 0.000 | 0.000 | 0.027 | ||
| 1 spectrum, AEDWCEELECR | 0.000 | 0.000 | 0.000 | 0.864 | 0.000 | 0.000 | 0.000 | 0.136 | ||
| 1 spectrum, HFIEKPR | 0.000 | 0.000 | 0.000 | 0.610 | 0.318 | 0.000 | 0.064 | 0.008 | ||
| 1 spectrum, YIYPTIEGLDHER | 0.000 | 0.000 | 0.000 | 0.670 | 0.225 | 0.000 | 0.072 | 0.032 | ||
| 1 spectrum, LSIWAIPSLK | 0.000 | 0.000 | 0.000 | 0.796 | 0.148 | 0.000 | 0.000 | 0.056 | ||
| 1 spectrum, DPLQVLEGVVGAVR | 0.000 | 0.000 | 0.000 | 0.773 | 0.084 | 0.000 | 0.079 | 0.064 | ||
| 2 spectra, QSAGAANELLR | 0.000 | 0.000 | 0.000 | 0.868 | 0.081 | 0.000 | 0.000 | 0.051 | ||
| 1 spectrum, SAVNIASIQNYLSK | 0.000 | 0.000 | 0.075 | 0.352 | 0.507 | 0.065 | 0.000 | 0.000 | ||
| 1 spectrum, EYLVTLAK | 0.000 | 0.000 | 0.000 | 0.755 | 0.186 | 0.000 | 0.000 | 0.059 | ||
| 1 spectrum, TFSTALSALR | 0.000 | 0.000 | 0.000 | 0.611 | 0.266 | 0.000 | 0.084 | 0.039 | ||
| 2 spectra, STTPEELYQR | 0.000 | 0.000 | 0.000 | 0.792 | 0.138 | 0.000 | 0.000 | 0.070 | ||
| 2 spectra, QGQEQDGIFK | 0.000 | 0.069 | 0.034 | 0.190 | 0.216 | 0.113 | 0.378 | 0.000 | ||
| 1 spectrum, CQVPK | 0.000 | 0.094 | 0.134 | 0.000 | 0.521 | 0.041 | 0.210 | 0.000 | ||
| 4 spectra, LAPCFR | 0.144 | 0.000 | 0.000 | 0.590 | 0.266 | 0.000 | 0.000 | 0.000 | ||
| 10 spectra, LVTVMLTR | 0.000 | 0.000 | 0.000 | 0.814 | 0.120 | 0.000 | 0.000 | 0.066 | ||
| 1 spectrum, LFWTGDPHLIK | 0.000 | 0.000 | 0.000 | 0.835 | 0.087 | 0.000 | 0.000 | 0.077 | ||
| 1 spectrum, VPENVDAAK | 0.000 | 0.000 | 0.000 | 0.703 | 0.232 | 0.000 | 0.000 | 0.065 | ||
| 1 spectrum, AMAWYR | 0.000 | 0.000 | 0.156 | 0.238 | 0.375 | 0.064 | 0.167 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
27 spectra |
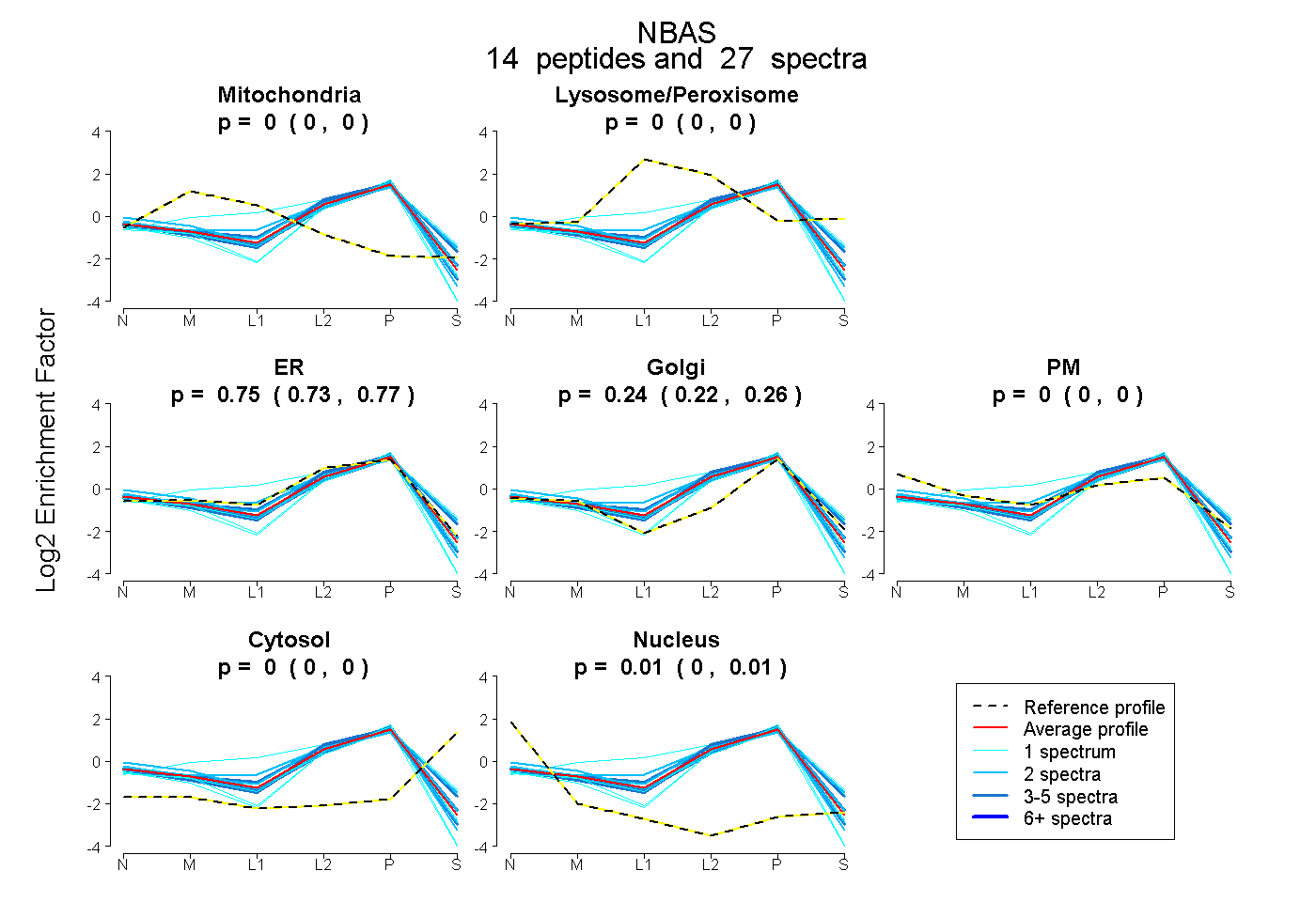 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.750 0.732 | 0.765 |
0.241 0.220 | 0.260 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.009 0.005 | 0.012 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
79 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
8 spectra |
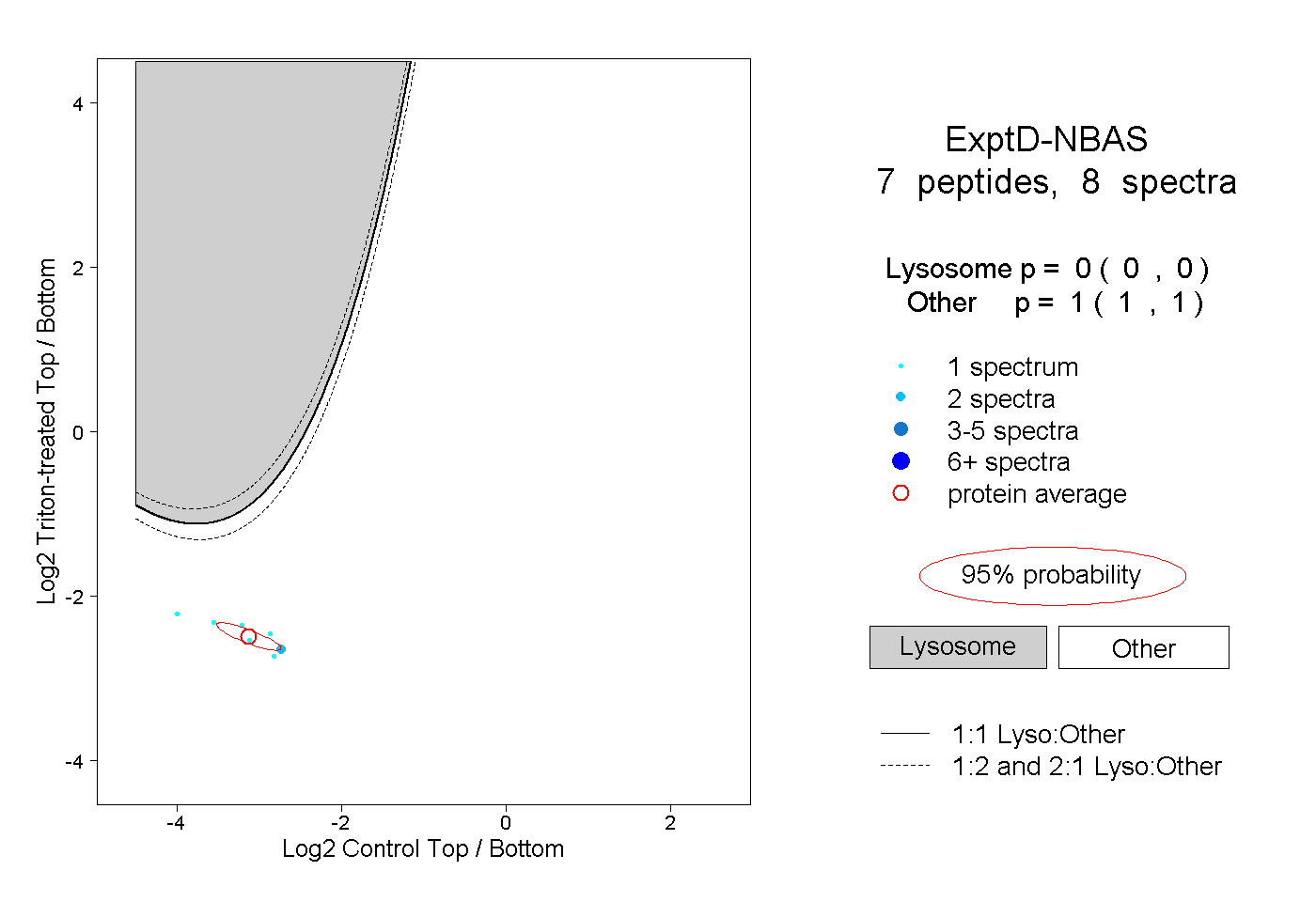 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |