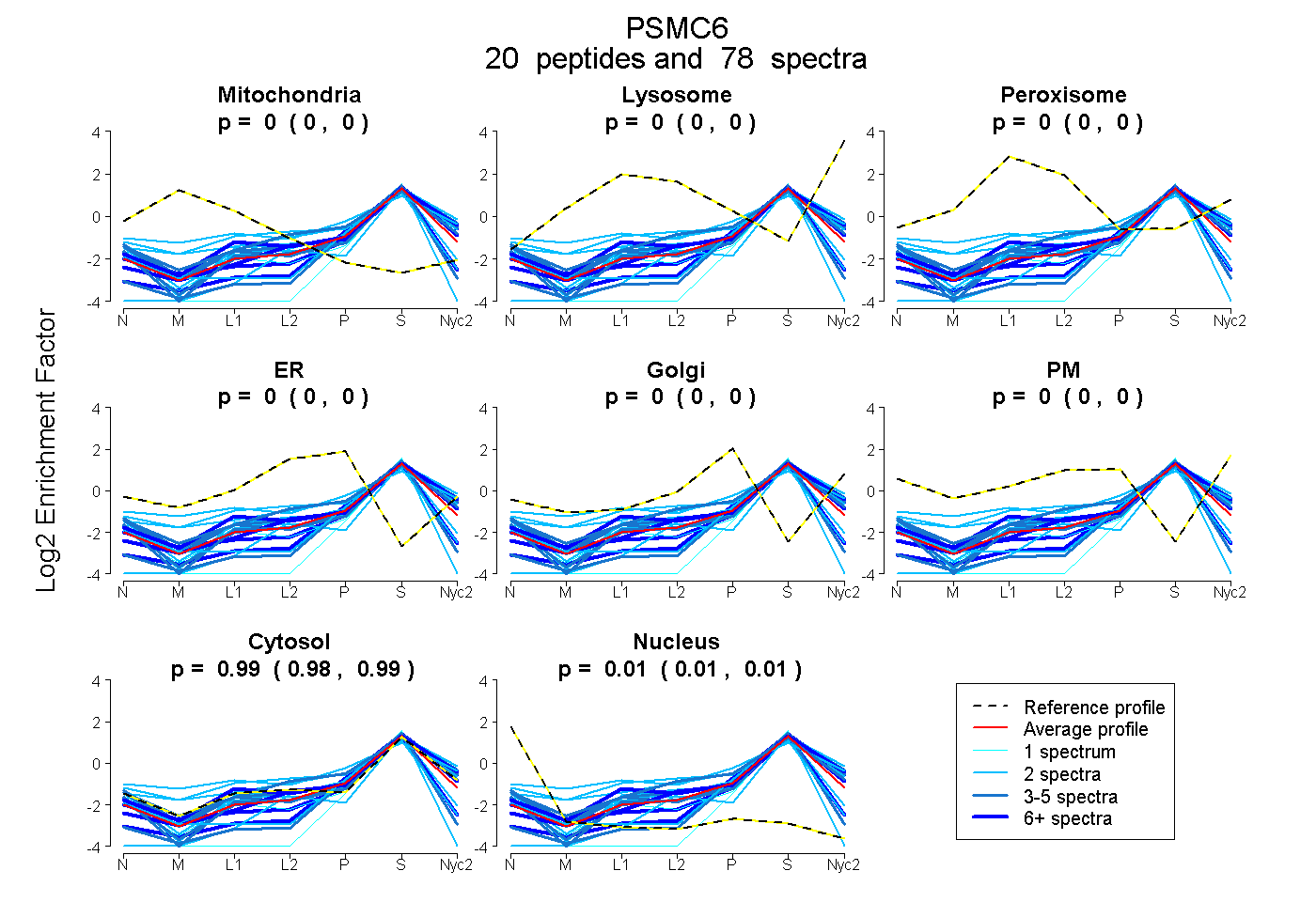
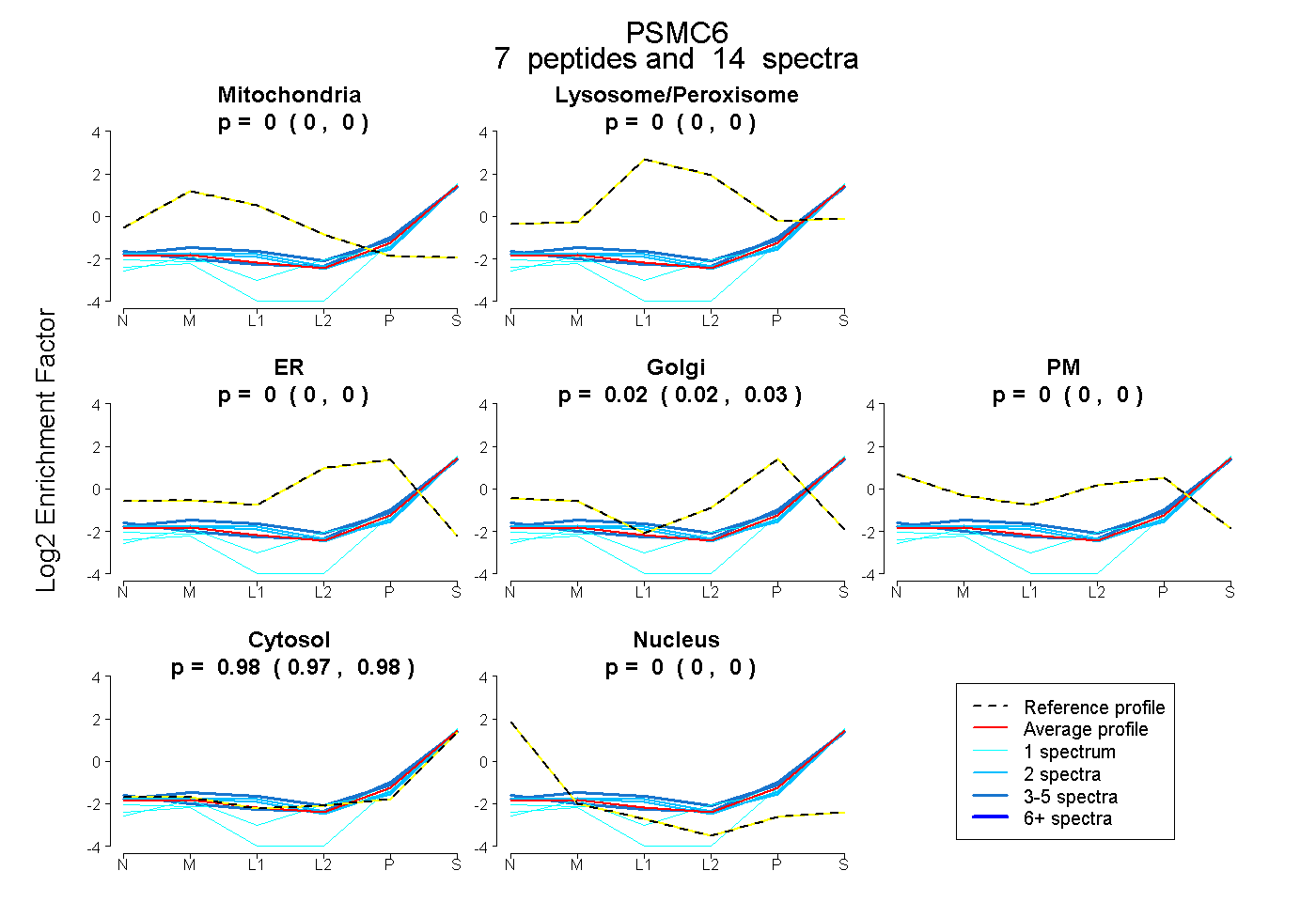
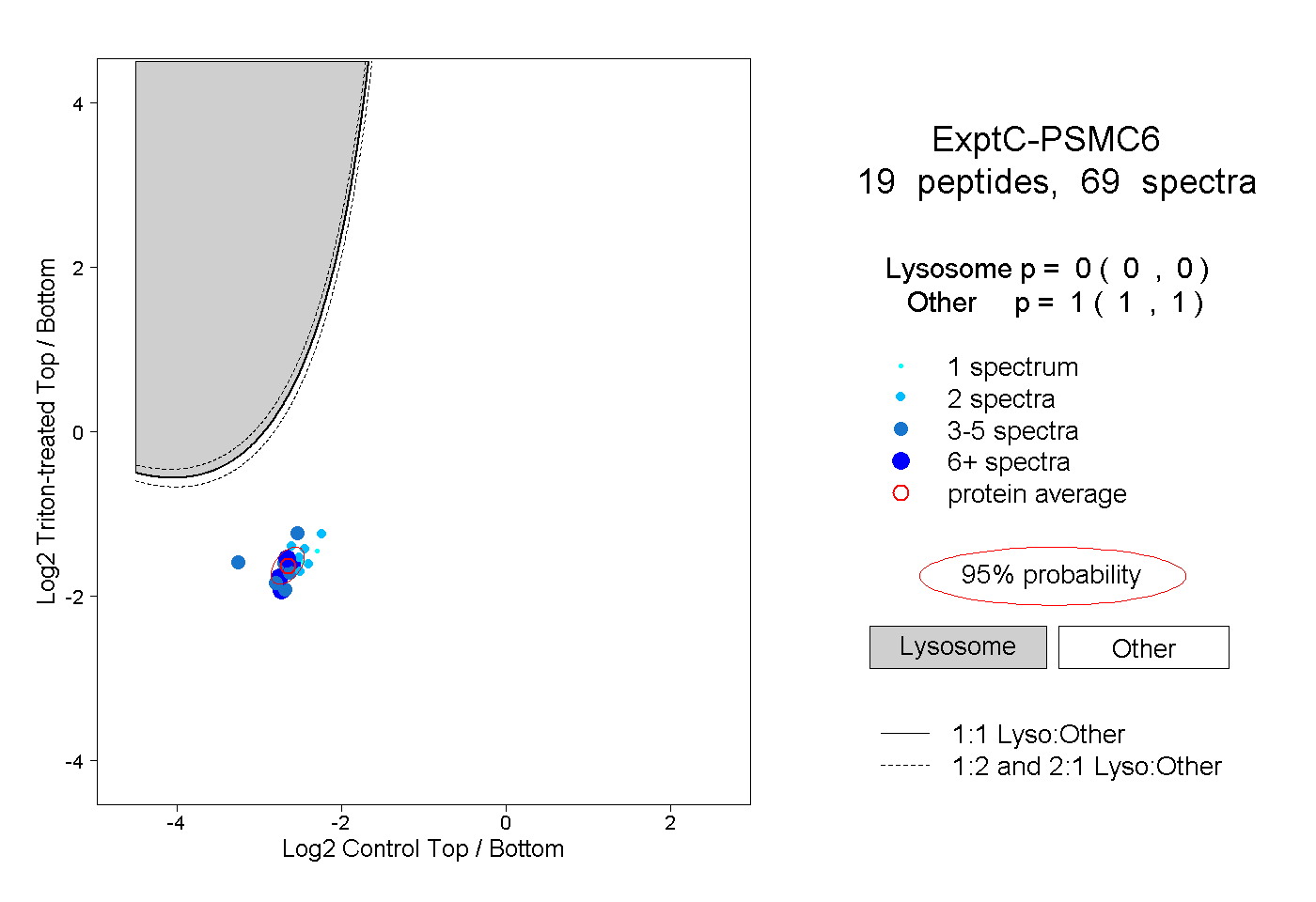
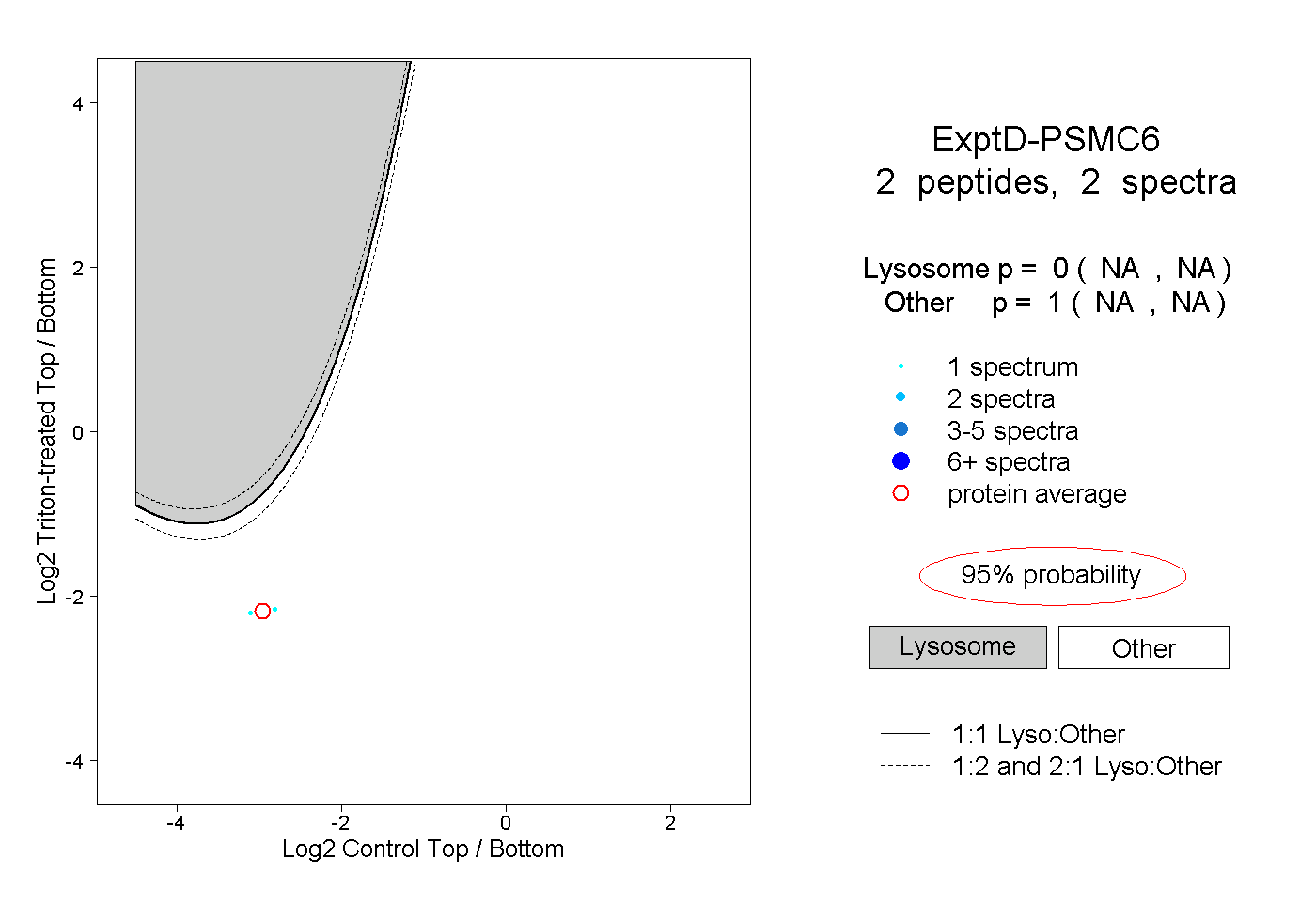
| 3 spectra, HGEIDYEAIVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, FSEGTSADR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VGIIPPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, TLMELLNQMDGFDTLHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LSDGFNGADLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VVSSSIVDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EVIELPLTNPELFQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, IHIDLPNEQAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ADHDFVVQEDFMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, AVASQLDCNFLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GCLLYGPPGTGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, YIGESAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, ALQDYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VADSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, NVCTEAGMFAIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, EMFNYAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, QLTEEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, IHAGPITK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, SENDLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |