peptides
spectra
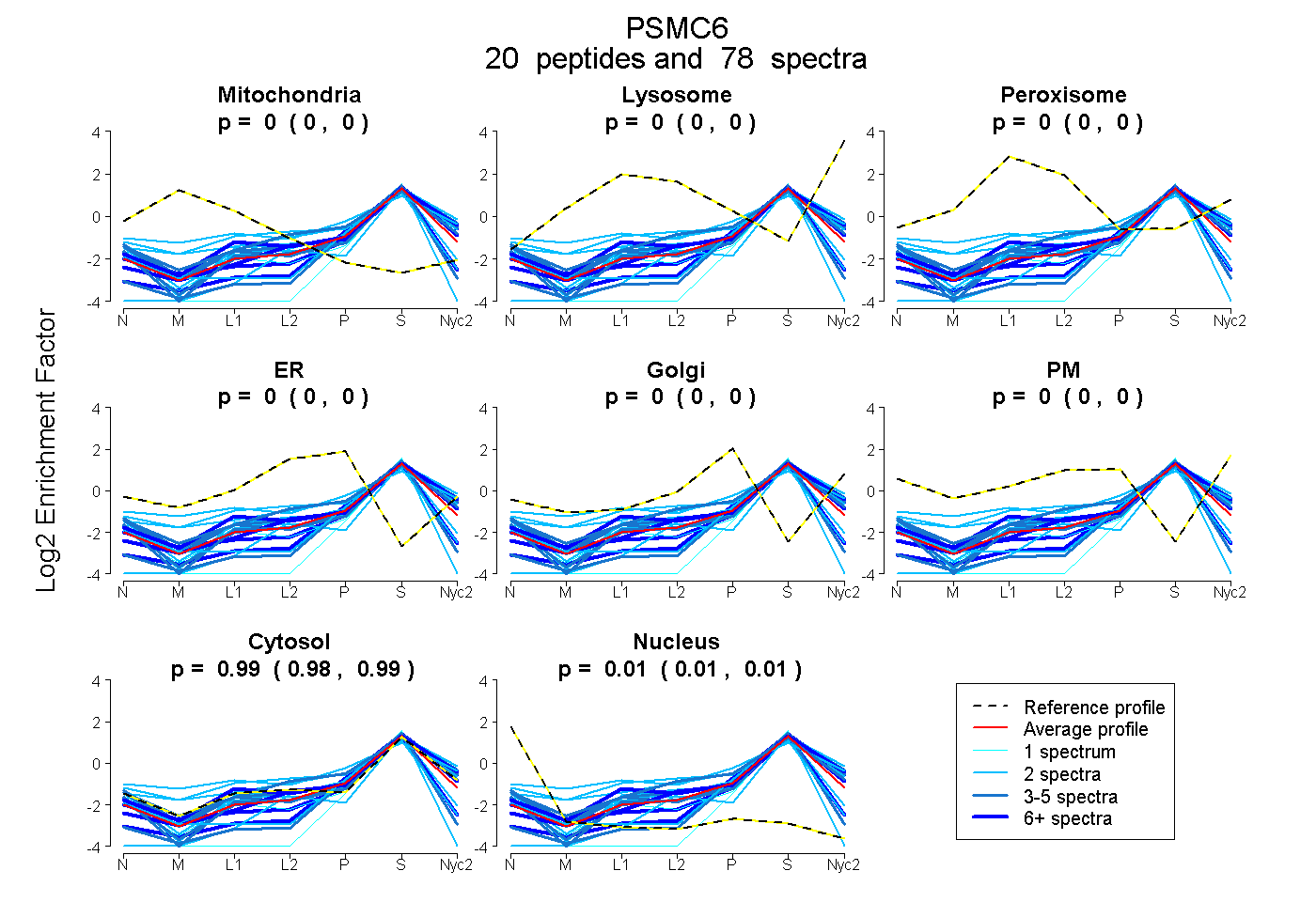
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.985 | 0.994
0.005 | 0.015
peptides
spectra
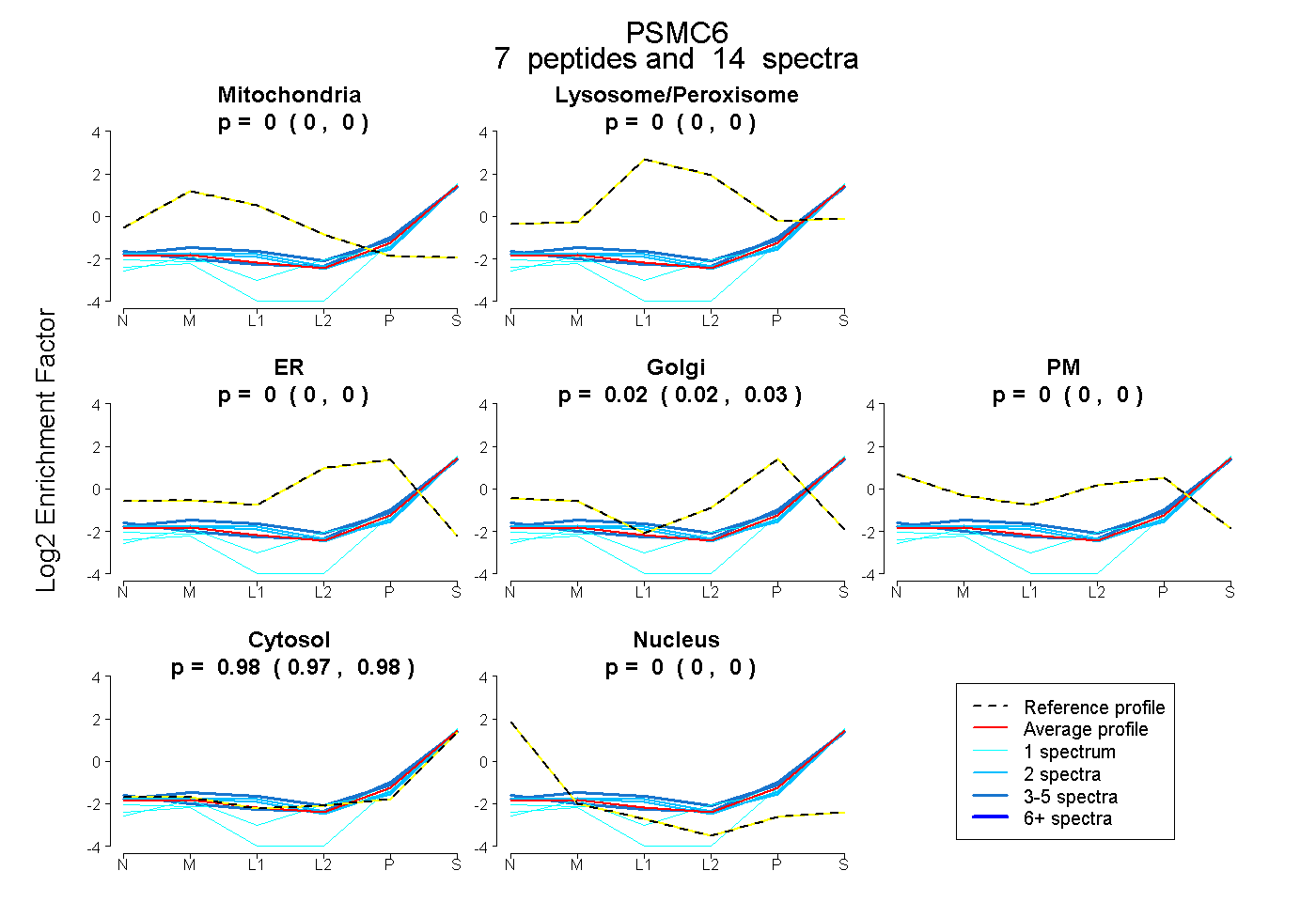
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.016 | 0.032
0.000 | 0.000
0.967 | 0.982
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
78 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.990 0.985 | 0.994 |
0.010 0.005 | 0.015 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
14 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.025 0.016 | 0.032 |
0.000 0.000 | 0.000 |
0.975 0.967 | 0.982 |
0.000 0.000 | 0.000 |
| 1 spectrum, HGEIDYEAIVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.990 | 0.010 | |||
| 1 spectrum, FSEGTSADR | 0.000 | 0.000 | 0.000 | 0.019 | 0.000 | 0.981 | 0.000 | |||
| 1 spectrum, TLMELLNQMDGFDTLHR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 4 spectra, LSDGFNGADLR | 0.000 | 0.000 | 0.000 | 0.069 | 0.000 | 0.931 | 0.000 | |||
| 2 spectra, YIGESAR | 0.000 | 0.000 | 0.000 | 0.009 | 0.000 | 0.991 | 0.000 | |||
| 3 spectra, IHIDLPNEQAR | 0.000 | 0.064 | 0.000 | 0.046 | 0.000 | 0.889 | 0.000 | |||
| 2 spectra, YVVGCR | 0.000 | 0.020 | 0.000 | 0.000 | 0.000 | 0.980 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
69 spectra |
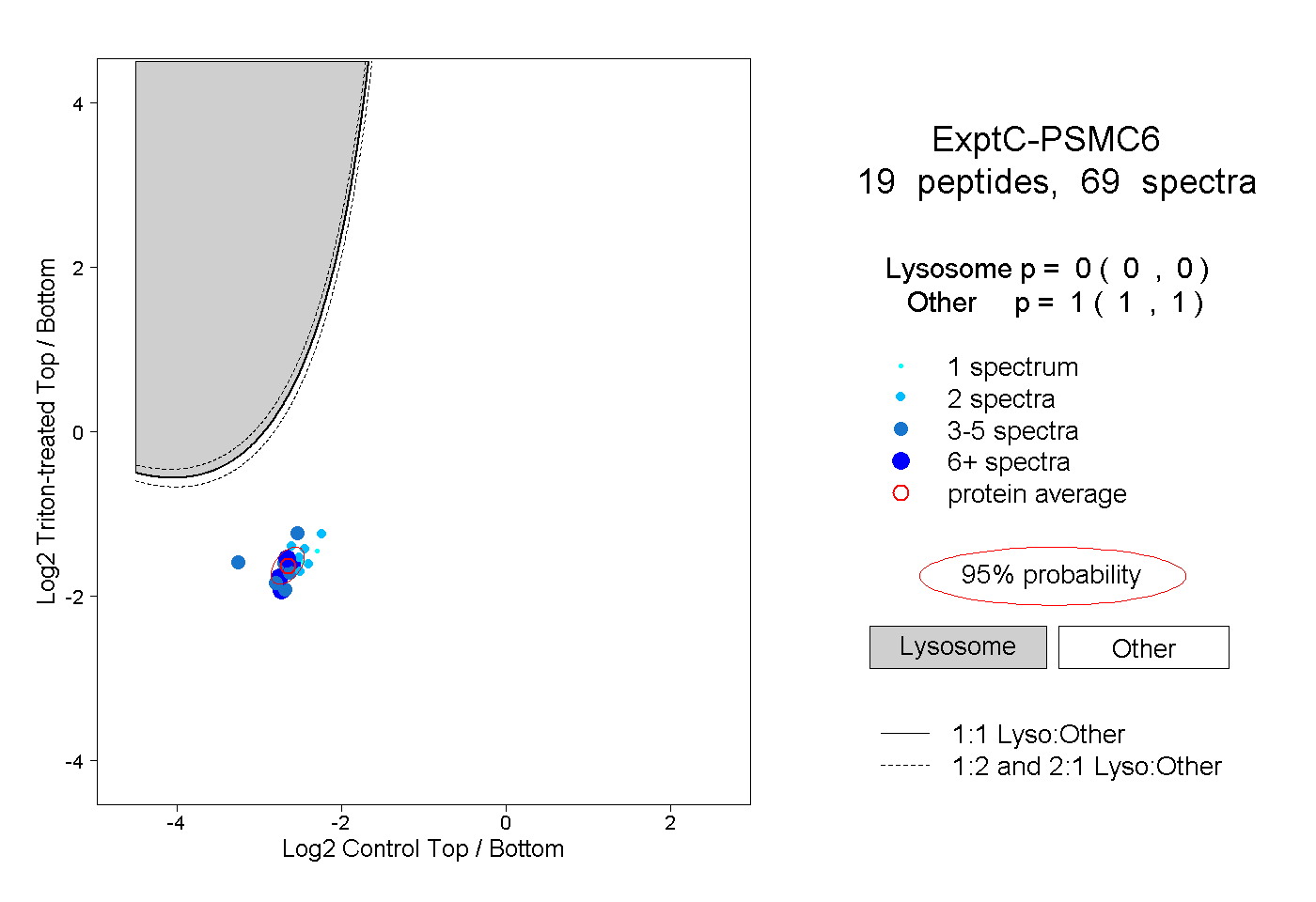 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
2 spectra |
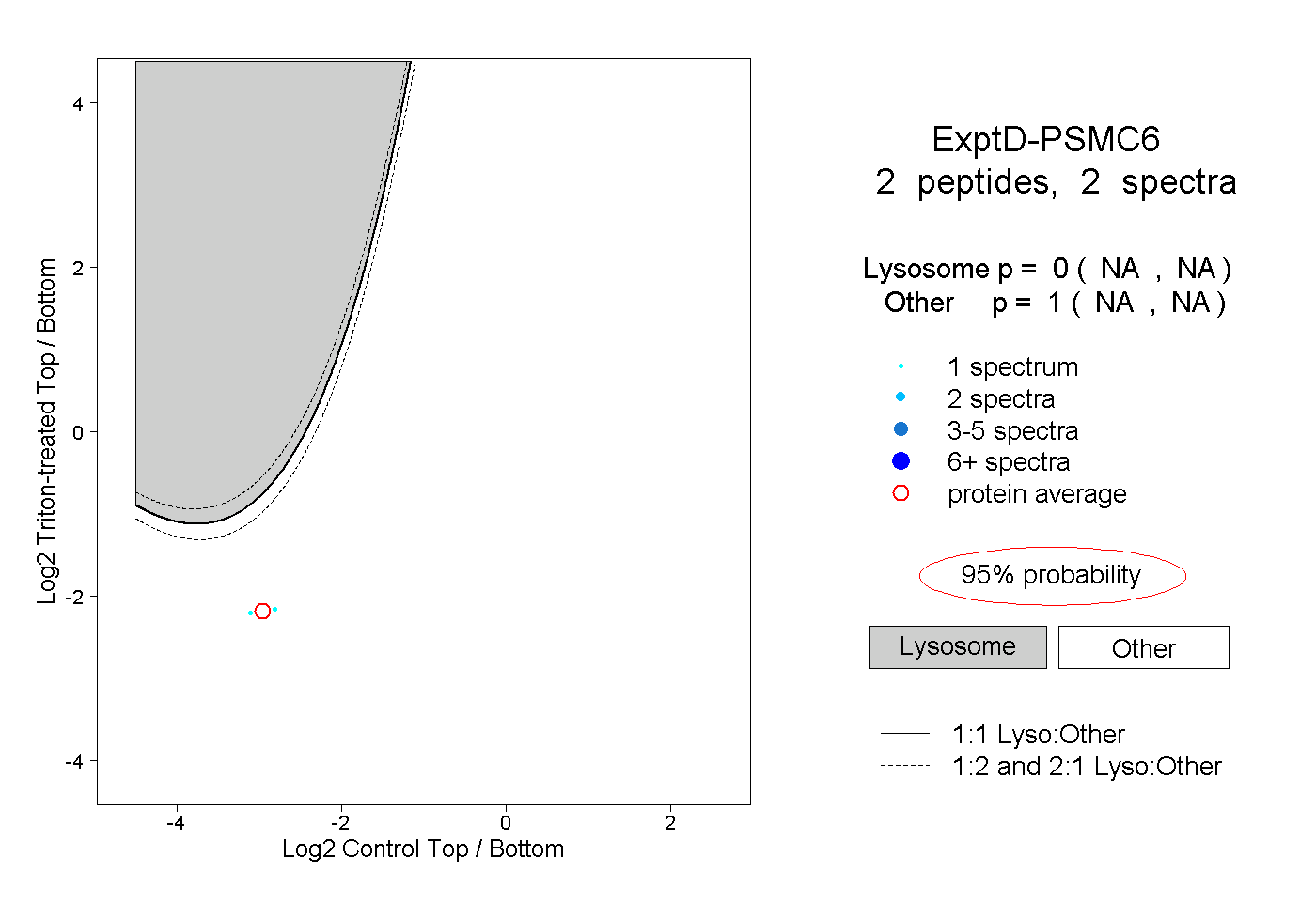 |
0.000 NA | NA |
1.000 NA | NA |