peptides
spectra
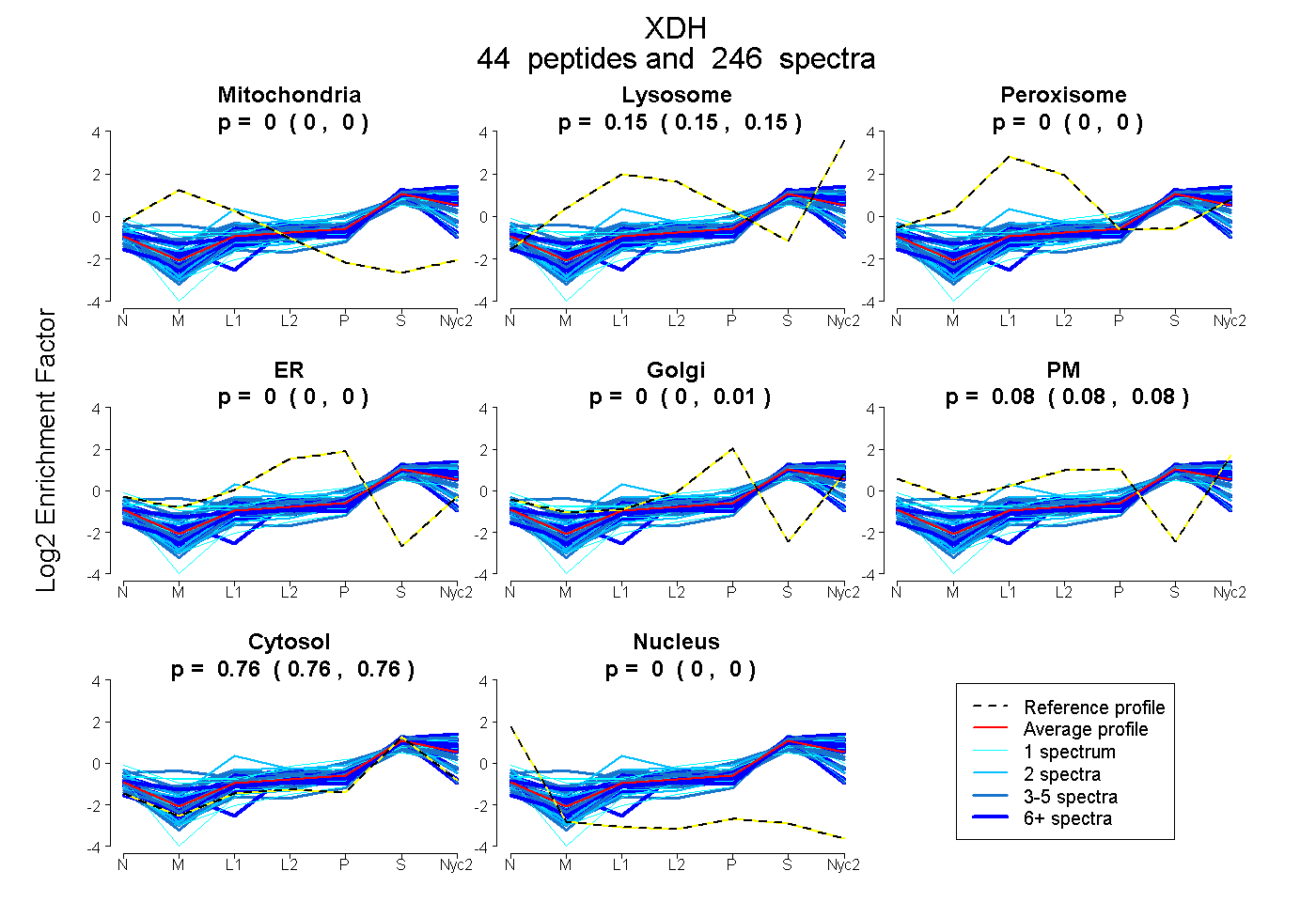
0.000 | 0.000
0.150 | 0.154
0.000 | 0.000
0.000 | 0.000
0.002 | 0.007
0.077 | 0.083
0.762 | 0.764
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
246 spectra |
 |
0.000 0.000 | 0.000 |
0.152 0.150 | 0.154 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.004 0.002 | 0.007 |
0.081 0.077 | 0.083 |
0.763 0.762 | 0.764 |
0.000 0.000 | 0.000 |
| 13 spectra, GVMEQLR | 0.000 | 0.222 | 0.000 | 0.000 | 0.009 | 0.000 | 0.770 | 0.000 | ||
| 5 spectra, AQHPDAK | 0.000 | 0.055 | 0.000 | 0.000 | 0.000 | 0.196 | 0.749 | 0.000 | ||
| 3 spectra, TADELVFFVNGK | 0.000 | 0.089 | 0.000 | 0.000 | 0.000 | 0.171 | 0.740 | 0.000 | ||
| 3 spectra, DEVTCVGHIIGAVVADTPEHAQR | 0.121 | 0.030 | 0.138 | 0.000 | 0.000 | 0.155 | 0.556 | 0.000 | ||
| 2 spectra, LGLCGTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.074 | 0.000 | 0.926 | 0.000 | ||
| 9 spectra, ALFHMDNAYK | 0.000 | 0.242 | 0.000 | 0.000 | 0.000 | 0.068 | 0.689 | 0.000 | ||
| 4 spectra, MGGGFGGK | 0.000 | 0.279 | 0.000 | 0.000 | 0.046 | 0.043 | 0.631 | 0.000 | ||
| 6 spectra, ADLEDMCGK | 0.000 | 0.000 | 0.000 | 0.122 | 0.002 | 0.000 | 0.875 | 0.000 | ||
| 1 spectrum, VTSGMR | 0.000 | 0.285 | 0.000 | 0.000 | 0.000 | 0.111 | 0.605 | 0.000 | ||
| 1 spectrum, EDDIAK | 0.000 | 0.016 | 0.000 | 0.000 | 0.110 | 0.079 | 0.795 | 0.000 | ||
| 3 spectra, VTWIQASTMEELLDLK | 0.000 | 0.260 | 0.000 | 0.000 | 0.000 | 0.000 | 0.740 | 0.000 | ||
| 5 spectra, ALYASK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.970 | 0.030 | ||
| 1 spectrum, STVVSTAVALAAHK | 0.000 | 0.230 | 0.000 | 0.000 | 0.000 | 0.000 | 0.770 | 0.000 | ||
| 9 spectra, GEAGEMELFVSTQNTMK | 0.000 | 0.166 | 0.000 | 0.000 | 0.000 | 0.135 | 0.700 | 0.000 | ||
| 23 spectra, MVQVASR | 0.000 | 0.295 | 0.000 | 0.000 | 0.017 | 0.000 | 0.688 | 0.000 | ||
| 1 spectrum, ENCWK | 0.000 | 0.316 | 0.000 | 0.000 | 0.000 | 0.000 | 0.684 | 0.000 | ||
| 4 spectra, HPFLAK | 0.000 | 0.148 | 0.000 | 0.000 | 0.000 | 0.000 | 0.852 | 0.000 | ||
| 23 spectra, LVTSTR | 0.000 | 0.232 | 0.000 | 0.000 | 0.000 | 0.019 | 0.749 | 0.000 | ||
| 4 spectra, ITSIDTSEAK | 0.000 | 0.231 | 0.000 | 0.000 | 0.047 | 0.000 | 0.721 | 0.000 | ||
| 1 spectrum, SWSVR | 0.000 | 0.215 | 0.000 | 0.000 | 0.000 | 0.189 | 0.595 | 0.000 | ||
| 1 spectrum, NLMDIAK | 0.000 | 0.000 | 0.039 | 0.000 | 0.000 | 0.410 | 0.551 | 0.000 | ||
| 4 spectra, EGDLTHFNQK | 0.000 | 0.146 | 0.000 | 0.000 | 0.015 | 0.000 | 0.839 | 0.000 | ||
| 2 spectra, TLSALK | 0.000 | 0.274 | 0.089 | 0.000 | 0.000 | 0.080 | 0.557 | 0.000 | ||
| 1 spectrum, NQPEPTVEEIENAFQGNLCR | 0.000 | 0.000 | 0.000 | 0.000 | 0.067 | 0.000 | 0.933 | 0.000 | ||
| 11 spectra, EGEFFSAFK | 0.000 | 0.196 | 0.000 | 0.000 | 0.000 | 0.063 | 0.741 | 0.000 | ||
| 7 spectra, LEGFTLPR | 0.000 | 0.258 | 0.000 | 0.000 | 0.000 | 0.026 | 0.716 | 0.000 | ||
| 2 spectra, IPAFGSIPIEFR | 0.000 | 0.190 | 0.000 | 0.000 | 0.000 | 0.000 | 0.810 | 0.000 | ||
| 9 spectra, YENELSLR | 0.000 | 0.222 | 0.000 | 0.000 | 0.000 | 0.071 | 0.707 | 0.000 | ||
| 2 spectra, TQSFVAK | 0.000 | 0.283 | 0.000 | 0.000 | 0.009 | 0.000 | 0.708 | 0.000 | ||
| 9 spectra, TNLPSNTAFR | 0.000 | 0.168 | 0.000 | 0.000 | 0.000 | 0.000 | 0.832 | 0.000 | ||
| 3 spectra, NADPETTLLVYLR | 0.000 | 0.147 | 0.000 | 0.000 | 0.099 | 0.004 | 0.750 | 0.000 | ||
| 3 spectra, GLCIIPTK | 0.000 | 0.012 | 0.099 | 0.000 | 0.074 | 0.000 | 0.815 | 0.000 | ||
| 2 spectra, DPPANVQLFQEVPK | 0.000 | 0.109 | 0.000 | 0.000 | 0.000 | 0.210 | 0.682 | 0.000 | ||
| 6 spectra, AQHGDNAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.090 | 0.016 | 0.894 | 0.000 | ||
| 3 spectra, CWDECIASSQYLAR | 0.013 | 0.000 | 0.185 | 0.000 | 0.000 | 0.172 | 0.630 | 0.000 | ||
| 15 spectra, LTLVSR | 0.000 | 0.196 | 0.000 | 0.000 | 0.064 | 0.028 | 0.712 | 0.000 | ||
| 7 spectra, DEDMLITGGR | 0.000 | 0.222 | 0.000 | 0.000 | 0.000 | 0.000 | 0.778 | 0.000 | ||
| 1 spectrum, LDPTFASATLLFQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.945 | 0.055 | ||
| 9 spectra, CTGYRPILQGFR | 0.000 | 0.000 | 0.000 | 0.036 | 0.184 | 0.000 | 0.754 | 0.026 | ||
| 8 spectra, GPSTYK | 0.000 | 0.214 | 0.000 | 0.000 | 0.000 | 0.018 | 0.768 | 0.000 | ||
| 3 spectra, MLGVPDNR | 0.000 | 0.228 | 0.000 | 0.000 | 0.000 | 0.000 | 0.772 | 0.000 | ||
| 8 spectra, MDHTFFPGYR | 0.000 | 0.161 | 0.000 | 0.000 | 0.067 | 0.009 | 0.763 | 0.000 | ||
| 4 spectra, QLFQLDSPATPEK | 0.000 | 0.078 | 0.000 | 0.000 | 0.131 | 0.112 | 0.679 | 0.000 | ||
| 5 spectra, LVVGNTEIGIEMK | 0.000 | 0.329 | 0.000 | 0.000 | 0.000 | 0.002 | 0.669 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
84 spectra |
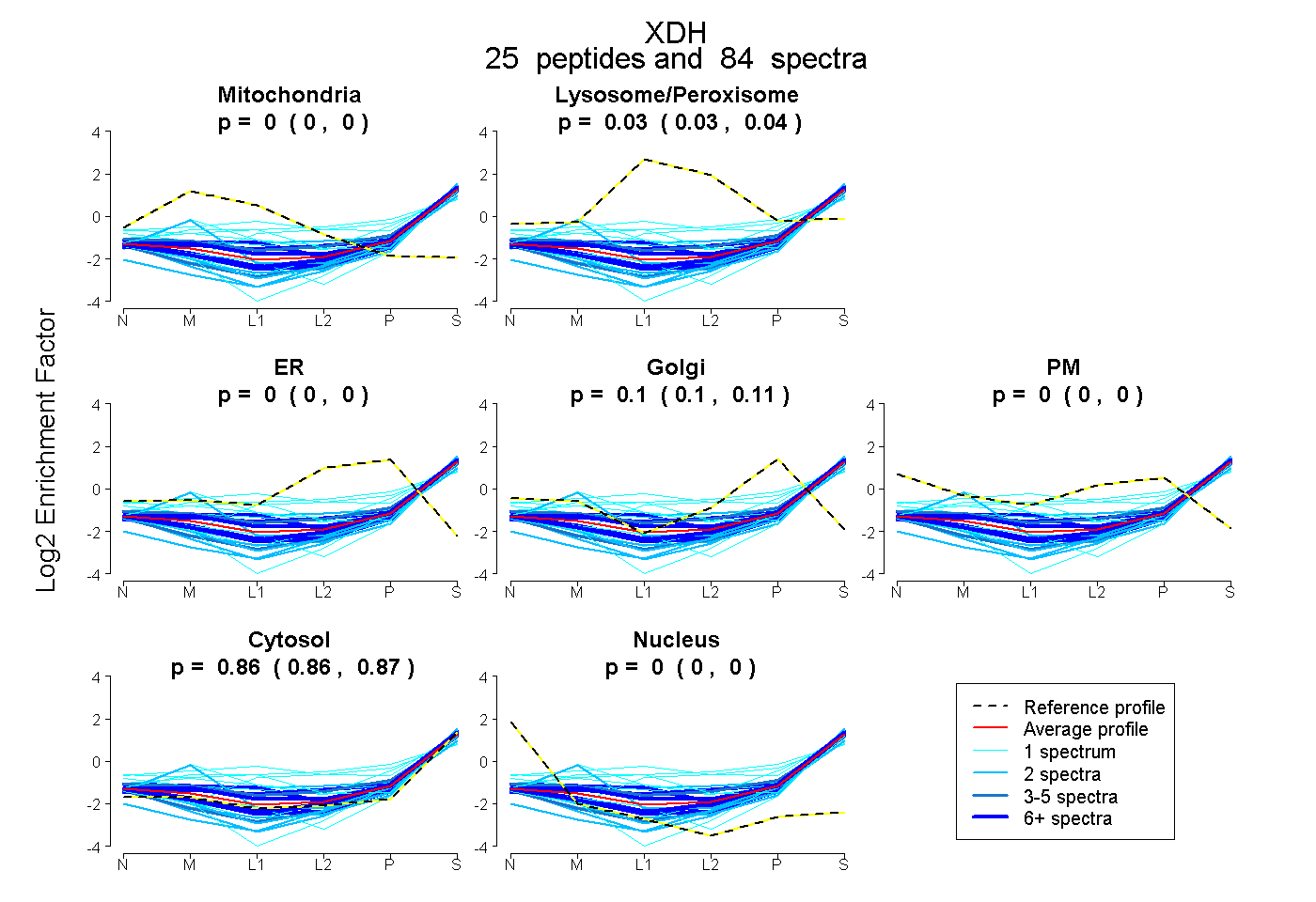 |
0.000 0.000 | 0.000 |
0.034 0.029 | 0.039 |
0.000 0.000 | 0.000 |
0.103 0.099 | 0.106 |
0.000 0.000 | 0.000 |
0.863 0.860 | 0.865 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
258 spectra |
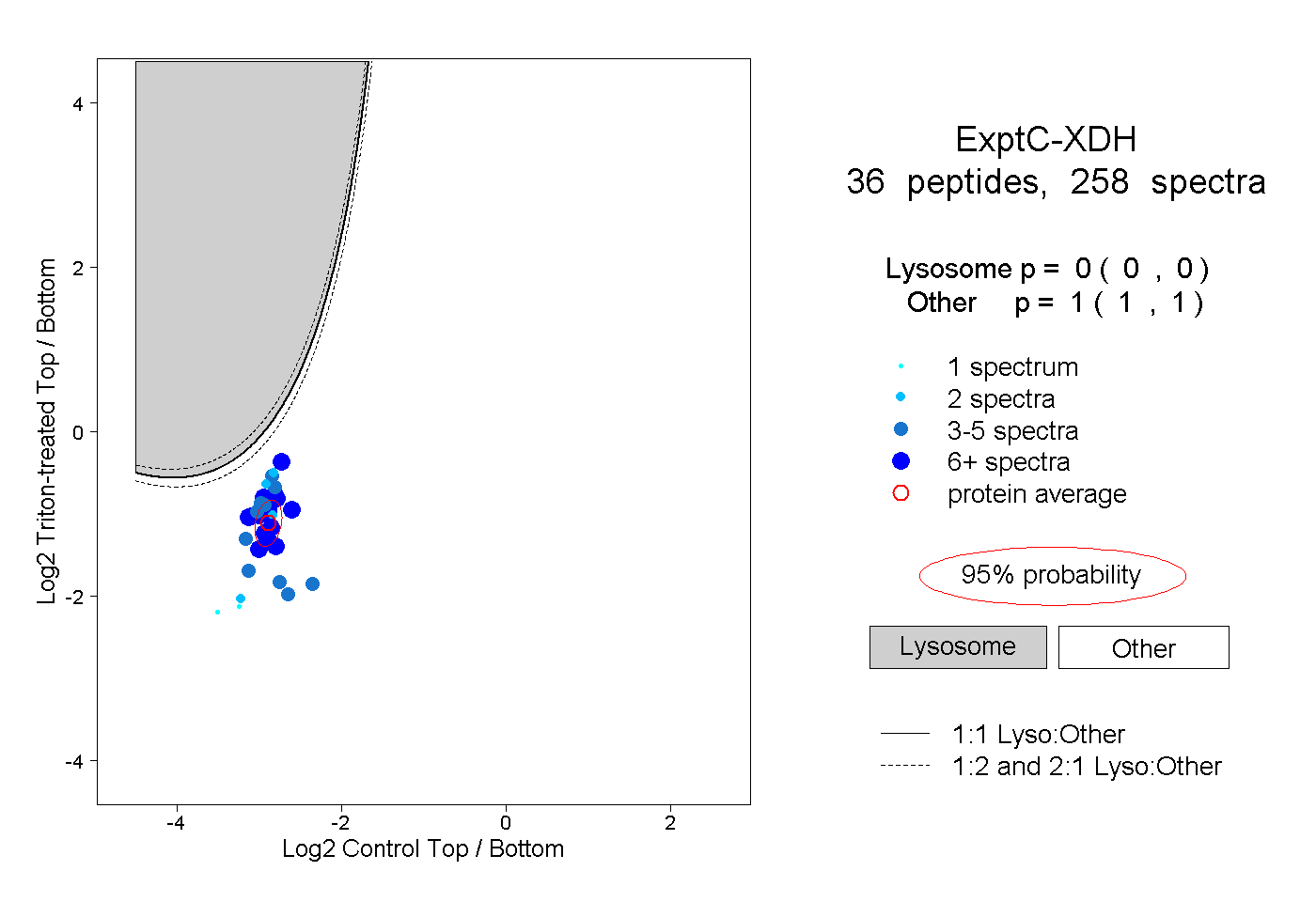 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
39 spectra |
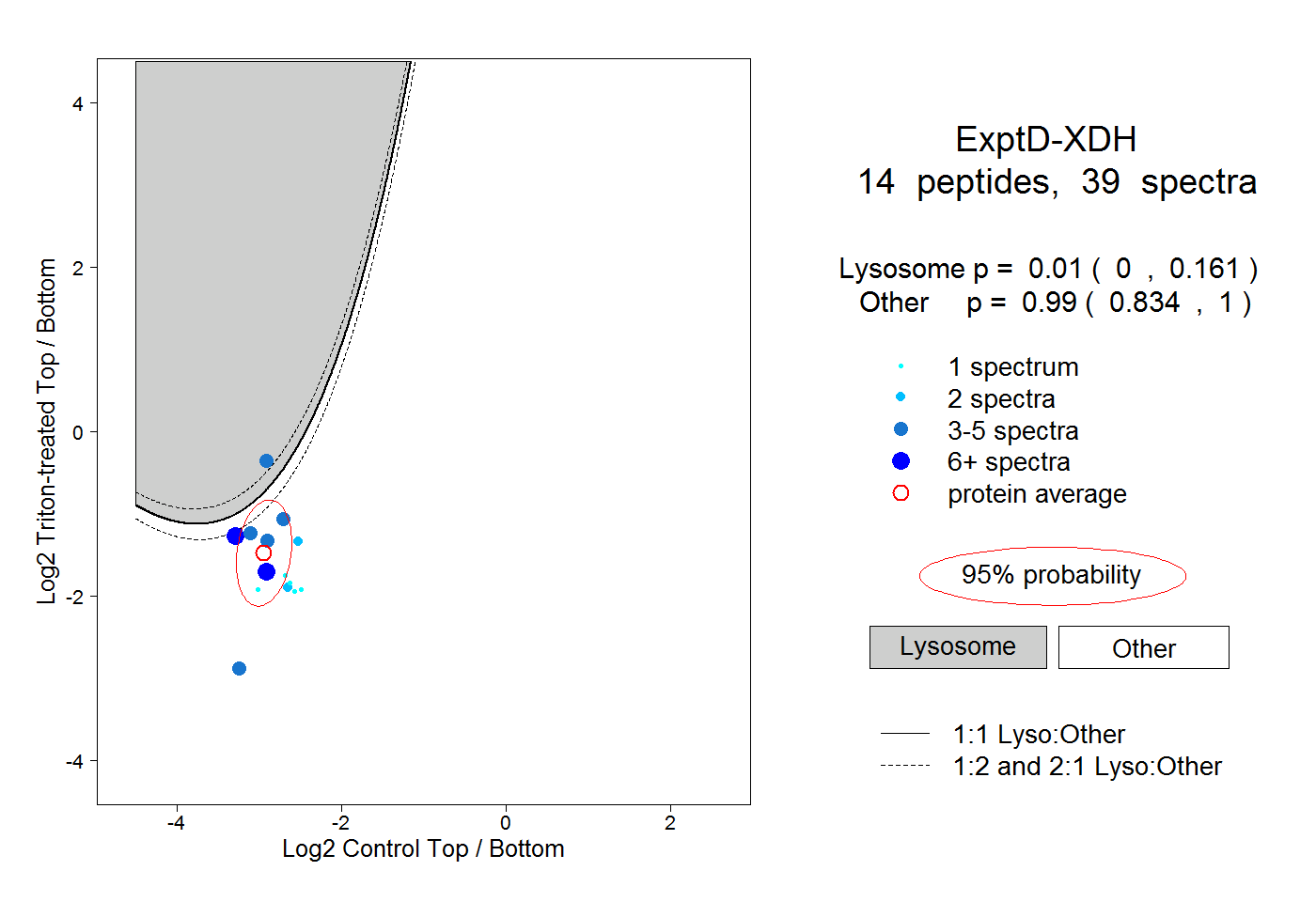 |
0.010 0.000 | 0.161 |
0.990 0.834 | 1.000 |