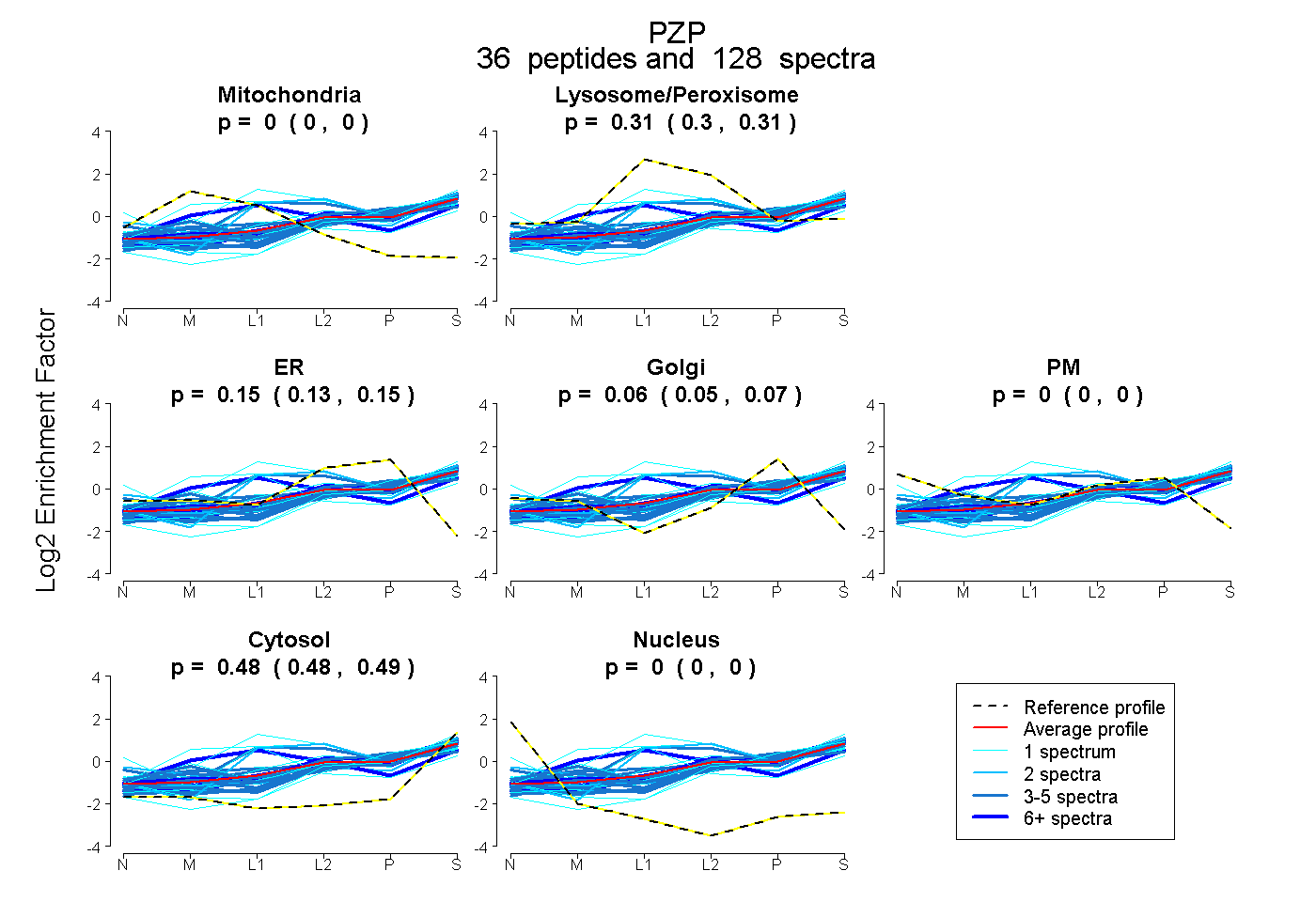
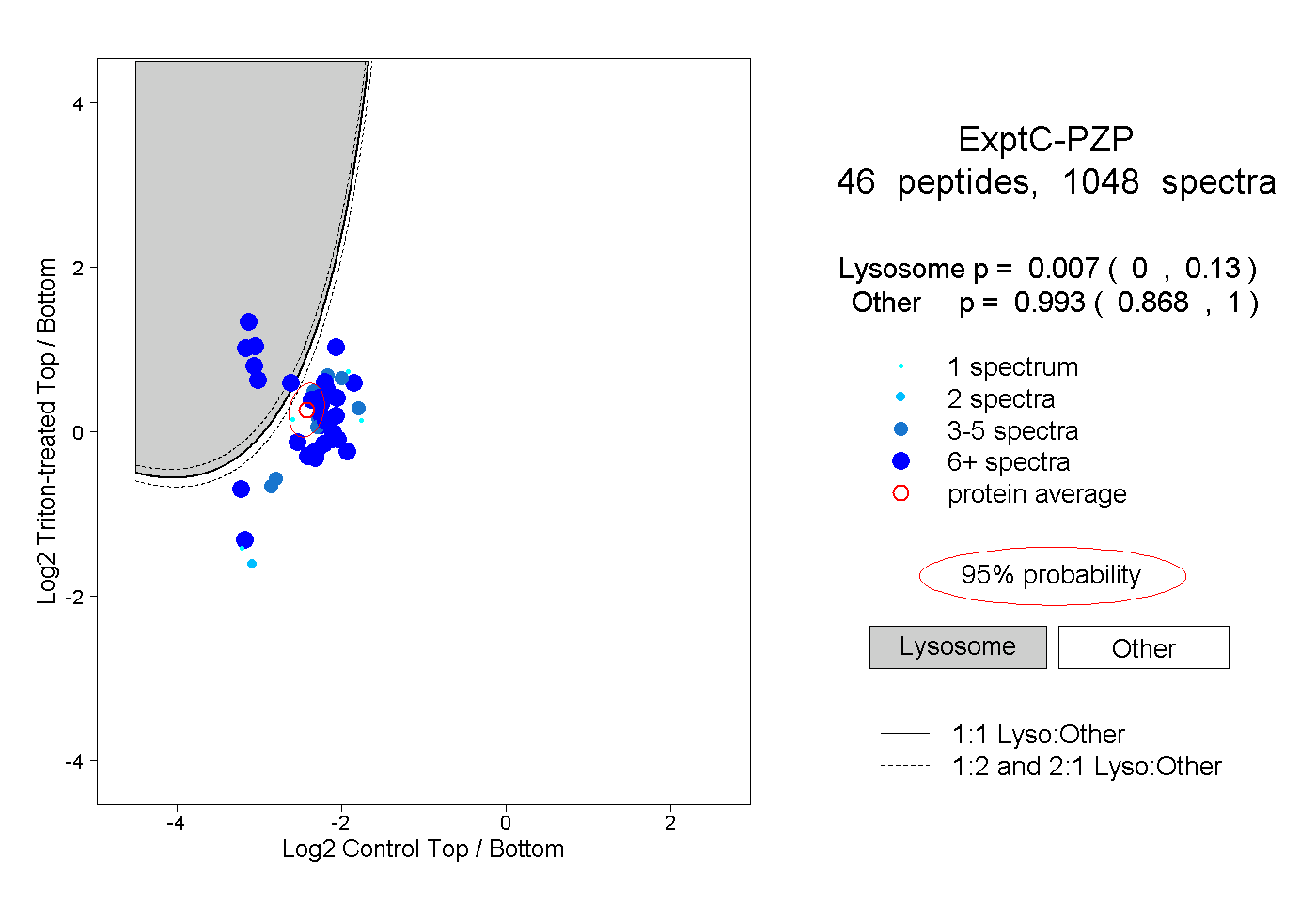
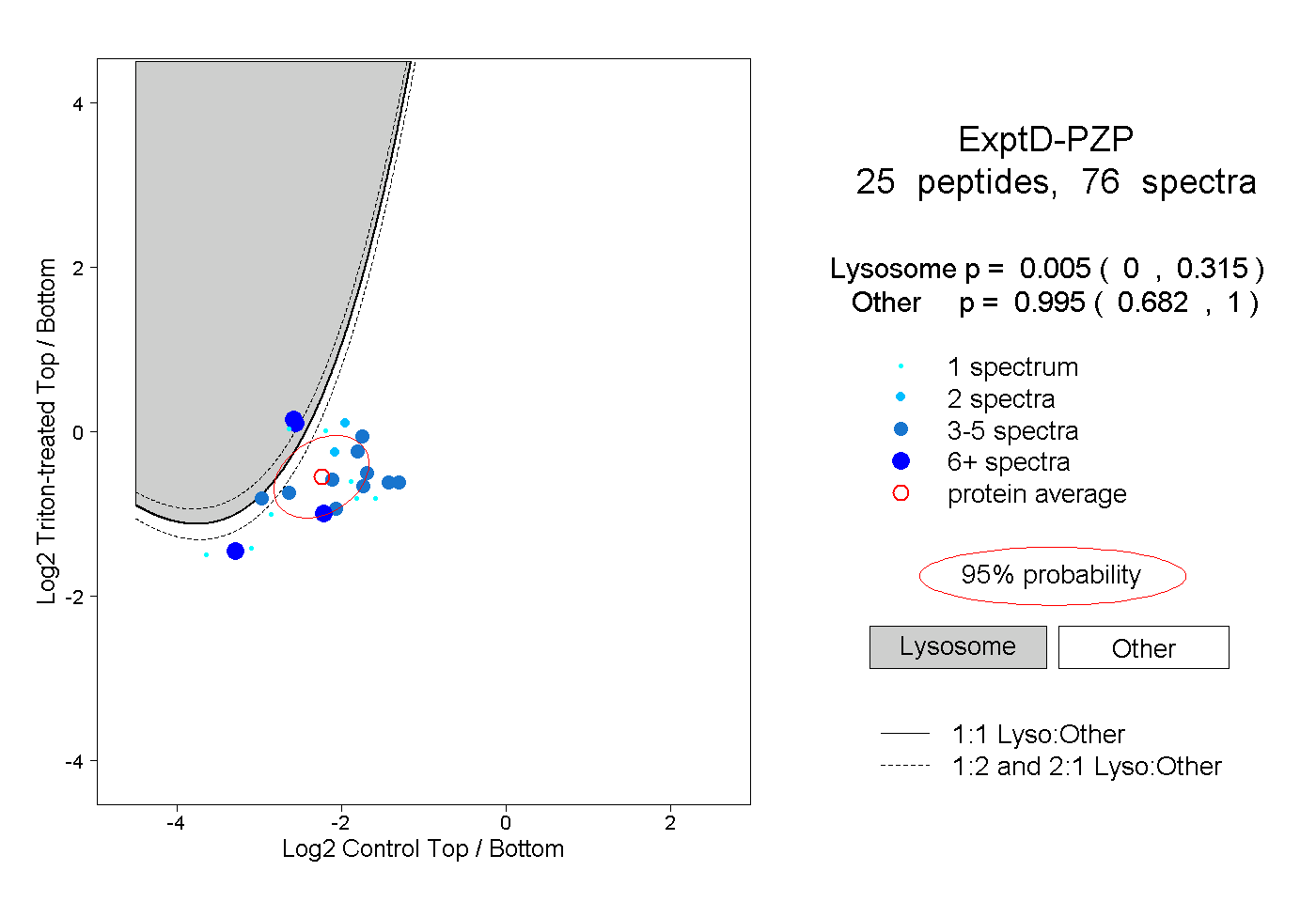
| 3 spectra, GGENCIK |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 2 spectra, DAVNEEESVHWQRPK |
|
0.003 |
|
|
|
|
|
|
|
0.997 |
| 8 spectra, GEAFILK |
|
0.881 |
|
|
|
|
|
|
|
0.119 |
| 1 spectrum, IEHSFEVK |
|
0.051 |
|
|
|
|
|
|
|
0.949 |
| 6 spectra, EYVLPK |
|
0.920 |
|
|
|
|
|
|
|
0.080 |
| 3 spectra, AEQGAYLGPLPYK |
|
0.431 |
|
|
|
|
|
|
|
0.569 |
| 4 spectra, LLLQEVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TEVNTNHVLIYIEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, FEVQVK |
|
0.880 |
|
|
|
|
|
|
|
0.120 |
| 8 spectra, YGAATFTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SICEEFSK |
|
0.029 |
|
|
|
|
|
|
|
0.971 |
| 3 spectra, GPTHHFIK |
|
0.092 |
|
|
|
|
|
|
|
0.908 |
| 3 spectra, LQDQSNIQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, IFTNTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GVVSFPIR |
|
0.003 |
|
|
|
|
|
|
|
0.997 |
| 3 spectra, SEVLESLNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, ATVLNYMPHCIR |
|
0.046 |
|
|
|
|
|
|
|
0.954 |
| 1 spectrum, HSQGNTWLTAFVLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, IFSPSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VAEVPALVQK |
|
0.061 |
|
|
|
|
|
|
|
0.939 |
| 4 spectra, SFSYKPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, QNNICFDNWWVDEYHTQADHSAAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TVSWAVTPK |
|
0.909 |
|
|
|
|
|
|
|
0.091 |
| 1 spectrum, LADLPGNYITK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, AEDITHNGIVYTPK |
|
0.099 |
|
|
|
|
|
|
|
0.901 |