peptides
spectra

0.000 | 0.000
0.434 | 0.436
0.000 | 0.000
0.000 | 0.000
0.105 | 0.107
0.000 | 0.000
0.458 | 0.459
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
364 spectra |
 |
0.000 0.000 | 0.000 |
0.435 0.434 | 0.436 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.106 0.105 | 0.107 |
0.000 0.000 | 0.000 |
0.459 0.458 | 0.459 |
0.000 0.000 | 0.000 |
| 6 spectra, GGENCIK | 0.000 | 0.336 | 0.000 | 0.238 | 0.000 | 0.000 | 0.426 | 0.000 | ||
| 3 spectra, THITNAFNWLSMK | 0.000 | 0.626 | 0.000 | 0.000 | 0.000 | 0.000 | 0.374 | 0.000 | ||
| 1 spectrum, DTVVKPVIVEPEGIEK | 0.000 | 0.333 | 0.000 | 0.000 | 0.000 | 0.217 | 0.450 | 0.000 | ||
| 2 spectra, DAVNEEESVHWQRPK | 0.000 | 0.237 | 0.040 | 0.000 | 0.000 | 0.249 | 0.474 | 0.000 | ||
| 3 spectra, EYVLPK | 0.000 | 0.706 | 0.000 | 0.000 | 0.000 | 0.000 | 0.294 | 0.000 | ||
| 2 spectra, AEQGAYLGPLPYK | 0.000 | 0.377 | 0.000 | 0.028 | 0.192 | 0.000 | 0.403 | 0.000 | ||
| 2 spectra, TSSMMMMGASEVAQEVEVR | 0.000 | 0.481 | 0.000 | 0.000 | 0.085 | 0.000 | 0.433 | 0.000 | ||
| 2 spectra, TEVNTNHVLIYIEK | 0.000 | 0.268 | 0.000 | 0.039 | 0.123 | 0.037 | 0.534 | 0.000 | ||
| 3 spectra, FEVQVK | 0.000 | 0.699 | 0.000 | 0.000 | 0.001 | 0.000 | 0.300 | 0.000 | ||
| 3 spectra, AFAQAQSYIYIEK | 0.000 | 0.364 | 0.000 | 0.000 | 0.075 | 0.000 | 0.561 | 0.000 | ||
| 2 spectra, VSGSGCVYLQTSLK | 0.000 | 0.196 | 0.000 | 0.175 | 0.000 | 0.000 | 0.628 | 0.000 | ||
| 19 spectra, SICEEFSK | 0.000 | 0.423 | 0.000 | 0.000 | 0.103 | 0.000 | 0.474 | 0.000 | ||
| 1 spectrum, LSPQSIYNLLPQK | 0.000 | 0.401 | 0.133 | 0.000 | 0.000 | 0.200 | 0.267 | 0.000 | ||
| 1 spectrum, MVSGFIPVKPSVK | 0.000 | 0.379 | 0.000 | 0.000 | 0.128 | 0.000 | 0.493 | 0.000 | ||
| 7 spectra, IEVEAK | 0.000 | 0.550 | 0.000 | 0.000 | 0.023 | 0.000 | 0.427 | 0.000 | ||
| 16 spectra, GPTHHFIK | 0.000 | 0.490 | 0.000 | 0.000 | 0.094 | 0.000 | 0.416 | 0.000 | ||
| 6 spectra, VNTLPLNFDK | 0.000 | 0.359 | 0.000 | 0.028 | 0.128 | 0.045 | 0.441 | 0.000 | ||
| 28 spectra, GVVSFPIR | 0.000 | 0.498 | 0.000 | 0.000 | 0.046 | 0.000 | 0.456 | 0.000 | ||
| 2 spectra, HSQGNTWLTAFVLK | 0.000 | 0.153 | 0.129 | 0.000 | 0.136 | 0.264 | 0.318 | 0.000 | ||
| 36 spectra, SFSYKPR | 0.000 | 0.326 | 0.000 | 0.041 | 0.154 | 0.000 | 0.479 | 0.000 | ||
| 1 spectrum, QNNICFDNWWVDEYHTQADHSAAR | 0.000 | 0.182 | 0.000 | 0.135 | 0.053 | 0.083 | 0.547 | 0.000 | ||
| 6 spectra, VEPGMAPVAK | 0.000 | 0.448 | 0.000 | 0.000 | 0.091 | 0.000 | 0.460 | 0.000 | ||
| 1 spectrum, NLKPAPVK | 0.000 | 0.352 | 0.000 | 0.000 | 0.094 | 0.085 | 0.469 | 0.000 | ||
| 4 spectra, VPDTITEWK | 0.000 | 0.581 | 0.000 | 0.000 | 0.000 | 0.000 | 0.419 | 0.000 | ||
| 1 spectrum, EDGTGIELTGTGSCEIANTLSK | 0.000 | 0.227 | 0.000 | 0.167 | 0.000 | 0.000 | 0.606 | 0.000 | ||
| 4 spectra, IHFLLNEDALK | 0.000 | 0.534 | 0.000 | 0.000 | 0.121 | 0.000 | 0.344 | 0.000 | ||
| 2 spectra, ENGCFQQSGSLLNNAMK | 0.000 | 0.345 | 0.000 | 0.000 | 0.167 | 0.000 | 0.489 | 0.000 | ||
| 5 spectra, GEAFILK | 0.000 | 0.692 | 0.000 | 0.000 | 0.000 | 0.000 | 0.308 | 0.000 | ||
| 2 spectra, QDLNDNDAYSVFQSIGLK | 0.000 | 0.340 | 0.000 | 0.000 | 0.188 | 0.000 | 0.472 | 0.000 | ||
| 11 spectra, LLLQEVR | 0.000 | 0.405 | 0.000 | 0.000 | 0.108 | 0.000 | 0.486 | 0.000 | ||
| 13 spectra, QLNYQHSDGSYSTFGDR | 0.000 | 0.456 | 0.000 | 0.000 | 0.095 | 0.000 | 0.449 | 0.000 | ||
| 5 spectra, YGAATFTK | 0.000 | 0.302 | 0.000 | 0.000 | 0.159 | 0.000 | 0.539 | 0.000 | ||
| 6 spectra, GQPIPNK | 0.000 | 0.473 | 0.000 | 0.000 | 0.043 | 0.000 | 0.484 | 0.000 | ||
| 15 spectra, AISYLISGYQR | 0.000 | 0.492 | 0.000 | 0.000 | 0.071 | 0.000 | 0.436 | 0.000 | ||
| 15 spectra, LQDQSNIQR | 0.000 | 0.448 | 0.000 | 0.000 | 0.092 | 0.000 | 0.460 | 0.000 | ||
| 21 spectra, IFTNTR | 0.000 | 0.460 | 0.000 | 0.000 | 0.144 | 0.011 | 0.386 | 0.000 | ||
| 10 spectra, SMWITK | 0.000 | 0.457 | 0.000 | 0.000 | 0.065 | 0.000 | 0.478 | 0.000 | ||
| 16 spectra, DLTFYYLIK | 0.000 | 0.495 | 0.000 | 0.000 | 0.037 | 0.000 | 0.469 | 0.000 | ||
| 3 spectra, SEVLESLNK | 0.000 | 0.432 | 0.000 | 0.000 | 0.067 | 0.000 | 0.501 | 0.000 | ||
| 19 spectra, ATVLNYMPHCIR | 0.000 | 0.239 | 0.217 | 0.000 | 0.134 | 0.000 | 0.409 | 0.000 | ||
| 30 spectra, IFSPSR | 0.000 | 0.567 | 0.000 | 0.000 | 0.069 | 0.000 | 0.364 | 0.000 | ||
| 2 spectra, VAEVPALVQK | 0.000 | 0.302 | 0.000 | 0.000 | 0.254 | 0.000 | 0.444 | 0.000 | ||
| 11 spectra, NVEENVR | 0.000 | 0.303 | 0.000 | 0.024 | 0.159 | 0.000 | 0.514 | 0.000 | ||
| 5 spectra, DLSSSDLTTASK | 0.000 | 0.326 | 0.000 | 0.000 | 0.121 | 0.000 | 0.554 | 0.000 | ||
| 7 spectra, LADLPGNYITK | 0.000 | 0.341 | 0.000 | 0.000 | 0.108 | 0.000 | 0.552 | 0.000 | ||
| 4 spectra, AEDITHNGIVYTPK | 0.000 | 0.219 | 0.000 | 0.000 | 0.109 | 0.074 | 0.598 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
128 spectra |
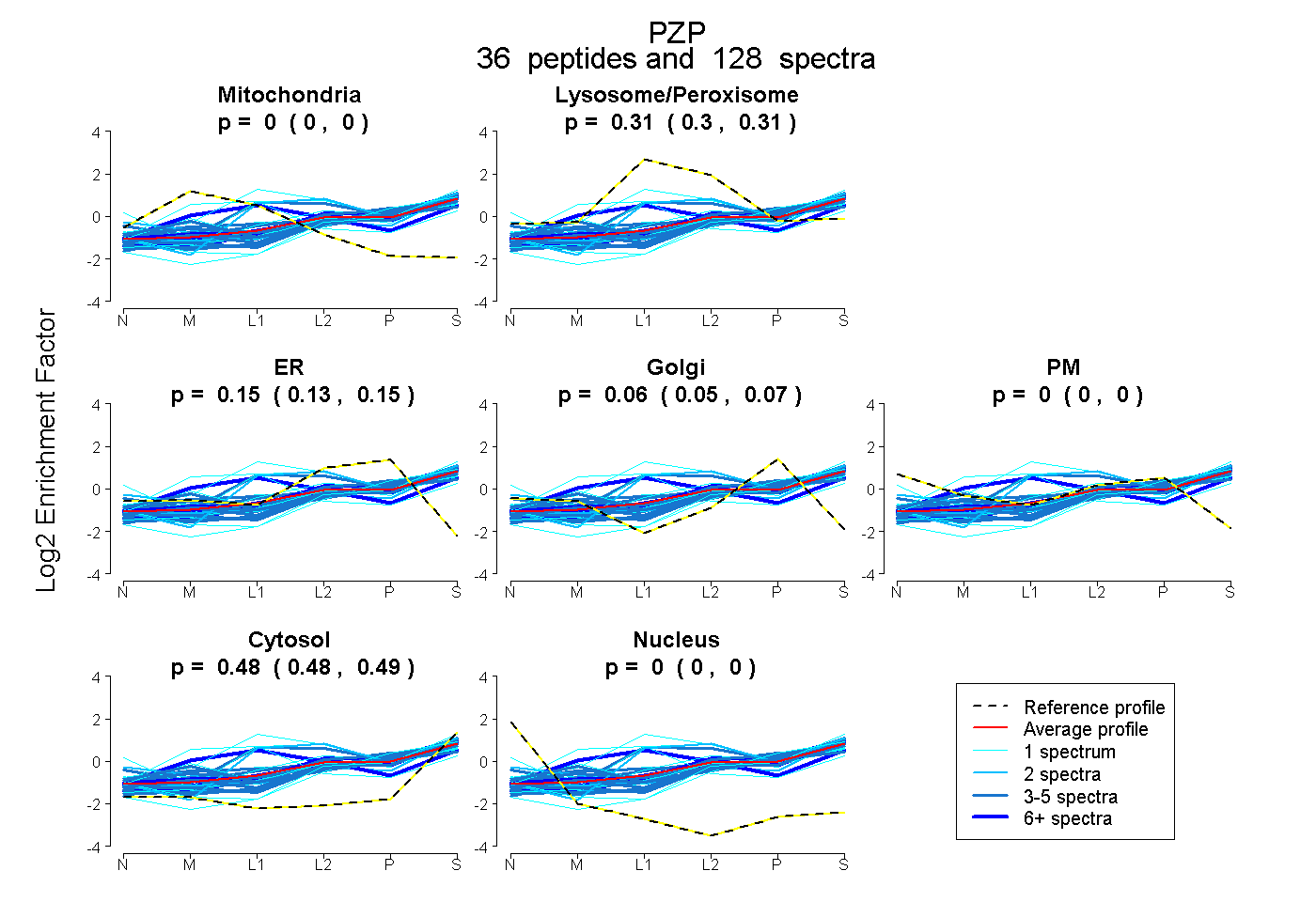 |
0.000 0.000 | 0.000 |
0.308 0.302 | 0.313 |
0.145 0.133 | 0.155 |
0.064 0.054 | 0.073 |
0.000 0.000 | 0.000 |
0.482 0.479 | 0.485 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1048 spectra |
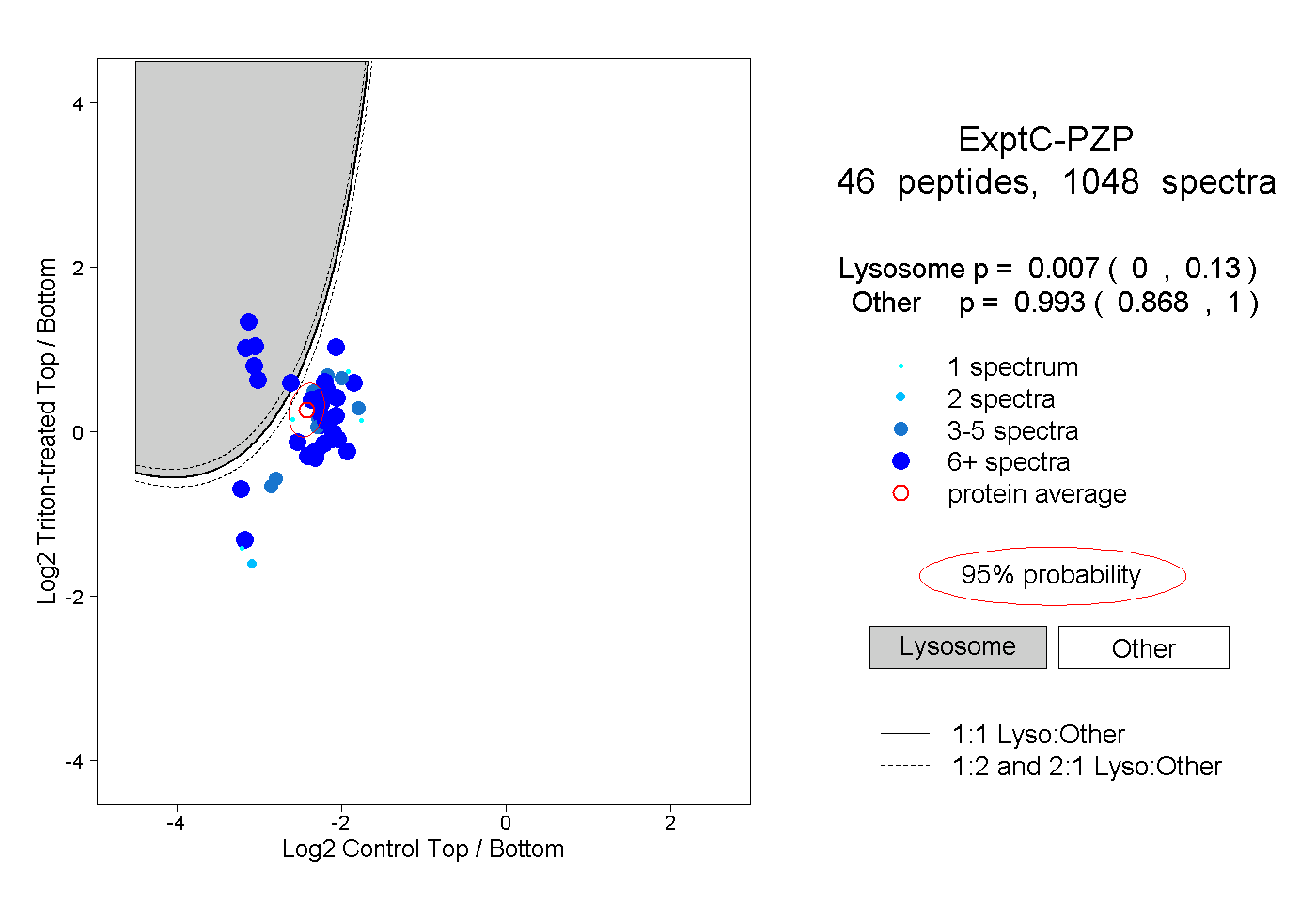 |
0.007 0.000 | 0.130 |
0.993 0.868 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
76 spectra |
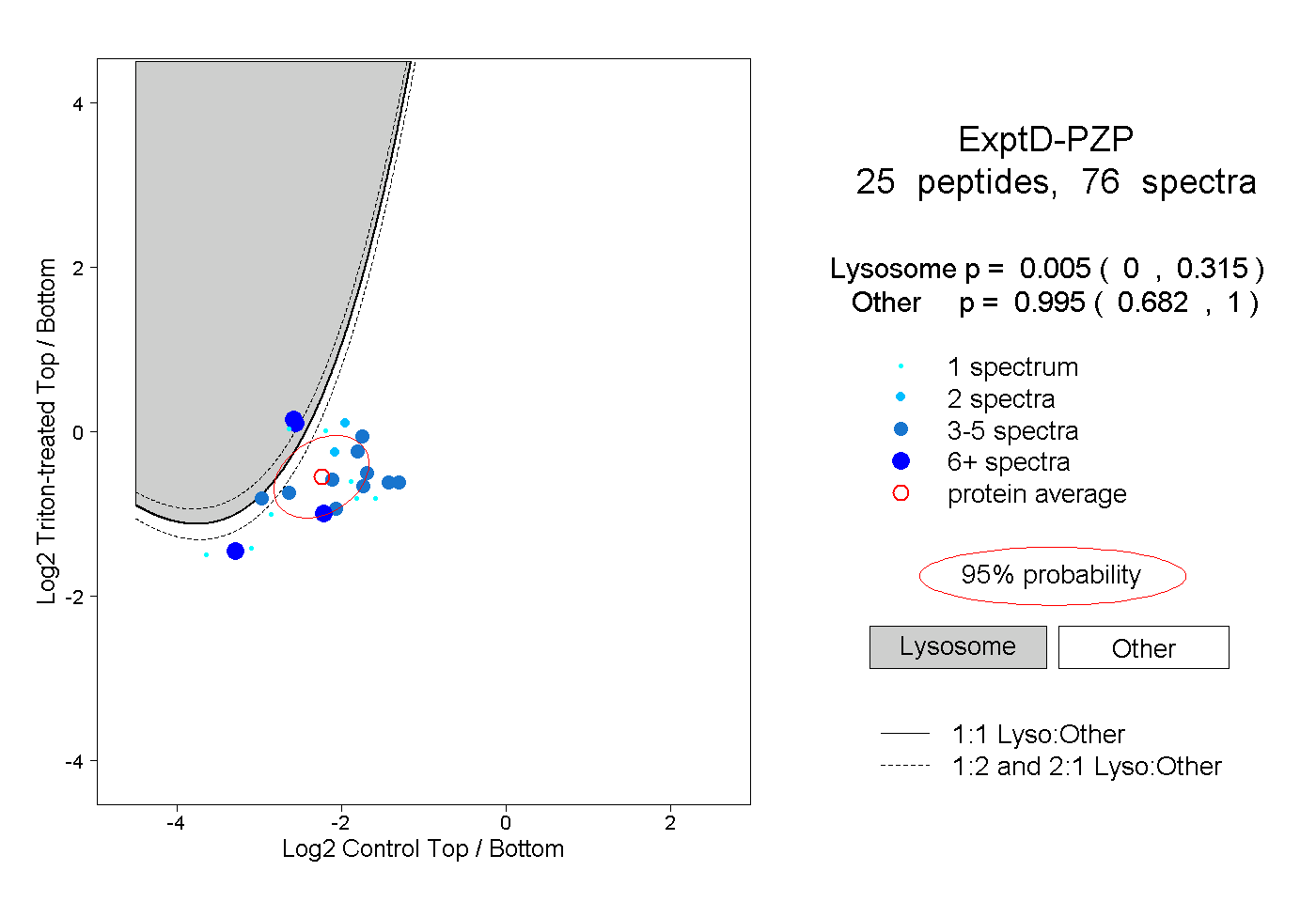 |
0.005 0.000 | 0.315 |
0.995 0.682 | 1.000 |