peptides
spectra
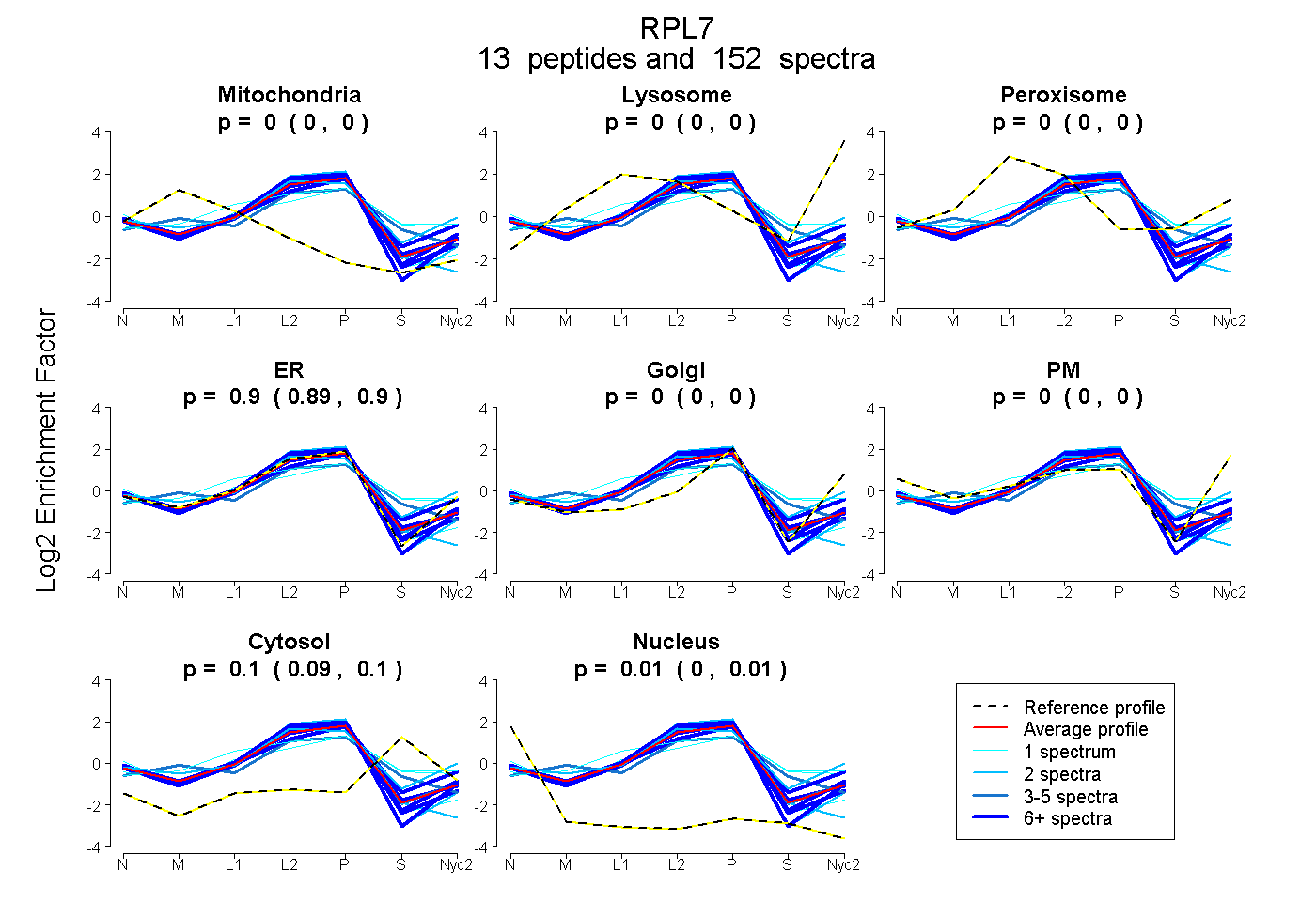
0.000 | 0.003
0.000 | 0.000
0.000 | 0.000
0.894 | 0.901
0.000 | 0.000
0.000 | 0.000
0.090 | 0.102
0.002 | 0.008
peptides
spectra
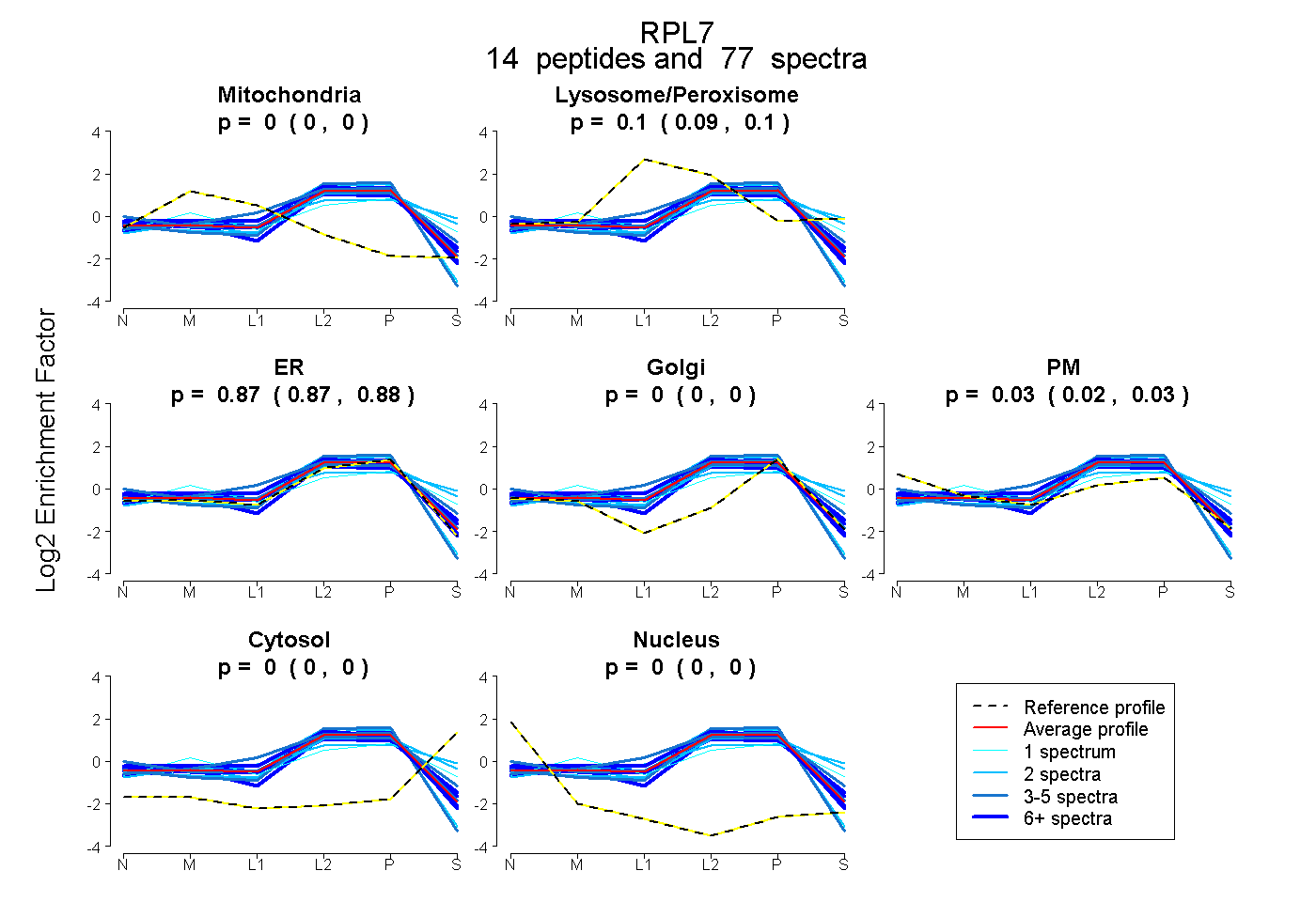
0.000 | 0.000
0.092 | 0.102
0.866 | 0.882
0.000 | 0.000
0.020 | 0.034
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
152 spectra |
 |
0.000 0.000 | 0.003 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.898 0.894 | 0.901 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.096 0.090 | 0.102 |
0.005 0.002 | 0.008 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
77 spectra |
 |
0.000 0.000 | 0.000 |
0.098 0.092 | 0.102 |
0.874 0.866 | 0.882 |
0.000 0.000 | 0.000 |
0.028 0.020 | 0.034 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, AGNFYVPAEPK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, QIFNGTFVK | 0.000 | 0.188 | 0.630 | 0.000 | 0.000 | 0.182 | 0.000 | |||
| 8 spectra, IVEPYIAWGYPNLK | 0.000 | 0.135 | 0.680 | 0.000 | 0.135 | 0.051 | 0.000 | |||
| 18 spectra, GINGVSPK | 0.004 | 0.058 | 0.853 | 0.000 | 0.085 | 0.000 | 0.000 | |||
| 8 spectra, VLAGLIR | 0.000 | 0.145 | 0.823 | 0.000 | 0.032 | 0.000 | 0.000 | |||
| 3 spectra, VPAVPETLK | 0.000 | 0.217 | 0.783 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, EANNFLWPFK | 0.000 | 0.127 | 0.873 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 10 spectra, LAFVIR | 0.000 | 0.053 | 0.947 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, VLELLR | 0.000 | 0.174 | 0.559 | 0.000 | 0.234 | 0.033 | 0.000 | |||
| 3 spectra, SVNELIYK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 14 spectra, ASVNMLR | 0.000 | 0.000 | 0.943 | 0.000 | 0.000 | 0.057 | 0.000 | |||
| 2 spectra, FGIICMEDLIHEIYTVGK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, NFAELK | 0.000 | 0.420 | 0.166 | 0.272 | 0.000 | 0.142 | 0.000 | |||
| 1 spectrum, TTHFVEGGDAGNR | 0.000 | 0.317 | 0.183 | 0.427 | 0.000 | 0.073 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
218 spectra |
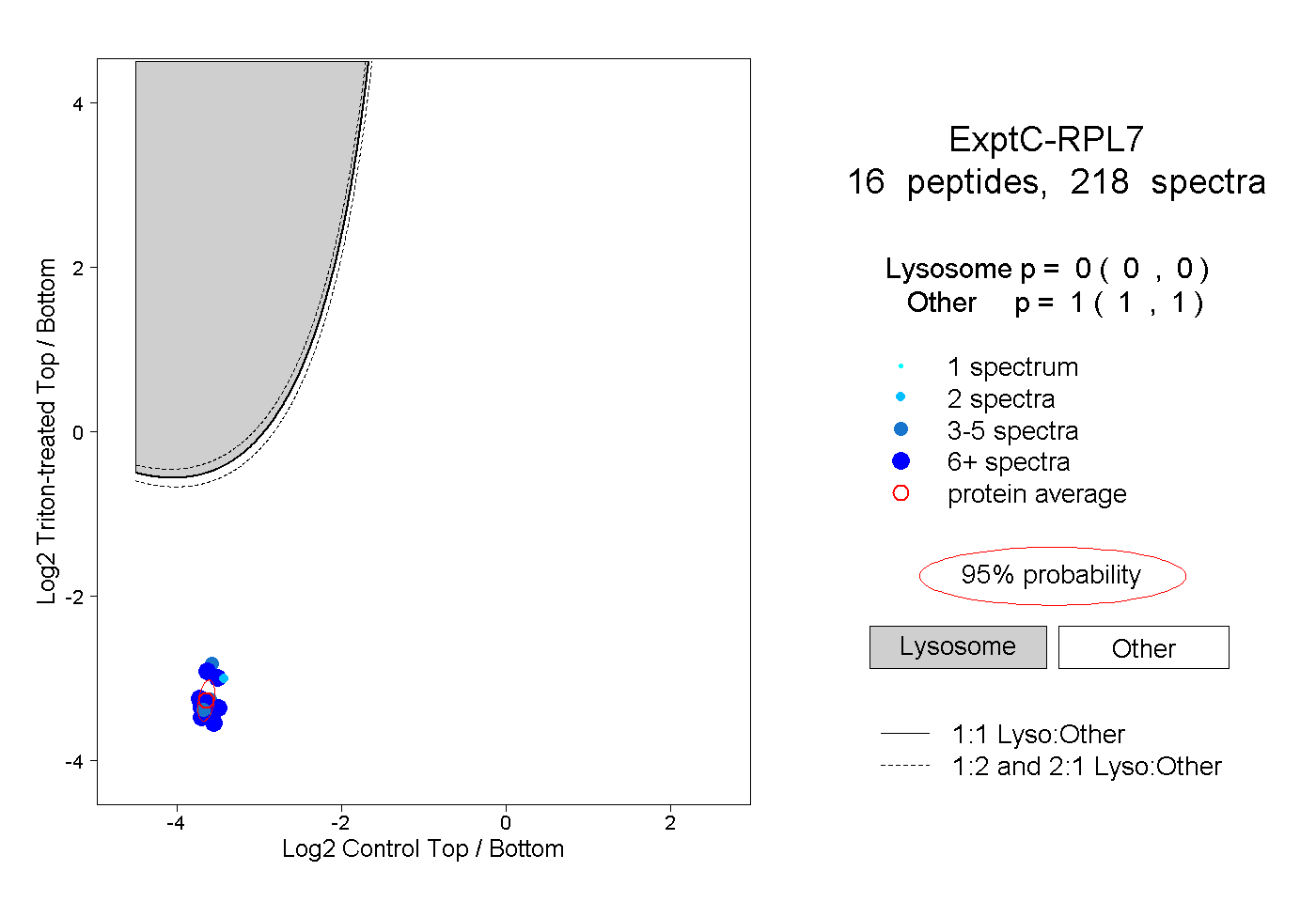 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
22 spectra |
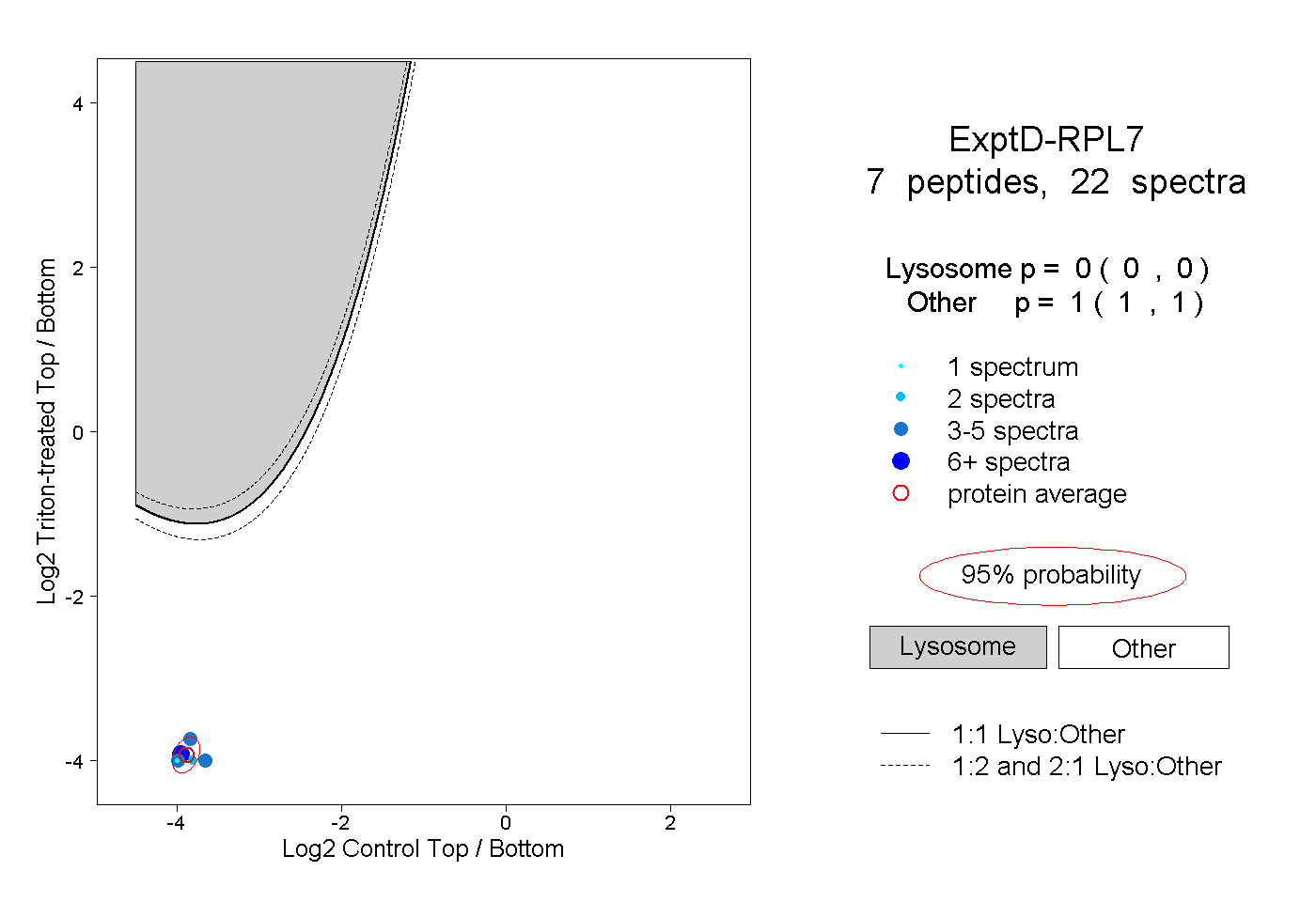 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |