peptides
spectra
0.983 | 0.987
0.012 | 0.017
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
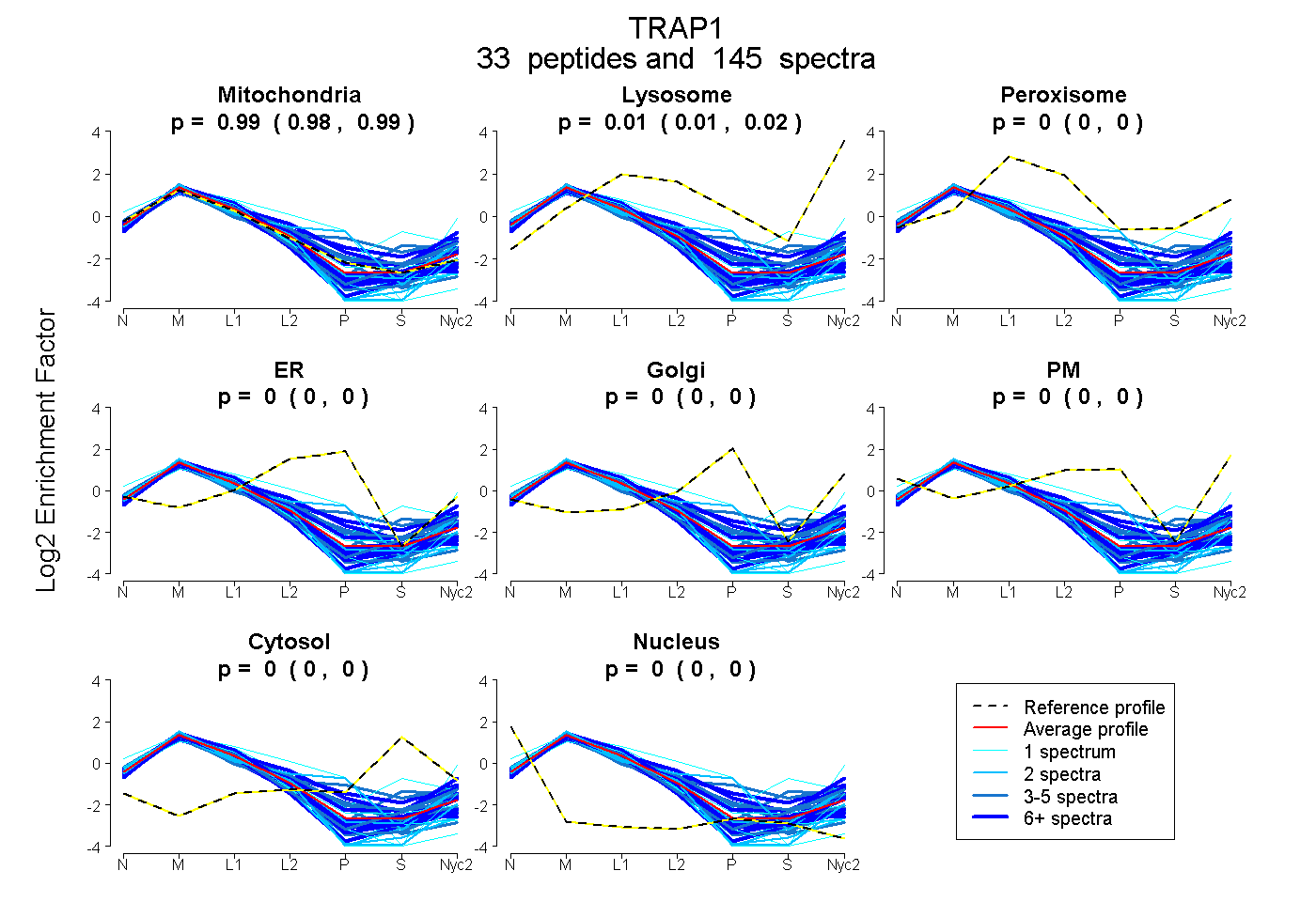
| Expt A |
peptides |
145 spectra |
 |
0.985 0.983 | 0.987 |
0.015 0.012 | 0.017 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, VQDVVTK | 0.941 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.059 | ||
| 5 spectra, EELVSNLGTIAR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 12 spectra, LDTHPAMVTVLEMGAAR | 0.771 | 0.182 | 0.000 | 0.000 | 0.000 | 0.046 | 0.000 | 0.000 | ||
| 8 spectra, ELGSSVALYSR | 0.991 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.009 | ||
| 7 spectra, ETEELMAWMR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, DFANESR | 0.827 | 0.013 | 0.000 | 0.000 | 0.000 | 0.000 | 0.161 | 0.000 | ||
| 6 spectra, FFIDQSK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, HEFQAETK | 0.982 | 0.000 | 0.006 | 0.000 | 0.000 | 0.000 | 0.012 | 0.000 | ||
| 2 spectra, LLDIVAR | 0.977 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.023 | ||
| 4 spectra, MQAGTR | 0.868 | 0.067 | 0.052 | 0.000 | 0.000 | 0.000 | 0.012 | 0.000 | ||
| 4 spectra, ELLQESALIR | 0.985 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.015 | ||
| 6 spectra, NIYYLCAPNR | 0.973 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.027 | ||
| 7 spectra, SIFYVPEMKPSMFDVSR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, HLAEHSPYYEAMK | 0.615 | 0.000 | 0.222 | 0.000 | 0.000 | 0.000 | 0.164 | 0.000 | ||
| 8 spectra, IIIHLK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, YSNFVSFPLYLNGR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, NALGSR | 0.707 | 0.000 | 0.000 | 0.160 | 0.065 | 0.069 | 0.000 | 0.000 | ||
| 1 spectrum, MQQLAK | 0.967 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.033 | ||
| 4 spectra, FEDTSPAGER | 0.994 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.006 | ||
| 2 spectra, TDAPLNIR | 0.945 | 0.055 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, INTLQAIWMMDPK | 0.868 | 0.123 | 0.000 | 0.000 | 0.000 | 0.000 | 0.009 | 0.000 | ||
| 4 spectra, EGIVTTAEQDIK | 0.702 | 0.097 | 0.003 | 0.000 | 0.112 | 0.000 | 0.087 | 0.000 | ||
| 2 spectra, AFLEALQHQAETSSR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, EEALHSIISNTEAVQGSVSK | 0.572 | 0.098 | 0.000 | 0.020 | 0.000 | 0.310 | 0.000 | 0.000 | ||
| 6 spectra, DVLQQR | 0.919 | 0.060 | 0.000 | 0.000 | 0.000 | 0.021 | 0.000 | 0.000 | ||
| 3 spectra, GTITIQDTGIGMTK | 0.943 | 0.000 | 0.039 | 0.018 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, AQLLQPTLEINPR | 0.997 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.003 | ||
| 14 spectra, DISEFQHEEFYR | 0.732 | 0.095 | 0.063 | 0.000 | 0.000 | 0.055 | 0.054 | 0.000 | ||
| 8 spectra, FFEDYGLFMR | 0.973 | 0.027 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, VCEGQVLPEMEIHLQTDAEK | 0.995 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.005 | ||
| 3 spectra, FILHYK | 0.905 | 0.032 | 0.000 | 0.000 | 0.023 | 0.000 | 0.040 | 0.000 | ||
| 2 spectra, ELISNASDALEK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, YIAQAYDKPR | 0.955 | 0.030 | 0.000 | 0.000 | 0.000 | 0.000 | 0.015 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
71 spectra |
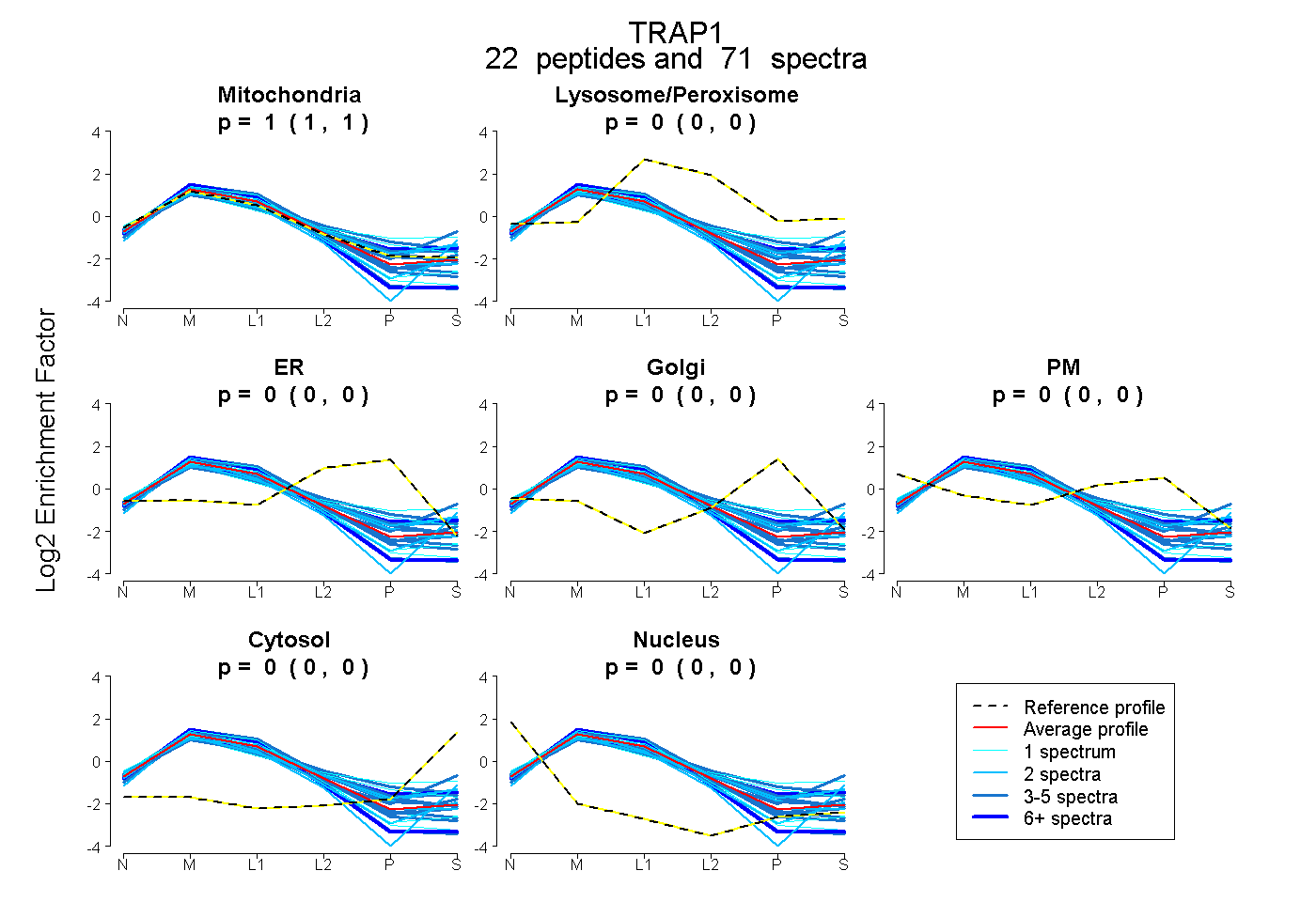 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
612 spectra |
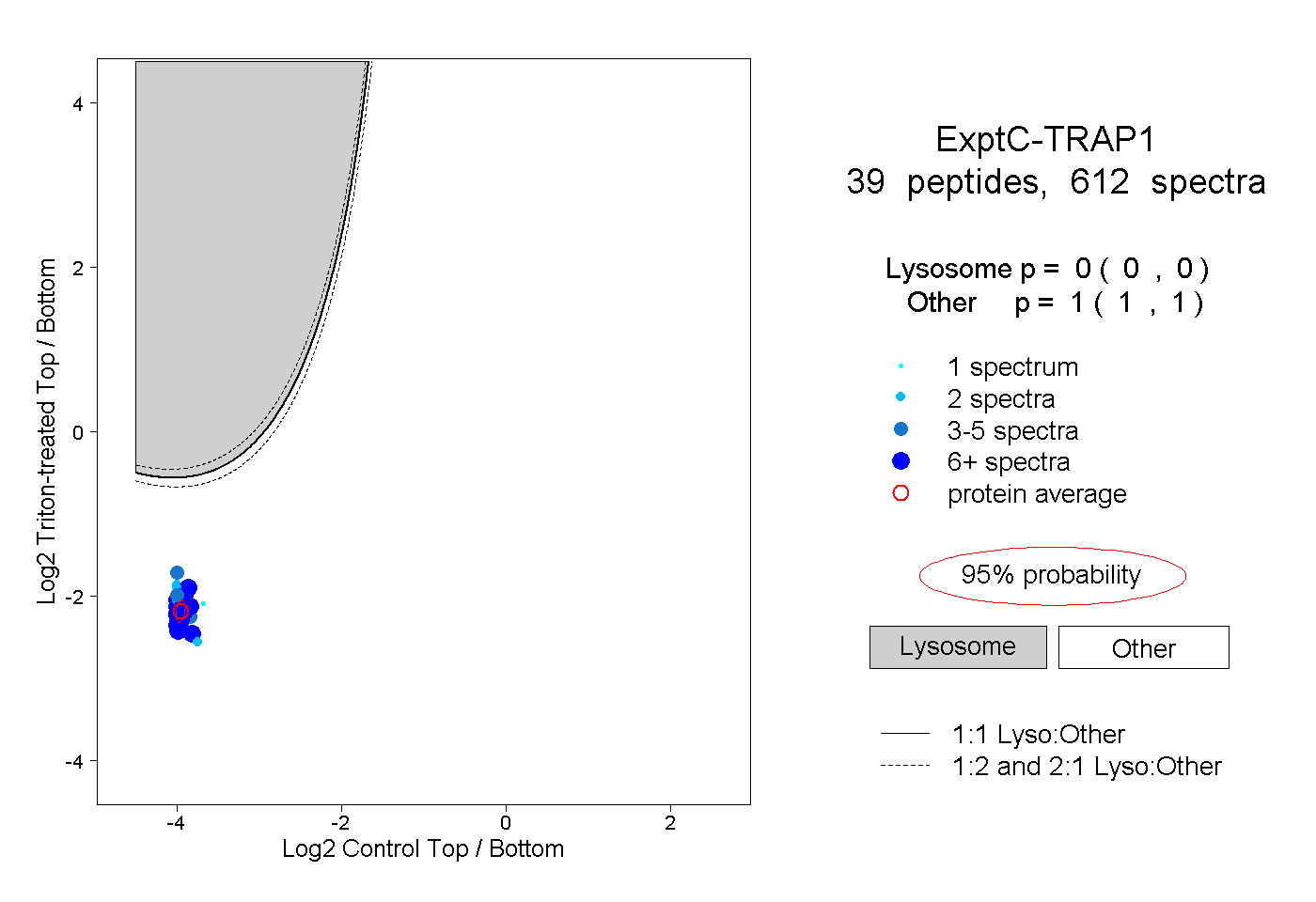 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
34 spectra |
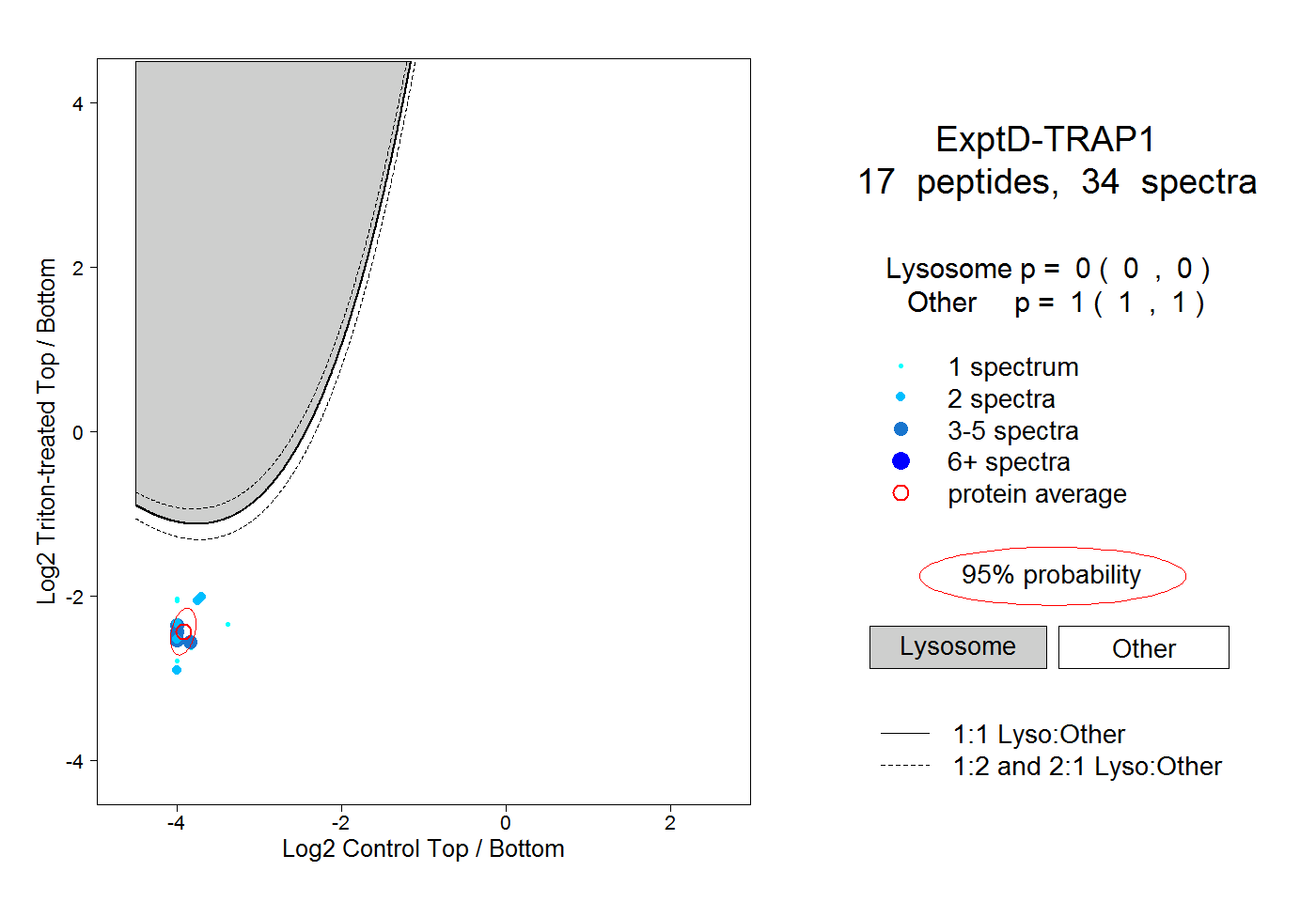 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |