peptides
spectra
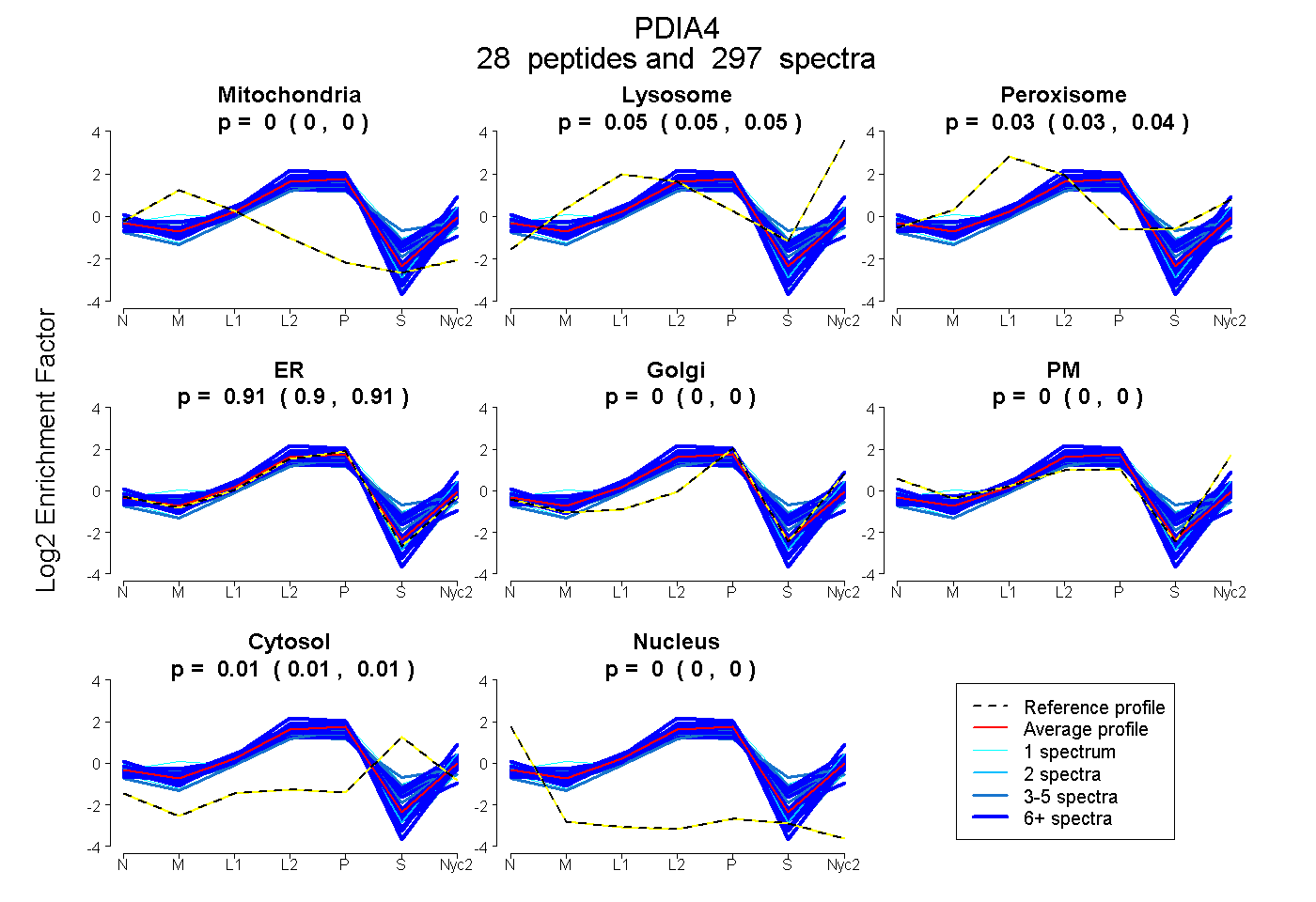
0.000 | 0.000
0.048 | 0.052
0.033 | 0.036
0.904 | 0.909
0.000 | 0.000
0.000 | 0.000
0.007 | 0.010
0.000 | 0.000
peptides
spectra
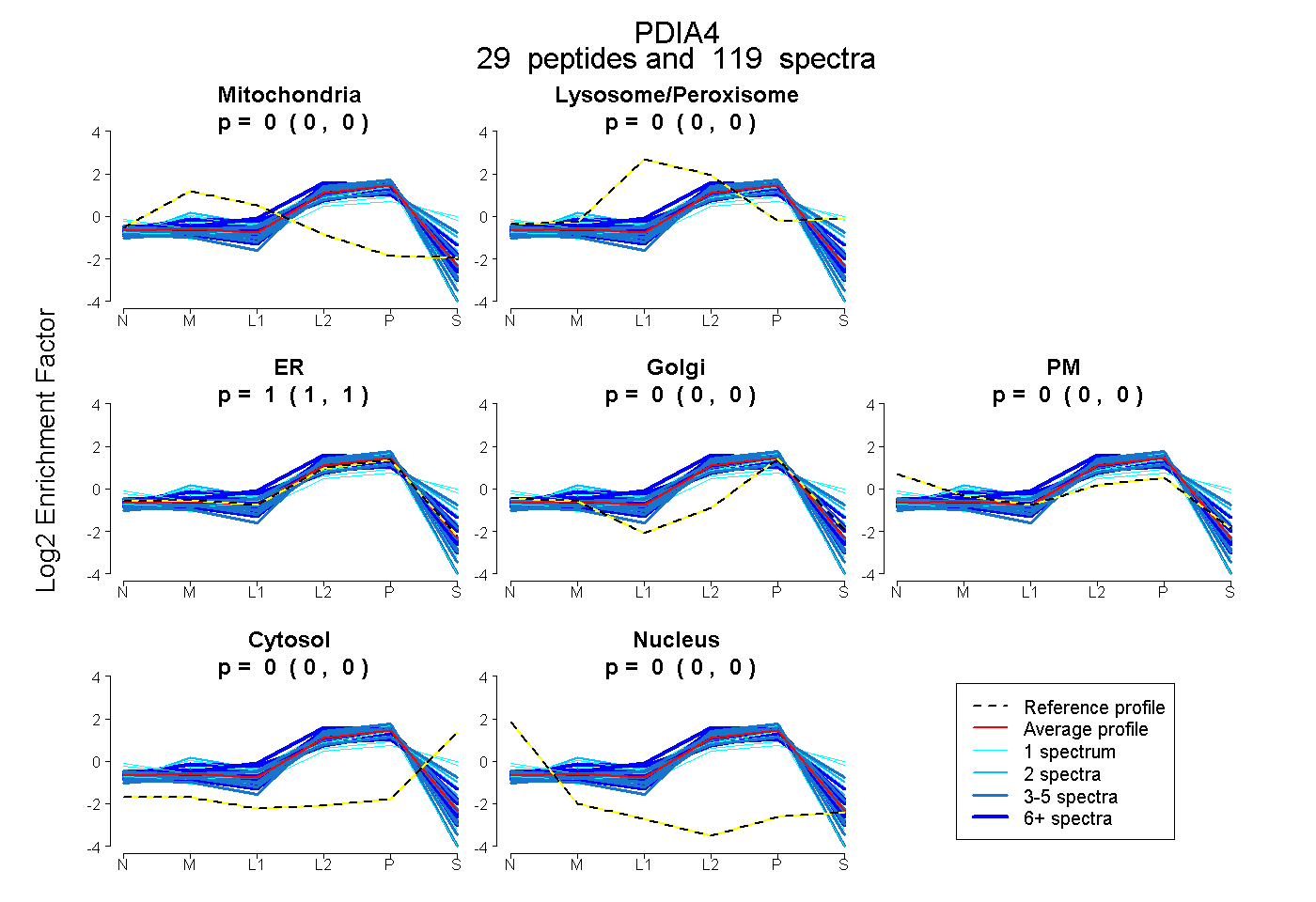
0.000 | 0.000
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
297 spectra |
 |
0.000 0.000 | 0.000 |
0.050 0.048 | 0.052 |
0.035 0.033 | 0.036 |
0.906 0.904 | 0.909 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.009 0.007 | 0.010 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
119 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, SPPIPLAK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, GQAVDYDGSR | 0.000 | 0.000 | 0.929 | 0.071 | 0.000 | 0.000 | 0.000 | |||
| 12 spectra, TQEEIVAK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LKPVIK | 0.000 | 0.152 | 0.632 | 0.107 | 0.000 | 0.109 | 0.000 | |||
| 1 spectrum, EVSQPDWTPPPEVTLTLTK | 0.012 | 0.252 | 0.527 | 0.209 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, FAMEPEEFDSDALR | 0.000 | 0.233 | 0.216 | 0.235 | 0.094 | 0.222 | 0.000 | |||
| 1 spectrum, EILTLK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, LAPEYEK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, QLEPVYTSLGK | 0.000 | 0.000 | 0.926 | 0.074 | 0.000 | 0.000 | 0.000 | |||
| 12 spectra, HALPLVGHR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, DNDPPIAVAK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, VLEVAK | 0.000 | 0.034 | 0.966 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 12 spectra, GRPFDYNGPR | 0.000 | 0.149 | 0.656 | 0.195 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, IDATSASMLASK | 0.000 | 0.000 | 0.937 | 0.063 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, FIDEHATK | 0.000 | 0.037 | 0.963 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, TFDAIVMDPK | 0.000 | 0.000 | 0.977 | 0.000 | 0.000 | 0.023 | 0.000 | |||
| 1 spectrum, SQPVPK | 0.050 | 0.000 | 0.950 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, MDATANDITNDR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, YGIVDYMVEQSGPPSK | 0.000 | 0.242 | 0.462 | 0.202 | 0.000 | 0.094 | 0.000 | |||
| 3 spectra, VEGFPTIYFAPSGDK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, QFAPEYEK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, VDATEQTDLAK | 0.000 | 0.193 | 0.454 | 0.206 | 0.133 | 0.015 | 0.000 | |||
| 6 spectra, TATQFWR | 0.000 | 0.097 | 0.903 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, FDVSGYPTIK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, LVLMQPEK | 0.000 | 0.281 | 0.464 | 0.254 | 0.000 | 0.001 | 0.000 | |||
| 2 spectra, EFVMAFK | 0.078 | 0.134 | 0.719 | 0.069 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, QVQEFLK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, FEGGNR | 0.000 | 0.361 | 0.193 | 0.307 | 0.000 | 0.139 | 0.000 | |||
| 7 spectra, DLEHLSK | 0.000 | 0.046 | 0.954 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
740 spectra |
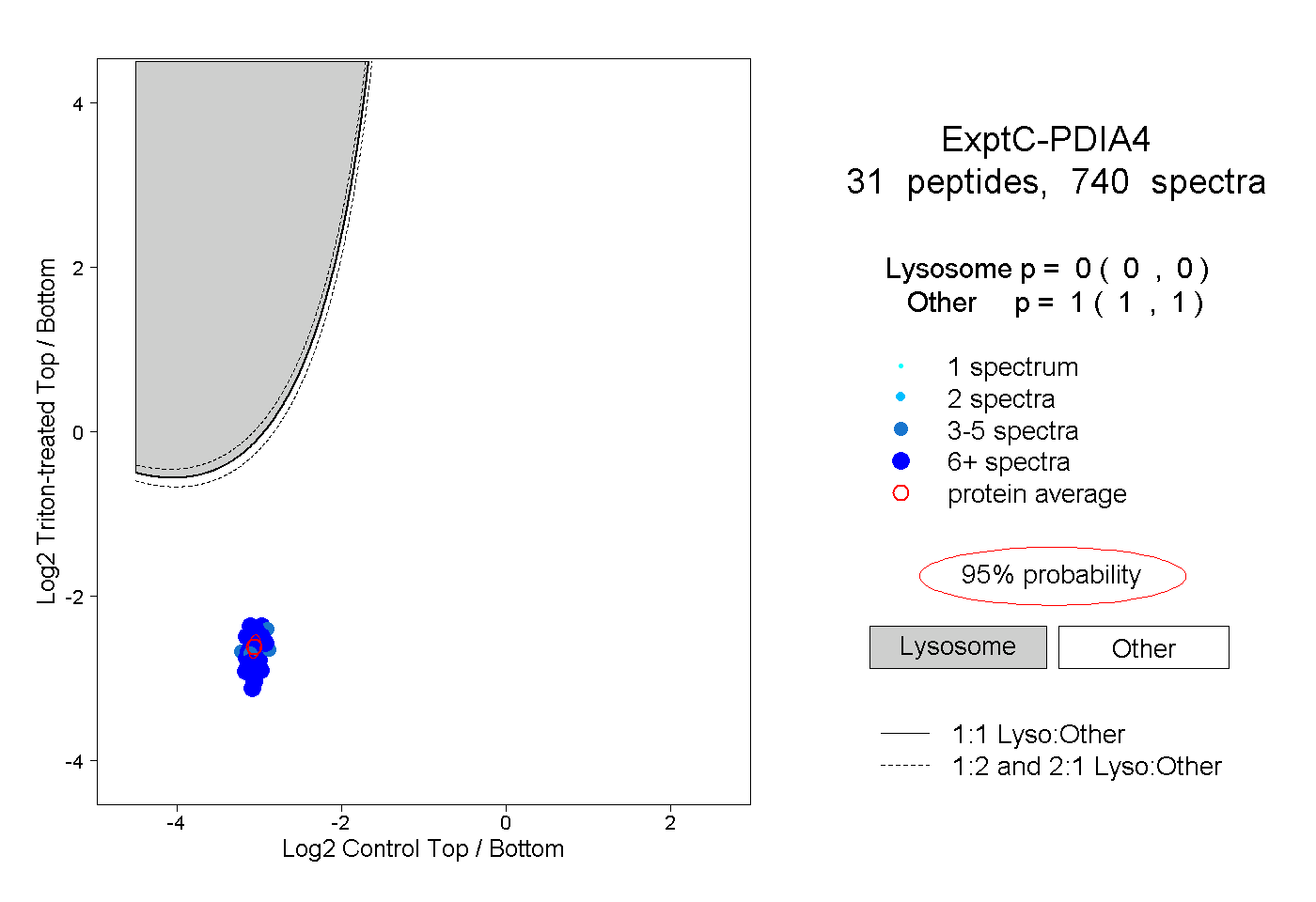 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
95 spectra |
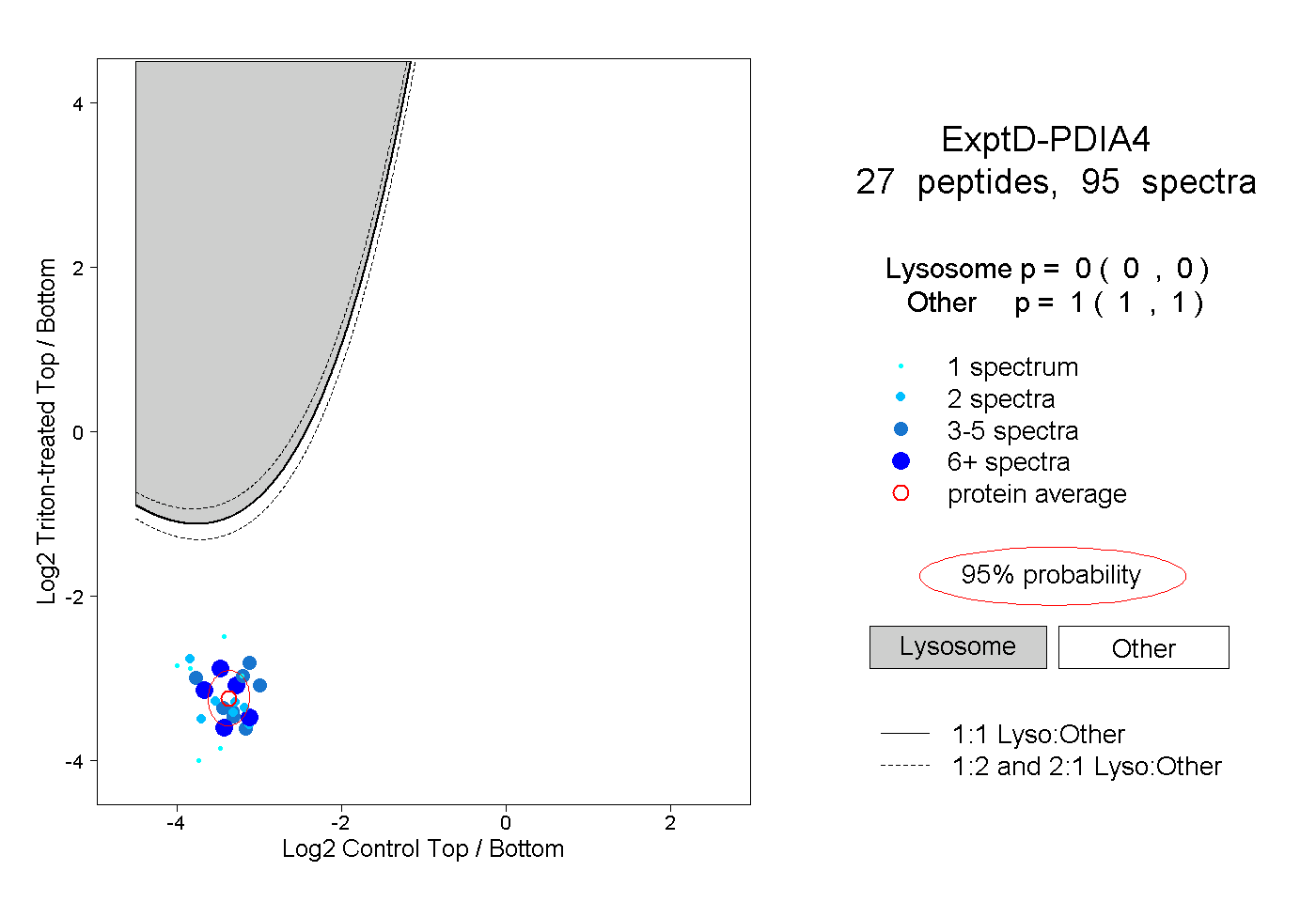 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |