peptides
spectra
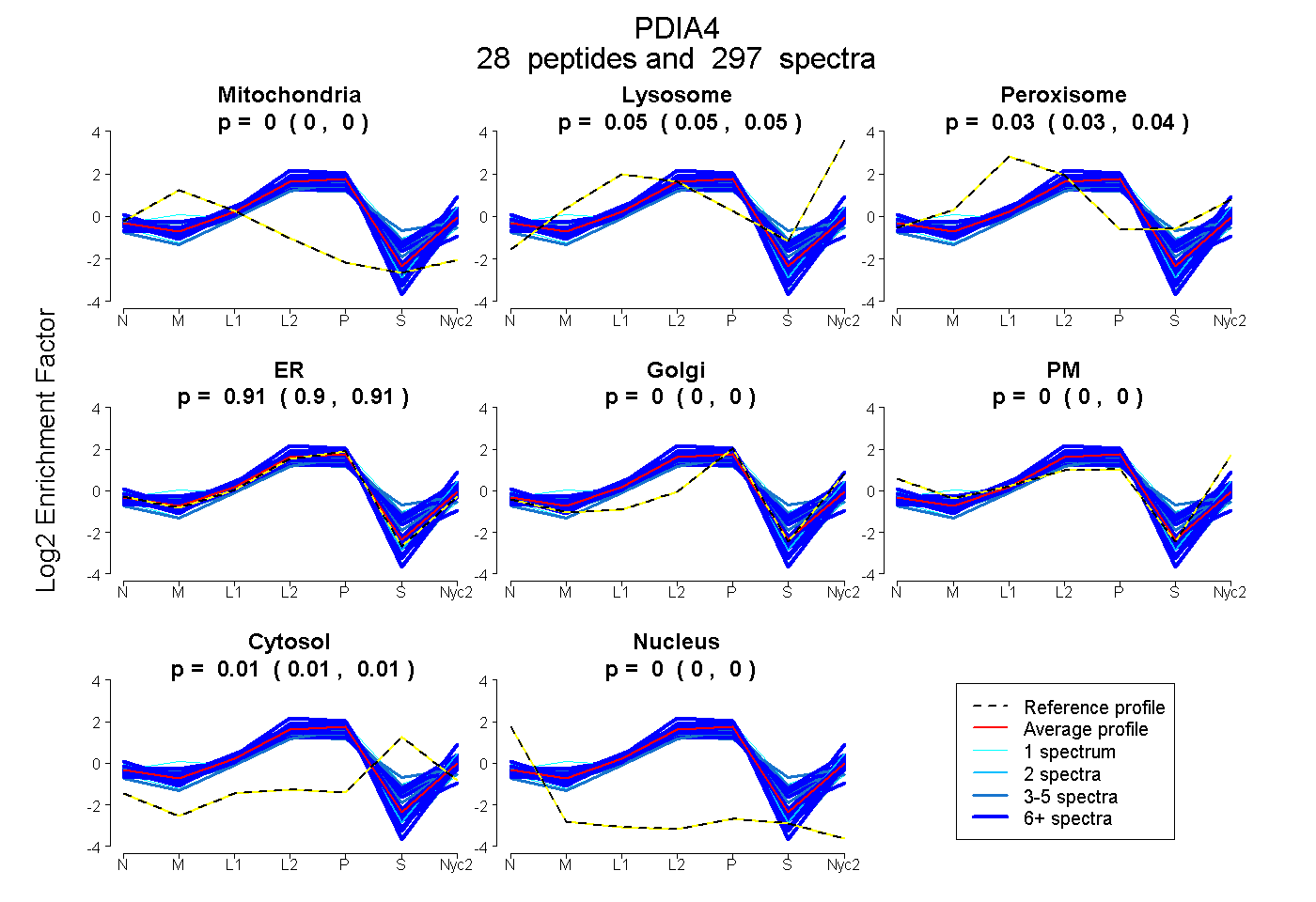
0.000 | 0.000
0.048 | 0.052
0.033 | 0.036
0.904 | 0.909
0.000 | 0.000
0.000 | 0.000
0.007 | 0.010
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
297 spectra |
 |
0.000 0.000 | 0.000 |
0.050 0.048 | 0.052 |
0.035 0.033 | 0.036 |
0.906 0.904 | 0.909 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.009 0.007 | 0.010 |
0.000 0.000 | 0.000 |
| 3 spectra, SPPIPLAK | 0.000 | 0.000 | 0.043 | 0.721 | 0.089 | 0.051 | 0.096 | 0.000 | ||
| 16 spectra, GQAVDYDGSR | 0.000 | 0.000 | 0.084 | 0.831 | 0.000 | 0.000 | 0.085 | 0.000 | ||
| 22 spectra, TQEEIVAK | 0.000 | 0.090 | 0.000 | 0.910 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, LKPVIK | 0.111 | 0.000 | 0.000 | 0.889 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, DLVLAK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, EVSQPDWTPPPEVTLTLTK | 0.000 | 0.050 | 0.025 | 0.774 | 0.000 | 0.000 | 0.150 | 0.000 | ||
| 16 spectra, LAPEYEK | 0.000 | 0.000 | 0.000 | 0.978 | 0.000 | 0.022 | 0.000 | 0.000 | ||
| 8 spectra, QLEPVYTSLGK | 0.000 | 0.111 | 0.087 | 0.515 | 0.052 | 0.089 | 0.146 | 0.000 | ||
| 17 spectra, HALPLVGHR | 0.045 | 0.011 | 0.105 | 0.747 | 0.077 | 0.015 | 0.000 | 0.000 | ||
| 5 spectra, DNDPPIAVAK | 0.000 | 0.002 | 0.144 | 0.742 | 0.000 | 0.000 | 0.113 | 0.000 | ||
| 10 spectra, VLEVAK | 0.000 | 0.052 | 0.000 | 0.935 | 0.000 | 0.000 | 0.013 | 0.000 | ||
| 4 spectra, MHVMDVQGSTEASAIK | 0.000 | 0.000 | 0.148 | 0.599 | 0.000 | 0.019 | 0.234 | 0.000 | ||
| 22 spectra, GRPFDYNGPR | 0.000 | 0.119 | 0.015 | 0.799 | 0.000 | 0.068 | 0.000 | 0.000 | ||
| 6 spectra, IDATSASMLASK | 0.000 | 0.159 | 0.000 | 0.641 | 0.004 | 0.196 | 0.000 | 0.000 | ||
| 5 spectra, FIDEHATK | 0.000 | 0.039 | 0.000 | 0.806 | 0.000 | 0.155 | 0.000 | 0.000 | ||
| 7 spectra, TFDAIVMDPK | 0.000 | 0.000 | 0.084 | 0.838 | 0.000 | 0.000 | 0.000 | 0.077 | ||
| 30 spectra, SQPVPK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 24 spectra, MDATANDITNDR | 0.000 | 0.115 | 0.068 | 0.714 | 0.000 | 0.000 | 0.104 | 0.000 | ||
| 7 spectra, YGIVDYMVEQSGPPSK | 0.000 | 0.000 | 0.059 | 0.908 | 0.000 | 0.000 | 0.033 | 0.000 | ||
| 8 spectra, QFAPEYEK | 0.000 | 0.073 | 0.000 | 0.863 | 0.000 | 0.064 | 0.000 | 0.000 | ||
| 22 spectra, VDATEQTDLAK | 0.000 | 0.000 | 0.048 | 0.851 | 0.000 | 0.094 | 0.007 | 0.000 | ||
| 18 spectra, TATQFWR | 0.000 | 0.078 | 0.000 | 0.922 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 12 spectra, FDVSGYPTIK | 0.000 | 0.018 | 0.000 | 0.927 | 0.000 | 0.054 | 0.000 | 0.000 | ||
| 2 spectra, QVEEFLK | 0.000 | 0.017 | 0.000 | 0.753 | 0.000 | 0.229 | 0.000 | 0.000 | ||
| 6 spectra, TSNDAK | 0.000 | 0.054 | 0.000 | 0.937 | 0.000 | 0.000 | 0.009 | 0.000 | ||
| 5 spectra, LVLMQPEK | 0.000 | 0.000 | 0.034 | 0.749 | 0.000 | 0.000 | 0.217 | 0.000 | ||
| 8 spectra, QVQEFLK | 0.000 | 0.066 | 0.000 | 0.918 | 0.002 | 0.000 | 0.013 | 0.000 | ||
| 7 spectra, DLEHLSK | 0.000 | 0.000 | 0.001 | 0.999 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
119 spectra |
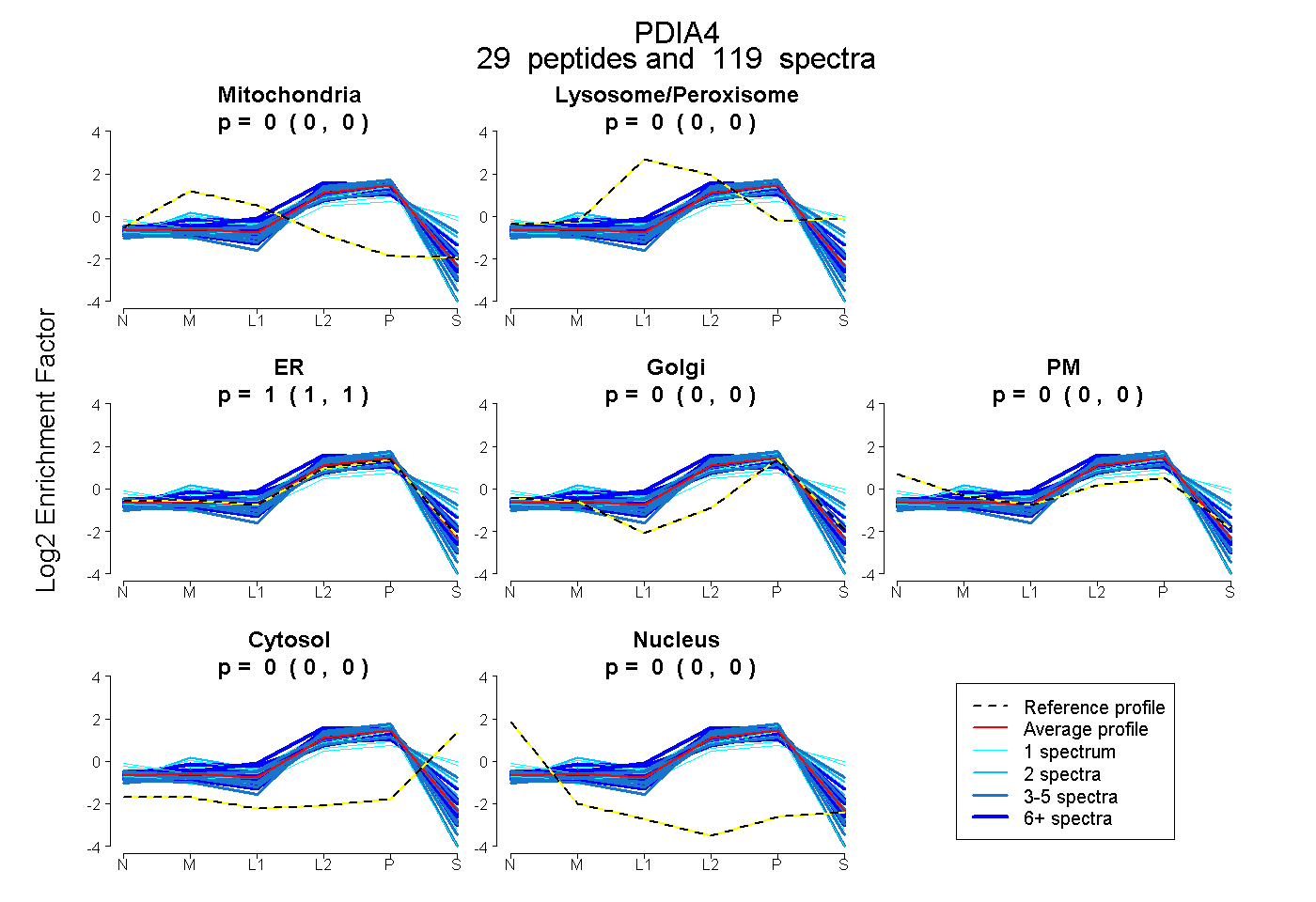 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
740 spectra |
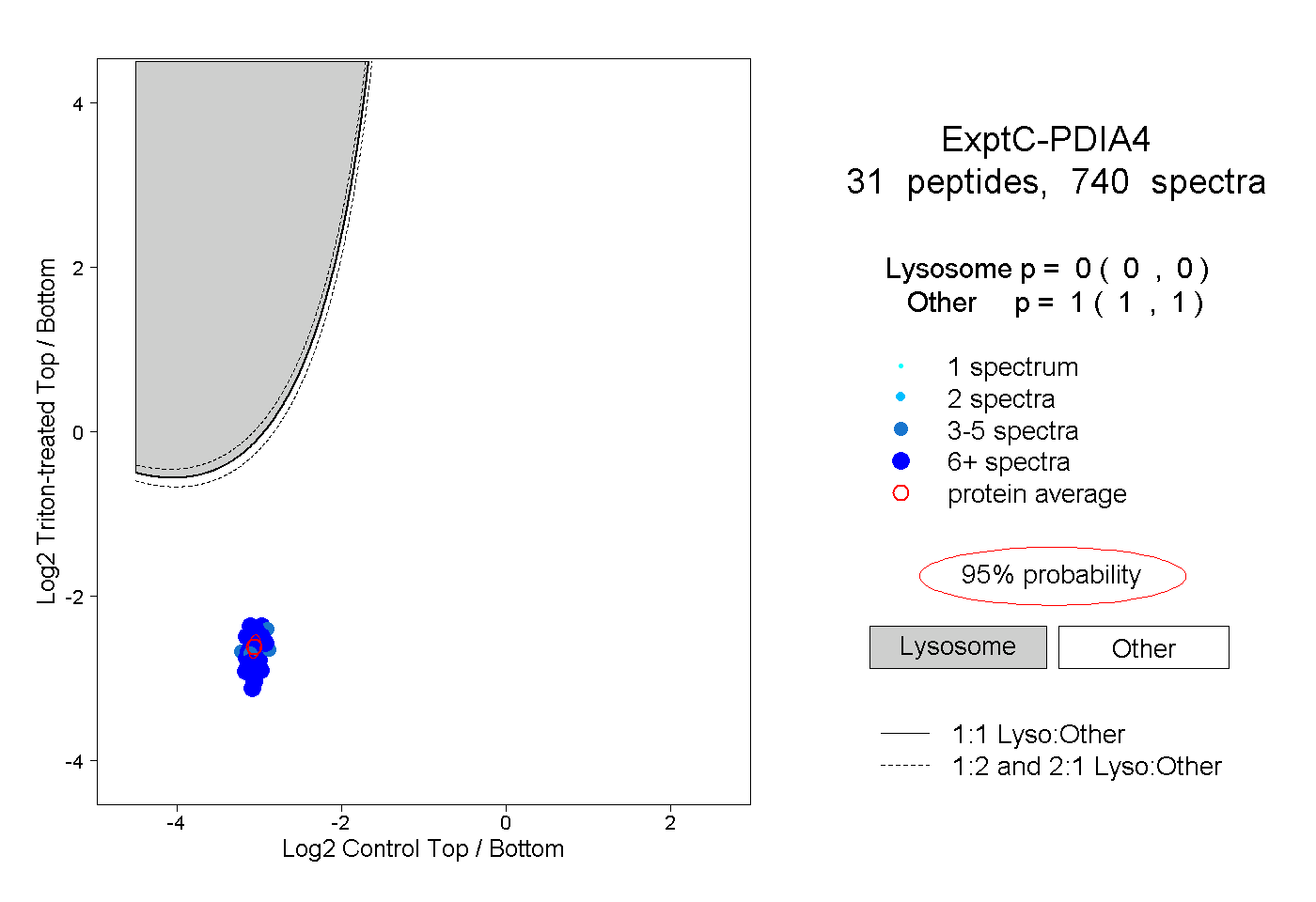 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
95 spectra |
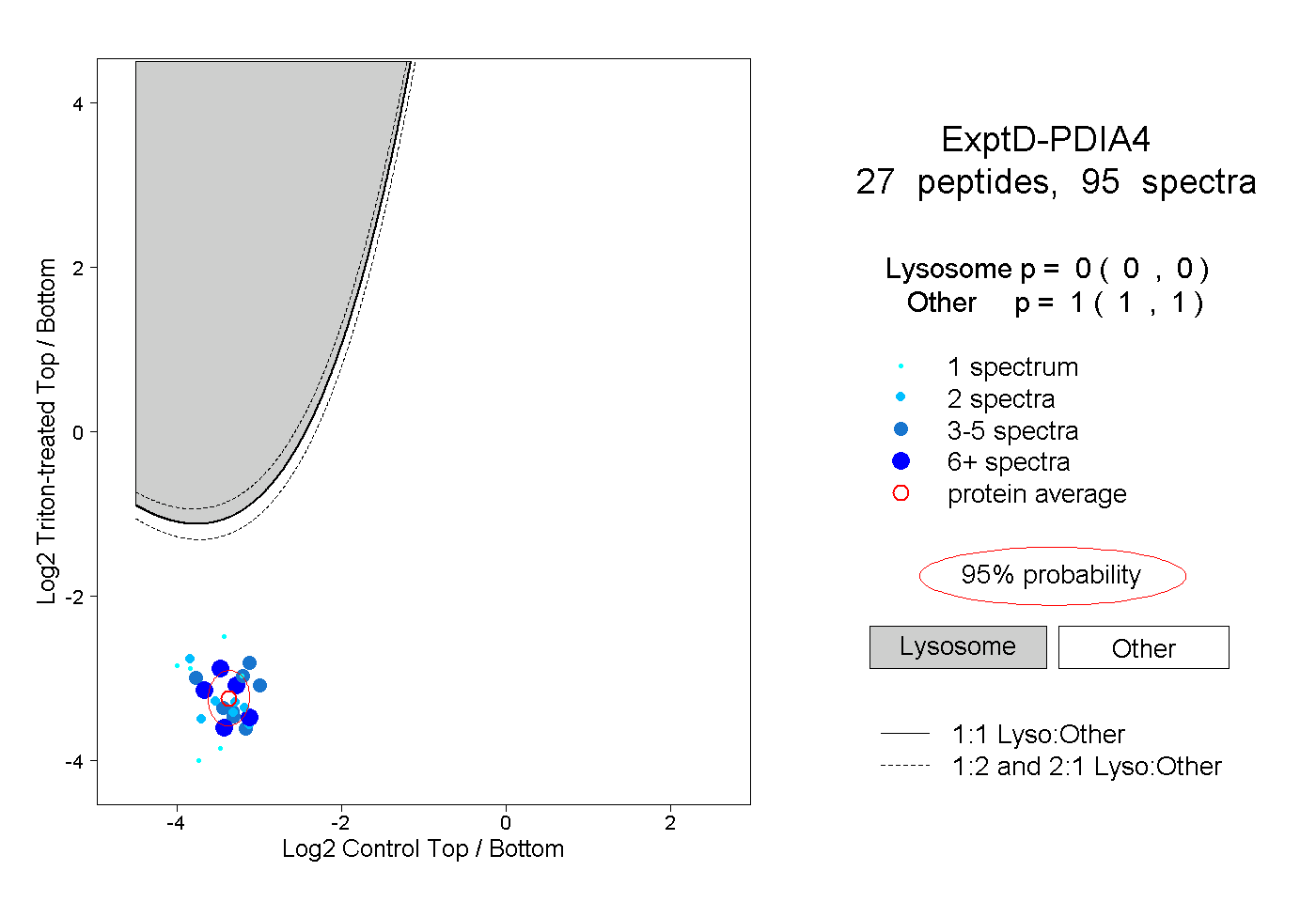 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |