peptides
spectra
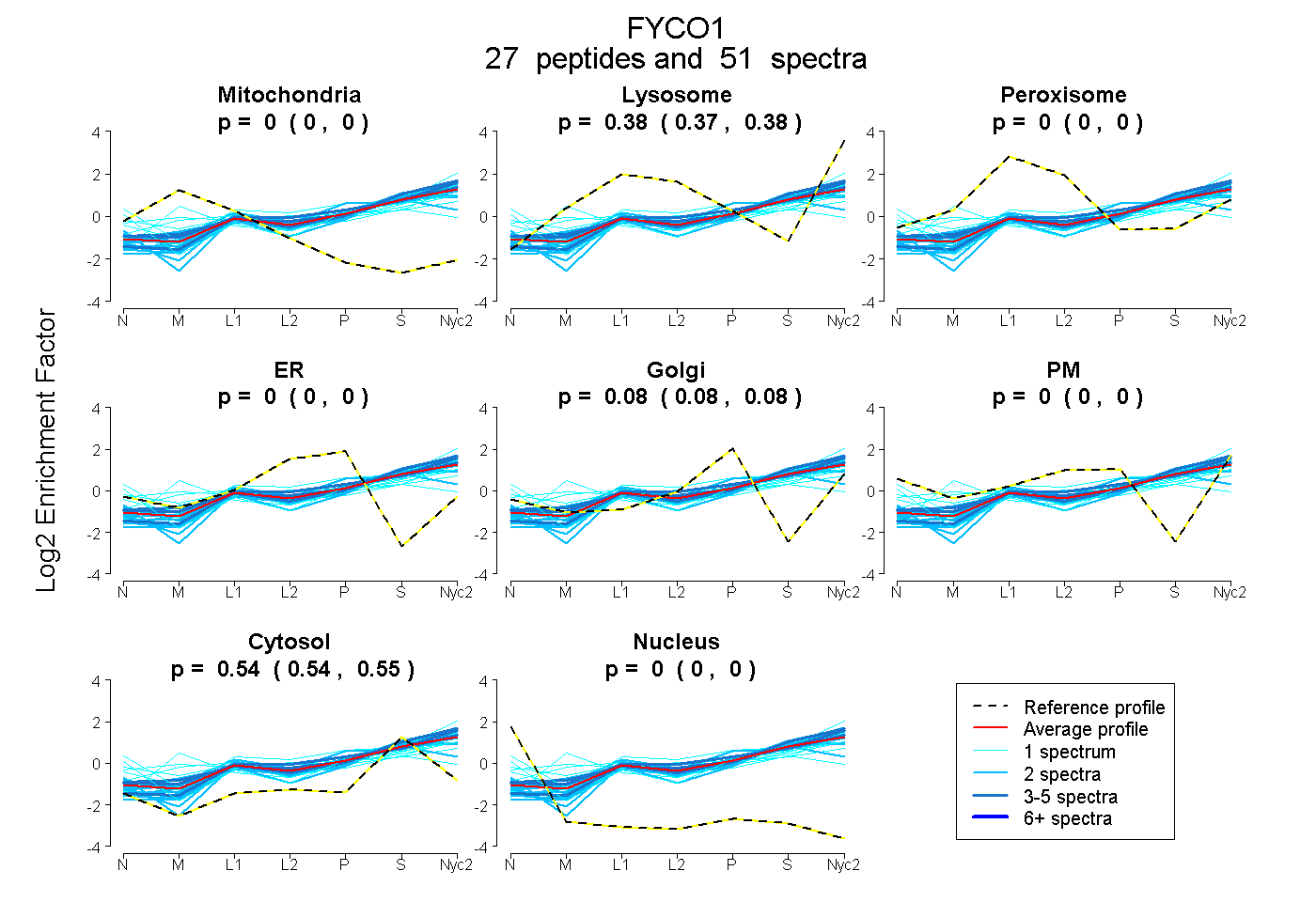
0.000 | 0.000
0.374 | 0.381
0.000 | 0.000
0.000 | 0.000
0.076 | 0.082
0.000 | 0.000
0.540 | 0.545
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
51 spectra |
 |
0.000 0.000 | 0.000 |
0.378 0.374 | 0.381 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.079 0.076 | 0.082 |
0.000 0.000 | 0.000 |
0.543 0.540 | 0.545 |
0.000 0.000 | 0.000 |
| 5 spectra, VNQELQK | 0.000 | 0.410 | 0.000 | 0.000 | 0.109 | 0.000 | 0.481 | 0.000 | ||
| 2 spectra, GADQDELQK | 0.000 | 0.284 | 0.000 | 0.000 | 0.147 | 0.000 | 0.569 | 0.000 | ||
| 1 spectrum, QEQELR | 0.000 | 0.371 | 0.000 | 0.000 | 0.042 | 0.000 | 0.587 | 0.000 | ||
| 1 spectrum, EAAIQGSLASLEAEQASIR | 0.134 | 0.023 | 0.205 | 0.000 | 0.080 | 0.130 | 0.428 | 0.000 | ||
| 2 spectra, LELDQLEVR | 0.000 | 0.375 | 0.000 | 0.000 | 0.000 | 0.000 | 0.625 | 0.000 | ||
| 2 spectra, LCQEVTNR | 0.000 | 0.172 | 0.145 | 0.000 | 0.129 | 0.000 | 0.554 | 0.000 | ||
| 2 spectra, EGILQEESIYK | 0.000 | 0.385 | 0.000 | 0.000 | 0.020 | 0.000 | 0.595 | 0.000 | ||
| 2 spectra, AHIQELLQCSER | 0.000 | 0.402 | 0.000 | 0.000 | 0.060 | 0.000 | 0.538 | 0.000 | ||
| 1 spectrum, ALQAELSQVR | 0.148 | 0.354 | 0.000 | 0.000 | 0.076 | 0.000 | 0.423 | 0.000 | ||
| 2 spectra, GYDLDAAWPTFAR | 0.000 | 0.404 | 0.000 | 0.000 | 0.000 | 0.000 | 0.596 | 0.000 | ||
| 1 spectrum, FQEYYNK | 0.000 | 0.379 | 0.000 | 0.000 | 0.013 | 0.000 | 0.608 | 0.000 | ||
| 1 spectrum, VTSDWYYAR | 0.000 | 0.067 | 0.000 | 0.000 | 0.000 | 0.359 | 0.574 | 0.000 | ||
| 2 spectra, ELQNMAVR | 0.000 | 0.397 | 0.000 | 0.000 | 0.027 | 0.000 | 0.576 | 0.000 | ||
| 1 spectrum, GANDGIR | 0.000 | 0.295 | 0.000 | 0.000 | 0.021 | 0.210 | 0.474 | 0.000 | ||
| 2 spectra, EAALQER | 0.000 | 0.481 | 0.000 | 0.000 | 0.000 | 0.000 | 0.519 | 0.000 | ||
| 1 spectrum, LEYLLQFDQK | 0.000 | 0.504 | 0.000 | 0.000 | 0.078 | 0.000 | 0.418 | 0.000 | ||
| 2 spectra, QLQEHVQQLNR | 0.000 | 0.349 | 0.000 | 0.000 | 0.178 | 0.000 | 0.472 | 0.000 | ||
| 2 spectra, QGEVTQATVK | 0.000 | 0.369 | 0.000 | 0.000 | 0.048 | 0.000 | 0.583 | 0.000 | ||
| 4 spectra, VLIPTTR | 0.000 | 0.416 | 0.000 | 0.000 | 0.000 | 0.000 | 0.584 | 0.000 | ||
| 2 spectra, GQHCLQEEQVNNATVR | 0.000 | 0.242 | 0.000 | 0.000 | 0.000 | 0.115 | 0.644 | 0.000 | ||
| 4 spectra, TEAQAQELR | 0.000 | 0.429 | 0.000 | 0.000 | 0.069 | 0.000 | 0.502 | 0.000 | ||
| 1 spectrum, DAVPLQEELSGK | 0.000 | 0.181 | 0.092 | 0.000 | 0.000 | 0.281 | 0.446 | 0.000 | ||
| 2 spectra, EQNEALNR | 0.000 | 0.436 | 0.000 | 0.000 | 0.014 | 0.000 | 0.551 | 0.000 | ||
| 2 spectra, MLADLDDLNR | 0.000 | 0.405 | 0.000 | 0.000 | 0.000 | 0.000 | 0.595 | 0.000 | ||
| 1 spectrum, EAVQELK | 0.043 | 0.426 | 0.000 | 0.000 | 0.070 | 0.000 | 0.461 | 0.000 | ||
| 1 spectrum, TLVQQLK | 0.000 | 0.144 | 0.000 | 0.000 | 0.000 | 0.421 | 0.434 | 0.000 | ||
| 2 spectra, LNCTGSHLAECQATLLR | 0.000 | 0.377 | 0.000 | 0.000 | 0.088 | 0.000 | 0.535 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
14 spectra |
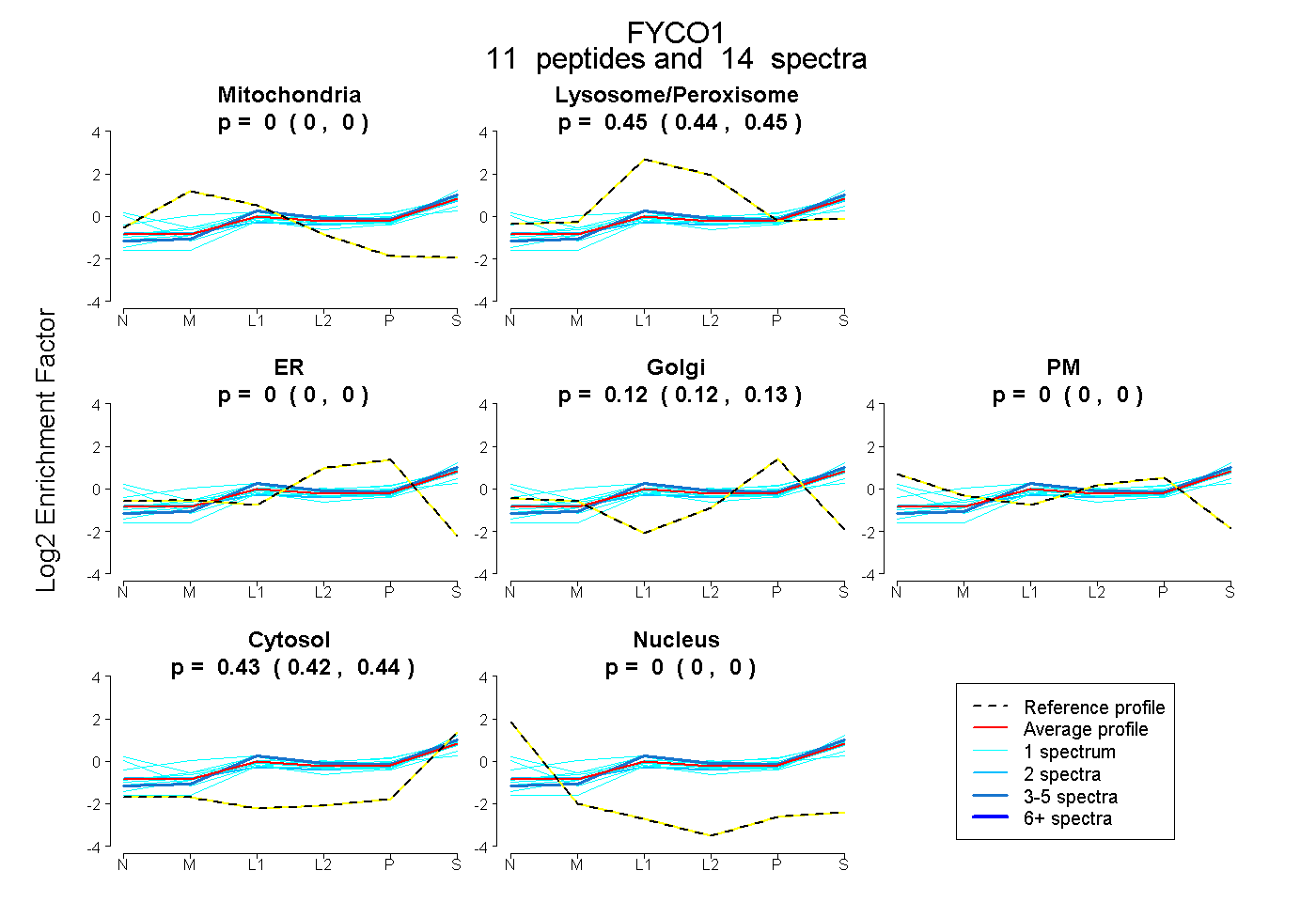 |
0.000 0.000 | 0.000 |
0.445 0.439 | 0.450 |
0.000 0.000 | 0.000 |
0.124 0.115 | 0.132 |
0.000 0.000 | 0.000 |
0.431 0.422 | 0.438 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
84 spectra |
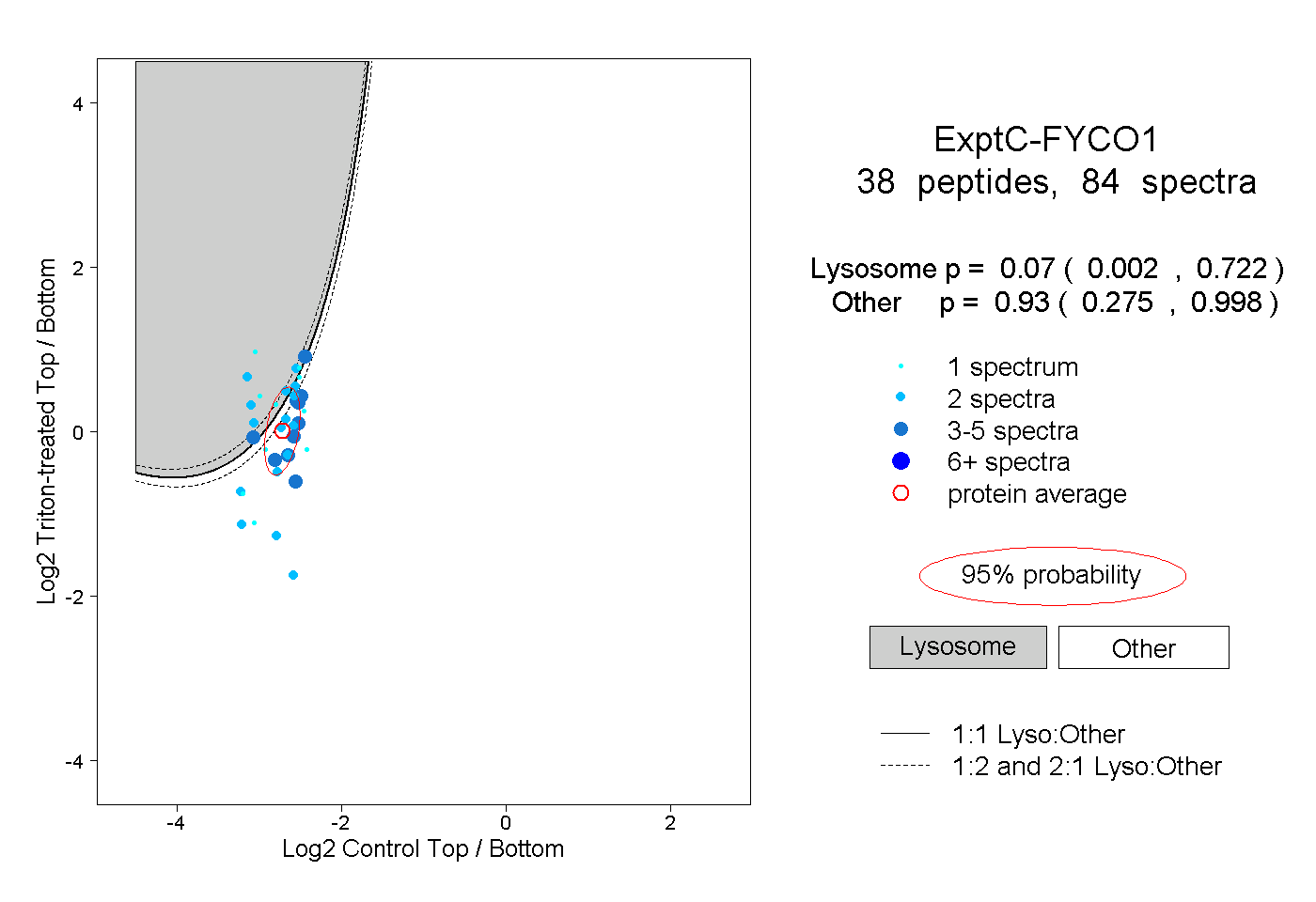 |
0.070 0.002 | 0.722 |
0.930 0.275 | 0.998 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
14 spectra |
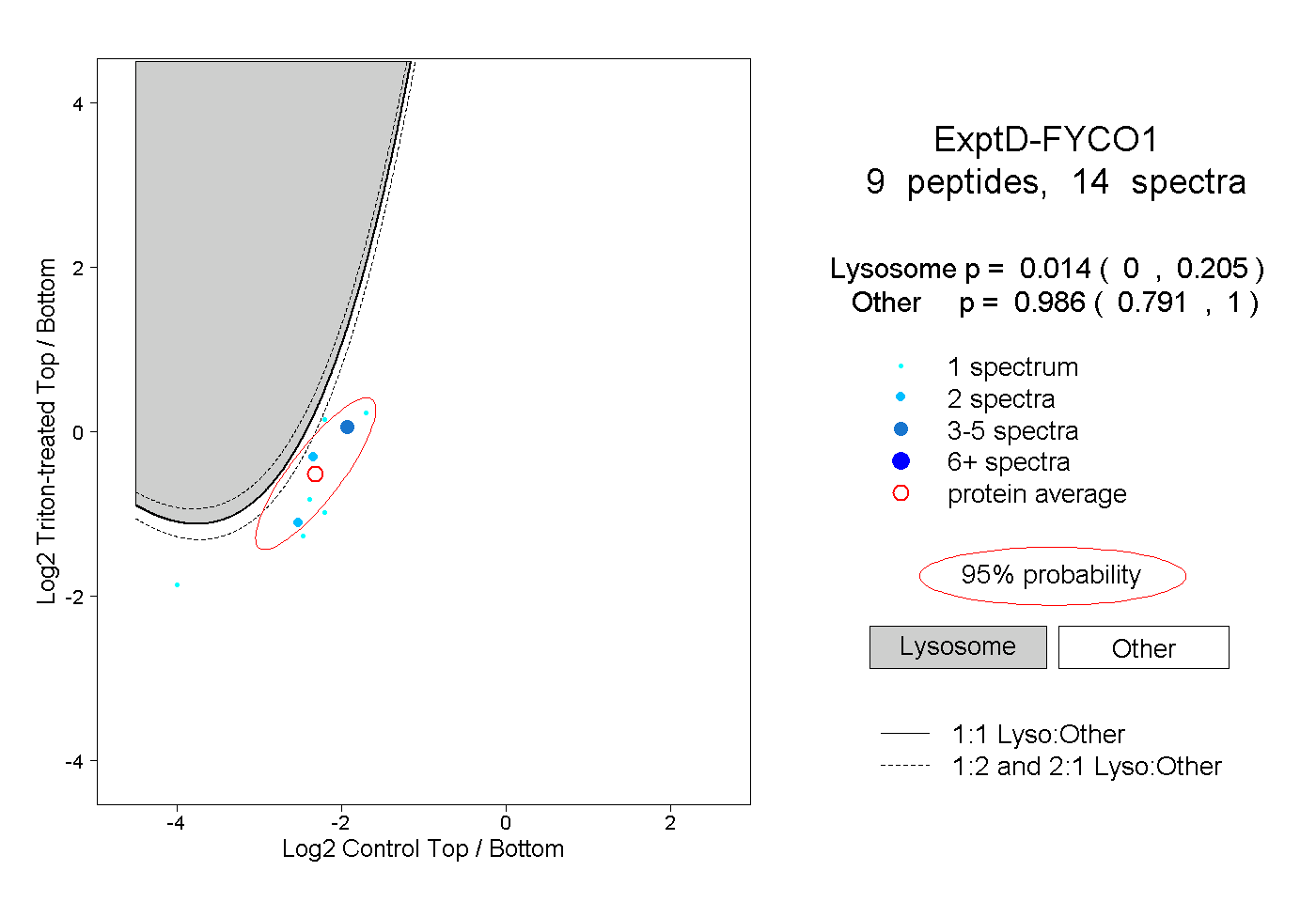 |
0.014 0.000 | 0.205 |
0.986 0.791 | 1.000 |