peptides
spectra
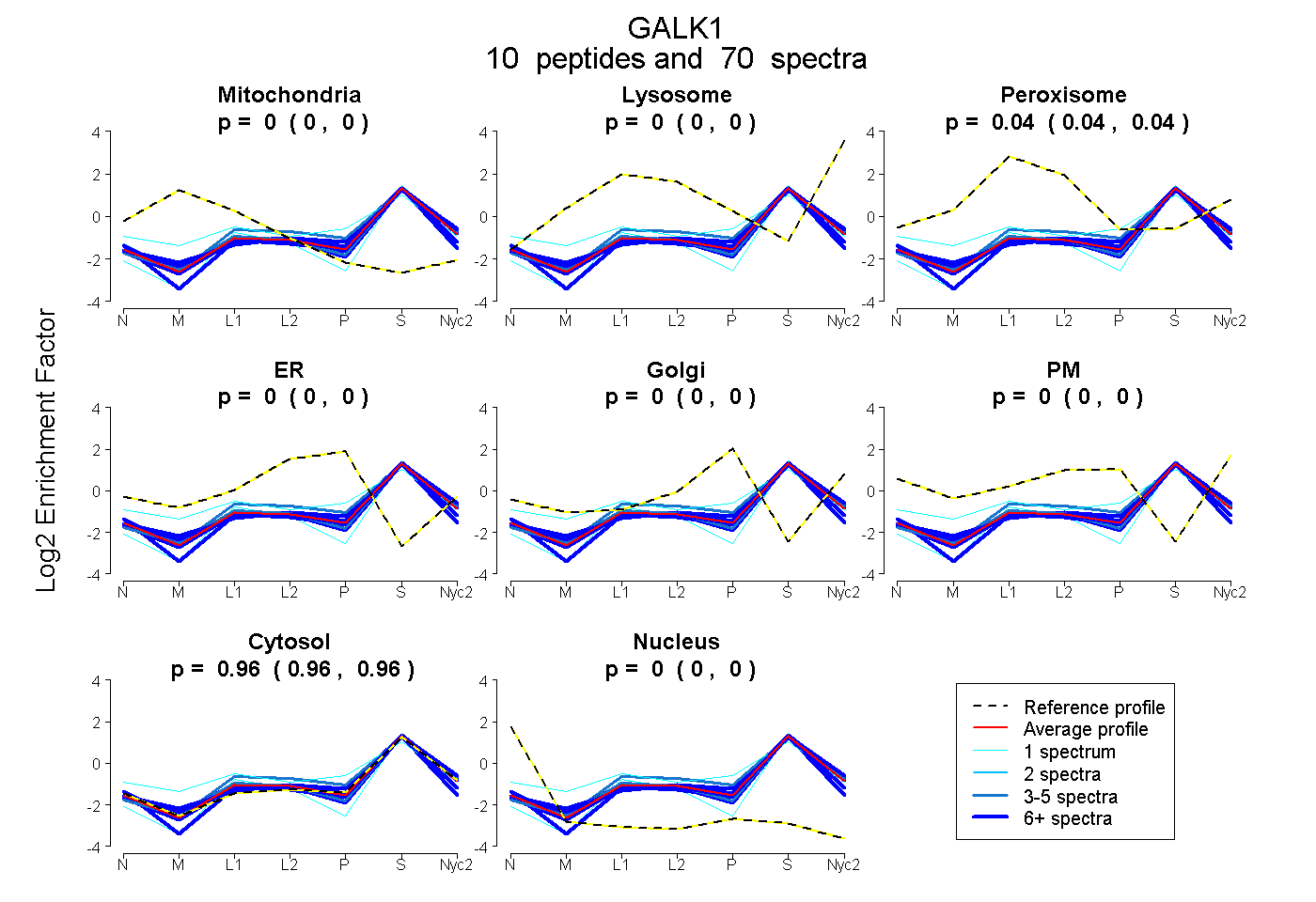
0.000 | 0.000
0.000 | 0.000
0.036 | 0.042
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.958 | 0.963
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
70 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.039 0.036 | 0.042 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.961 0.958 | 0.963 |
0.000 0.000 | 0.000 |
| 11 spectra, VEELLAEAR | 0.000 | 0.024 | 0.020 | 0.000 | 0.000 | 0.000 | 0.956 | 0.000 | ||
| 6 spectra, QCEEVAQALGK | 0.000 | 0.000 | 0.018 | 0.000 | 0.000 | 0.000 | 0.965 | 0.017 | ||
| 1 spectrum, LMVESHYSLR | 0.057 | 0.000 | 0.154 | 0.026 | 0.034 | 0.000 | 0.728 | 0.000 | ||
| 1 spectrum, AFMEEFGAEPELAVSAPGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 6 spectra, HVVSEIR | 0.003 | 0.055 | 0.000 | 0.000 | 0.000 | 0.000 | 0.942 | 0.000 | ||
| 5 spectra, TAQGAAALSR | 0.000 | 0.000 | 0.052 | 0.000 | 0.000 | 0.000 | 0.948 | 0.000 | ||
| 12 spectra, AQVCQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.977 | 0.023 | ||
| 12 spectra, MEELEAGR | 0.000 | 0.000 | 0.009 | 0.000 | 0.000 | 0.000 | 0.991 | 0.000 | ||
| 4 spectra, GYALLIDCR | 0.000 | 0.000 | 0.130 | 0.000 | 0.000 | 0.000 | 0.870 | 0.000 | ||
| 12 spectra, LTVLITNSNVR | 0.000 | 0.000 | 0.046 | 0.000 | 0.000 | 0.000 | 0.954 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
26 spectra |
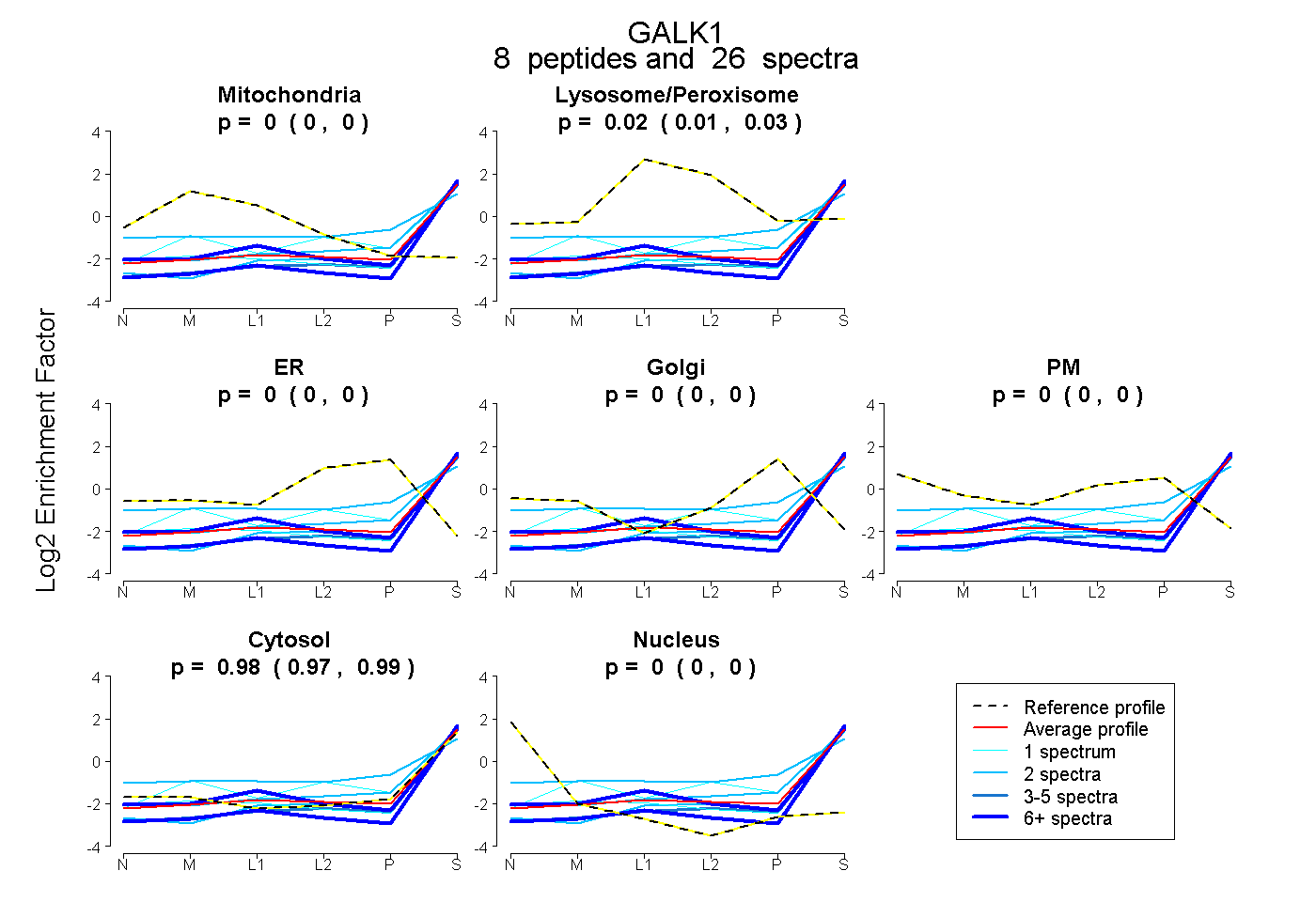 |
0.000 0.000 | 0.000 |
0.018 0.007 | 0.027 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.982 0.971 | 0.991 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
57 spectra |
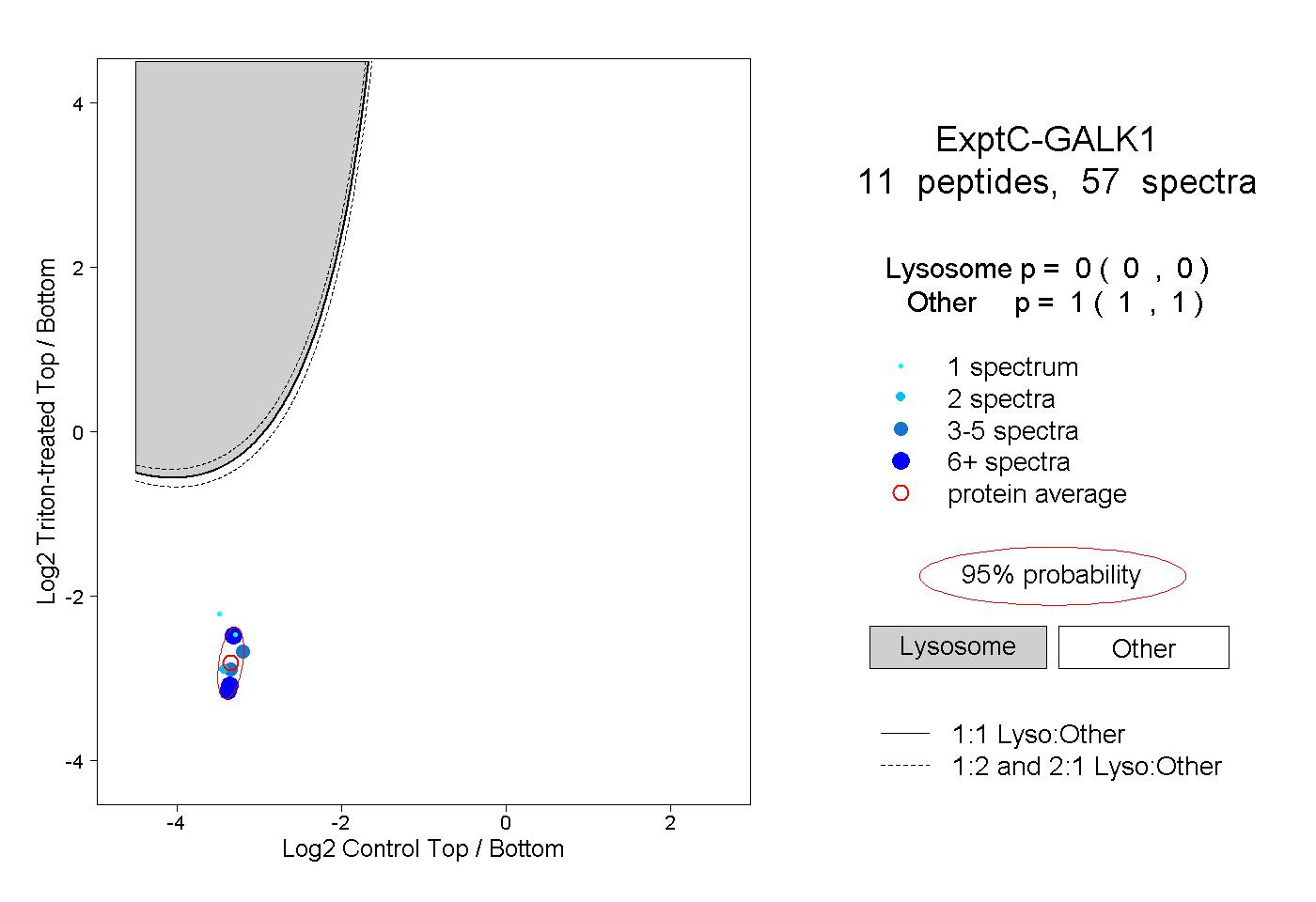 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
8 spectra |
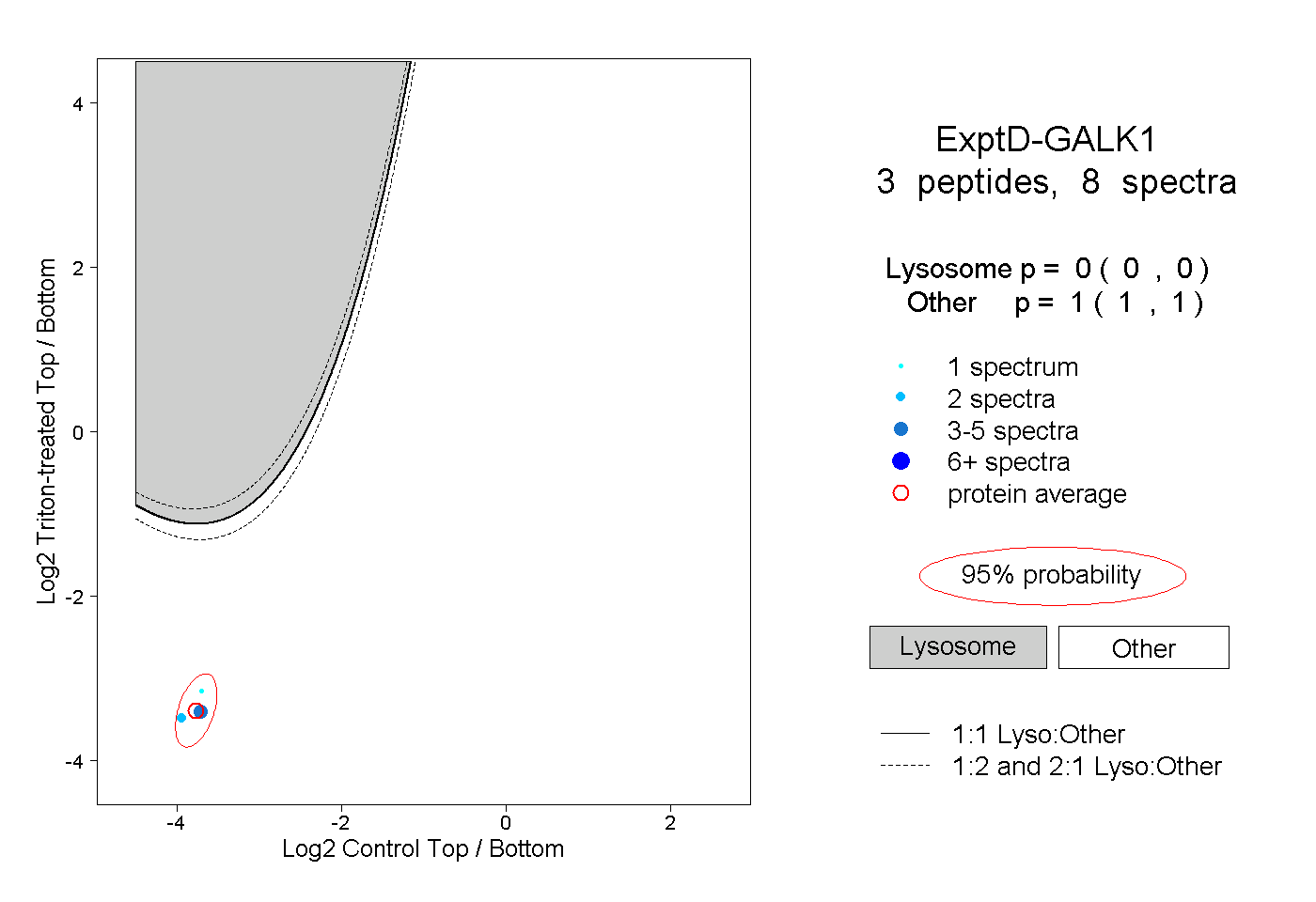 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |