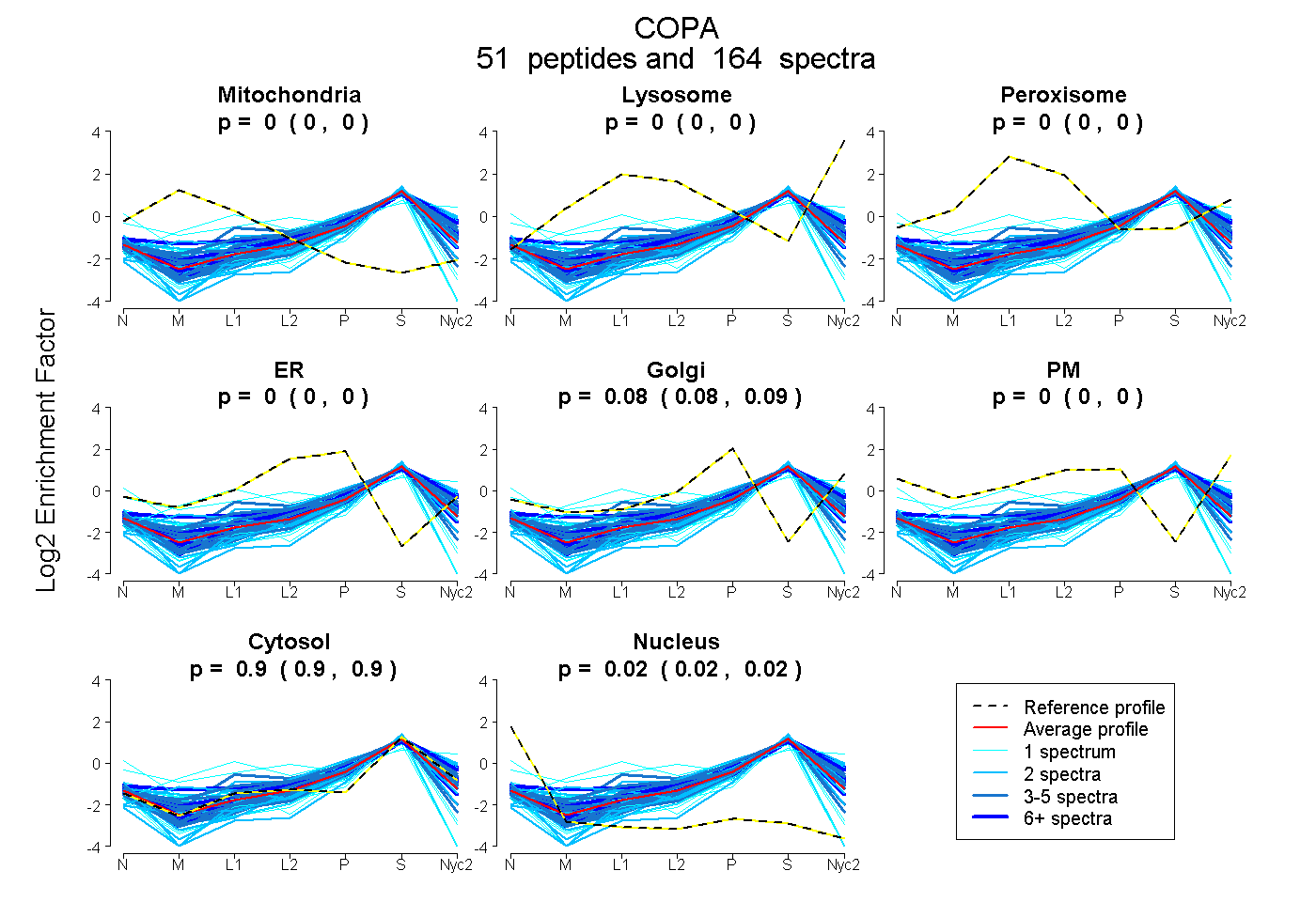
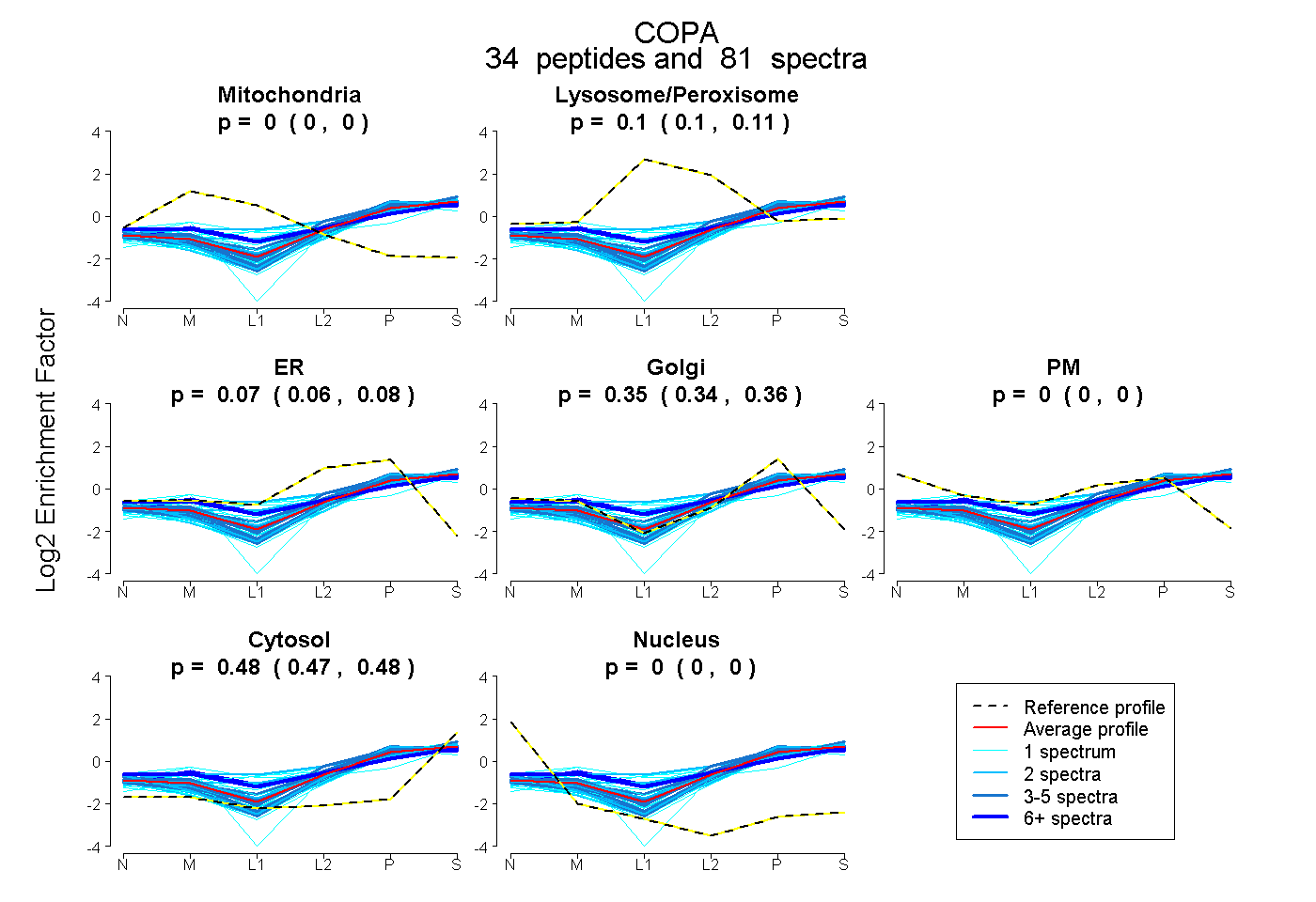
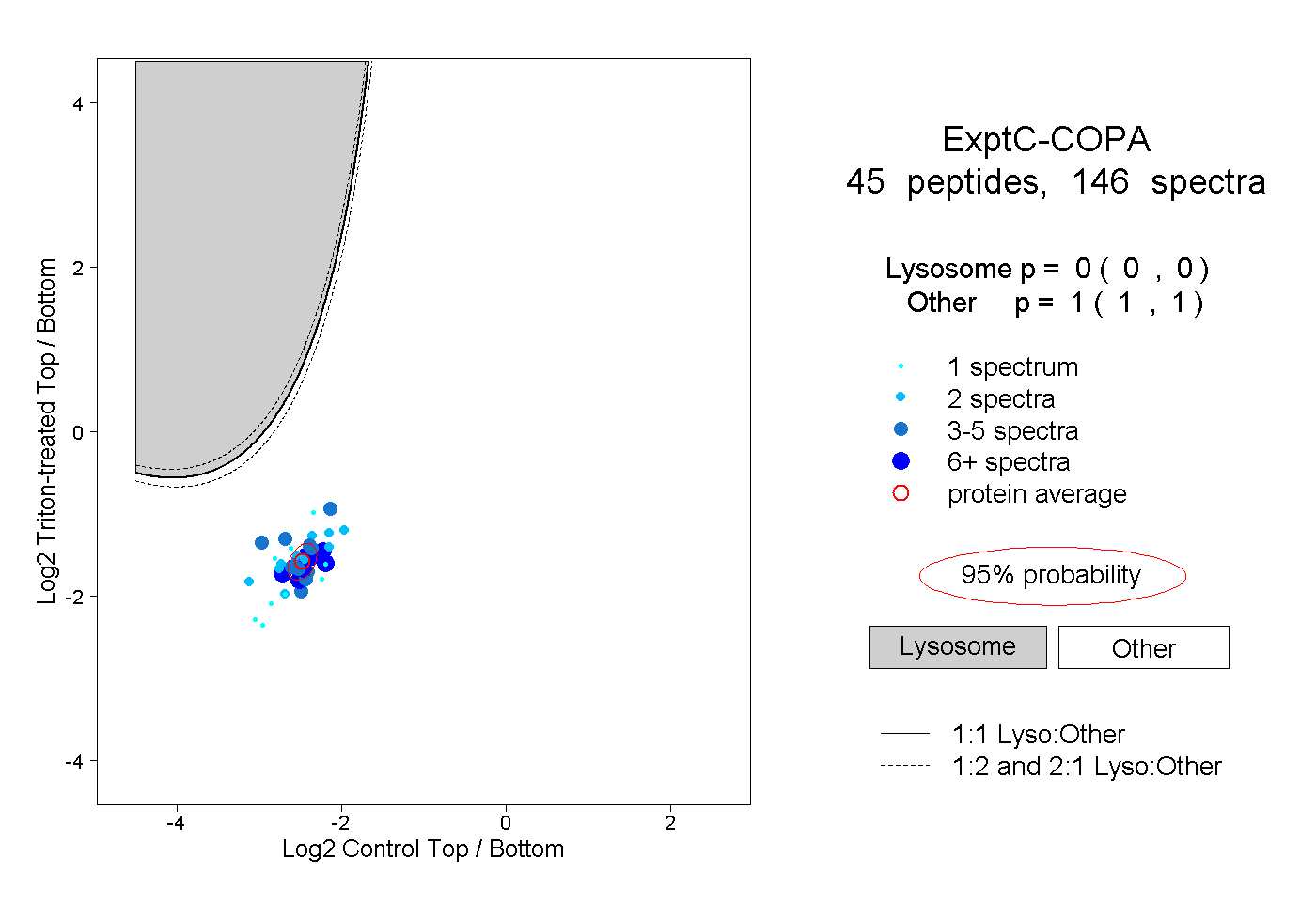
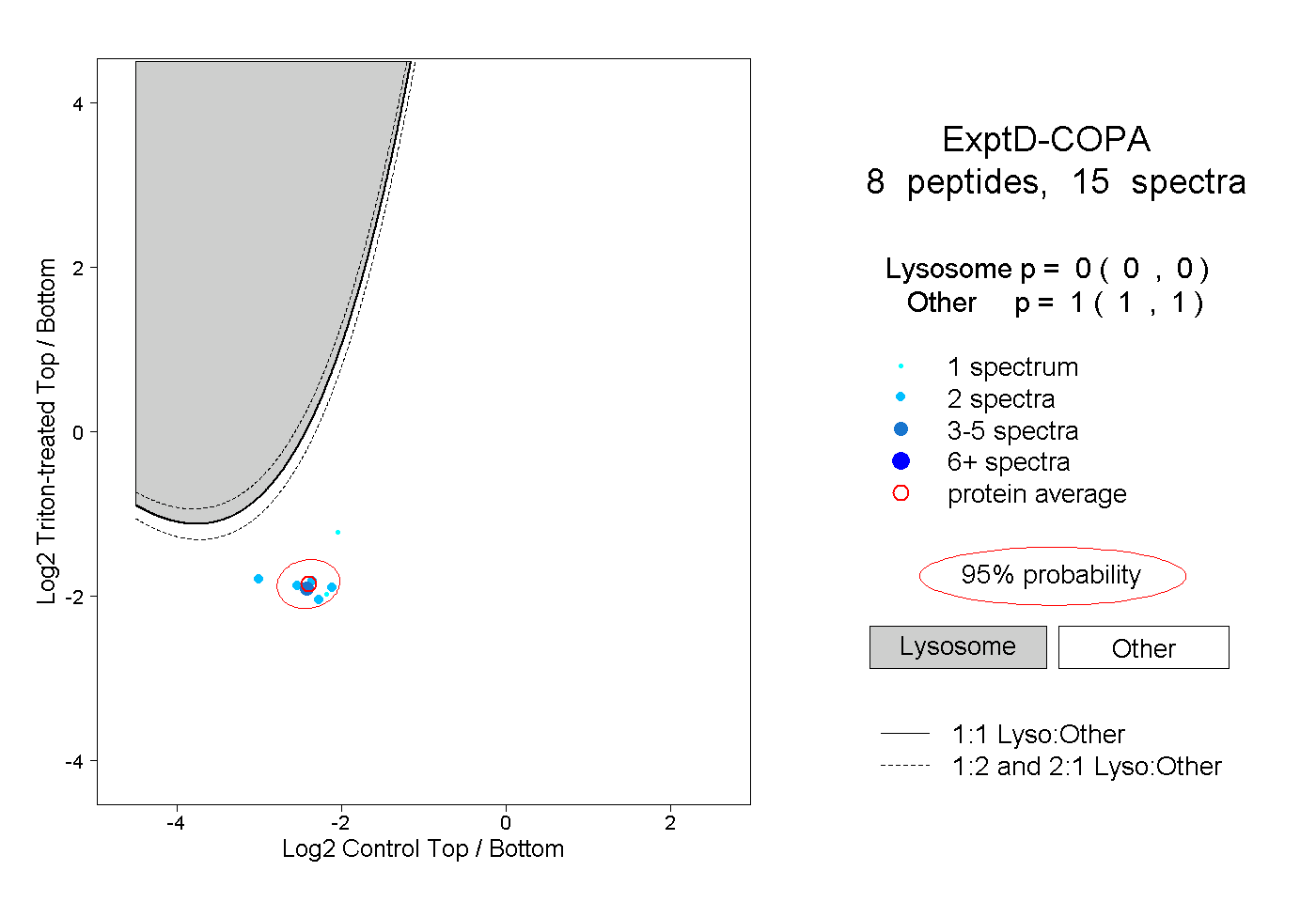
| 1 spectrum, QELILSNSEDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, AWEVDTCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, GKPVEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TLASVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, LALINR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, GFFEGSIASK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, LNDLIQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, YDEVLHMVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ETFDPEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, ETLDQQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, ISPLQFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, HAIVICNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LQLCYQLSTVGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, HVLEGHDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, VWNWQSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, DVIGLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, ILSACEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GNNVYCLDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QLFLQTYAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, FAVLDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GLSFHPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LGEVALLQGNHQIVEMCYQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, FEDAVEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GITGVDLFGTTDAVVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VWDISGLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, DVAVMQLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, IALIDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LDALCNIHENIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, FDEHDGPVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, MHSLLIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, NLSPGAVESDVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, LLELGPKPEVAQQTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, TALNLFFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, GIDFHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, CPLSGACYSPEFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, IQVPNCDEIFYAGTGNLLLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QLDFNSSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, YAVTTGDHGIIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TAATFAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, TGVQTFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VTTVTEIGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, TLDLPIYVTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, LLHDQVGVVQFGPYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, VLTIDPTEFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SSGLTAVWVAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |