peptides
spectra
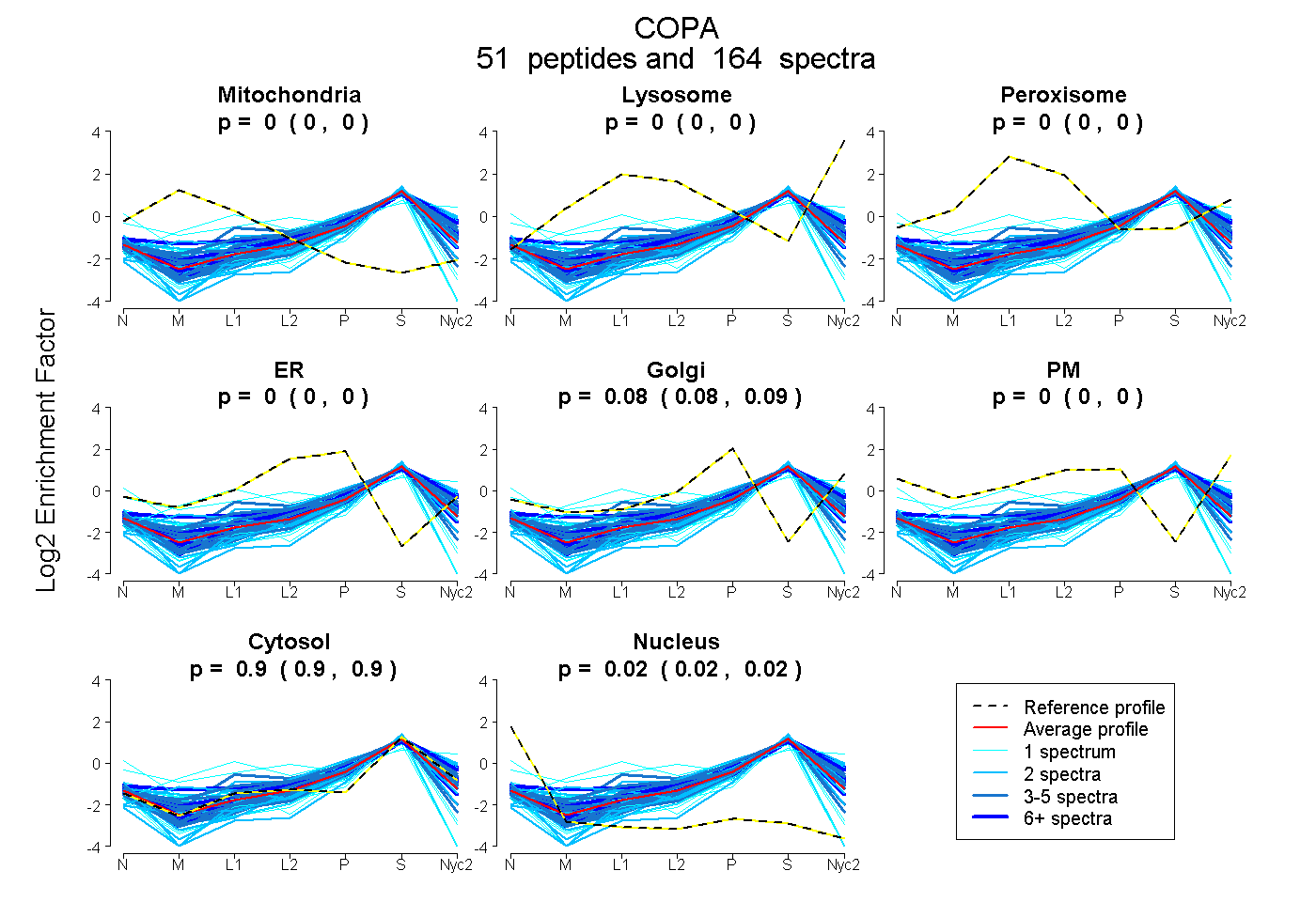
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.083 | 0.086
0.000 | 0.000
0.897 | 0.899
0.015 | 0.019
peptides
spectra
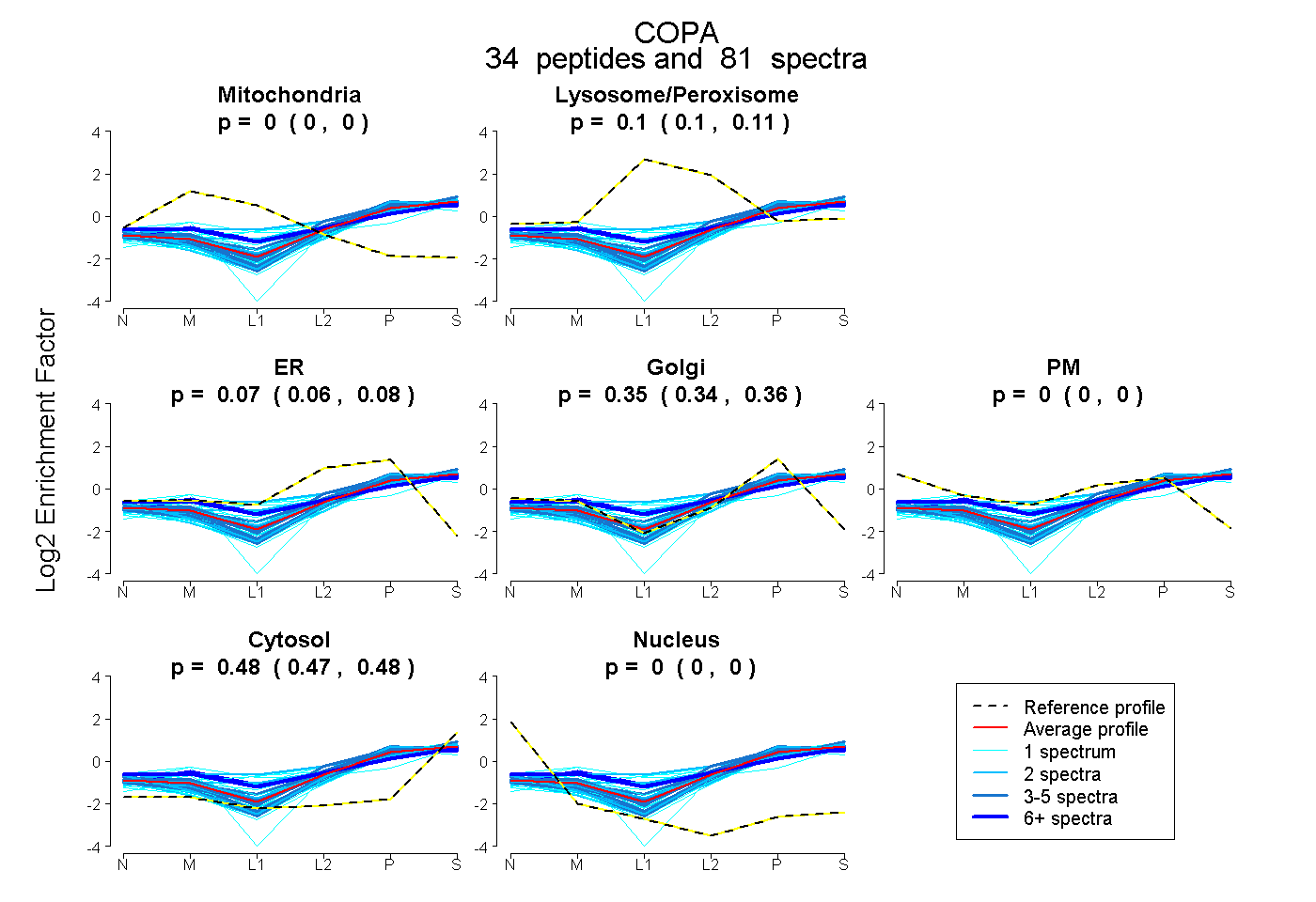
0.000 | 0.000
0.097 | 0.110
0.060 | 0.083
0.336 | 0.355
0.000 | 0.000
0.473 | 0.480
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
164 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.085 0.083 | 0.086 |
0.000 0.000 | 0.000 |
0.898 0.897 | 0.899 |
0.017 0.015 | 0.019 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
81 spectra |
 |
0.000 0.000 | 0.000 |
0.104 0.097 | 0.110 |
0.072 0.060 | 0.083 |
0.347 0.336 | 0.355 |
0.000 0.000 | 0.000 |
0.477 0.473 | 0.480 |
0.000 0.000 | 0.000 |
| 1 spectrum, DADSQNPDAPEGK | 0.000 | 0.298 | 0.000 | 0.331 | 0.000 | 0.371 | 0.000 | |||
| 2 spectra, QELILSNSEDK | 0.000 | 0.348 | 0.000 | 0.289 | 0.000 | 0.363 | 0.000 | |||
| 1 spectrum, AWEVDTCR | 0.000 | 0.062 | 0.000 | 0.433 | 0.000 | 0.506 | 0.000 | |||
| 2 spectra, QEIAEAQQLITICR | 0.000 | 0.262 | 0.000 | 0.312 | 0.000 | 0.425 | 0.000 | |||
| 1 spectrum, LALINR | 0.000 | 0.318 | 0.000 | 0.334 | 0.000 | 0.348 | 0.000 | |||
| 1 spectrum, GFFEGSIASK | 0.000 | 0.000 | 0.000 | 0.590 | 0.000 | 0.410 | 0.000 | |||
| 1 spectrum, LNDLIQR | 0.000 | 0.000 | 0.285 | 0.204 | 0.000 | 0.511 | 0.000 | |||
| 4 spectra, LVGQSIIAYLQK | 0.000 | 0.094 | 0.148 | 0.278 | 0.000 | 0.479 | 0.000 | |||
| 3 spectra, ISPLQFR | 0.000 | 0.108 | 0.126 | 0.310 | 0.000 | 0.457 | 0.000 | |||
| 1 spectrum, HAIVICNR | 0.000 | 0.000 | 0.052 | 0.373 | 0.000 | 0.575 | 0.000 | |||
| 1 spectrum, LQLCYQLSTVGK | 0.000 | 0.000 | 0.000 | 0.412 | 0.000 | 0.588 | 0.000 | |||
| 6 spectra, HVLEGHDR | 0.000 | 0.234 | 0.000 | 0.376 | 0.000 | 0.390 | 0.000 | |||
| 2 spectra, VWNWQSR | 0.000 | 0.148 | 0.029 | 0.327 | 0.000 | 0.496 | 0.000 | |||
| 1 spectrum, ILSACEK | 0.000 | 0.013 | 0.168 | 0.247 | 0.000 | 0.571 | 0.000 | |||
| 2 spectra, GNNVYCLDR | 0.000 | 0.051 | 0.000 | 0.419 | 0.000 | 0.530 | 0.000 | |||
| 3 spectra, QLFLQTYAR | 0.000 | 0.001 | 0.168 | 0.310 | 0.000 | 0.520 | 0.000 | |||
| 4 spectra, FAVLDR | 0.000 | 0.000 | 0.125 | 0.349 | 0.000 | 0.526 | 0.000 | |||
| 1 spectrum, LGEVALLQGNHQIVEMCYQR | 0.006 | 0.262 | 0.000 | 0.126 | 0.140 | 0.465 | 0.000 | |||
| 1 spectrum, FEDAVEK | 0.000 | 0.000 | 0.199 | 0.213 | 0.000 | 0.588 | 0.000 | |||
| 1 spectrum, SILLSVPLLVVDNK | 0.000 | 0.171 | 0.000 | 0.374 | 0.000 | 0.455 | 0.000 | |||
| 3 spectra, VWDISGLR | 0.000 | 0.058 | 0.198 | 0.273 | 0.000 | 0.471 | 0.000 | |||
| 4 spectra, DVAVMQLR | 0.000 | 0.011 | 0.091 | 0.361 | 0.000 | 0.536 | 0.000 | |||
| 2 spectra, FDEHDGPVR | 0.000 | 0.000 | 0.150 | 0.250 | 0.000 | 0.600 | 0.000 | |||
| 1 spectrum, MHSLLIK | 0.000 | 0.177 | 0.271 | 0.065 | 0.000 | 0.488 | 0.000 | |||
| 1 spectrum, LLELGPKPEVAQQTR | 0.000 | 0.000 | 0.187 | 0.304 | 0.000 | 0.509 | 0.000 | |||
| 3 spectra, TALNLFFK | 0.000 | 0.000 | 0.134 | 0.271 | 0.000 | 0.595 | 0.000 | |||
| 4 spectra, GIDFHK | 0.000 | 0.159 | 0.045 | 0.398 | 0.000 | 0.398 | 0.000 | |||
| 1 spectrum, CPLSGACYSPEFK | 0.000 | 0.224 | 0.000 | 0.308 | 0.000 | 0.468 | 0.000 | |||
| 9 spectra, YAVTTGDHGIIR | 0.000 | 0.247 | 0.000 | 0.335 | 0.000 | 0.419 | 0.000 | |||
| 4 spectra, TAATFAR | 0.000 | 0.124 | 0.004 | 0.421 | 0.000 | 0.452 | 0.000 | |||
| 3 spectra, TGVQTFR | 0.000 | 0.074 | 0.100 | 0.368 | 0.000 | 0.457 | 0.000 | |||
| 2 spectra, TLDLPIYVTR | 0.000 | 0.000 | 0.091 | 0.445 | 0.000 | 0.463 | 0.000 | |||
| 2 spectra, QQPLFVSGGDDYK | 0.000 | 0.030 | 0.211 | 0.236 | 0.000 | 0.523 | 0.000 | |||
| 3 spectra, SSGLTAVWVAR | 0.000 | 0.000 | 0.396 | 0.114 | 0.000 | 0.490 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
146 spectra |
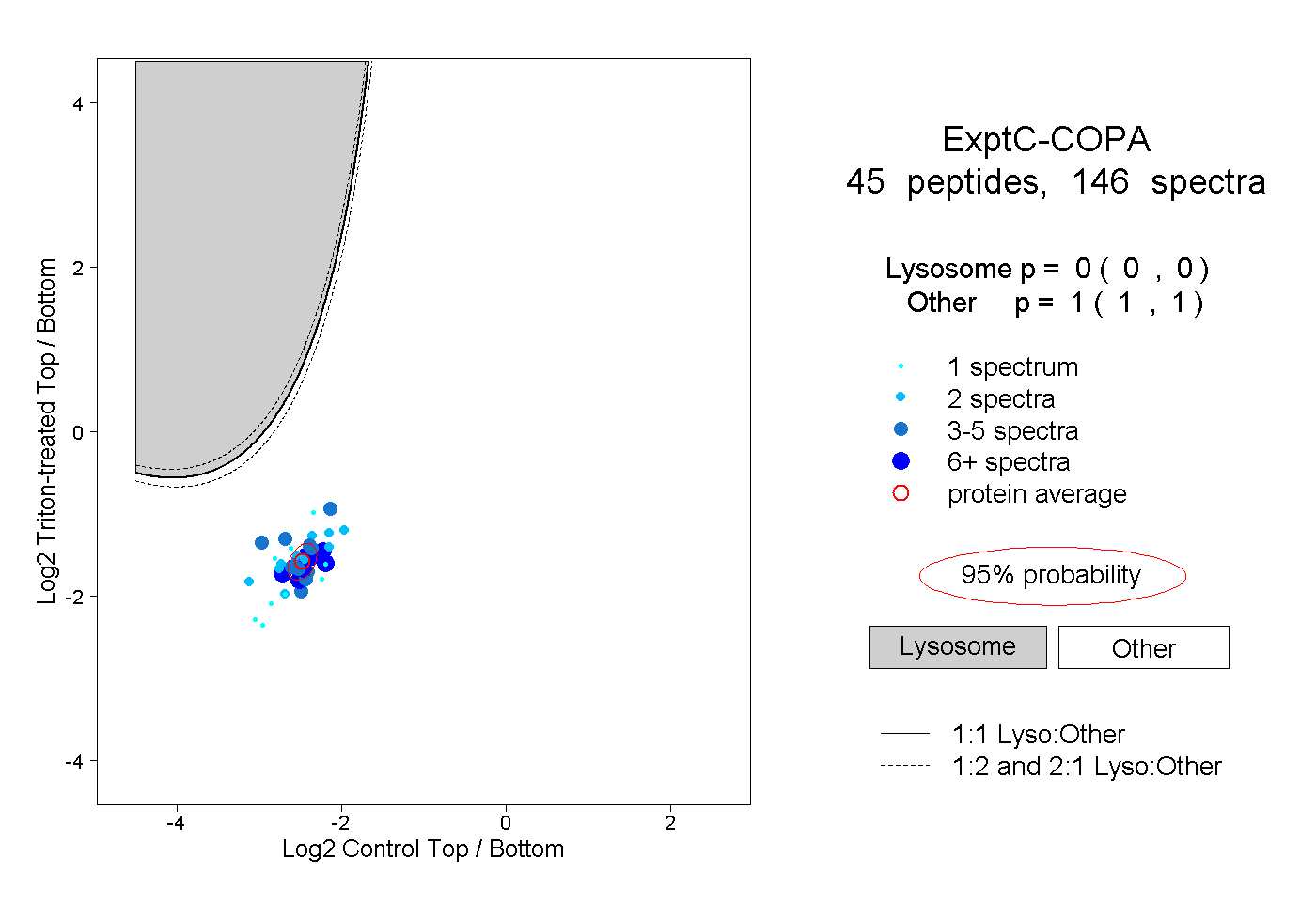 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
15 spectra |
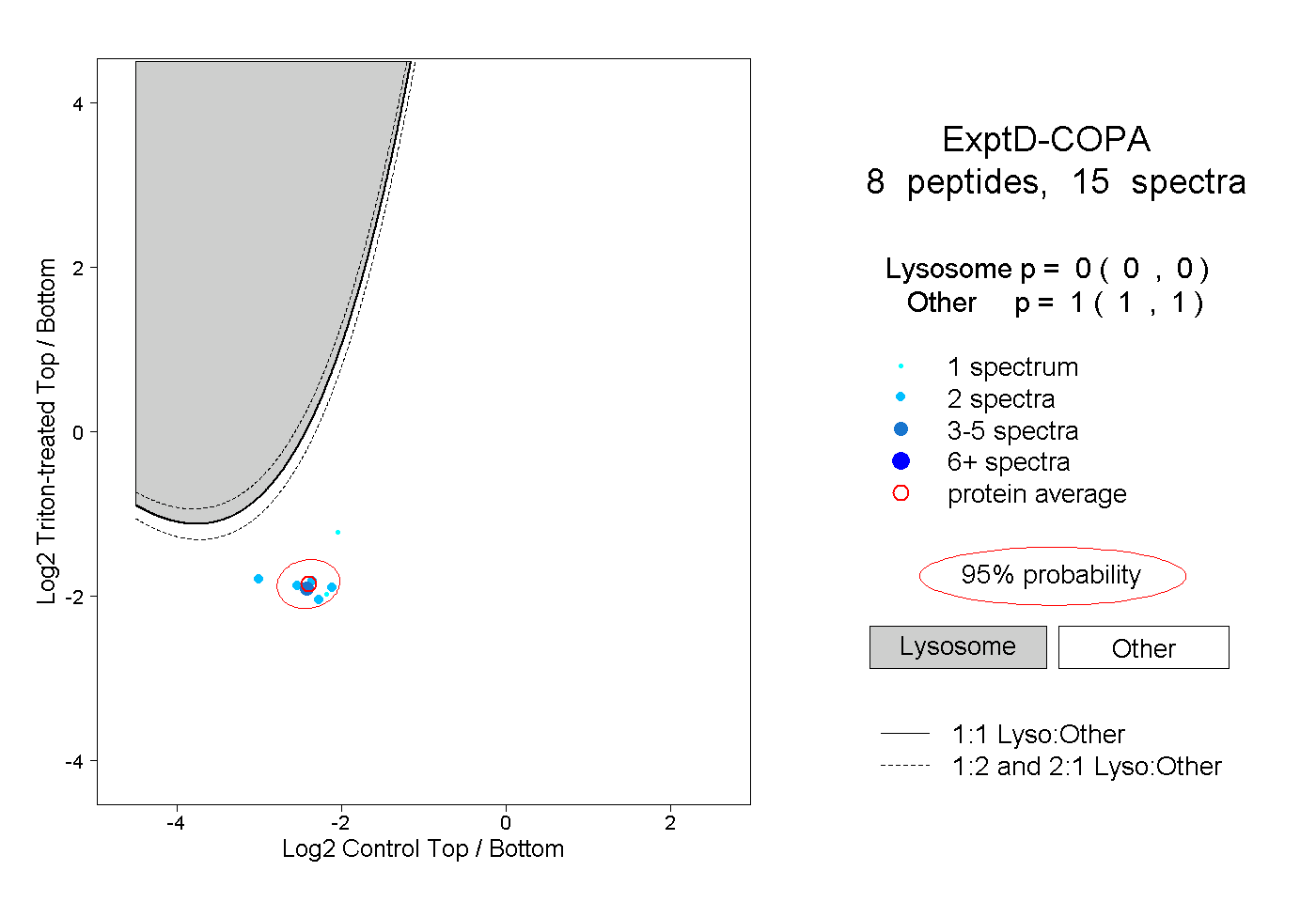 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |