peptides
spectra
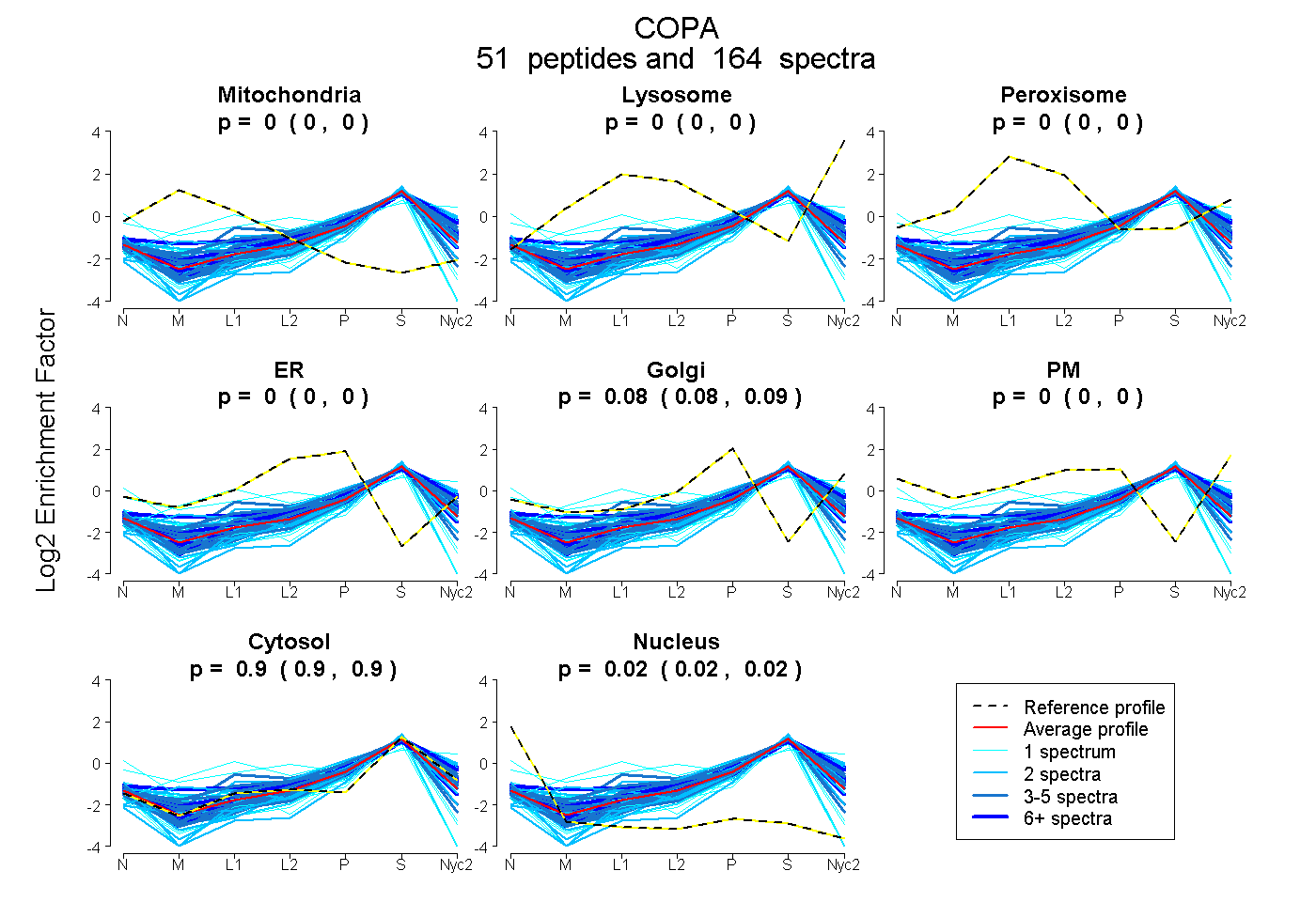
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.083 | 0.086
0.000 | 0.000
0.897 | 0.899
0.015 | 0.019
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
164 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.085 0.083 | 0.086 |
0.000 0.000 | 0.000 |
0.898 0.897 | 0.899 |
0.017 0.015 | 0.019 |
| 2 spectra, TTFFHHEYPWILSASDDQTIR | 0.079 | 0.010 | 0.000 | 0.000 | 0.083 | 0.000 | 0.828 | 0.000 | ||
| 2 spectra, DADSQNPDAPEGK | 0.000 | 0.001 | 0.000 | 0.000 | 0.151 | 0.000 | 0.848 | 0.000 | ||
| 1 spectrum, GHYNNVSCAVFHPR | 0.034 | 0.000 | 0.210 | 0.088 | 0.000 | 0.086 | 0.581 | 0.000 | ||
| 5 spectra, QELILSNSEDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.114 | 0.000 | 0.886 | 0.000 | ||
| 10 spectra, AWEVDTCR | 0.000 | 0.000 | 0.000 | 0.142 | 0.000 | 0.000 | 0.851 | 0.007 | ||
| 1 spectrum, DADSITLFDVQQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.183 | 0.000 | 0.817 | 0.000 | ||
| 1 spectrum, TLASVK | 0.308 | 0.000 | 0.000 | 0.102 | 0.000 | 0.000 | 0.590 | 0.000 | ||
| 1 spectrum, LALINR | 0.000 | 0.059 | 0.000 | 0.000 | 0.188 | 0.000 | 0.753 | 0.000 | ||
| 4 spectra, GFFEGSIASK | 0.000 | 0.000 | 0.000 | 0.000 | 0.131 | 0.000 | 0.869 | 0.000 | ||
| 6 spectra, LNDLIQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.146 | 0.000 | 0.847 | 0.007 | ||
| 5 spectra, YDEVLHMVR | 0.008 | 0.000 | 0.000 | 0.000 | 0.121 | 0.000 | 0.870 | 0.000 | ||
| 1 spectrum, NPTDACQLNYDMHNPFDICAASYRPIYR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.778 | 0.222 | ||
| 4 spectra, ISPLQFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.080 | 0.000 | 0.900 | 0.021 | ||
| 5 spectra, HAIVICNR | 0.000 | 0.000 | 0.000 | 0.127 | 0.000 | 0.000 | 0.812 | 0.061 | ||
| 2 spectra, LQLCYQLSTVGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.755 | 0.245 | ||
| 4 spectra, HVLEGHDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.076 | 0.000 | 0.903 | 0.021 | ||
| 3 spectra, VWNWQSR | 0.000 | 0.035 | 0.048 | 0.000 | 0.128 | 0.000 | 0.790 | 0.000 | ||
| 5 spectra, DVIGLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.074 | 0.000 | 0.913 | 0.013 | ||
| 2 spectra, ILSACEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.133 | 0.000 | 0.867 | 0.000 | ||
| 6 spectra, GNNVYCLDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.141 | 0.000 | 0.859 | 0.000 | ||
| 7 spectra, QLFLQTYAR | 0.073 | 0.000 | 0.051 | 0.000 | 0.115 | 0.000 | 0.761 | 0.000 | ||
| 7 spectra, FAVLDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.067 | 0.000 | 0.910 | 0.023 | ||
| 4 spectra, LGEVALLQGNHQIVEMCYQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.878 | 0.122 | ||
| 4 spectra, FEDAVEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.024 | 0.000 | 0.963 | 0.013 | ||
| 1 spectrum, DMSGHYQNALYLGDVSER | 0.062 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.709 | 0.228 | ||
| 1 spectrum, GYPEVALHFVK | 0.049 | 0.000 | 0.000 | 0.000 | 0.063 | 0.000 | 0.888 | 0.000 | ||
| 1 spectrum, SILLSVPLLVVDNK | 0.000 | 0.000 | 0.000 | 0.000 | 0.206 | 0.140 | 0.630 | 0.024 | ||
| 4 spectra, GVNWAAFHPTMPLIVSGADDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.048 | 0.000 | 0.952 | 0.000 | ||
| 3 spectra, YVIWSADMSHVALLAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.101 | 0.000 | 0.899 | 0.000 | ||
| 4 spectra, DVAVMQLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.063 | 0.000 | 0.917 | 0.020 | ||
| 2 spectra, ERPAYAVHGNMLHYVK | 0.004 | 0.000 | 0.000 | 0.109 | 0.000 | 0.000 | 0.850 | 0.037 | ||
| 1 spectrum, LDALCNIHENIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.196 | 0.000 | 0.797 | 0.008 | ||
| 3 spectra, FDEHDGPVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.063 | 0.000 | 0.933 | 0.004 | ||
| 5 spectra, NLSPGAVESDVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.055 | 0.000 | 0.928 | 0.017 | ||
| 2 spectra, MHSLLIK | 0.000 | 0.040 | 0.000 | 0.000 | 0.255 | 0.000 | 0.705 | 0.000 | ||
| 2 spectra, TTYQALPCLPSMYSYPNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.888 | 0.112 | ||
| 2 spectra, TALNLFFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.039 | 0.000 | 0.926 | 0.035 | ||
| 3 spectra, GIDFHK | 0.000 | 0.000 | 0.052 | 0.160 | 0.000 | 0.000 | 0.788 | 0.000 | ||
| 1 spectrum, CPLSGACYSPEFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.817 | 0.183 | ||
| 1 spectrum, IQVPNCDEIFYAGTGNLLLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.833 | 0.167 | ||
| 2 spectra, QLDFNSSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.952 | 0.048 | ||
| 4 spectra, YAVTTGDHGIIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.177 | 0.000 | 0.823 | 0.000 | ||
| 6 spectra, TAATFAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.127 | 0.000 | 0.873 | 0.000 | ||
| 2 spectra, VWDMSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.075 | 0.000 | 0.925 | 0.000 | ||
| 3 spectra, TGVQTFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.137 | 0.000 | 0.863 | 0.000 | ||
| 4 spectra, TLDLPIYVTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.003 | 0.000 | 0.959 | 0.037 | ||
| 2 spectra, LLHDQVGVVQFGPYK | 0.000 | 0.035 | 0.000 | 0.071 | 0.000 | 0.000 | 0.894 | 0.000 | ||
| 2 spectra, VLTIDPTEFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.054 | 0.000 | 0.901 | 0.045 | ||
| 1 spectrum, QQPLFVSGGDDYK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.947 | 0.053 | ||
| 1 spectrum, EYIVGLCMEIER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.827 | 0.173 | ||
| 9 spectra, SSGLTAVWVAR | 0.000 | 0.009 | 0.000 | 0.000 | 0.168 | 0.000 | 0.823 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
81 spectra |
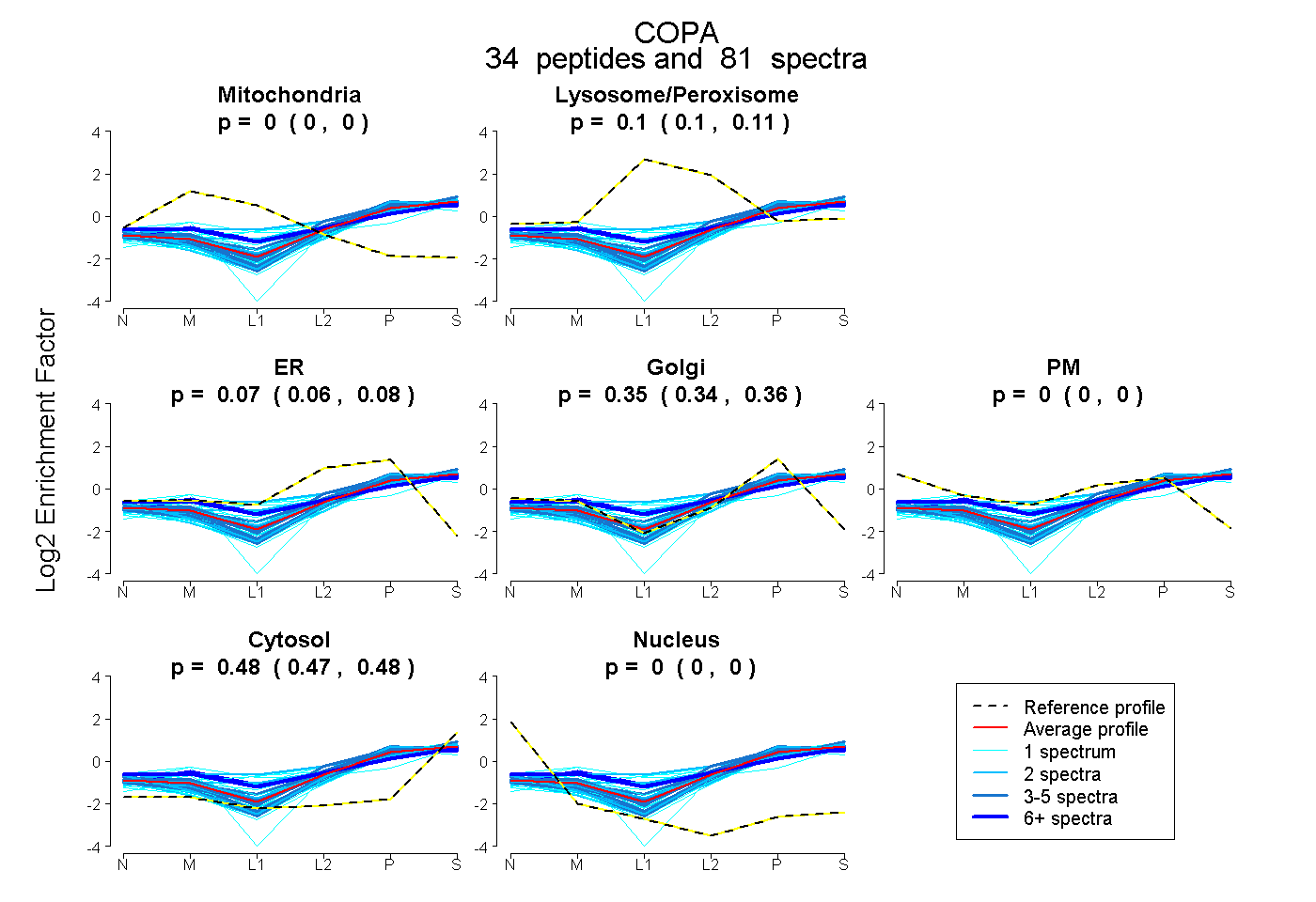 |
0.000 0.000 | 0.000 |
0.104 0.097 | 0.110 |
0.072 0.060 | 0.083 |
0.347 0.336 | 0.355 |
0.000 0.000 | 0.000 |
0.477 0.473 | 0.480 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
146 spectra |
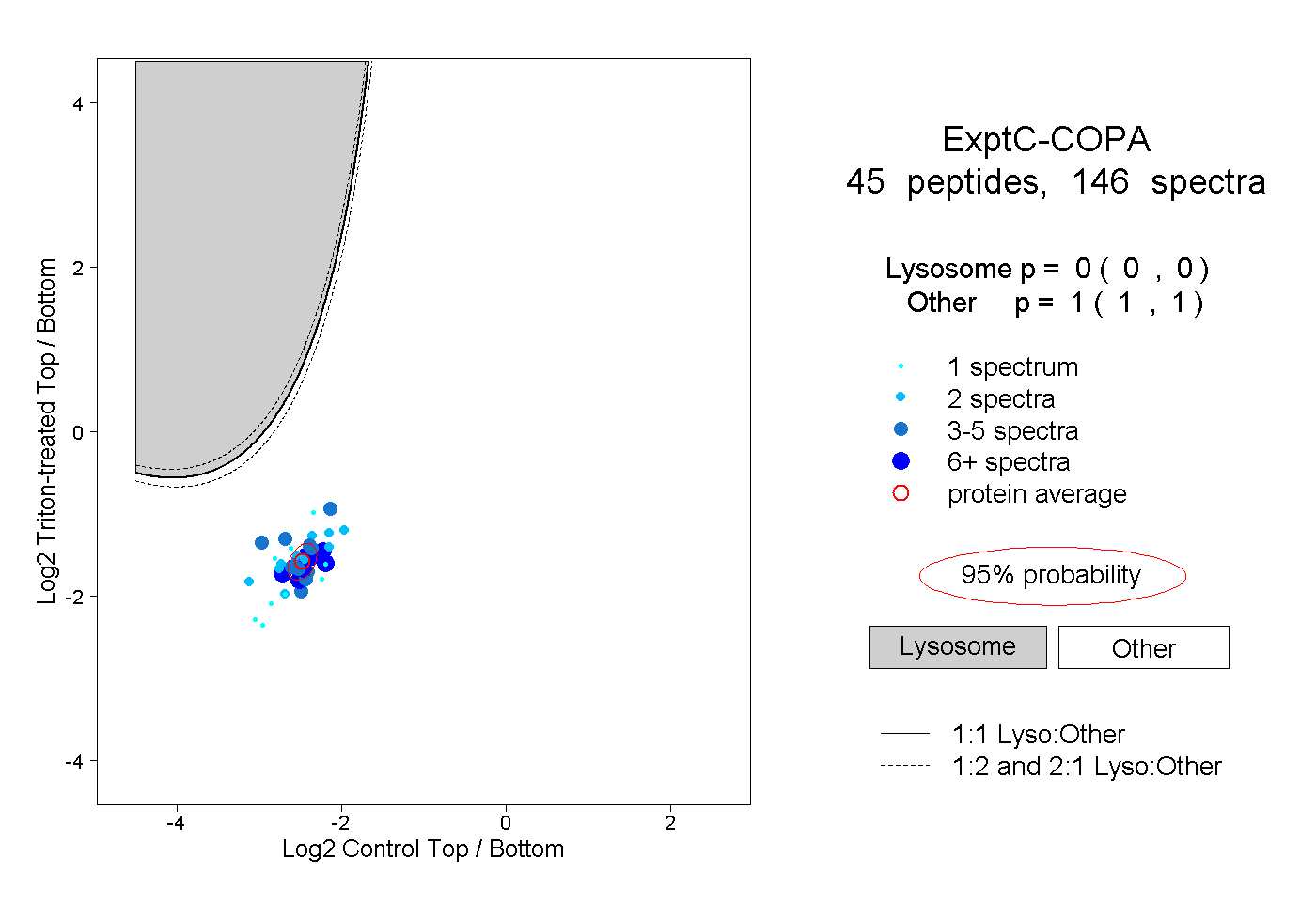 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
15 spectra |
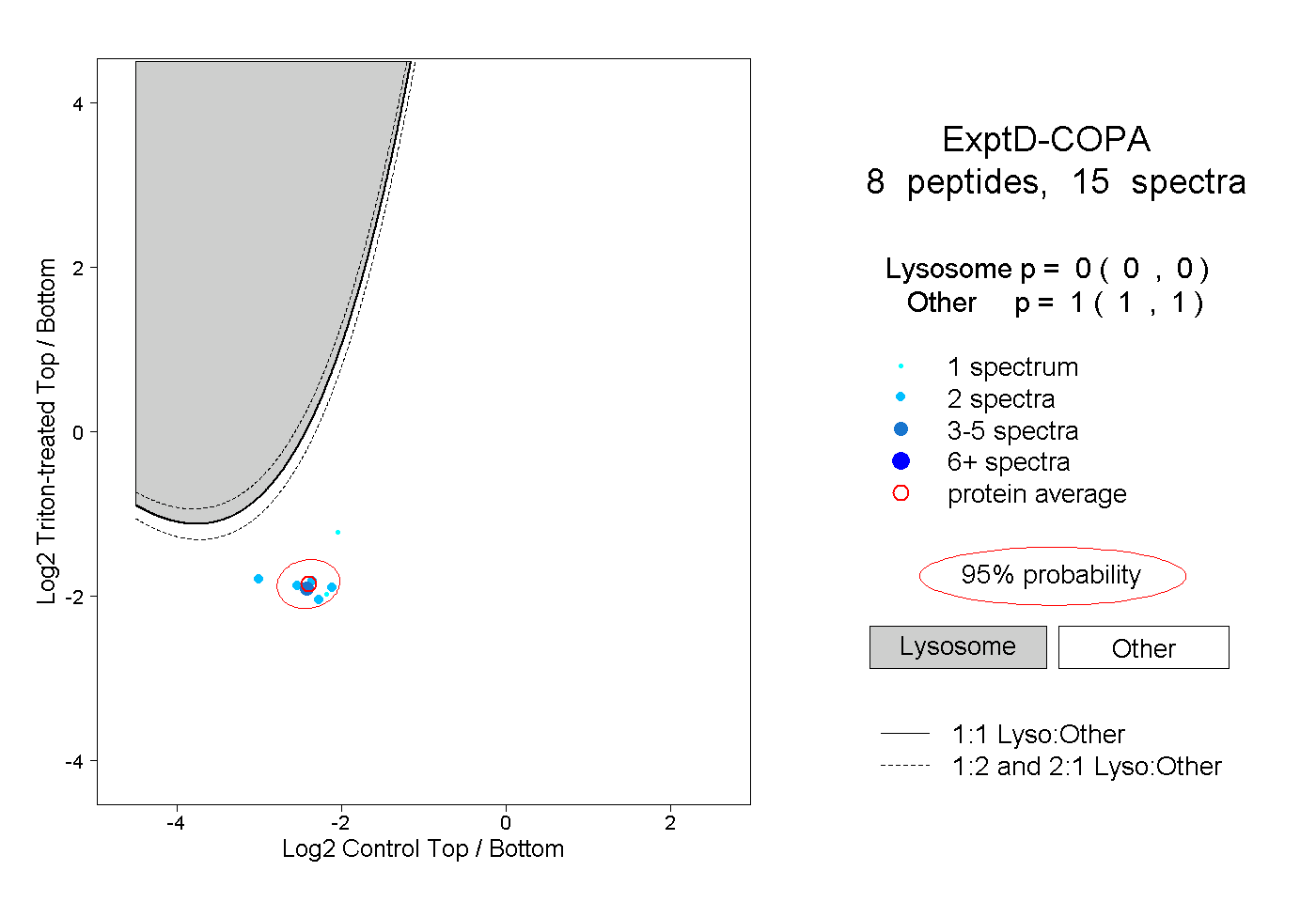 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |