peptides
spectra
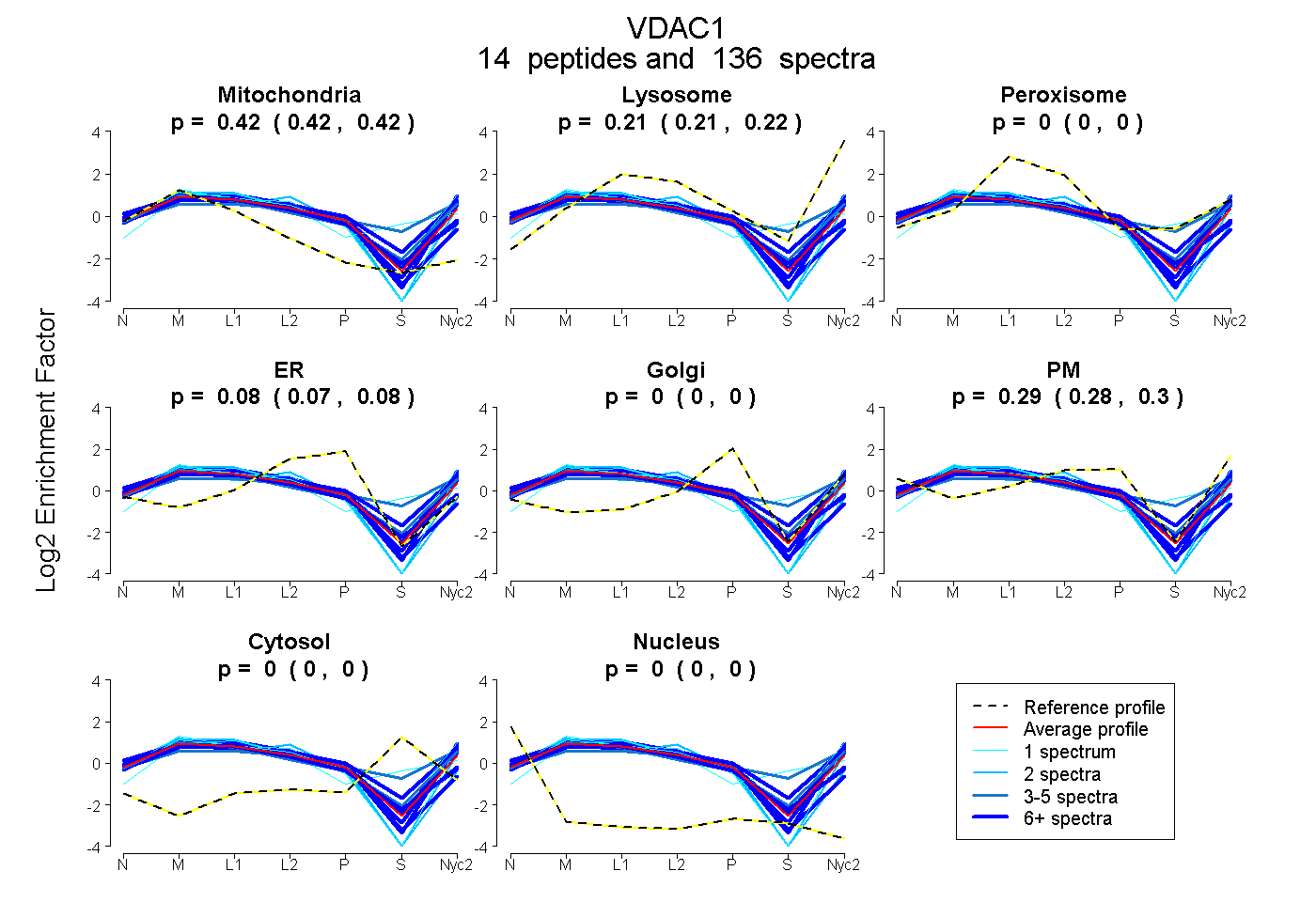
0.419 | 0.424
0.208 | 0.216
0.000 | 0.002
0.070 | 0.083
0.000 | 0.000
0.280 | 0.297
0.000 | 0.000
0.000 | 0.000
peptides
spectra
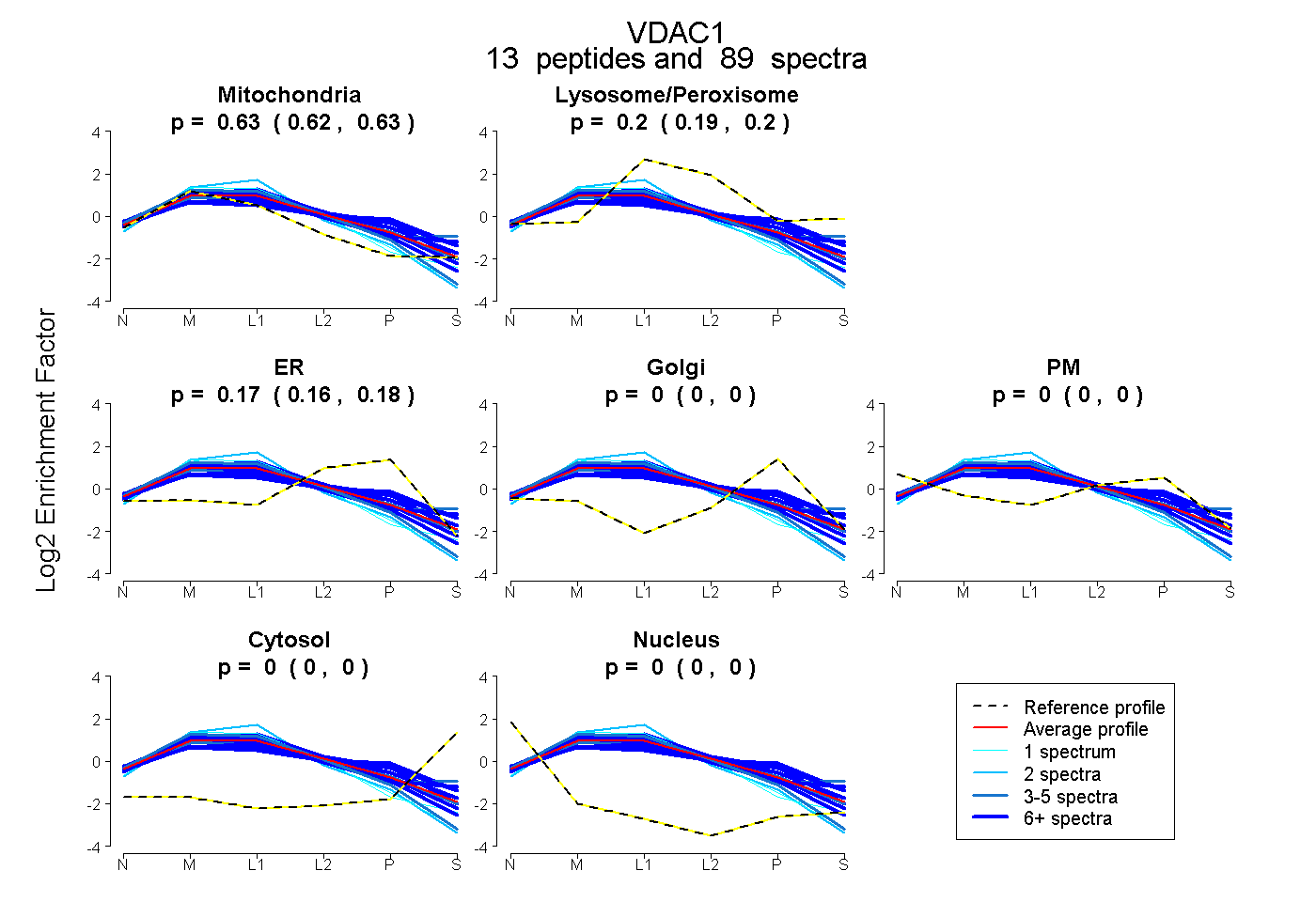
0.625 | 0.633
0.194 | 0.205
0.165 | 0.175
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
136 spectra |
 |
0.422 0.419 | 0.424 |
0.212 0.208 | 0.216 |
0.000 0.000 | 0.002 |
0.077 0.070 | 0.083 |
0.000 0.000 | 0.000 |
0.289 0.280 | 0.297 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
89 spectra |
 |
0.630 0.625 | 0.633 |
0.200 0.194 | 0.205 |
0.171 0.165 | 0.175 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 5 spectra, VNGSLETK | 0.571 | 0.322 | 0.000 | 0.045 | 0.027 | 0.035 | 0.000 | |||
| 1 spectrum, LETAVNLAWTAGNSNTR | 0.874 | 0.000 | 0.126 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, VTQSNFAVGYK | 0.452 | 0.272 | 0.128 | 0.118 | 0.030 | 0.000 | 0.000 | |||
| 6 spectra, LGLGLEFQA | 0.389 | 0.274 | 0.038 | 0.178 | 0.121 | 0.000 | 0.000 | |||
| 6 spectra, WTEYGLTFTEK | 0.637 | 0.282 | 0.000 | 0.081 | 0.000 | 0.000 | 0.000 | |||
| 23 spectra, GYGFGLIK | 0.572 | 0.236 | 0.192 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 10 spectra, LTLSALLDGK | 0.542 | 0.146 | 0.312 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, YQVDPDACFSAK | 0.780 | 0.065 | 0.154 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, AVPPTYADLGK | 0.875 | 0.098 | 0.027 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, VDGSLETK | 0.690 | 0.152 | 0.158 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, NVNAGGHK | 0.643 | 0.163 | 0.161 | 0.000 | 0.034 | 0.000 | 0.000 | |||
| 1 spectrum, TDEFQLHTNVNDGTEFGGSIYQK | 0.834 | 0.166 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, FGIAAK | 0.632 | 0.224 | 0.144 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
742 spectra |
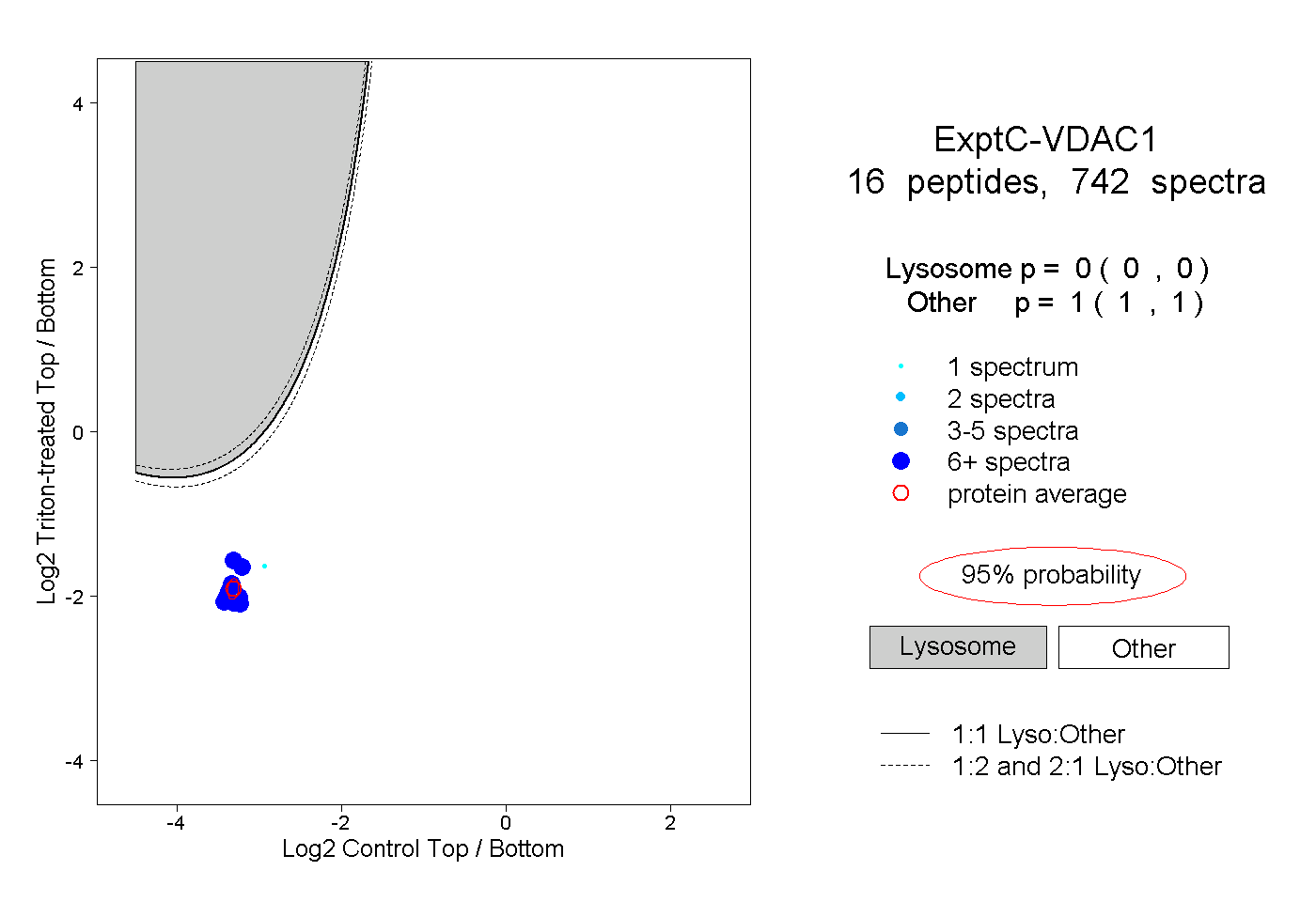 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
61 spectra |
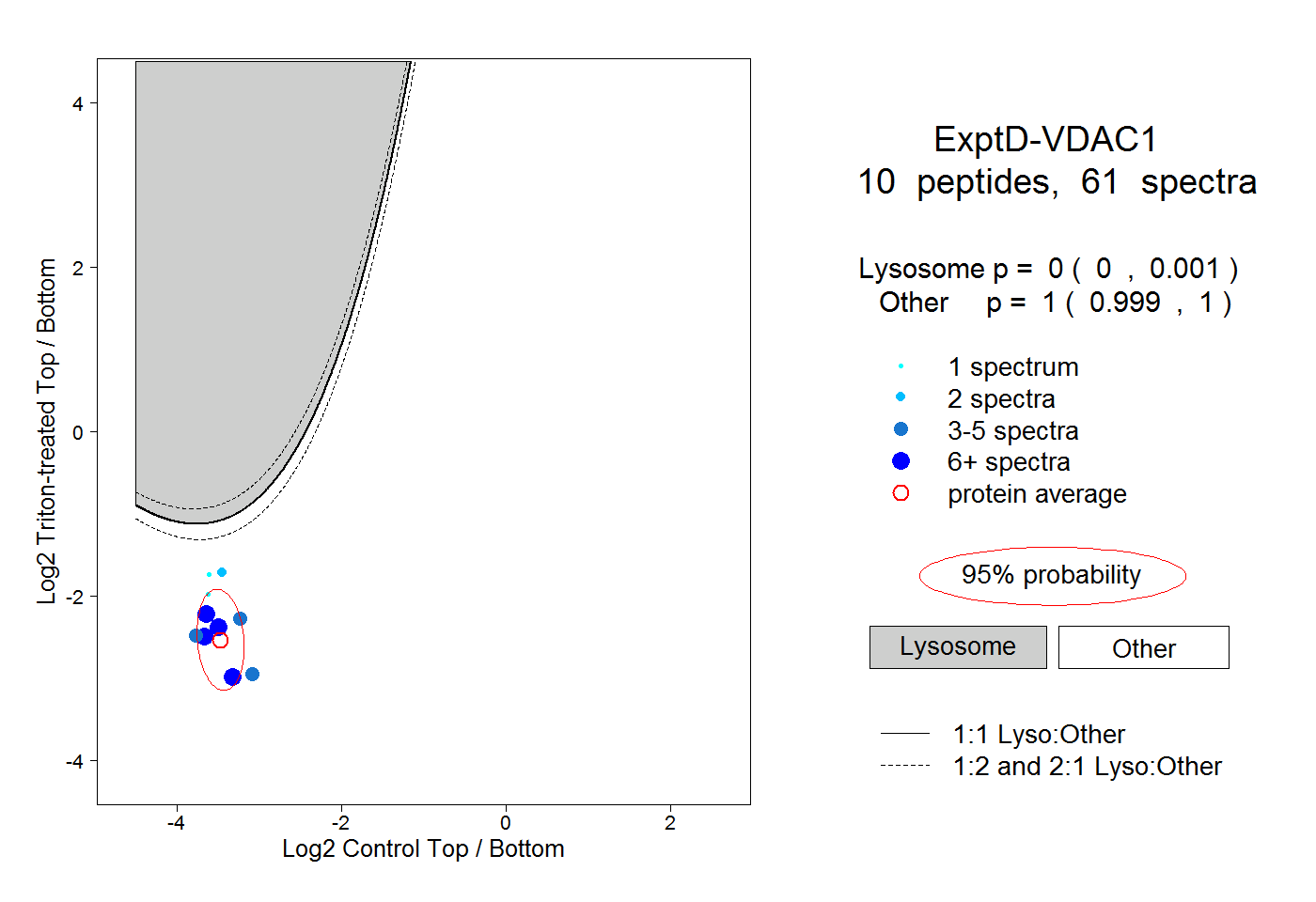 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |