peptides
spectra
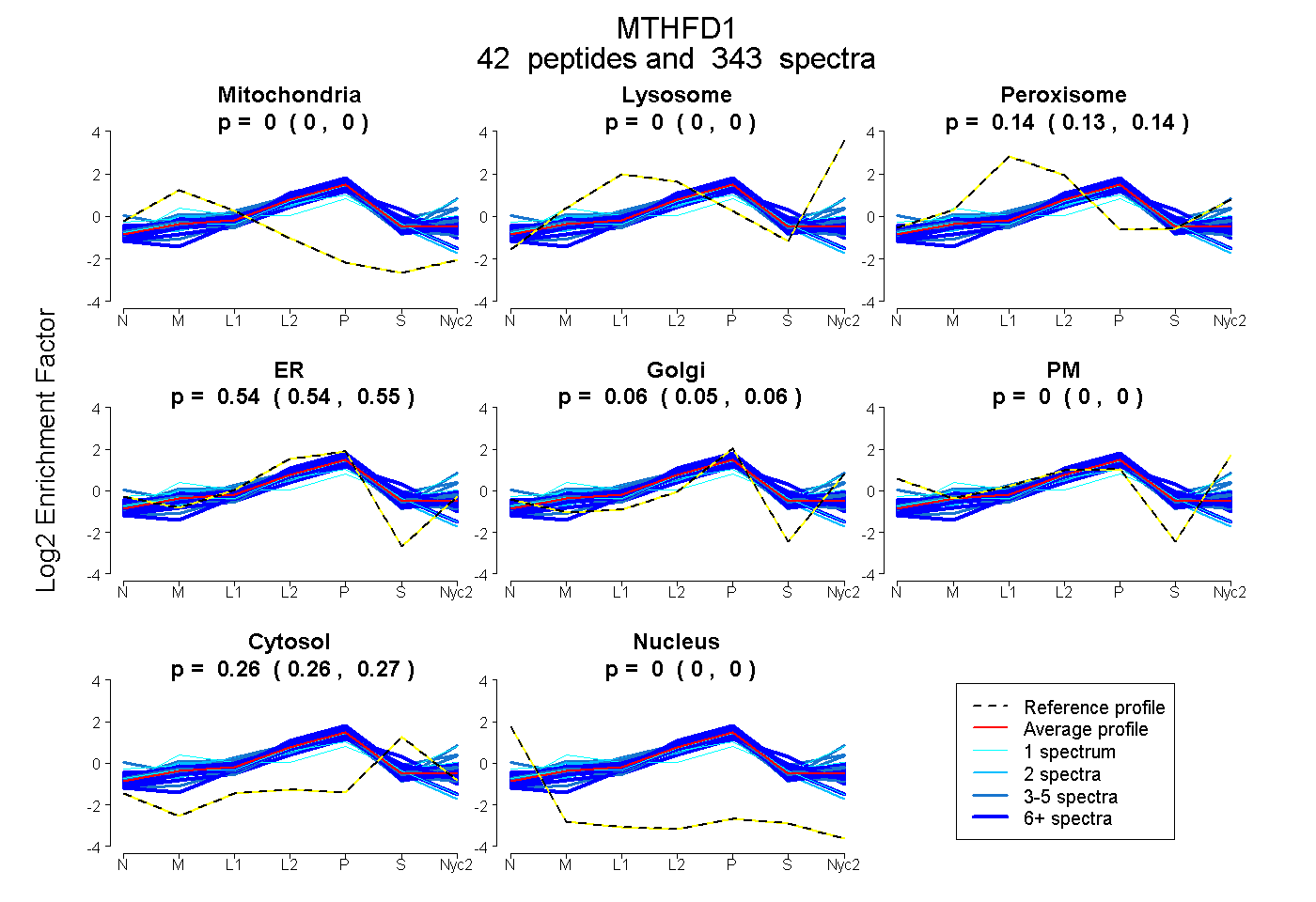
0.000 | 0.000
0.000 | 0.000
0.135 | 0.137
0.539 | 0.545
0.054 | 0.060
0.000 | 0.000
0.264 | 0.266
0.000 | 0.000
peptides
spectra
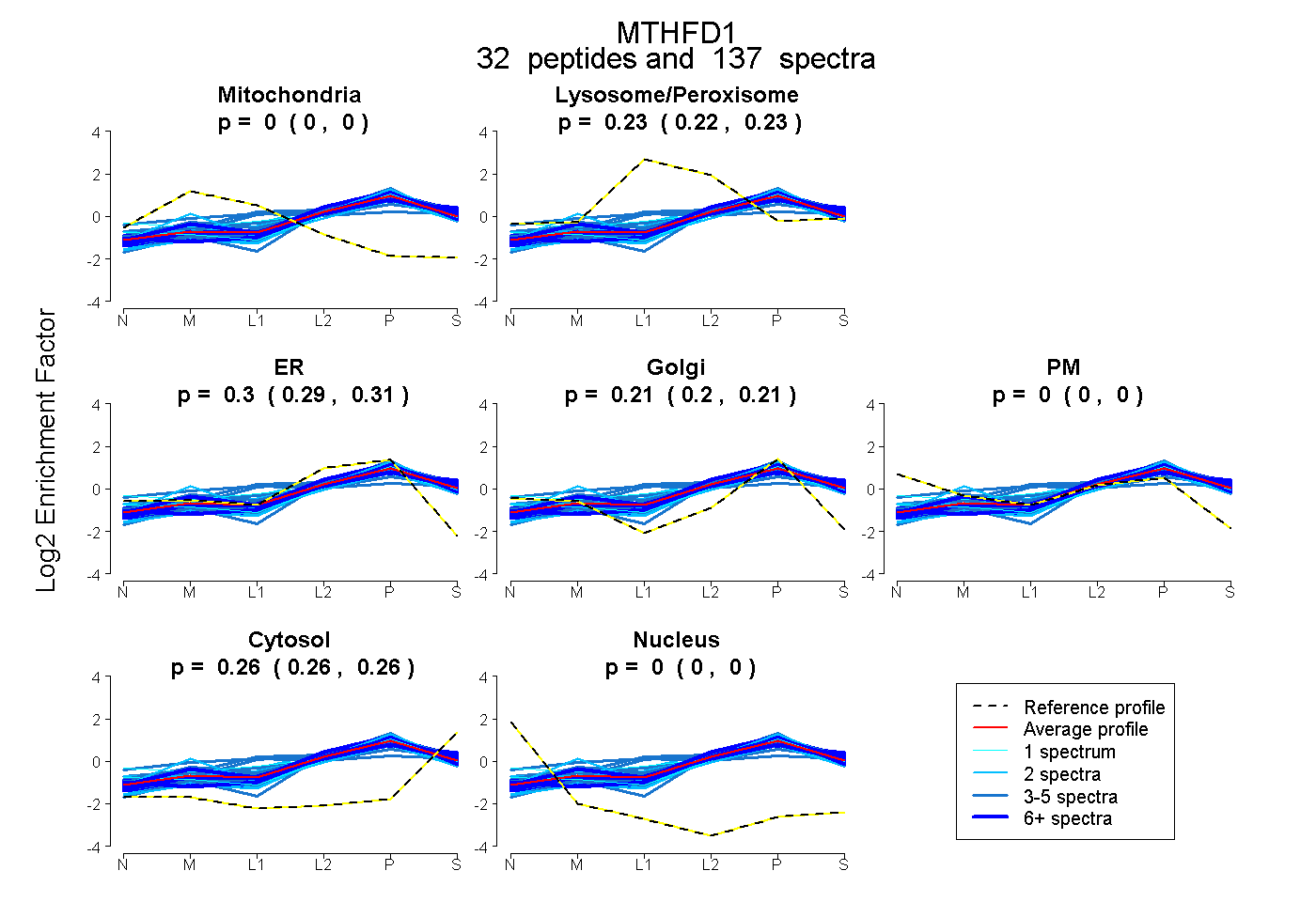
0.000 | 0.000
0.224 | 0.231
0.295 | 0.310
0.200 | 0.212
0.000 | 0.000
0.260 | 0.265
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
343 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.136 0.135 | 0.137 |
0.542 0.539 | 0.545 |
0.057 0.054 | 0.060 |
0.000 0.000 | 0.000 |
0.265 0.264 | 0.266 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
137 spectra |
 |
0.000 0.000 | 0.000 |
0.228 0.224 | 0.231 |
0.303 0.295 | 0.310 |
0.206 0.200 | 0.212 |
0.000 0.000 | 0.000 |
0.263 0.260 | 0.265 |
0.000 0.000 | 0.000 |
| 4 spectra, FSDIQIR | 0.000 | 0.251 | 0.250 | 0.273 | 0.000 | 0.225 | 0.000 | |||
| 2 spectra, TDPAALTDDEINR | 0.000 | 0.137 | 0.481 | 0.076 | 0.000 | 0.305 | 0.000 | |||
| 2 spectra, VVGDVAYDEAK | 0.000 | 0.016 | 0.623 | 0.000 | 0.000 | 0.361 | 0.000 | |||
| 2 spectra, TSTESEVLK | 0.000 | 0.277 | 0.036 | 0.490 | 0.000 | 0.197 | 0.000 | |||
| 3 spectra, GCLELIK | 0.000 | 0.208 | 0.409 | 0.099 | 0.000 | 0.285 | 0.000 | |||
| 4 spectra, HAVVVGR | 0.000 | 0.329 | 0.106 | 0.403 | 0.000 | 0.162 | 0.000 | |||
| 1 spectrum, APAGILNGK | 0.000 | 0.083 | 0.492 | 0.000 | 0.000 | 0.424 | 0.000 | |||
| 9 spectra, MFGVPVVVAMNAFK | 0.000 | 0.196 | 0.430 | 0.000 | 0.000 | 0.374 | 0.000 | |||
| 4 spectra, VLDTNDR | 0.000 | 0.141 | 0.461 | 0.130 | 0.000 | 0.268 | 0.000 | |||
| 2 spectra, ITIGQAPTEK | 0.000 | 0.366 | 0.000 | 0.499 | 0.000 | 0.135 | 0.000 | |||
| 2 spectra, QPSQGPTFGIK | 0.000 | 0.146 | 0.410 | 0.139 | 0.000 | 0.306 | 0.000 | |||
| 2 spectra, AEIYTK | 0.000 | 0.352 | 0.168 | 0.302 | 0.000 | 0.178 | 0.000 | |||
| 5 spectra, GVPTGFVLPIR | 0.000 | 0.125 | 0.498 | 0.078 | 0.000 | 0.299 | 0.000 | |||
| 1 spectrum, WTIQYNK | 0.000 | 0.203 | 0.185 | 0.374 | 0.000 | 0.238 | 0.000 | |||
| 14 spectra, VLLSALDR | 0.000 | 0.152 | 0.541 | 0.042 | 0.000 | 0.266 | 0.000 | |||
| 3 spectra, CTHWAEGGQGALALAQAVQR | 0.004 | 0.471 | 0.000 | 0.314 | 0.000 | 0.210 | 0.000 | |||
| 5 spectra, EIGLLTEEVELYGETK | 0.000 | 0.401 | 0.000 | 0.368 | 0.000 | 0.231 | 0.000 | |||
| 6 spectra, YSGLQPHVVVLVATVR | 0.000 | 0.278 | 0.165 | 0.300 | 0.000 | 0.257 | 0.000 | |||
| 5 spectra, LVPSVNGVR | 0.000 | 0.043 | 0.641 | 0.014 | 0.000 | 0.302 | 0.000 | |||
| 8 spectra, ETGVQIAGR | 0.000 | 0.082 | 0.530 | 0.000 | 0.000 | 0.388 | 0.000 | |||
| 5 spectra, MVVASSK | 0.000 | 0.004 | 0.591 | 0.000 | 0.000 | 0.404 | 0.000 | |||
| 3 spectra, QIENAR | 0.000 | 0.447 | 0.000 | 0.431 | 0.000 | 0.122 | 0.000 | |||
| 3 spectra, IFHELTQTDK | 0.000 | 0.480 | 0.000 | 0.387 | 0.000 | 0.133 | 0.000 | |||
| 1 spectrum, TPVPSDIAISR | 0.000 | 0.408 | 0.000 | 0.465 | 0.000 | 0.127 | 0.000 | |||
| 3 spectra, LAVNLAR | 0.000 | 0.112 | 0.555 | 0.010 | 0.000 | 0.323 | 0.000 | |||
| 8 spectra, VVSAQIR | 0.000 | 0.137 | 0.451 | 0.081 | 0.000 | 0.330 | 0.000 | |||
| 5 spectra, AYTEEDLDLVEK | 0.000 | 0.358 | 0.030 | 0.407 | 0.000 | 0.205 | 0.000 | |||
| 5 spectra, AAQEIGIK | 0.000 | 0.277 | 0.226 | 0.284 | 0.000 | 0.214 | 0.000 | |||
| 8 spectra, TDTDAELDLIGR | 0.000 | 0.100 | 0.571 | 0.019 | 0.000 | 0.311 | 0.000 | |||
| 2 spectra, GFSNLR | 0.000 | 0.031 | 0.629 | 0.000 | 0.000 | 0.339 | 0.000 | |||
| 6 spectra, QGFGNLPICMAK | 0.000 | 0.271 | 0.224 | 0.208 | 0.000 | 0.297 | 0.000 | |||
| 4 spectra, LDIDPETITWQR | 0.000 | 0.352 | 0.023 | 0.481 | 0.000 | 0.144 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
653 spectra |
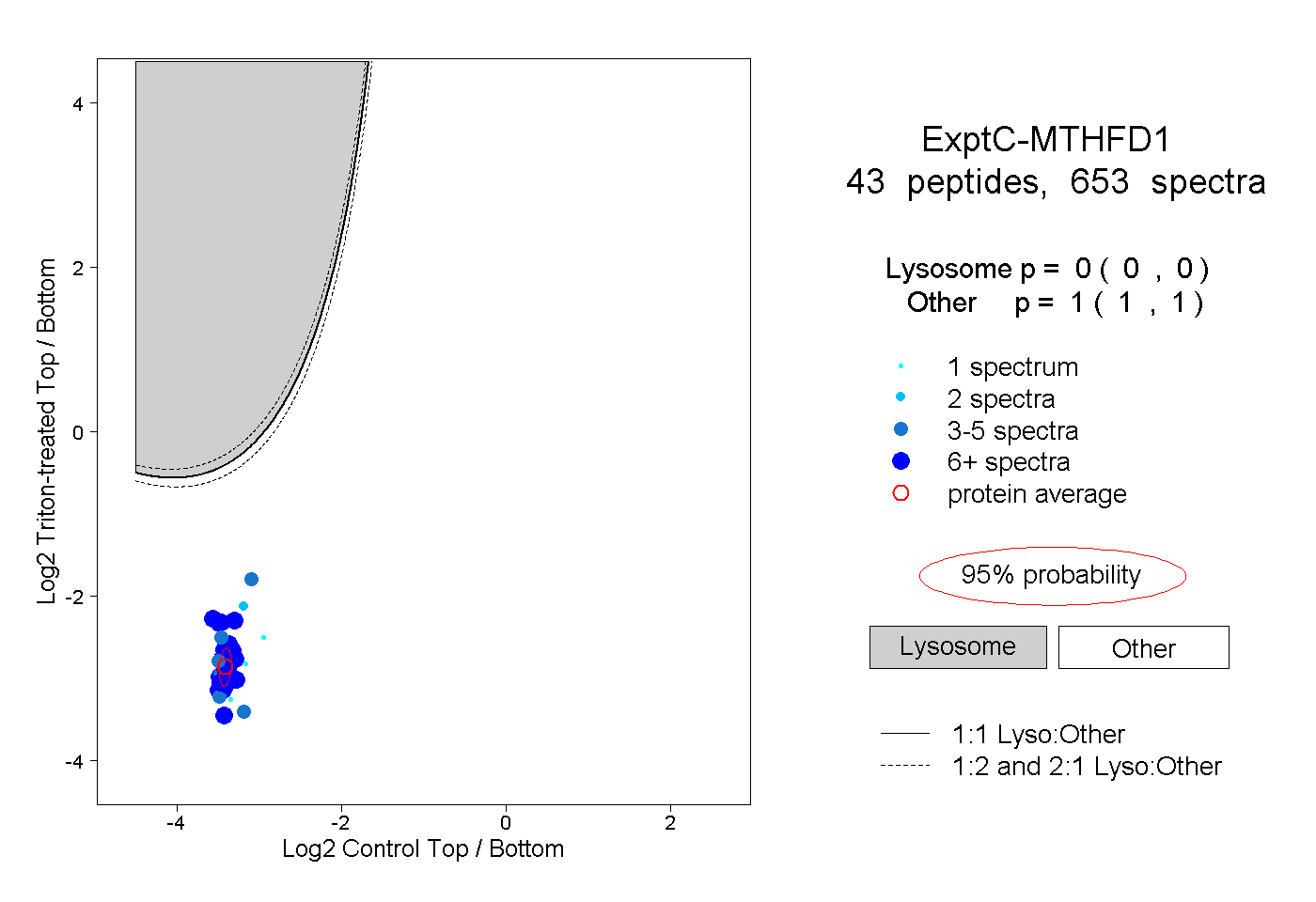 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
70 spectra |
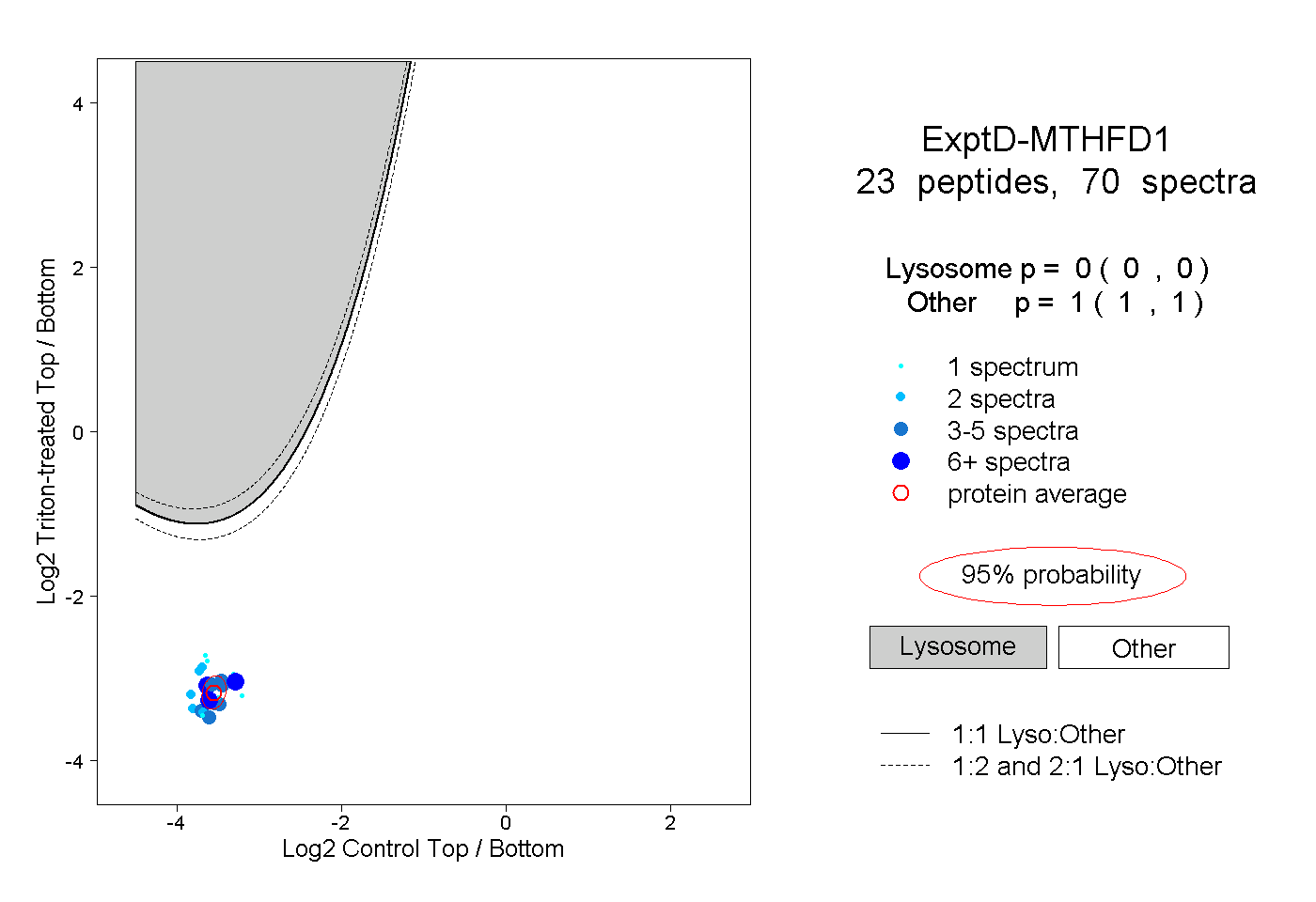 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |