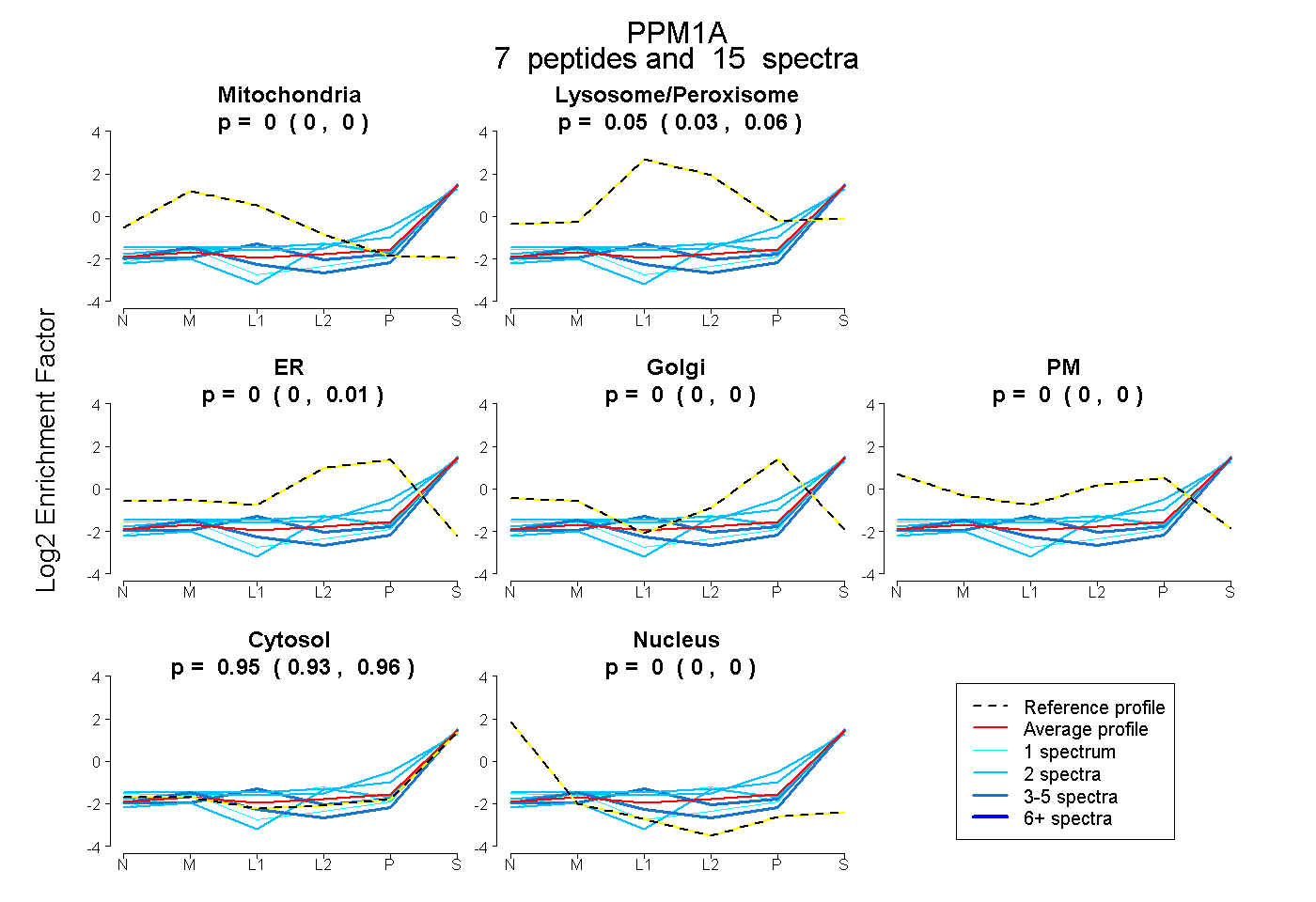
peptides
spectra

0.000 | 0.000
0.007 | 0.029
0.009 | 0.039
0.012 | 0.056
0.000 | 0.038
0.000 | 0.000
0.894 | 0.908
0.000 | 0.000
peptides
spectra
0.000 | 0.000
0.026 | 0.063
0.000 | 0.011
0.000 | 0.000
0.000 | 0.000
0.933 | 0.965
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
61 spectra |
 |
0.000 0.000 | 0.000 |
0.021 0.007 | 0.029 |
0.022 0.009 | 0.039 |
0.042 0.012 | 0.056 |
0.012 0.000 | 0.038 |
0.000 0.000 | 0.000 |
0.902 0.894 | 0.908 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
15 spectra |
 |
0.000 0.000 | 0.000 |
0.049 0.026 | 0.063 |
0.000 0.000 | 0.011 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.951 0.933 | 0.965 |
0.000 0.000 | 0.000 |
| 2 spectra, TGFLEIDEHMR | 0.000 | 0.107 | 0.000 | 0.127 | 0.000 | 0.767 | 0.000 | |||
| 1 spectrum, GSAGAPSVENVK | 0.000 | 0.135 | 0.000 | 0.000 | 0.000 | 0.865 | 0.000 | |||
| 1 spectrum, GPTEQLVSPEPEVHDIER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, QGEGVPDLVHVMR | 0.000 | 0.153 | 0.000 | 0.000 | 0.000 | 0.847 | 0.000 | |||
| 2 spectra, NVIEAVYNR | 0.000 | 0.000 | 0.000 | 0.080 | 0.000 | 0.920 | 0.000 | |||
| 4 spectra, IQNAGGSVMIQR | 0.000 | 0.076 | 0.000 | 0.000 | 0.000 | 0.924 | 0.000 | |||
| 3 spectra, VNGSLAVSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
24 spectra |
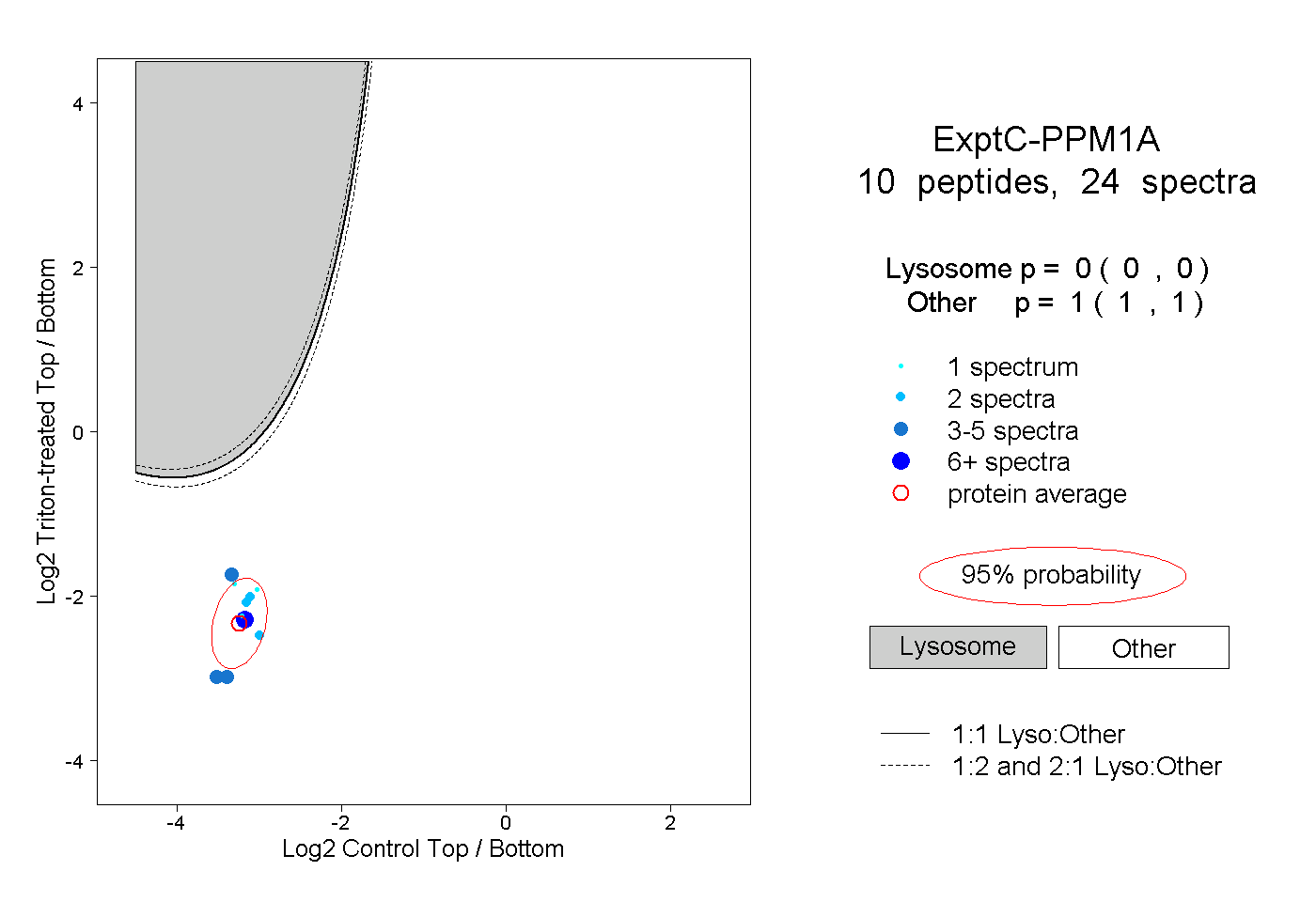 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
2 spectra |
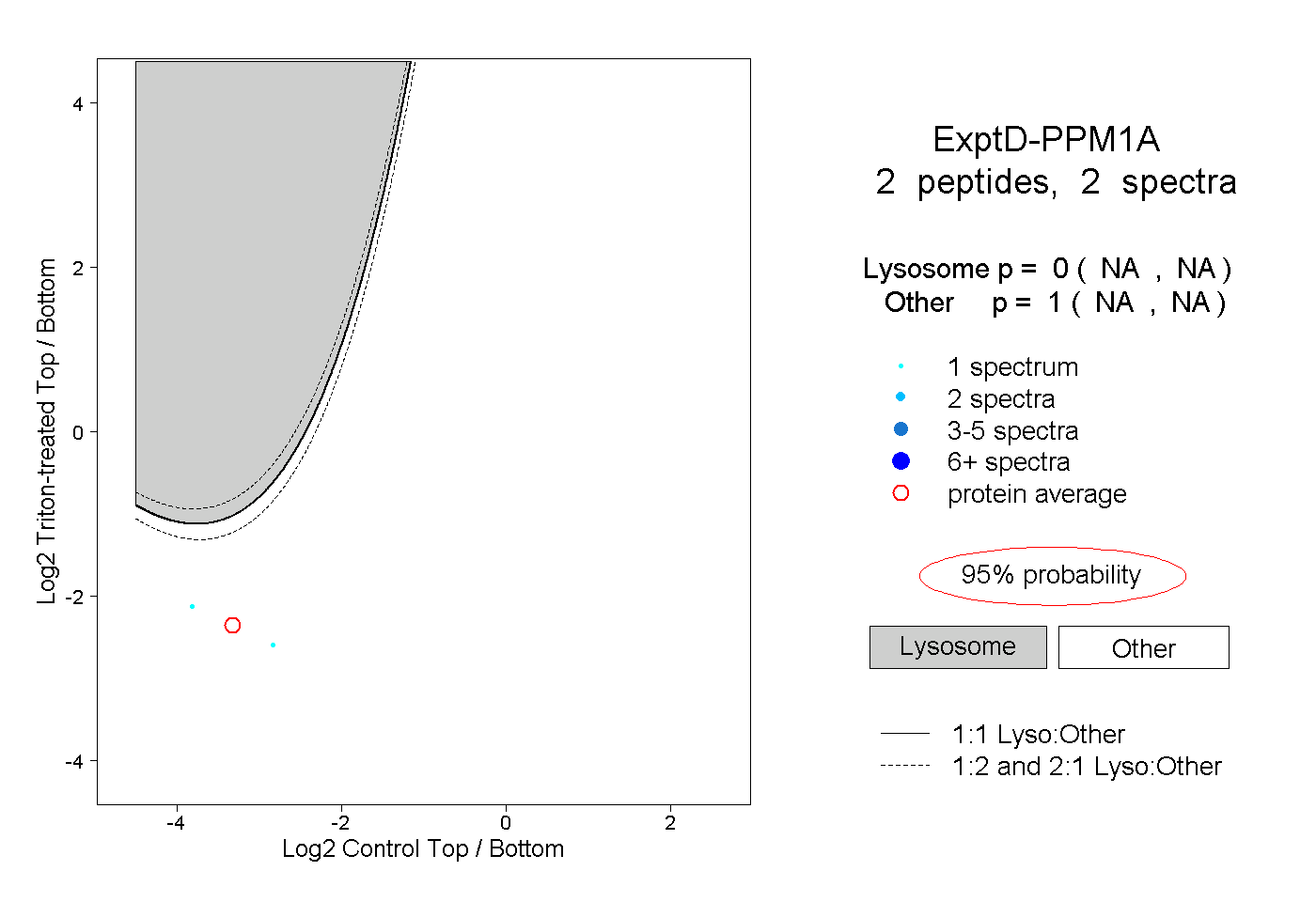 |
0.000 NA | NA |
1.000 NA | NA |