peptides
spectra
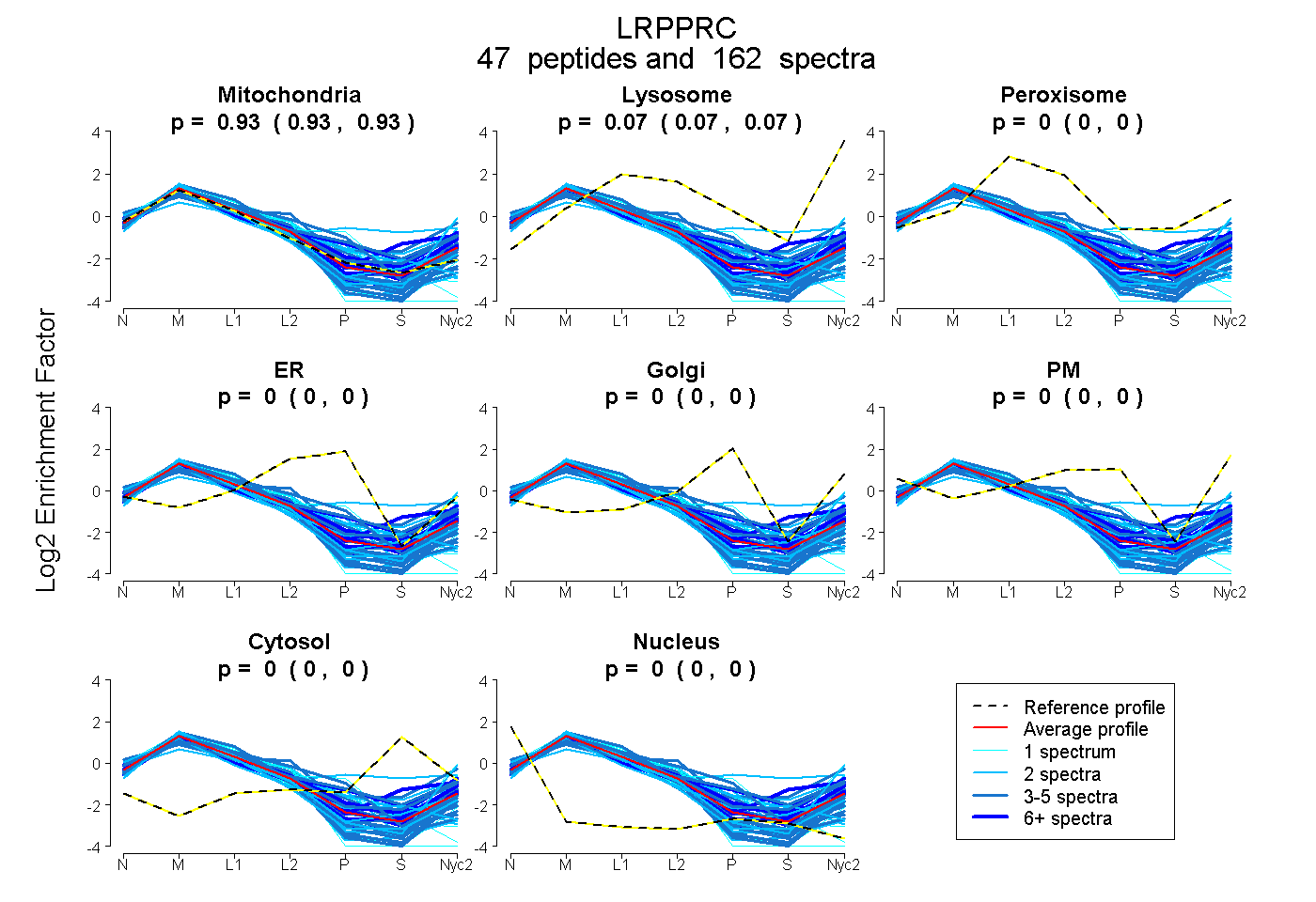
0.930 | 0.934
0.066 | 0.069
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
162 spectra |
 |
0.932 0.930 | 0.934 |
0.068 0.066 | 0.069 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 11 spectra, MVFINNIALAQMK | 0.855 | 0.013 | 0.052 | 0.000 | 0.000 | 0.080 | 0.000 | 0.000 | ||
| 8 spectra, LDNSVR | 0.732 | 0.114 | 0.000 | 0.000 | 0.000 | 0.000 | 0.154 | 0.000 | ||
| 3 spectra, SGSPGSNQALLLLR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 9 spectra, QYFHQLR | 0.728 | 0.078 | 0.007 | 0.000 | 0.004 | 0.140 | 0.042 | 0.000 | ||
| 4 spectra, DAYNIFLK | 0.933 | 0.000 | 0.000 | 0.067 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, MLLSDCR | 0.985 | 0.013 | 0.001 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, ADAVWNK | 0.708 | 0.121 | 0.051 | 0.000 | 0.000 | 0.064 | 0.056 | 0.000 | ||
| 4 spectra, SGSQFDWALMR | 0.914 | 0.086 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, LFECDR | 0.776 | 0.174 | 0.000 | 0.000 | 0.029 | 0.000 | 0.021 | 0.000 | ||
| 1 spectrum, AGYPQYVSEILEK | 0.965 | 0.000 | 0.035 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, LIAAYCSVGDIEGASK | 0.824 | 0.000 | 0.000 | 0.176 | 0.000 | 0.000 | 0.000 | 0.001 | ||
| 7 spectra, MQEENLIPR | 0.815 | 0.178 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.007 | ||
| 2 spectra, DEGFPIR | 0.750 | 0.051 | 0.000 | 0.000 | 0.000 | 0.199 | 0.000 | 0.000 | ||
| 2 spectra, LQQLGTVYDVSHYNALLK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, VALETLK | 0.960 | 0.034 | 0.000 | 0.000 | 0.000 | 0.000 | 0.006 | 0.000 | ||
| 2 spectra, CIANNQVETLEK | 0.997 | 0.003 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, LLAGILK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, DETSSSFGSFFLR | 0.939 | 0.059 | 0.000 | 0.000 | 0.002 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, HDNAEDALNLK | 0.935 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.065 | ||
| 5 spectra, VIEEQMEPALEK | 0.789 | 0.154 | 0.022 | 0.000 | 0.000 | 0.000 | 0.000 | 0.035 | ||
| 3 spectra, TLLELIPELR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, LIQALALQGDVK | 0.915 | 0.085 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, LQWFCDR | 0.999 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.001 | ||
| 4 spectra, ISGDWQR | 0.889 | 0.111 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, IHDVLCK | 0.763 | 0.237 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, LDDLFLK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, VFESTCR | 0.900 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.031 | 0.069 | ||
| 3 spectra, QAGIEPGPDTYLALLNAHAEK | 0.966 | 0.034 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, IIETPGIR | 0.913 | 0.087 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, VYLQNEYR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, DLPITEAVFSALVTGHAR | 0.848 | 0.000 | 0.026 | 0.114 | 0.000 | 0.000 | 0.000 | 0.013 | ||
| 3 spectra, SCGSLLPELSLAER | 0.970 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.030 | ||
| 2 spectra, AALQENK | 0.440 | 0.060 | 0.135 | 0.000 | 0.157 | 0.000 | 0.209 | 0.000 | ||
| 8 spectra, ILGFMK | 0.962 | 0.038 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, HCVTMDTPAEK | 0.974 | 0.000 | 0.000 | 0.026 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, VYSCSMK | 0.825 | 0.175 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, LVELTEK | 0.991 | 0.009 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, DLPEEPAPVR | 0.884 | 0.000 | 0.053 | 0.014 | 0.000 | 0.000 | 0.026 | 0.022 | ||
| 3 spectra, LSIMSER | 0.956 | 0.044 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, SIPDAMNLILLLVTEK | 0.967 | 0.033 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, YVALVK | 0.737 | 0.025 | 0.001 | 0.238 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, THYFWPLLVGHQK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, STTFAQAEVR | 0.910 | 0.090 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, GSLILGFR | 0.932 | 0.068 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, SMNIDLWSK | 0.708 | 0.141 | 0.000 | 0.000 | 0.106 | 0.000 | 0.045 | 0.000 | ||
| 5 spectra, AGDMENAENILTVMK | 0.661 | 0.260 | 0.000 | 0.000 | 0.000 | 0.000 | 0.079 | 0.000 | ||
| 7 spectra, MEGANIQPNR | 0.926 | 0.074 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
59 spectra |
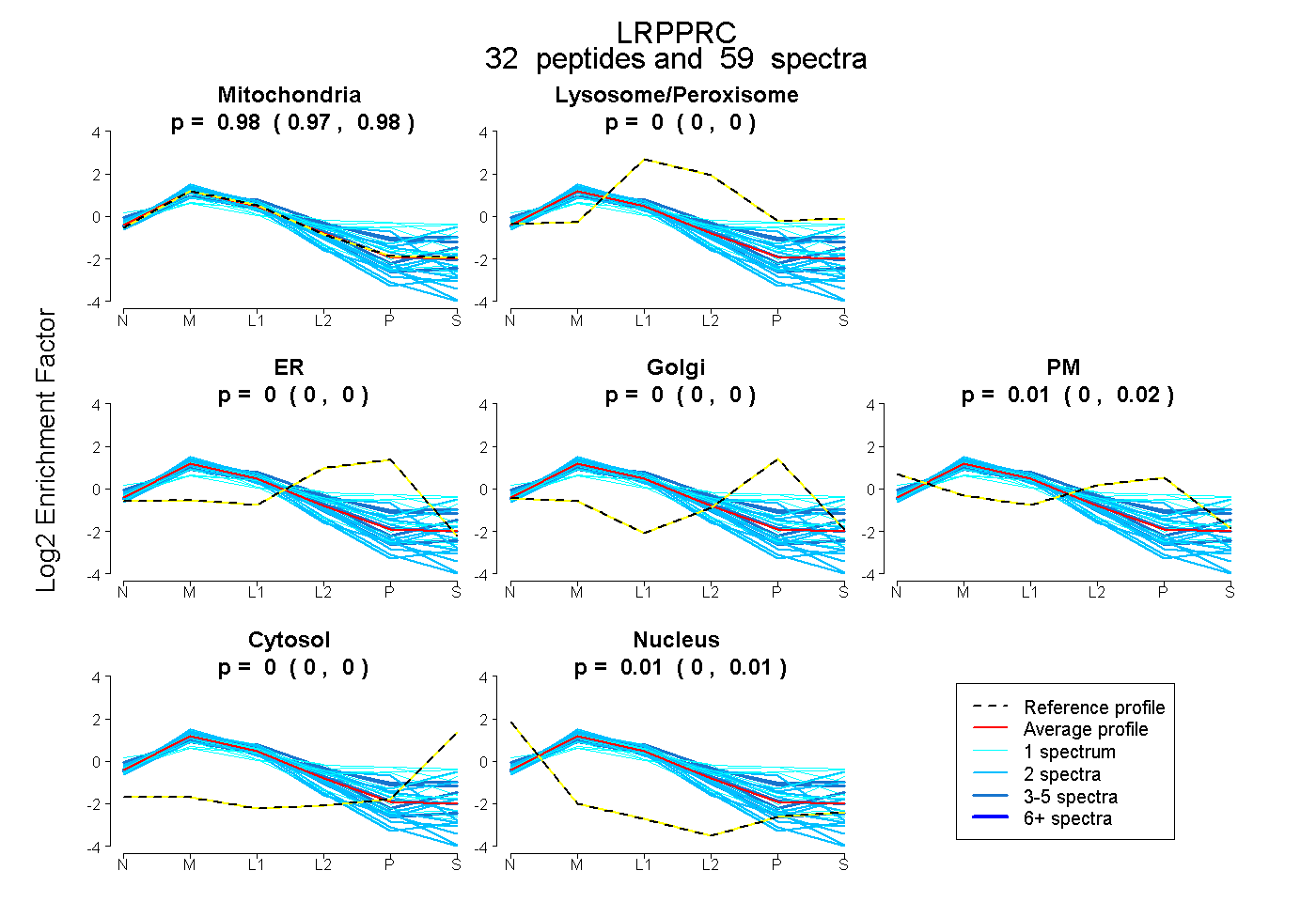 |
0.979 0.973 | 0.985 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.012 0.003 | 0.020 |
0.000 0.000 | 0.000 |
0.009 0.005 | 0.012 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
642 spectra |
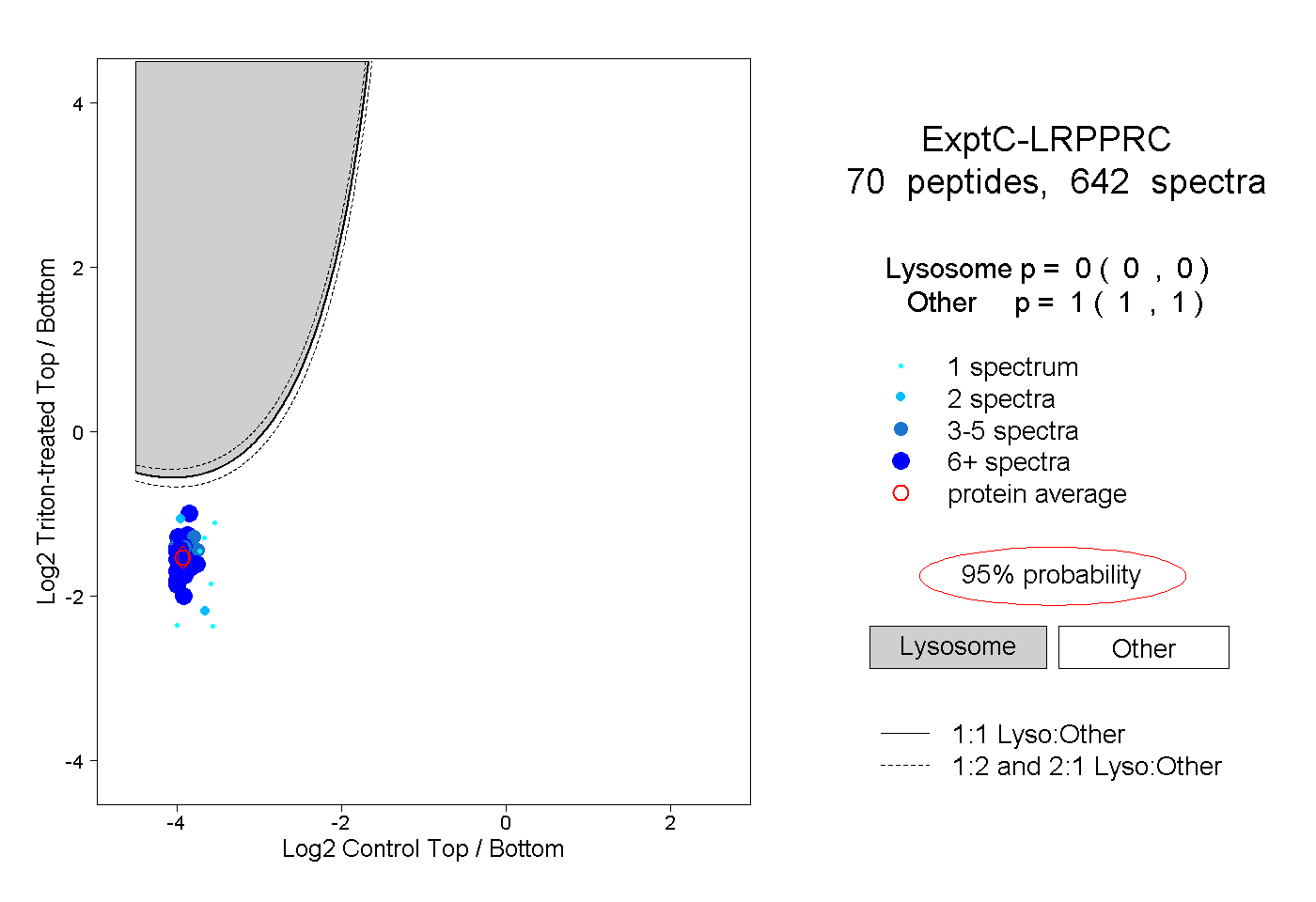 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
68 spectra |
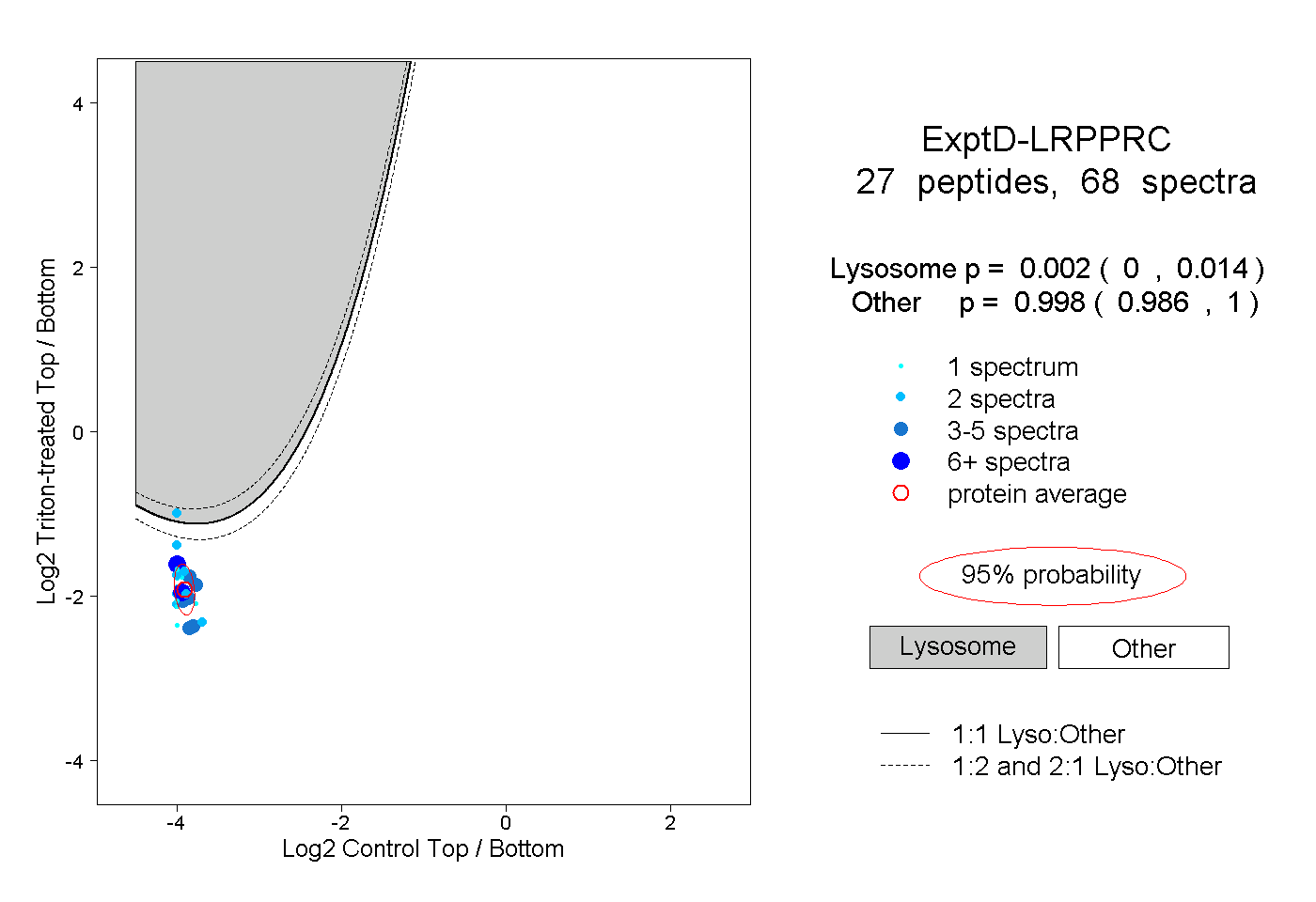 |
0.002 0.000 | 0.014 |
0.998 0.986 | 1.000 |