peptides
spectra
0.016 | 0.021
0.000 | 0.000
0.000 | 0.000
0.036 | 0.044
0.025 | 0.036
0.715 | 0.723
0.008 | 0.017
0.175 | 0.179
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
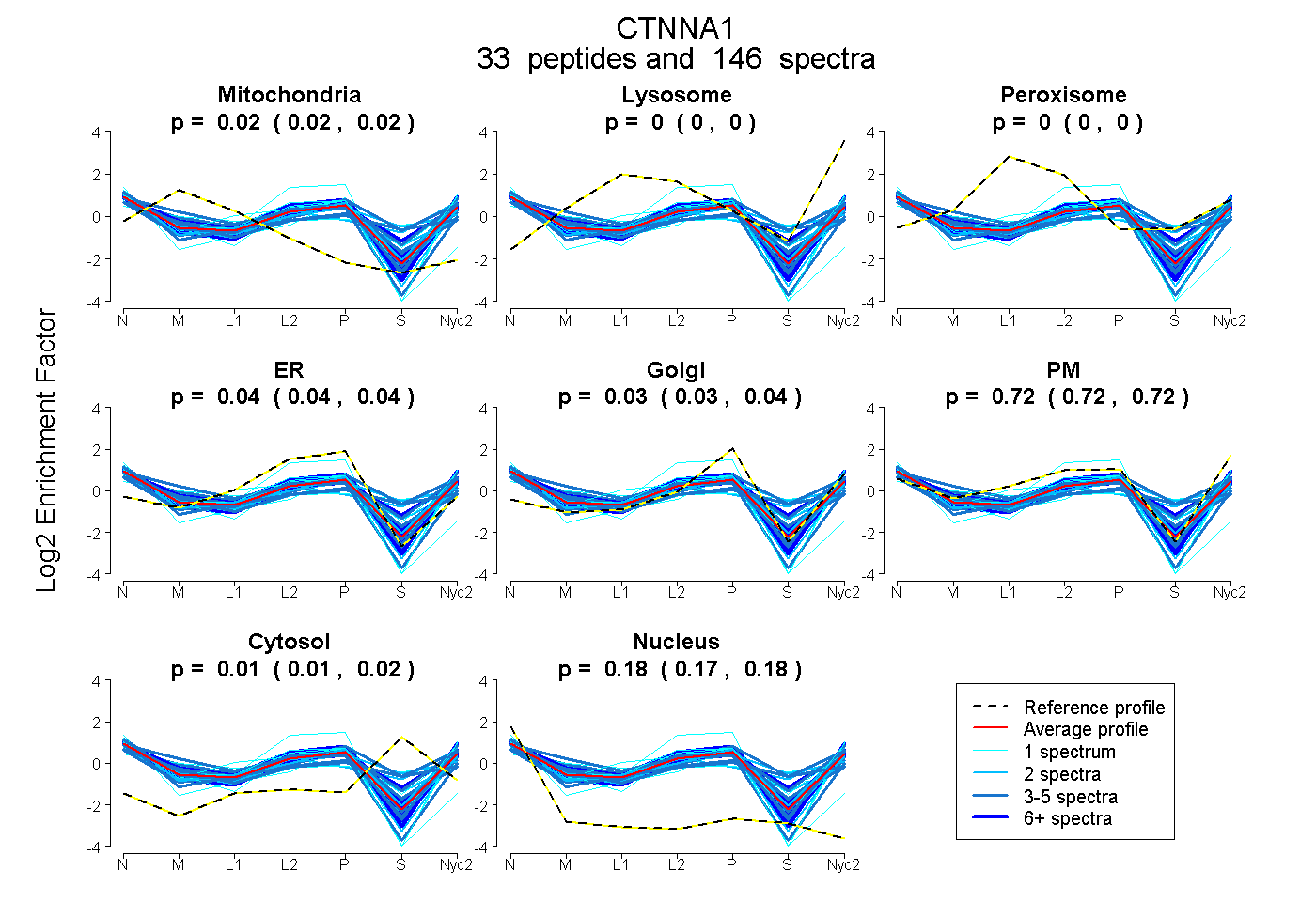
| Expt A |
peptides |
146 spectra |
 |
0.019 0.016 | 0.021 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.040 0.036 | 0.044 |
0.031 0.025 | 0.036 |
0.720 0.715 | 0.723 |
0.013 0.008 | 0.017 |
0.177 0.175 | 0.179 |
| 5 spectra, TLAVER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.710 | 0.182 | 0.108 | ||
| 2 spectra, ASYVASTK | 0.149 | 0.000 | 0.000 | 0.000 | 0.015 | 0.553 | 0.154 | 0.129 | ||
| 7 spectra, IAEAGSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.672 | 0.206 | 0.122 | ||
| 1 spectrum, HVNPVQALSEFK | 0.000 | 0.000 | 0.000 | 0.597 | 0.000 | 0.041 | 0.000 | 0.362 | ||
| 5 spectra, QGDLMK | 0.019 | 0.000 | 0.000 | 0.000 | 0.055 | 0.784 | 0.002 | 0.140 | ||
| 5 spectra, WDDSGNDIIVLAK | 0.112 | 0.000 | 0.000 | 0.000 | 0.000 | 0.504 | 0.314 | 0.070 | ||
| 1 spectrum, TSVQTEDDQLIAGQSAR | 0.000 | 0.000 | 0.000 | 0.028 | 0.000 | 0.842 | 0.000 | 0.130 | ||
| 2 spectra, LVYDGIR | 0.000 | 0.000 | 0.000 | 0.065 | 0.023 | 0.697 | 0.000 | 0.215 | ||
| 1 spectrum, EELVAAVDDVR | 0.000 | 0.000 | 0.000 | 0.366 | 0.000 | 0.599 | 0.000 | 0.036 | ||
| 4 spectra, LDAEVSK | 0.000 | 0.000 | 0.000 | 0.002 | 0.063 | 0.607 | 0.317 | 0.012 | ||
| 2 spectra, TAVHTGNINFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.065 | 0.742 | 0.036 | 0.156 | ||
| 2 spectra, CVIALQEK | 0.000 | 0.000 | 0.117 | 0.000 | 0.000 | 0.550 | 0.247 | 0.086 | ||
| 18 spectra, DQMAAAR | 0.000 | 0.000 | 0.000 | 0.039 | 0.054 | 0.736 | 0.032 | 0.139 | ||
| 1 spectrum, IVAECNAVR | 0.205 | 0.000 | 0.085 | 0.000 | 0.000 | 0.399 | 0.311 | 0.000 | ||
| 2 spectra, AVLMIR | 0.050 | 0.000 | 0.000 | 0.096 | 0.051 | 0.638 | 0.000 | 0.165 | ||
| 3 spectra, NTSDVISAAK | 0.226 | 0.000 | 0.000 | 0.146 | 0.000 | 0.535 | 0.000 | 0.094 | ||
| 3 spectra, EYAQVFR | 0.000 | 0.000 | 0.000 | 0.088 | 0.034 | 0.668 | 0.000 | 0.211 | ||
| 5 spectra, VVEDGILK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.797 | 0.000 | 0.203 | ||
| 1 spectrum, NLMNAVVQTVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.094 | 0.650 | 0.132 | 0.124 | ||
| 4 spectra, AIMAQLPQEQK | 0.000 | 0.000 | 0.000 | 0.040 | 0.000 | 0.813 | 0.000 | 0.147 | ||
| 4 spectra, IAEQVASFQEEK | 0.188 | 0.000 | 0.000 | 0.000 | 0.185 | 0.491 | 0.082 | 0.054 | ||
| 5 spectra, DVDGLDR | 0.041 | 0.000 | 0.000 | 0.029 | 0.171 | 0.608 | 0.000 | 0.151 | ||
| 1 spectrum, NAGNEQDLGIQYR | 0.000 | 0.000 | 0.000 | 0.060 | 0.000 | 0.785 | 0.000 | 0.154 | ||
| 4 spectra, LIVQIK | 0.007 | 0.000 | 0.000 | 0.000 | 0.000 | 0.803 | 0.000 | 0.190 | ||
| 1 spectrum, SQGMASLNLPAVSWK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.865 | 0.000 | 0.135 | ||
| 6 spectra, ALLSAVTR | 0.000 | 0.000 | 0.000 | 0.185 | 0.000 | 0.626 | 0.060 | 0.129 | ||
| 2 spectra, VIHVVTSEMDNYEPGVYTEK | 0.000 | 0.000 | 0.000 | 0.069 | 0.000 | 0.713 | 0.000 | 0.218 | ||
| 8 spectra, FRPSLEER | 0.017 | 0.000 | 0.000 | 0.037 | 0.000 | 0.747 | 0.000 | 0.199 | ||
| 6 spectra, LLILADMADVYK | 0.000 | 0.000 | 0.000 | 0.020 | 0.001 | 0.774 | 0.000 | 0.206 | ||
| 3 spectra, SAAGEFADDPCSSVK | 0.174 | 0.000 | 0.000 | 0.043 | 0.045 | 0.498 | 0.123 | 0.118 | ||
| 5 spectra, SDALNSAIDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.839 | 0.000 | 0.161 | ||
| 2 spectra, LAQENMDLFK | 0.000 | 0.000 | 0.000 | 0.042 | 0.000 | 0.552 | 0.344 | 0.063 | ||
| 25 spectra, LLSNTVMPR | 0.022 | 0.000 | 0.000 | 0.004 | 0.000 | 0.851 | 0.000 | 0.124 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
34 spectra |
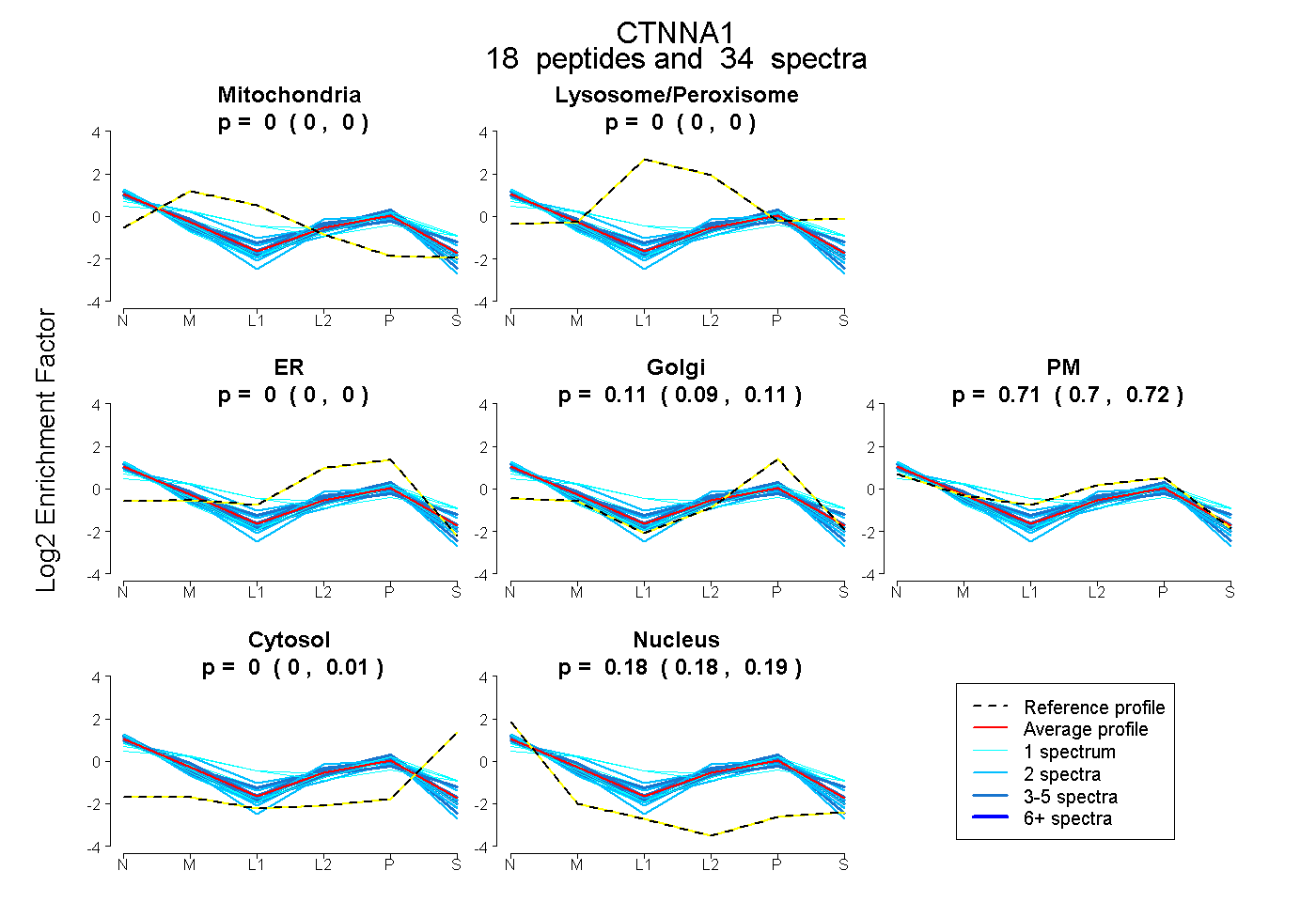 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.106 0.095 | 0.115 |
0.710 0.698 | 0.720 |
0.000 0.000 | 0.006 |
0.184 0.179 | 0.186 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
197 spectra |
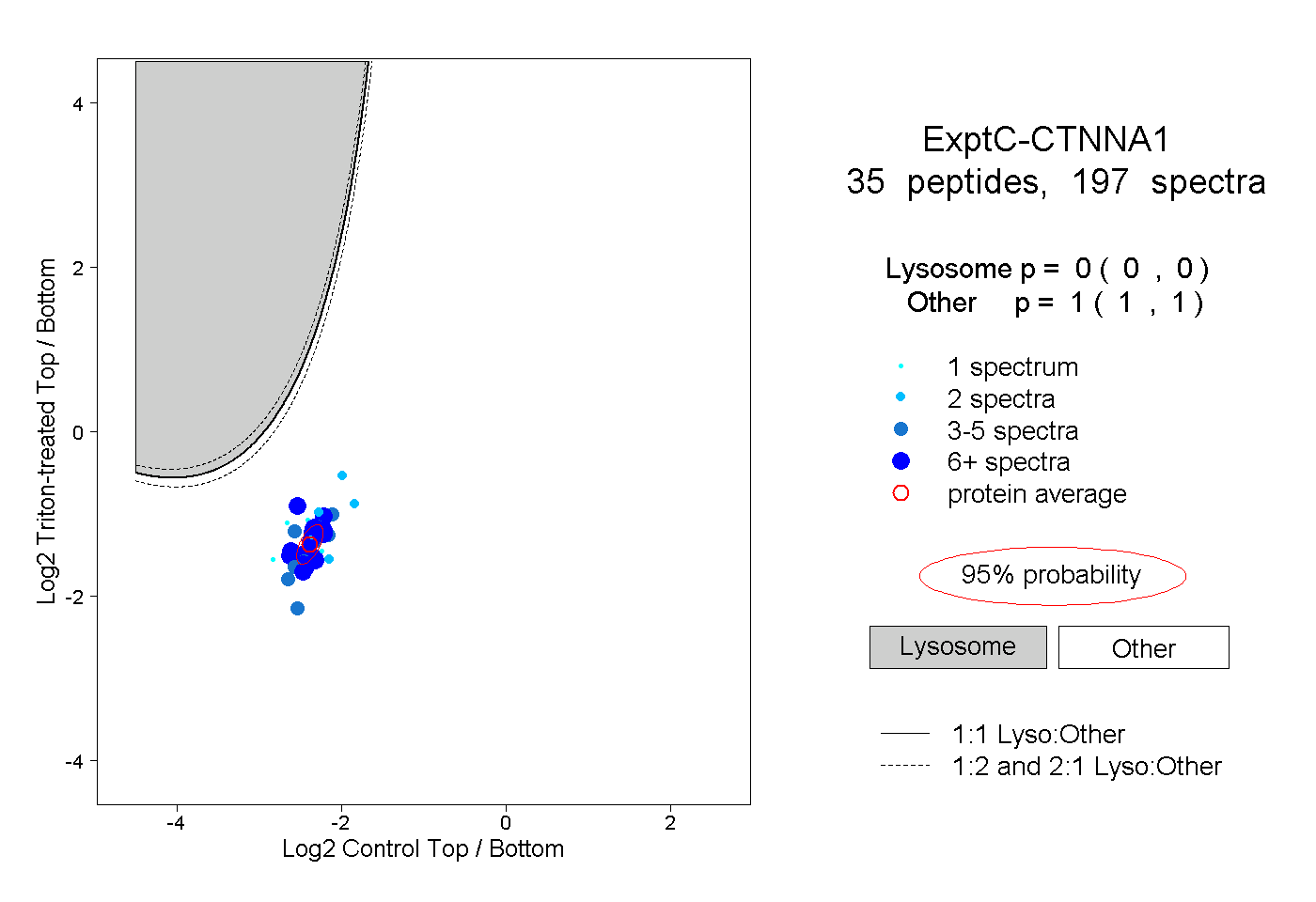 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
25 spectra |
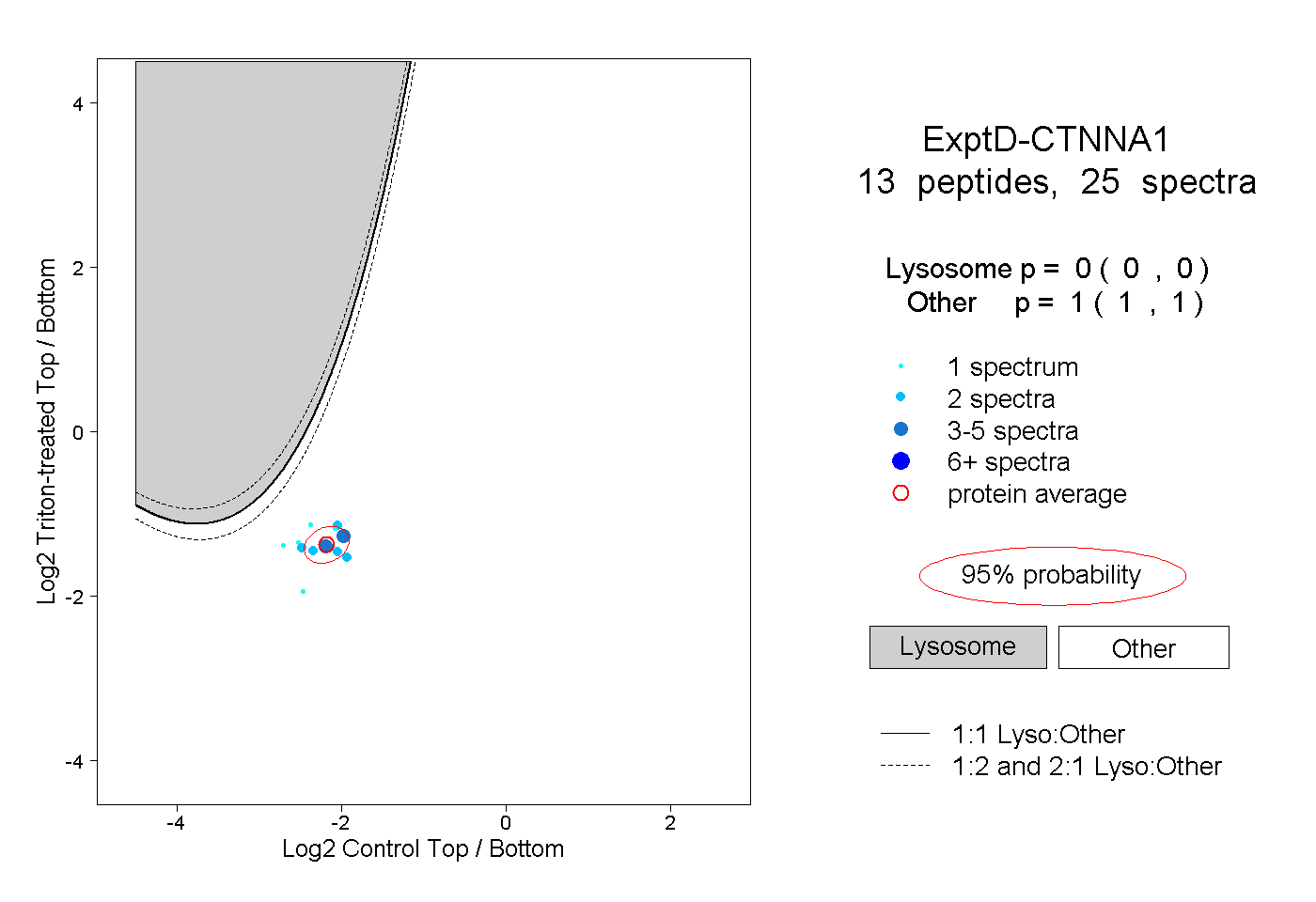 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |