peptides
spectra
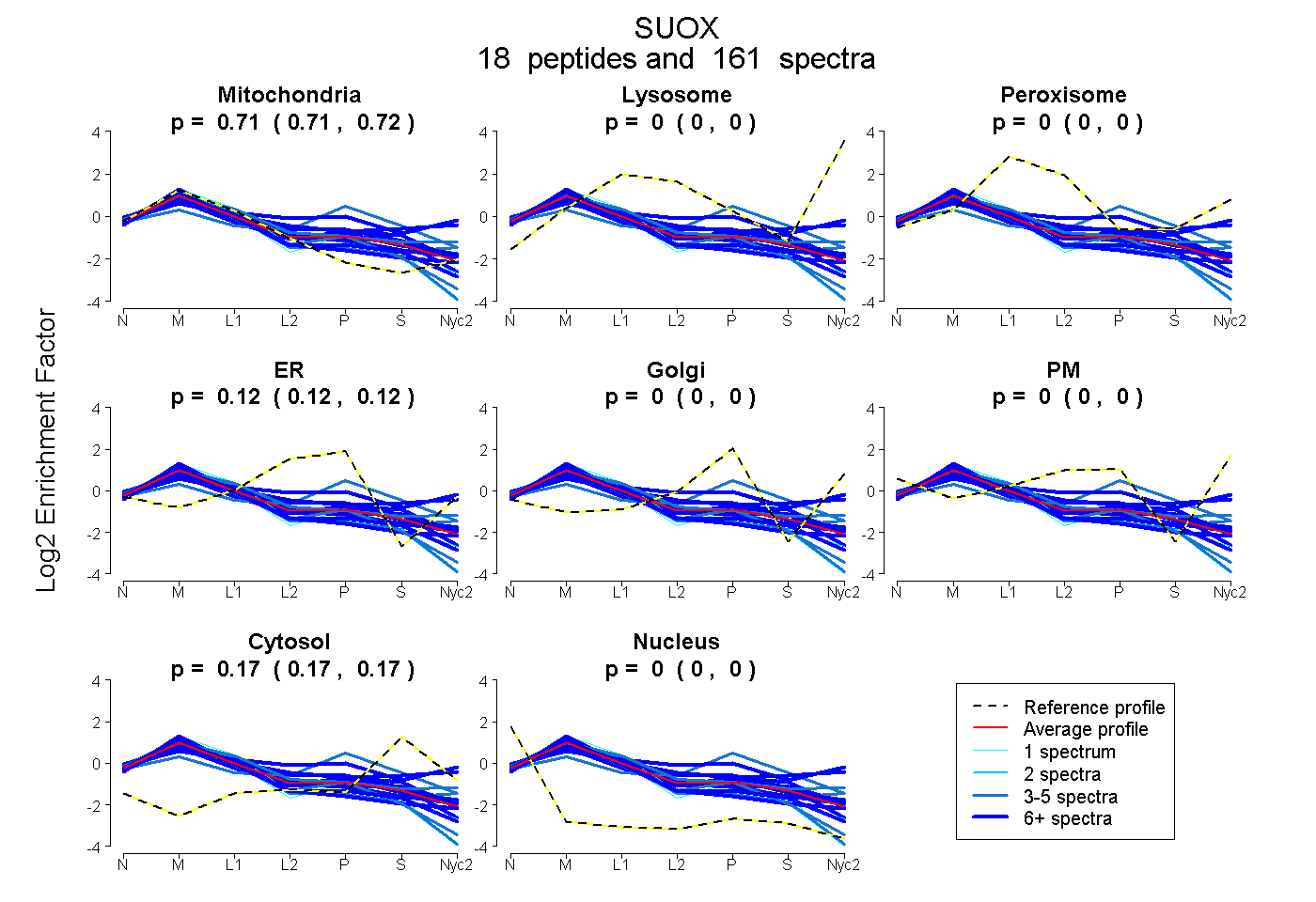
0.708 | 0.715
0.000 | 0.000
0.000 | 0.000
0.117 | 0.124
0.000 | 0.000
0.000 | 0.000
0.165 | 0.170
0.000 | 0.000
peptides
spectra
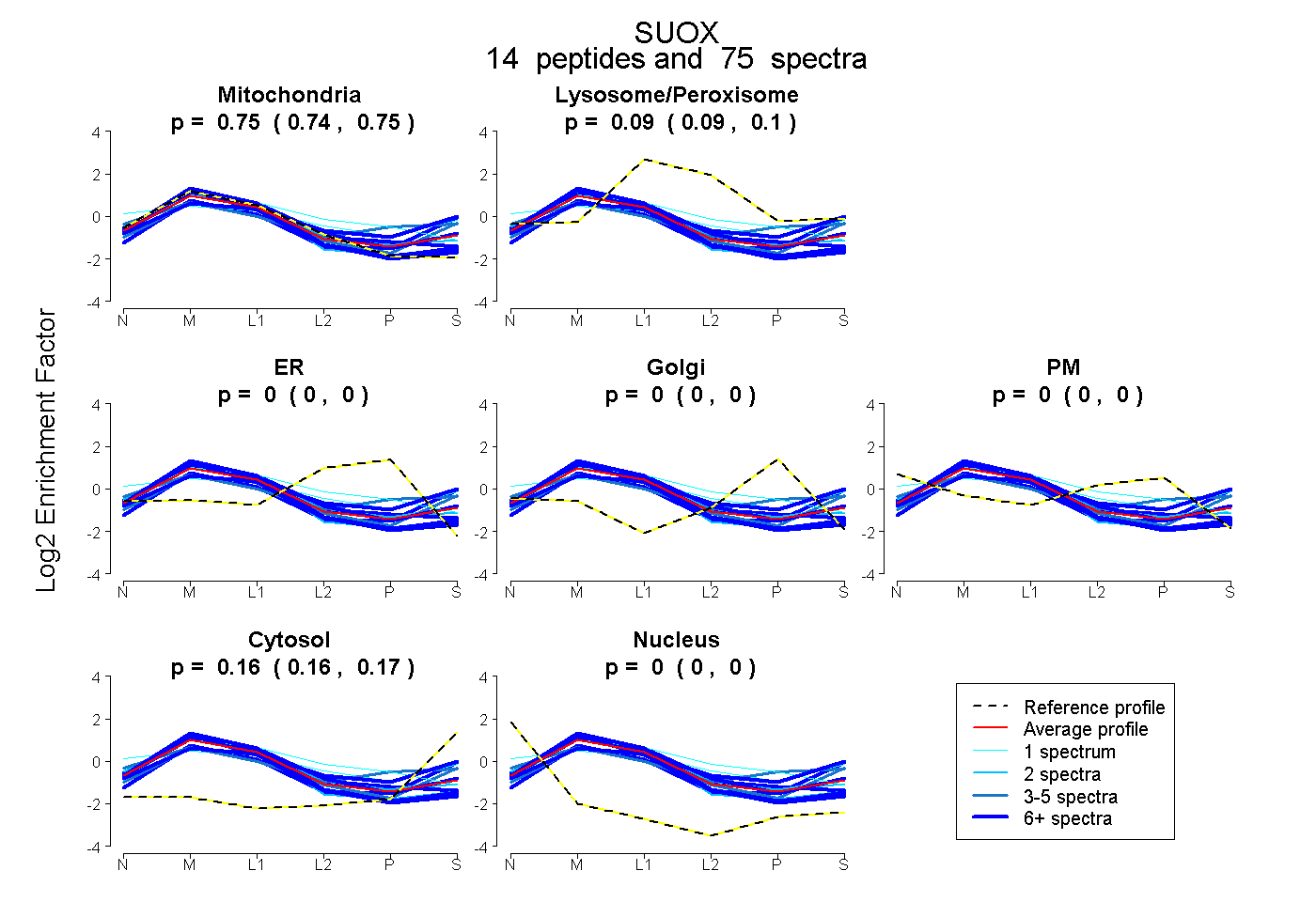
0.737 | 0.752
0.088 | 0.098
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.157 | 0.166
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
161 spectra |
 |
0.712 0.708 | 0.715 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.120 0.117 | 0.124 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.168 0.165 | 0.170 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
75 spectra |
 |
0.745 0.737 | 0.752 |
0.093 0.088 | 0.098 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.162 0.157 | 0.166 |
0.000 0.000 | 0.000 |
| 11 spectra, VVVPGVVGAR | 0.960 | 0.000 | 0.000 | 0.000 | 0.000 | 0.040 | 0.000 | |||
| 2 spectra, FVDLHPGGQSK | 0.731 | 0.134 | 0.000 | 0.000 | 0.000 | 0.135 | 0.000 | |||
| 1 spectrum, ELNIICK | 0.359 | 0.261 | 0.000 | 0.000 | 0.161 | 0.208 | 0.012 | |||
| 9 spectra, TGAISTAR | 0.902 | 0.000 | 0.000 | 0.000 | 0.000 | 0.098 | 0.000 | |||
| 2 spectra, GYAWSGGGR | 0.923 | 0.000 | 0.000 | 0.000 | 0.000 | 0.077 | 0.000 | |||
| 8 spectra, IGELNPEDR | 0.936 | 0.000 | 0.000 | 0.000 | 0.000 | 0.064 | 0.000 | |||
| 7 spectra, DHGFPVR | 0.566 | 0.084 | 0.000 | 0.000 | 0.000 | 0.350 | 0.000 | |||
| 3 spectra, HEVTVTLQCAGNR | 0.429 | 0.180 | 0.000 | 0.200 | 0.000 | 0.192 | 0.000 | |||
| 4 spectra, GVLSNAWHR | 0.596 | 0.115 | 0.000 | 0.000 | 0.000 | 0.289 | 0.000 | |||
| 1 spectrum, LHVVGAPGGQSLSLSLDDLHK | 0.535 | 0.281 | 0.000 | 0.184 | 0.000 | 0.000 | 0.000 | |||
| 12 spectra, LCDVLAQAGHR | 0.715 | 0.148 | 0.000 | 0.000 | 0.000 | 0.137 | 0.000 | |||
| 6 spectra, ELLAEYK | 0.801 | 0.079 | 0.000 | 0.078 | 0.000 | 0.042 | 0.000 | |||
| 7 spectra, NHLPVPNLDPDTYR | 0.437 | 0.270 | 0.000 | 0.011 | 0.000 | 0.282 | 0.000 | |||
| 2 spectra, AHVPAEQK | 0.782 | 0.091 | 0.000 | 0.013 | 0.000 | 0.114 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
383 spectra |
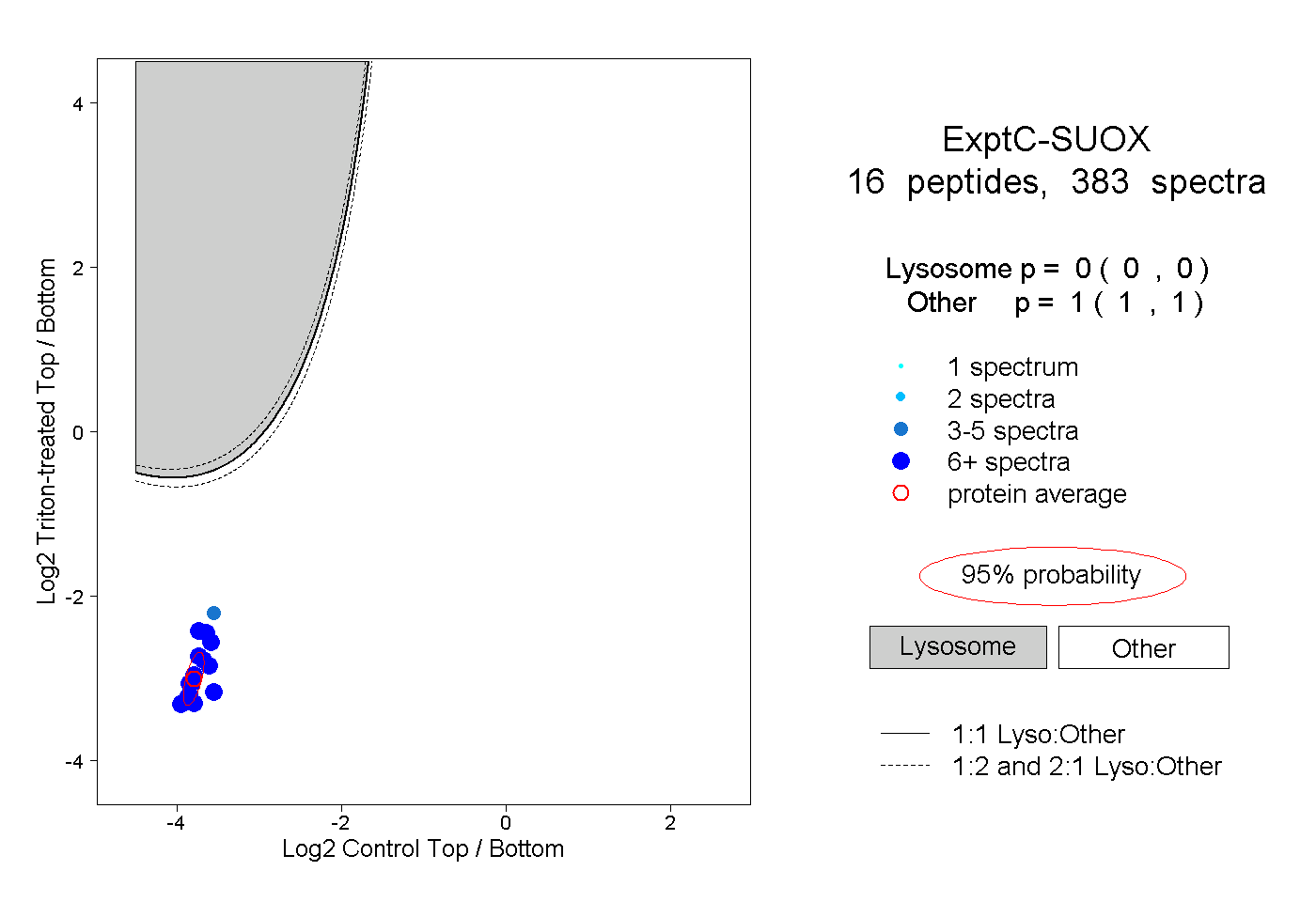 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
54 spectra |
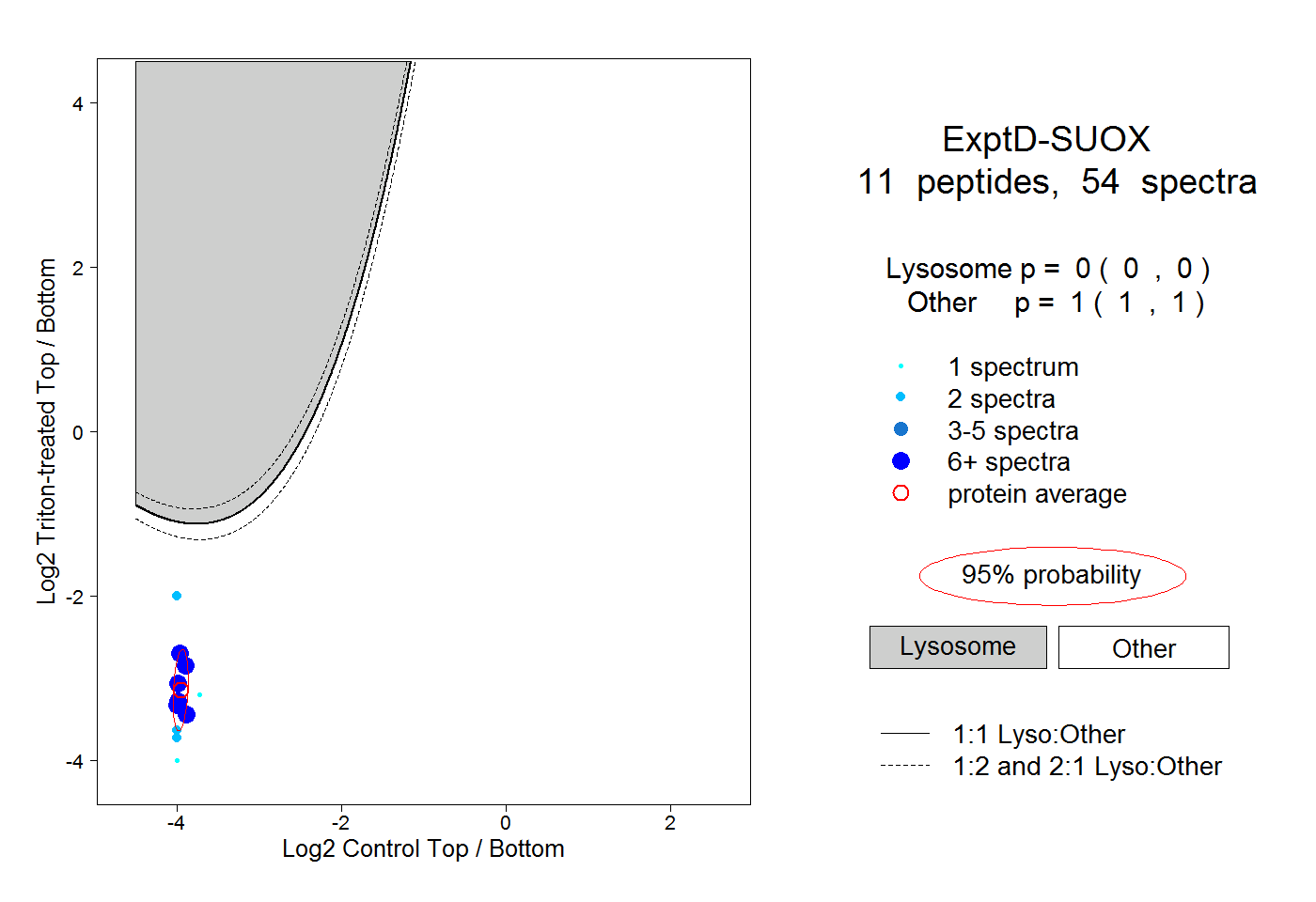 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |