peptides
spectra
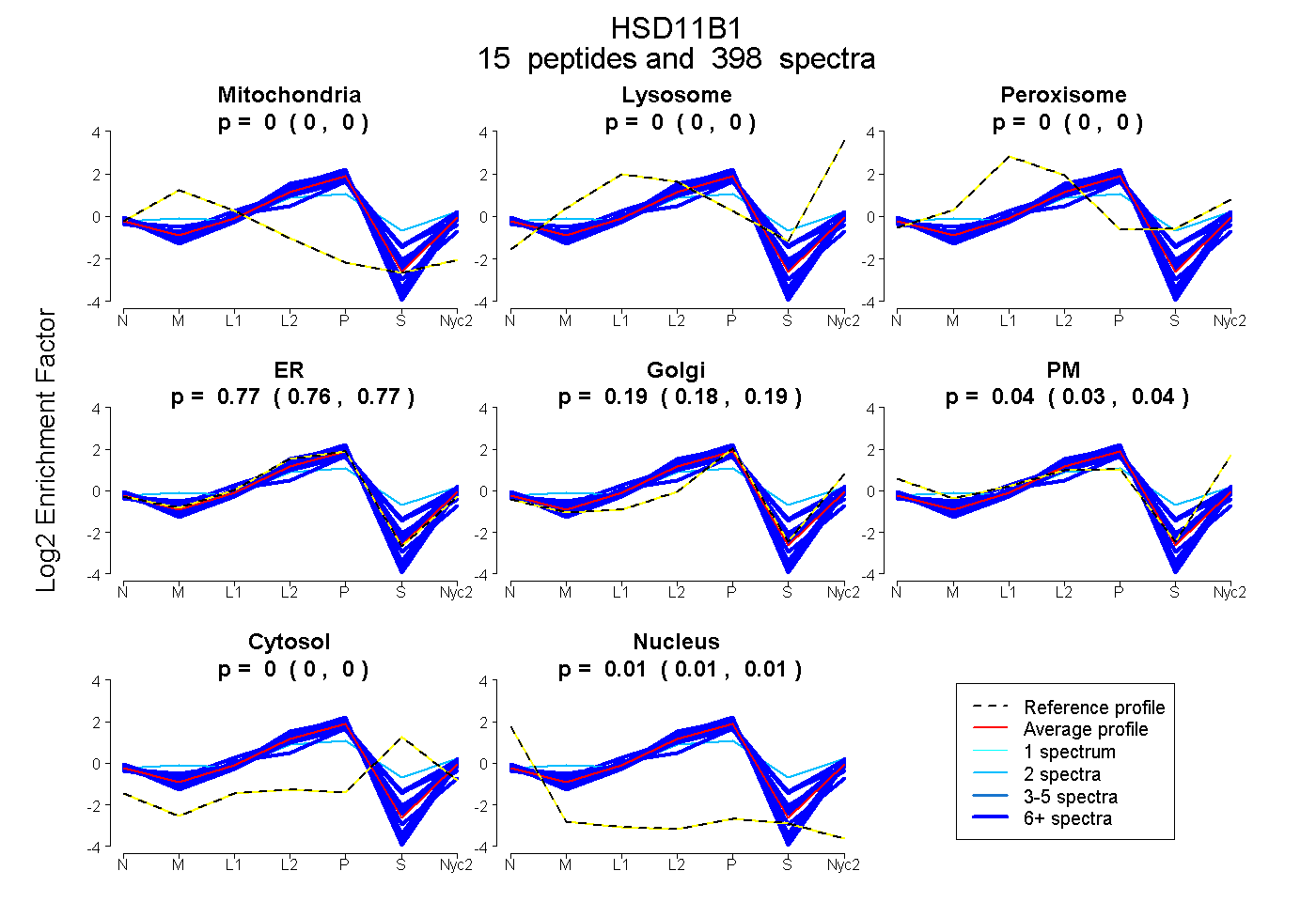
0.000 | 0.000
0.000 | 0.000
0.000 | 0.004
0.762 | 0.771
0.183 | 0.192
0.030 | 0.038
0.000 | 0.000
0.009 | 0.010
peptides
spectra
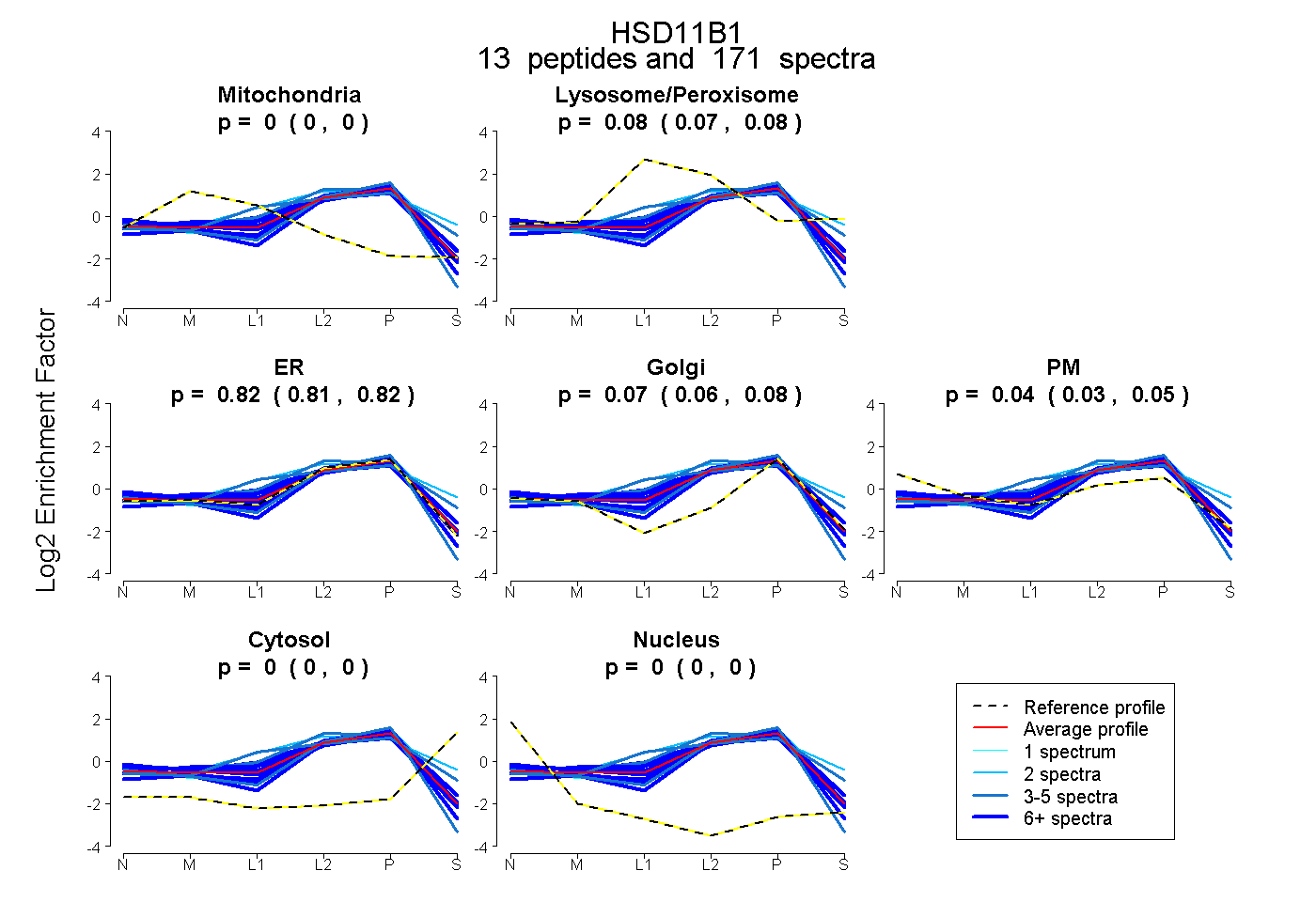
0.000 | 0.000
0.070 | 0.083
0.806 | 0.824
0.059 | 0.077
0.029 | 0.045
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
398 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.004 |
0.768 0.762 | 0.771 |
0.186 0.183 | 0.192 |
0.036 0.030 | 0.038 |
0.000 0.000 | 0.000 |
0.010 0.009 | 0.010 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
171 spectra |
 |
0.000 0.000 | 0.000 |
0.077 0.070 | 0.083 |
0.816 0.806 | 0.824 |
0.069 0.059 | 0.077 |
0.038 0.029 | 0.045 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 8 spectra, SEEGLQK | 0.000 | 0.047 | 0.697 | 0.050 | 0.207 | 0.000 | 0.000 | |||
| 41 spectra, IMEFLSLR | 0.000 | 0.000 | 0.801 | 0.199 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, EMAYHLSK | 0.000 | 0.163 | 0.808 | 0.000 | 0.029 | 0.000 | 0.000 | |||
| 2 spectra, EHLMTK | 0.000 | 0.001 | 0.939 | 0.000 | 0.000 | 0.061 | 0.000 | |||
| 5 spectra, VIVTGASK | 0.000 | 0.000 | 0.963 | 0.019 | 0.000 | 0.000 | 0.017 | |||
| 2 spectra, CLELGAASAHYIAGTMEDMAFAER | 0.000 | 0.461 | 0.334 | 0.143 | 0.000 | 0.062 | 0.000 | |||
| 4 spectra, SSWTPLLLGNPGR | 0.000 | 0.448 | 0.242 | 0.311 | 0.000 | 0.000 | 0.000 | |||
| 40 spectra, MGAHVVLTAR | 0.000 | 0.223 | 0.579 | 0.198 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, DEVYYDK | 0.000 | 0.000 | 0.931 | 0.069 | 0.000 | 0.000 | 0.000 | |||
| 14 spectra, EECALEIIK | 0.000 | 0.133 | 0.685 | 0.000 | 0.181 | 0.000 | 0.000 | |||
| 19 spectra, MTQPLIASYSASK | 0.000 | 0.015 | 0.876 | 0.036 | 0.000 | 0.073 | 0.000 | |||
| 21 spectra, FALDGFFSTIR | 0.000 | 0.000 | 0.983 | 0.000 | 0.000 | 0.000 | 0.017 | |||
| 11 spectra, ETSGIILSQAAPK | 0.011 | 0.069 | 0.698 | 0.000 | 0.221 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
404 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
36 spectra |
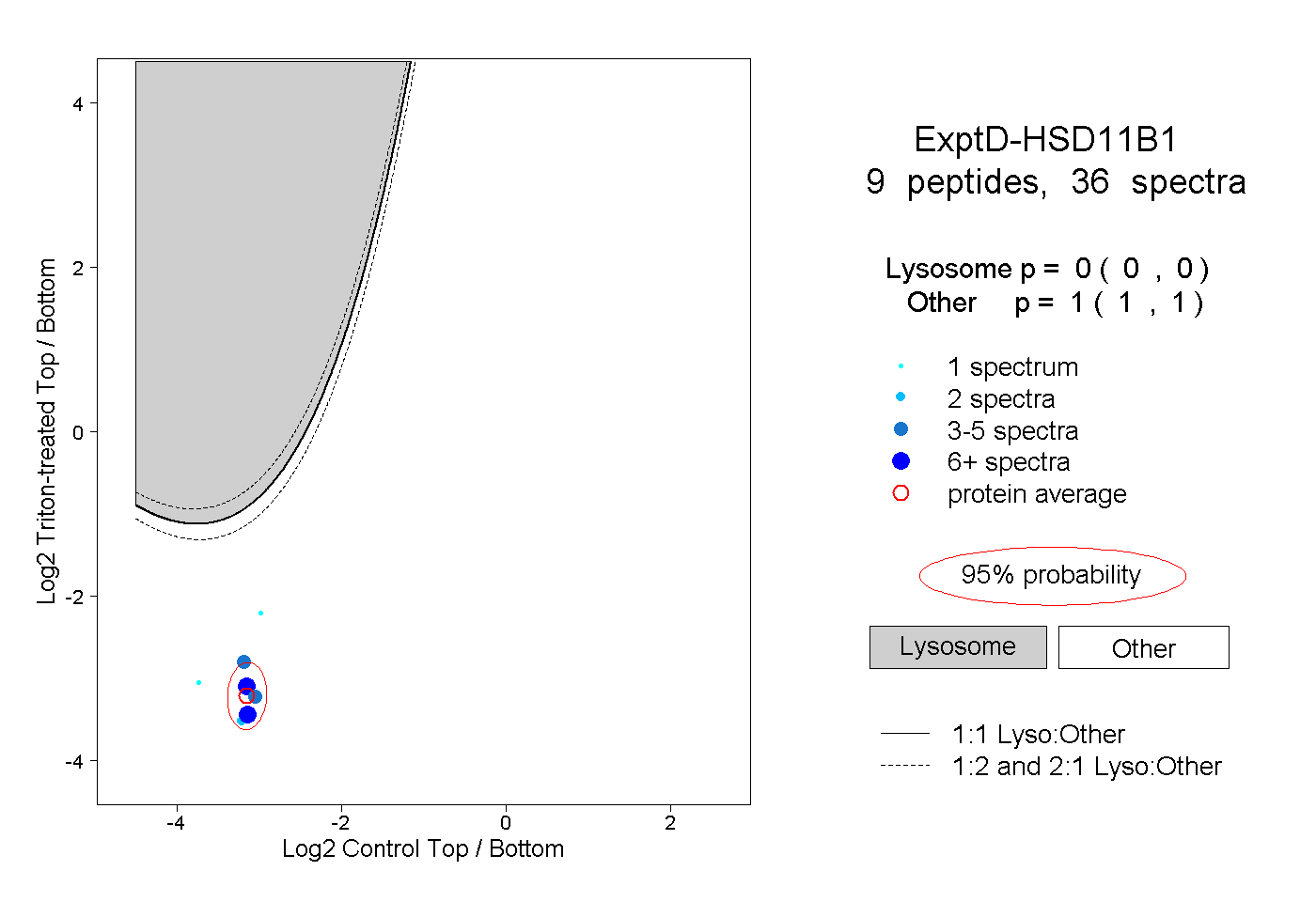 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |