peptides
spectra
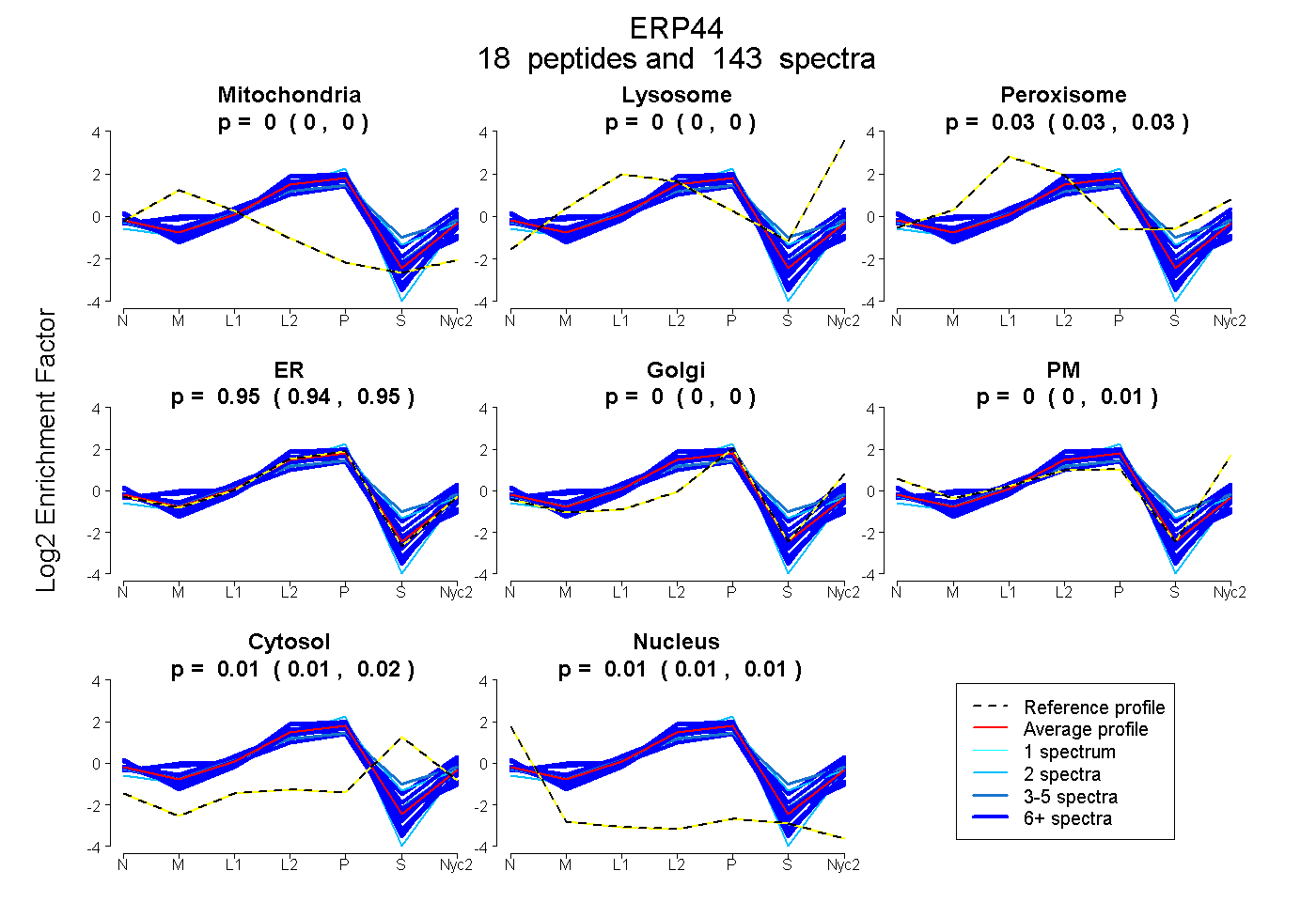
0.000 | 0.000
0.000 | 0.000
0.029 | 0.033
0.941 | 0.949
0.000 | 0.000
0.000 | 0.006
0.008 | 0.017
0.006 | 0.011
peptides
spectra
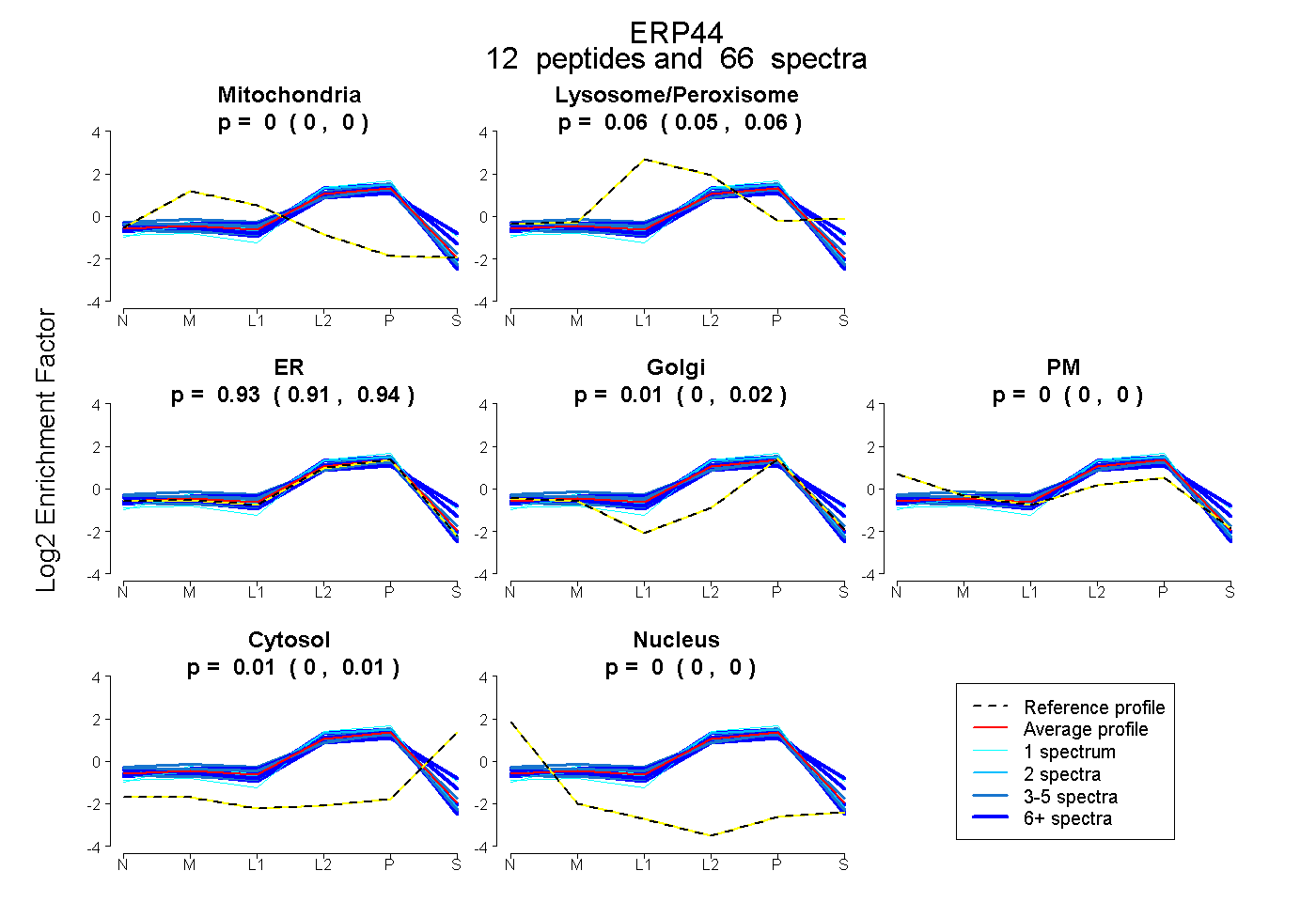
0.000 | 0.000
0.052 | 0.065
0.912 | 0.941
0.000 | 0.017
0.000 | 0.000
0.000 | 0.009
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
143 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.031 0.029 | 0.033 |
0.946 0.941 | 0.949 |
0.000 0.000 | 0.000 |
0.001 0.000 | 0.006 |
0.013 0.008 | 0.017 |
0.009 0.006 | 0.011 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
66 spectra |
 |
0.000 0.000 | 0.000 |
0.058 0.052 | 0.065 |
0.930 0.912 | 0.941 |
0.006 0.000 | 0.017 |
0.000 0.000 | 0.000 |
0.005 0.000 | 0.009 |
0.000 0.000 | 0.000 |
| 4 spectra, NIIGYFEQK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, VASILHDDCAFLSAFGDLSKPER | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 10 spectra, LAPSEYR | 0.000 | 0.056 | 0.806 | 0.041 | 0.000 | 0.098 | 0.000 | |||
| 7 spectra, SNPVHEIQSLDEVTNLDR | 0.000 | 0.270 | 0.475 | 0.175 | 0.000 | 0.081 | 0.000 | |||
| 8 spectra, AIADYLR | 0.000 | 0.055 | 0.909 | 0.000 | 0.035 | 0.000 | 0.000 | |||
| 4 spectra, QFVFDLHSGK | 0.000 | 0.128 | 0.802 | 0.053 | 0.000 | 0.017 | 0.000 | |||
| 4 spectra, YSGDNLIYKPPGR | 0.016 | 0.035 | 0.850 | 0.000 | 0.098 | 0.000 | 0.000 | |||
| 5 spectra, CVPLVR | 0.054 | 0.074 | 0.786 | 0.000 | 0.087 | 0.000 | 0.000 | |||
| 11 spectra, HPLLHIQK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, EDTESLEIFQNEVAR | 0.000 | 0.171 | 0.746 | 0.000 | 0.000 | 0.083 | 0.000 | |||
| 9 spectra, VDCDQHSDIAQR | 0.000 | 0.000 | 0.940 | 0.000 | 0.060 | 0.000 | 0.000 | |||
| 2 spectra, NQVVFAR | 0.000 | 0.026 | 0.974 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
162 spectra |
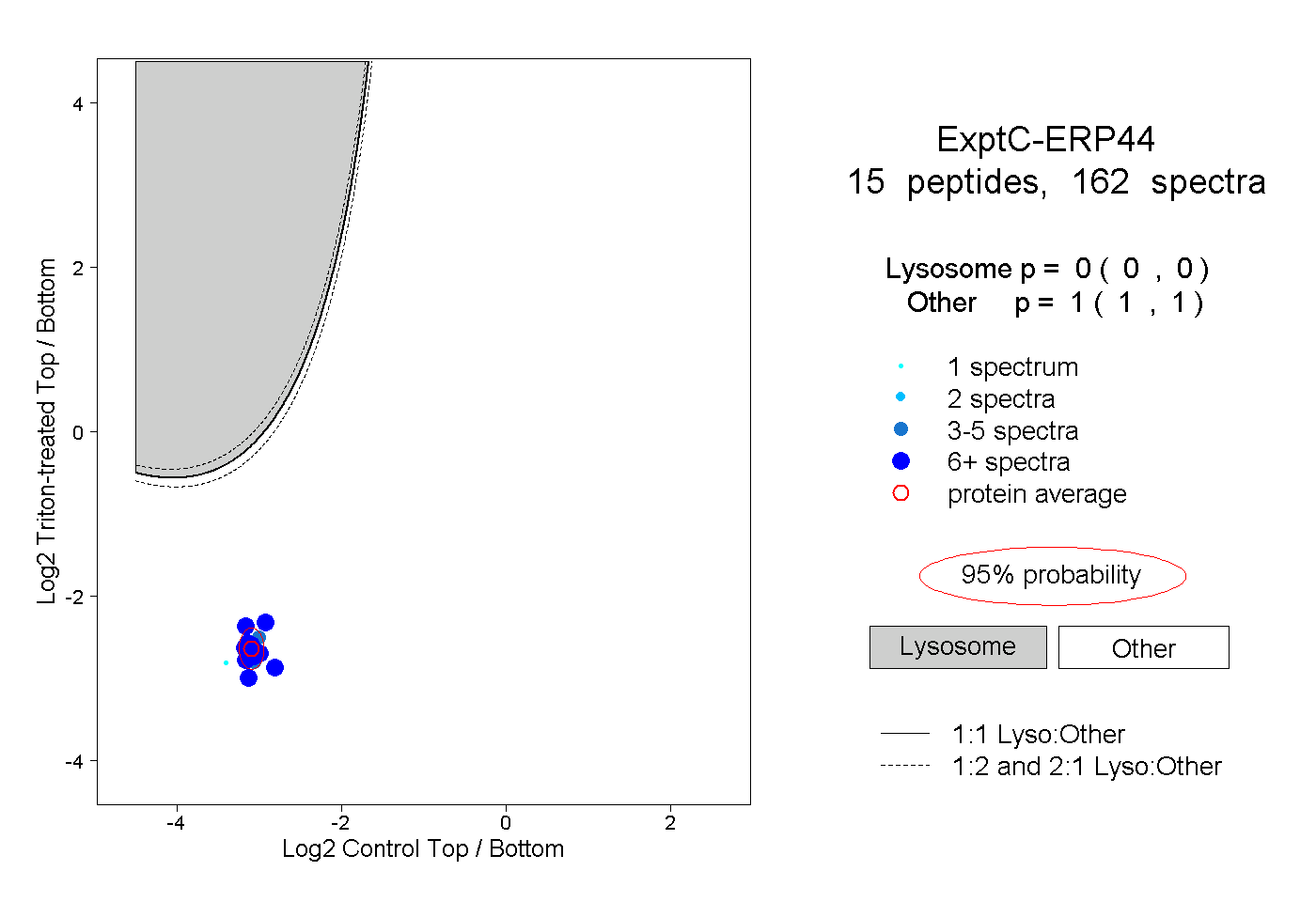 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
23 spectra |
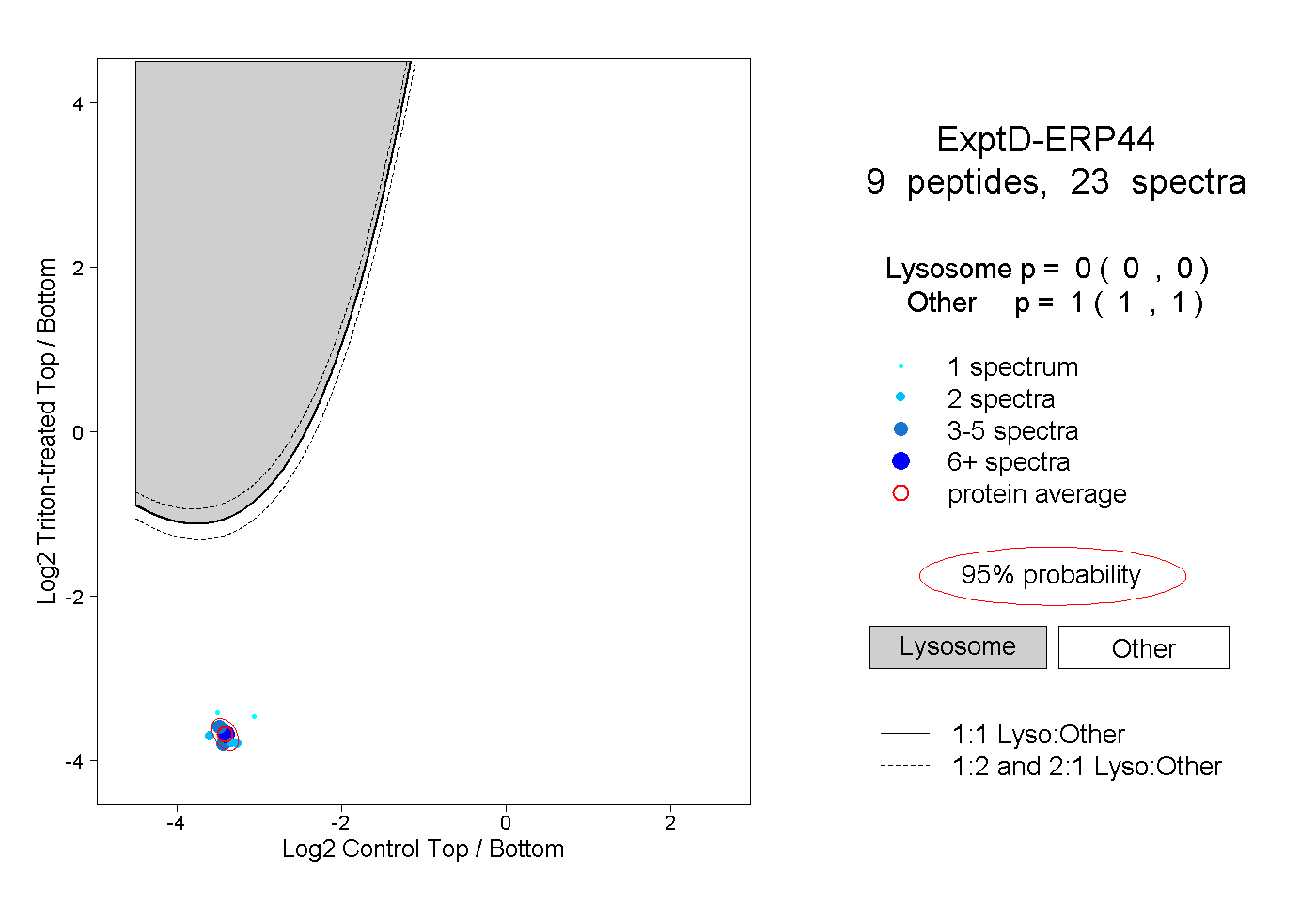 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |