peptides
spectra
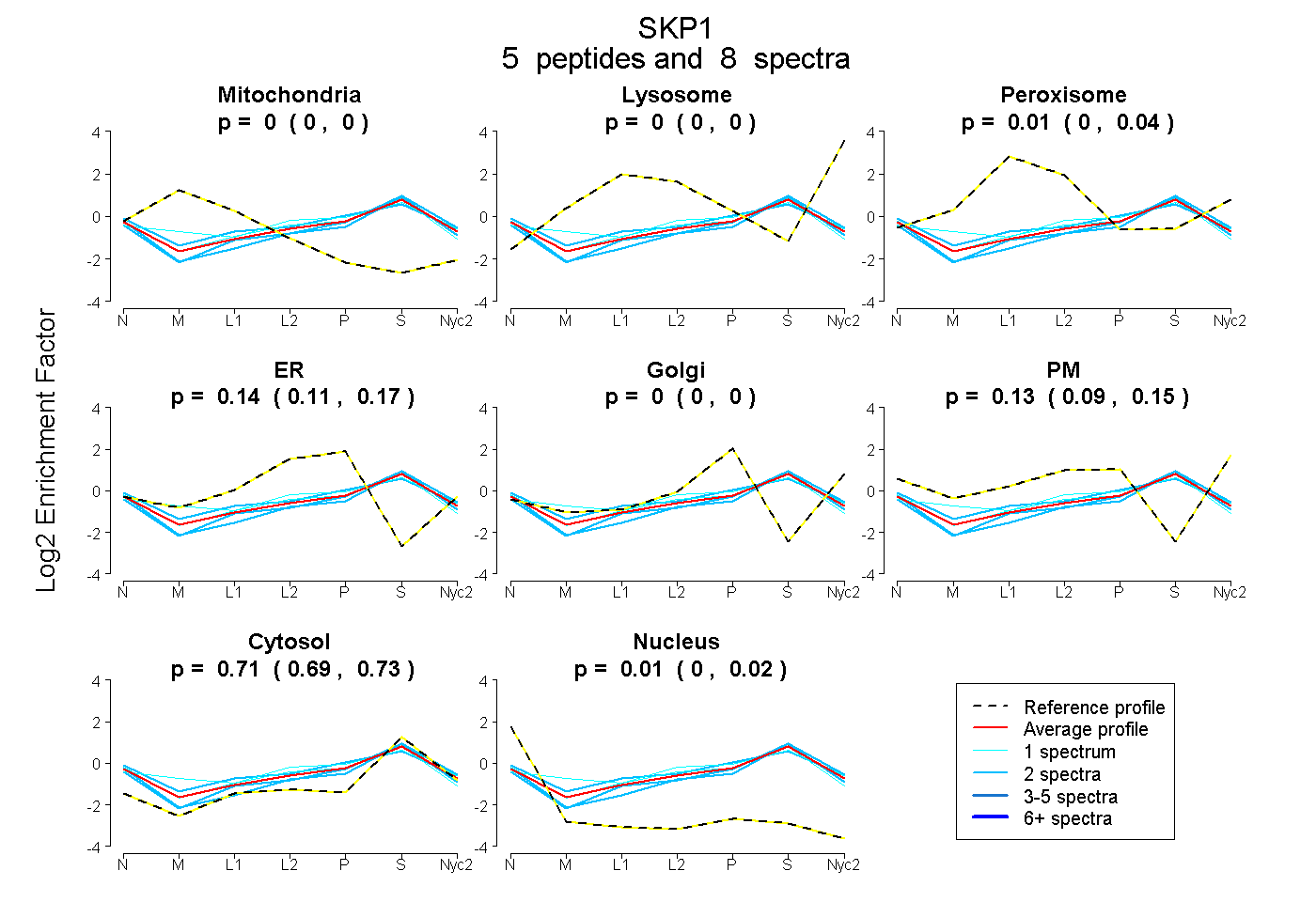
0.000 | 0.000
0.000 | 0.000
0.000 | 0.036
0.111 | 0.168
0.000 | 0.000
0.091 | 0.154
0.691 | 0.726
0.000 | 0.019
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
8 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.012 0.000 | 0.036 |
0.141 0.111 | 0.168 |
0.000 0.000 | 0.000 |
0.127 0.091 | 0.154 |
0.711 0.691 | 0.726 |
0.008 0.000 | 0.019 |
| 2 spectra, ENQWCEEK | 0.000 | 0.000 | 0.056 | 0.146 | 0.000 | 0.166 | 0.621 | 0.011 | ||
| 1 spectrum, VIQWCTHHK | 0.043 | 0.000 | 0.090 | 0.163 | 0.012 | 0.103 | 0.588 | 0.000 | ||
| 1 spectrum, QSVTIK | 0.000 | 0.000 | 0.071 | 0.222 | 0.000 | 0.000 | 0.671 | 0.036 | ||
| 2 spectra, TVANMIK | 0.000 | 0.000 | 0.000 | 0.052 | 0.043 | 0.127 | 0.779 | 0.000 | ||
| 2 spectra, NDFTEEEEAQVR | 0.000 | 0.000 | 0.000 | 0.101 | 0.000 | 0.079 | 0.763 | 0.057 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
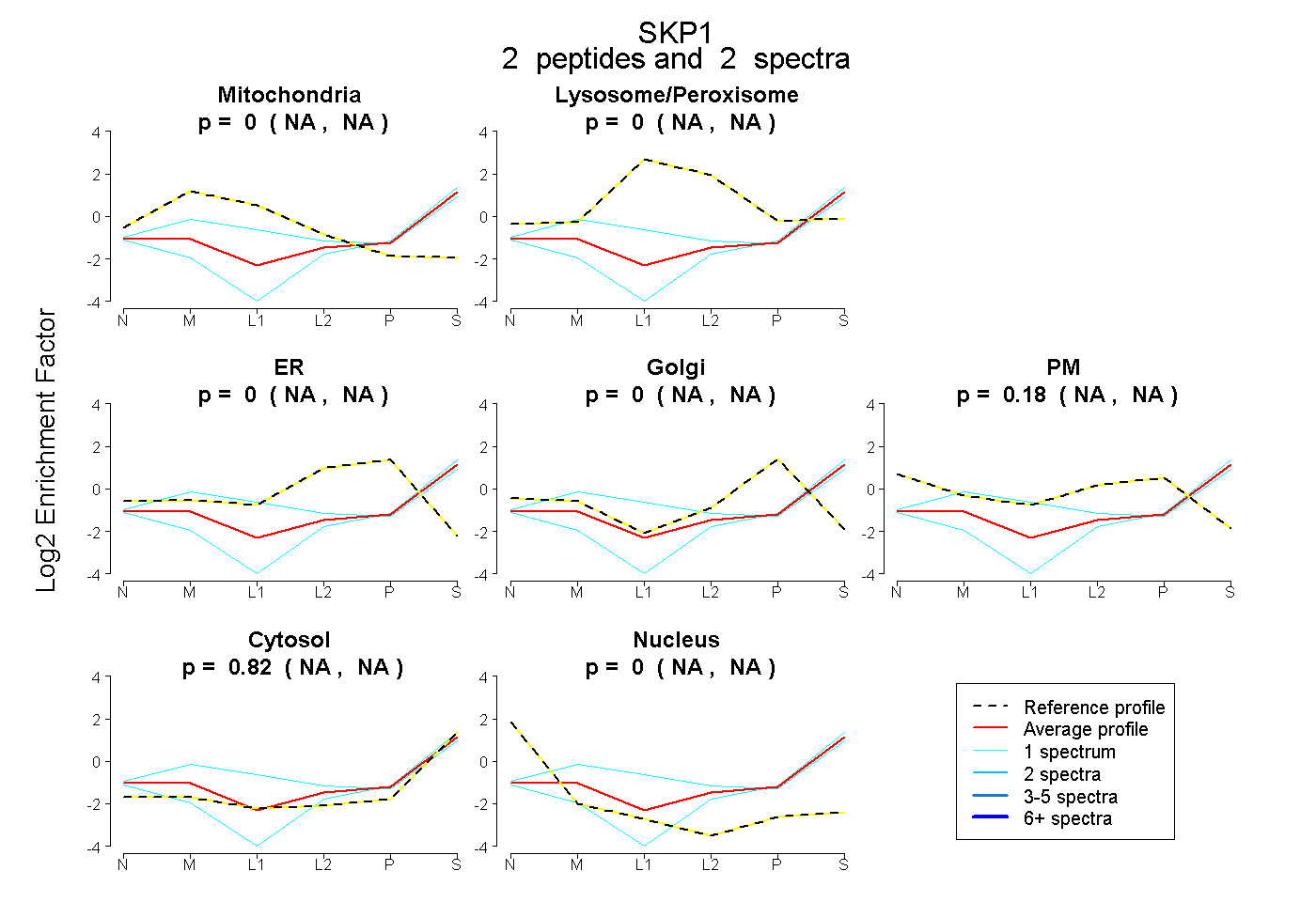 |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.185 NA | NA |
0.815 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
19 spectra |
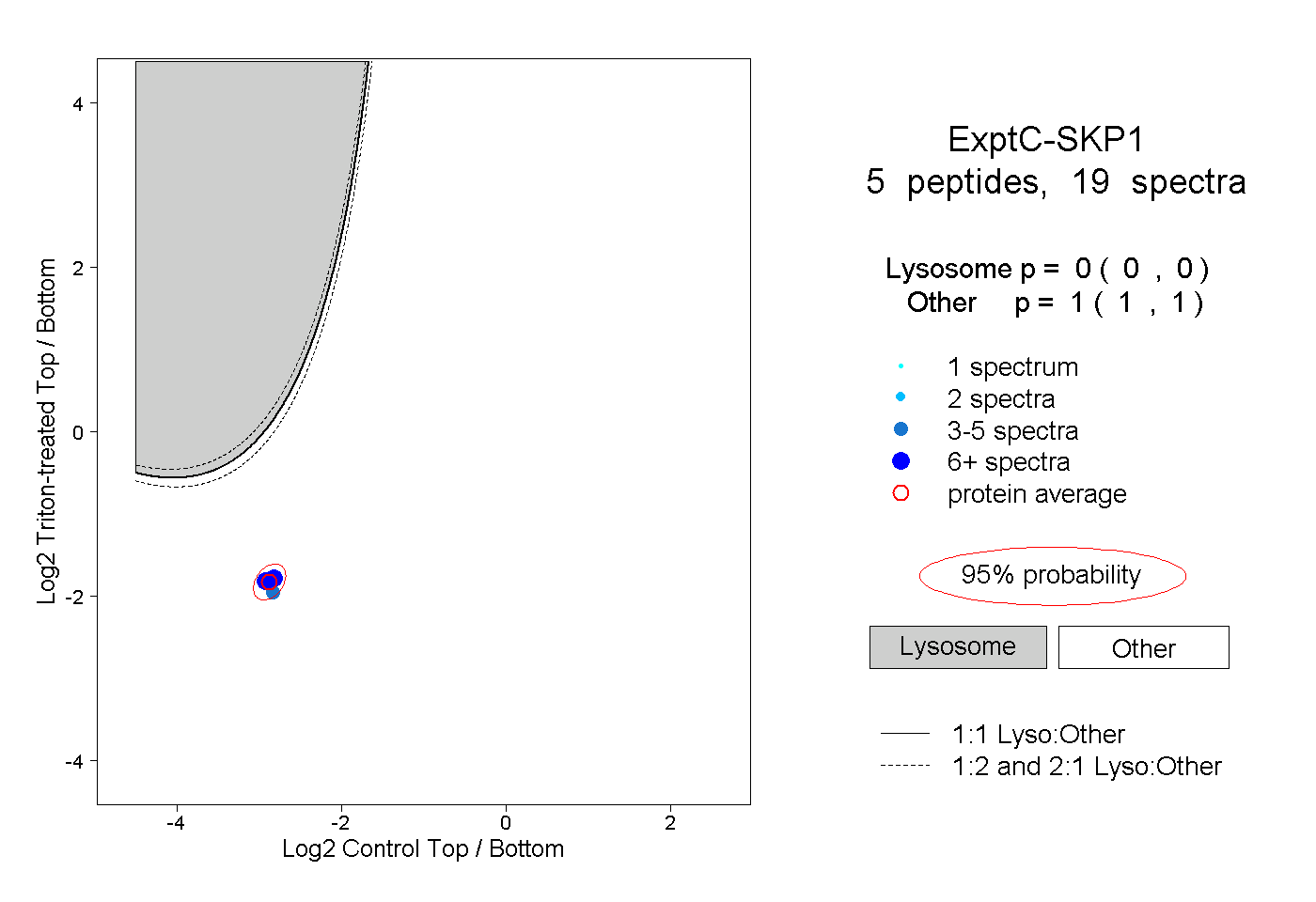 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |