peptides
spectra
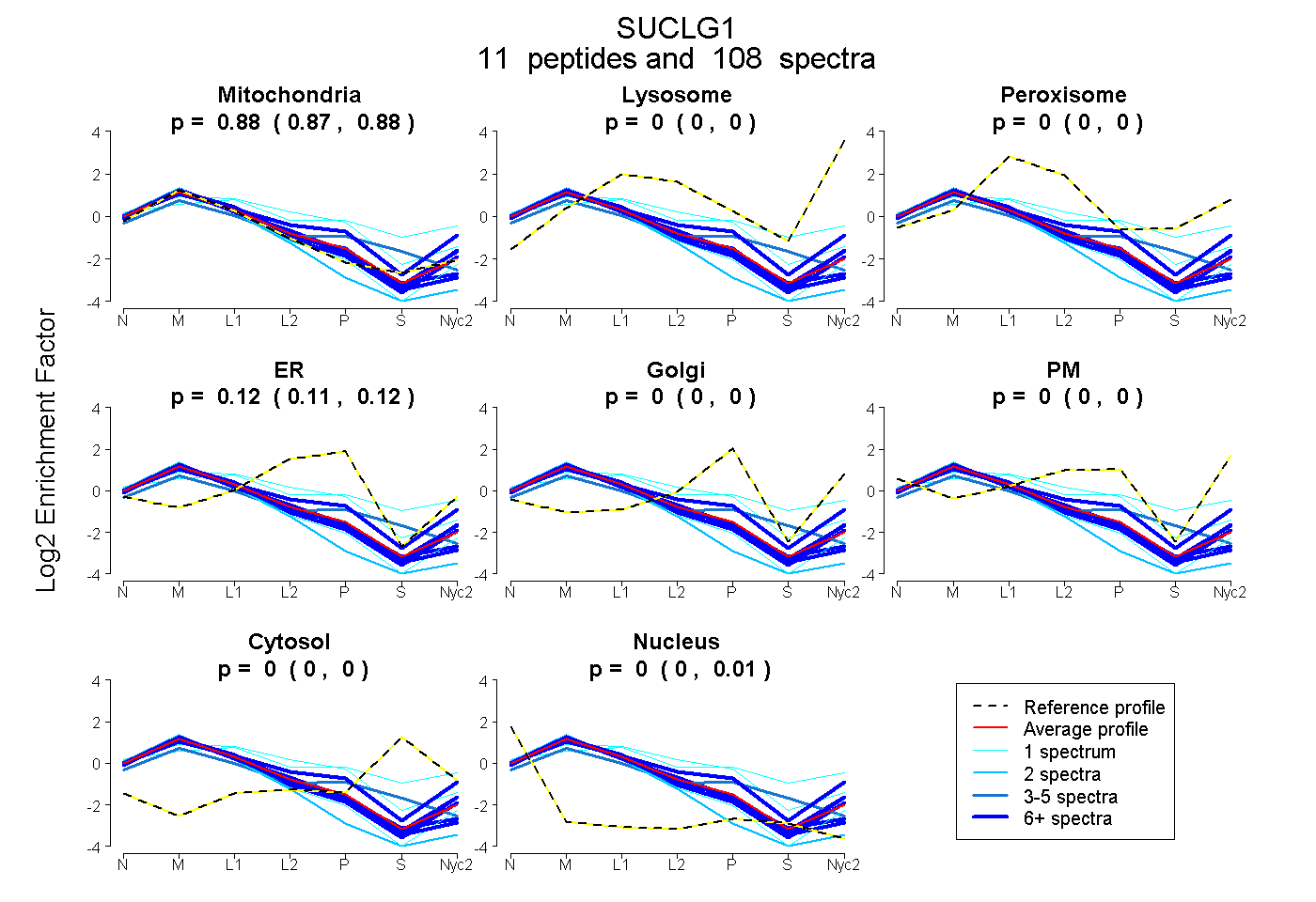
0.871 | 0.879
0.000 | 0.000
0.000 | 0.000
0.115 | 0.125
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.002 | 0.006
peptides
spectra
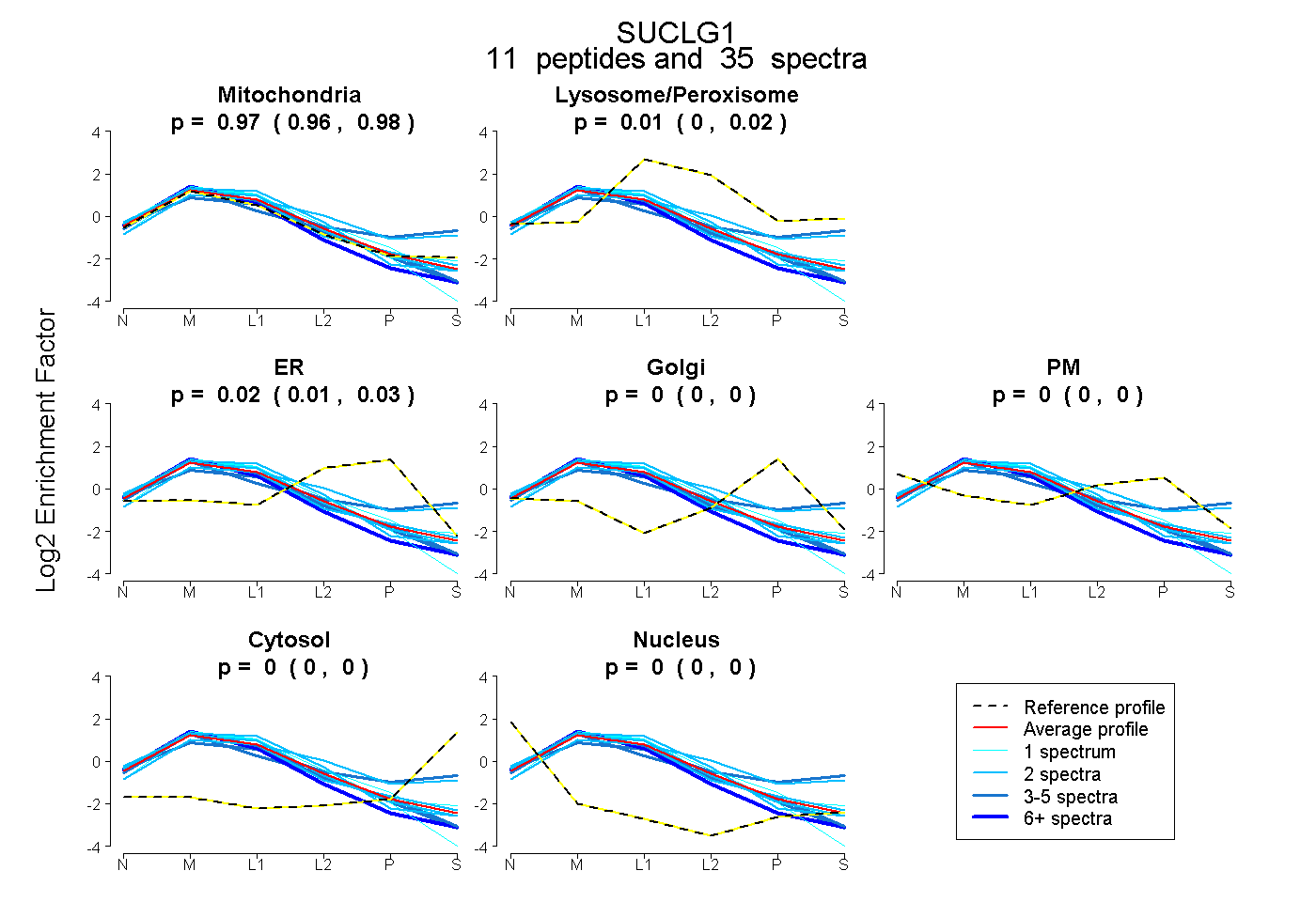
0.959 | 0.982
0.000 | 0.020
0.008 | 0.032
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
108 spectra |
 |
0.875 0.871 | 0.879 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.120 0.115 | 0.125 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.004 0.002 | 0.006 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
35 spectra |
 |
0.971 0.959 | 0.982 |
0.007 0.000 | 0.020 |
0.021 0.008 | 0.032 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 10 spectra, LGIVSR | 0.970 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.030 | |||
| 2 spectra, VICQGFTGK | 0.993 | 0.007 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, MGHAGAIIAGGK | 0.597 | 0.301 | 0.009 | 0.023 | 0.000 | 0.071 | 0.000 | |||
| 5 spectra, AKPVVSFIAGITAPPGR | 0.571 | 0.243 | 0.000 | 0.064 | 0.006 | 0.116 | 0.000 | |||
| 2 spectra, QGTFHSQQALEYGTK | 0.971 | 0.000 | 0.000 | 0.000 | 0.029 | 0.000 | 0.000 | |||
| 1 spectrum, LIGPNCPGIINPGECK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, NIYIDK | 0.948 | 0.052 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, EHNSGPK | 0.926 | 0.074 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, HLGLPVFNTVK | 0.913 | 0.000 | 0.087 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, IGIMPGHIHK | 0.944 | 0.000 | 0.038 | 0.000 | 0.000 | 0.000 | 0.018 | |||
| 4 spectra, LVGGTTPGK | 0.985 | 0.000 | 0.015 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
389 spectra |
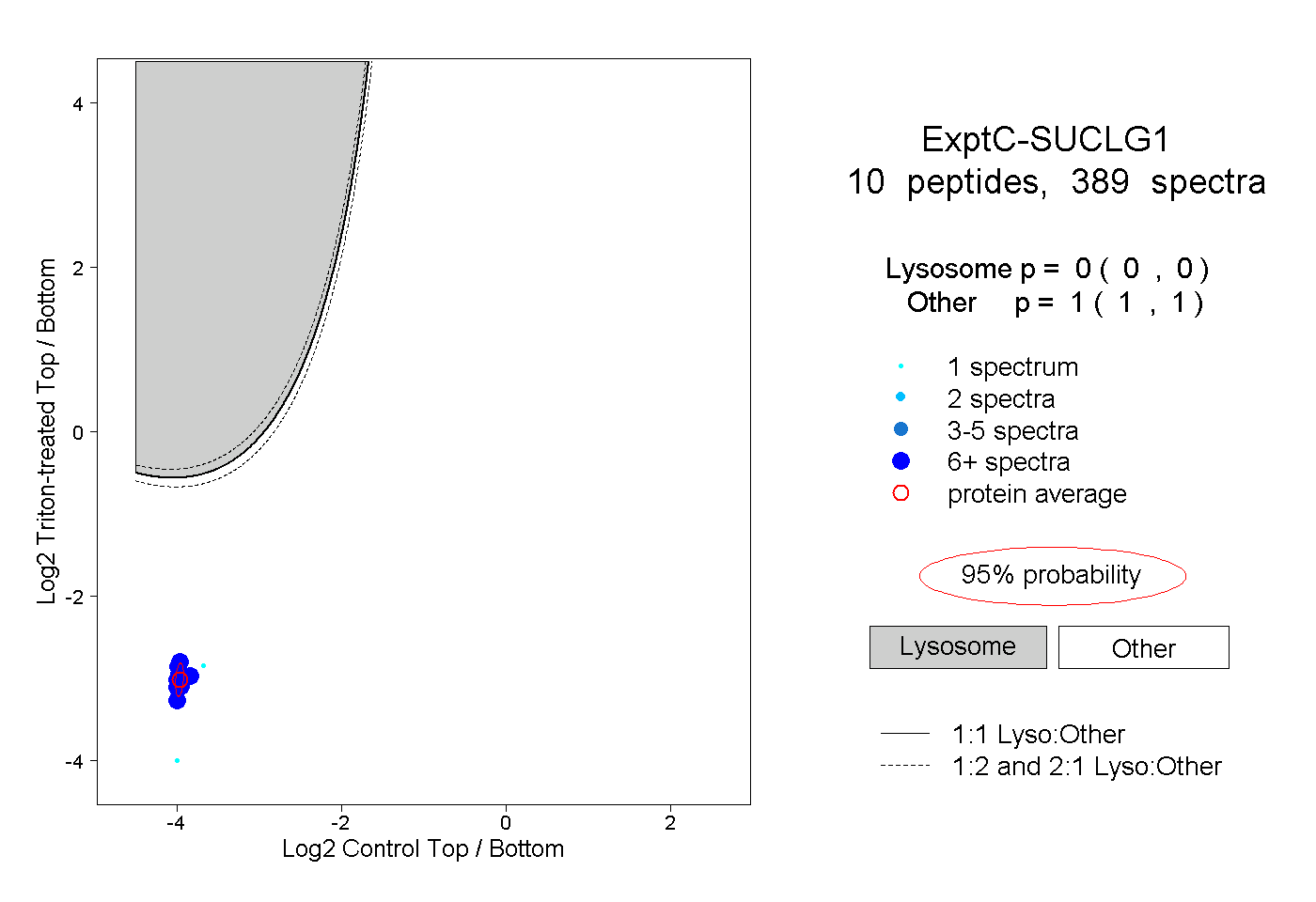 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
42 spectra |
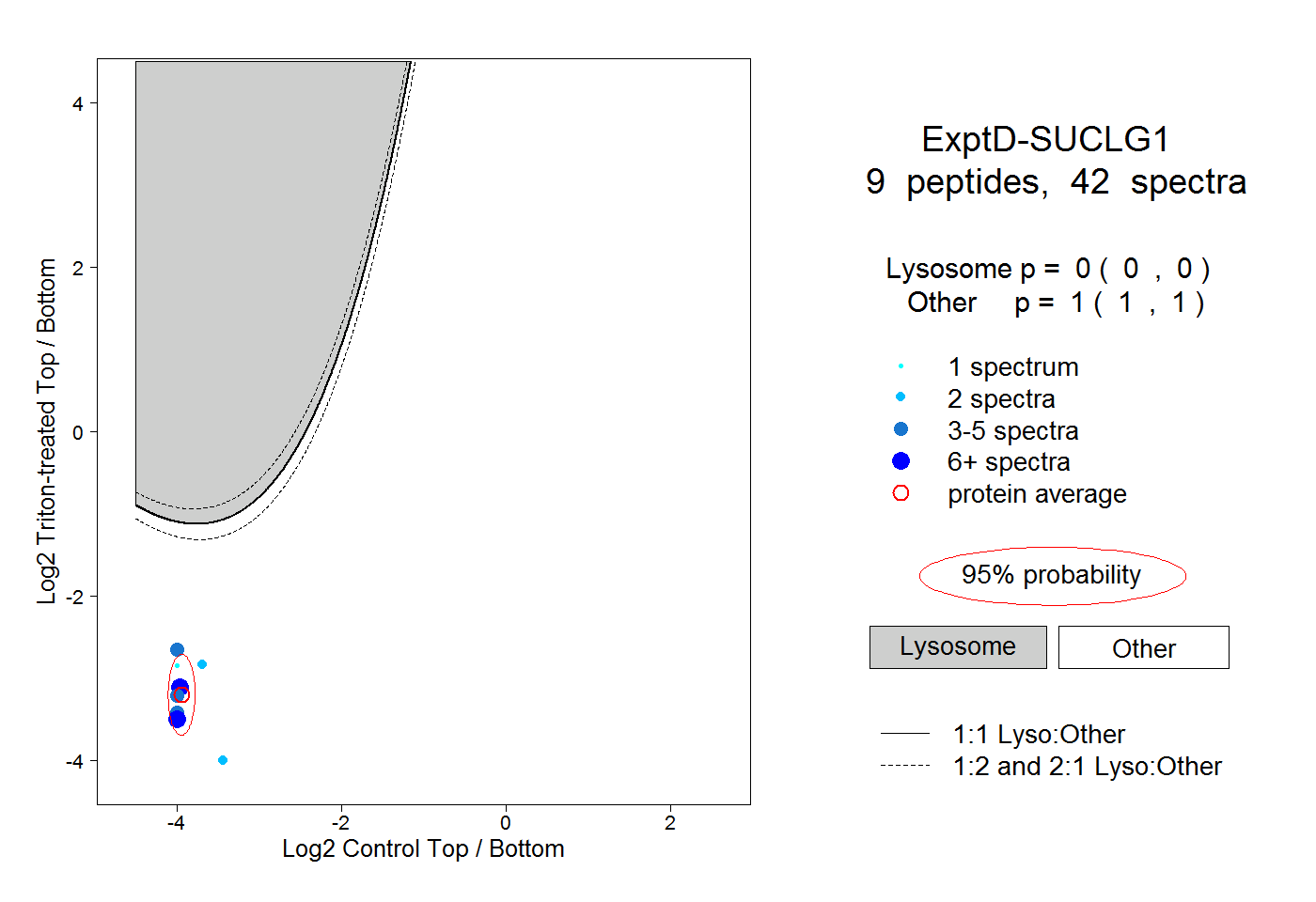 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |