peptides
spectra
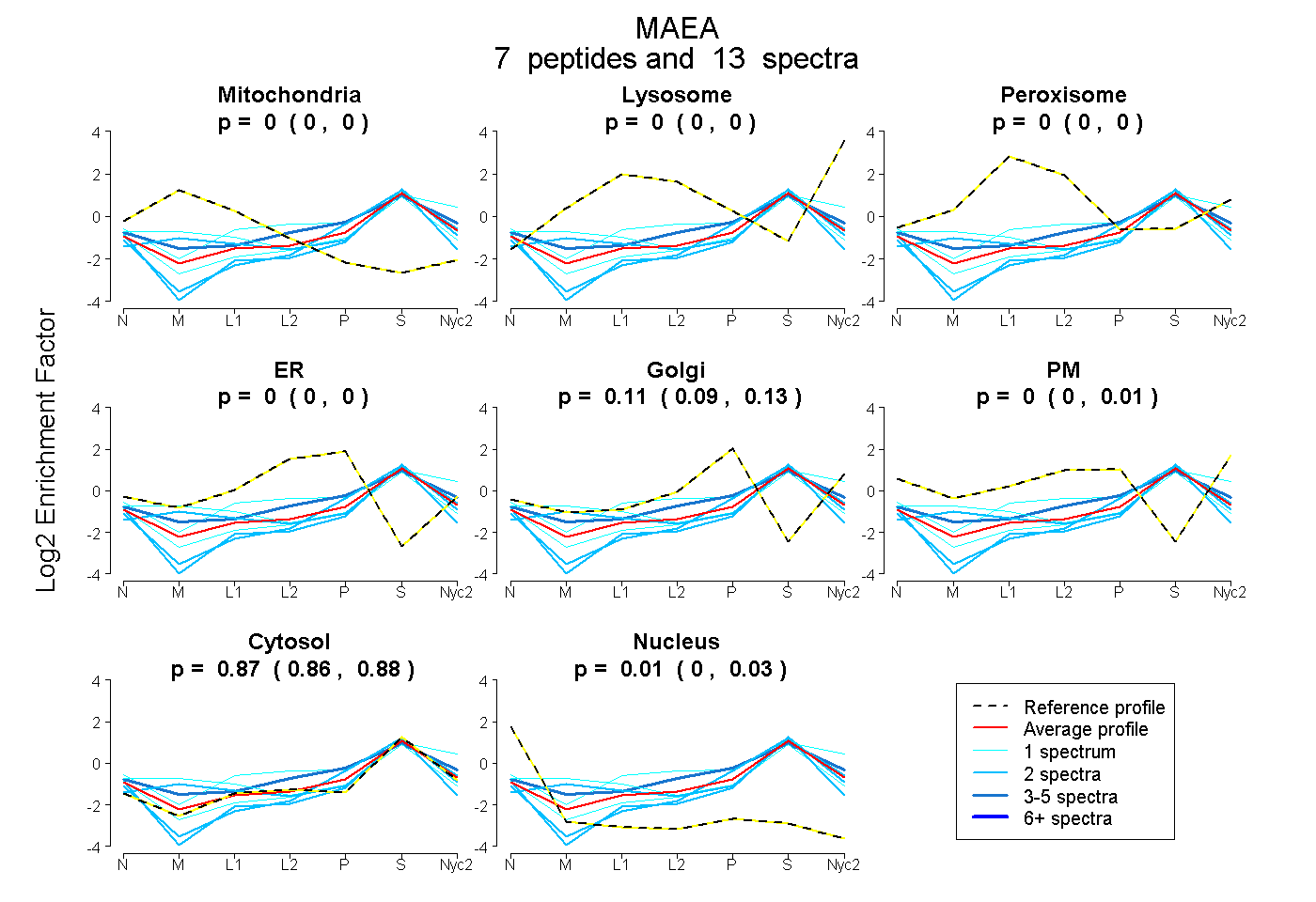
0.000 | 0.001
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.093 | 0.128
0.000 | 0.009
0.858 | 0.884
0.000 | 0.025
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
13 spectra |
 |
0.000 0.000 | 0.001 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.114 0.093 | 0.128 |
0.000 0.000 | 0.009 |
0.873 0.858 | 0.884 |
0.014 0.000 | 0.025 |
| 4 spectra, LAQPLPMAHCANSR | 0.000 | 0.000 | 0.017 | 0.000 | 0.136 | 0.110 | 0.737 | 0.000 | ||
| 2 spectra, SPDCPVCSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.892 | 0.108 | ||
| 1 spectrum, MLIQQFR | 0.253 | 0.000 | 0.020 | 0.000 | 0.016 | 0.000 | 0.712 | 0.000 | ||
| 2 spectra, EVEESLER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.897 | 0.103 | ||
| 1 spectrum, AVESIQAEDESAK | 0.000 | 0.132 | 0.001 | 0.000 | 0.000 | 0.175 | 0.692 | 0.000 | ||
| 2 spectra, MMVEHLLR | 0.134 | 0.058 | 0.000 | 0.000 | 0.000 | 0.000 | 0.809 | 0.000 | ||
| 1 spectrum, IQEFIELVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.019 | 0.000 | 0.921 | 0.060 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
4 spectra |
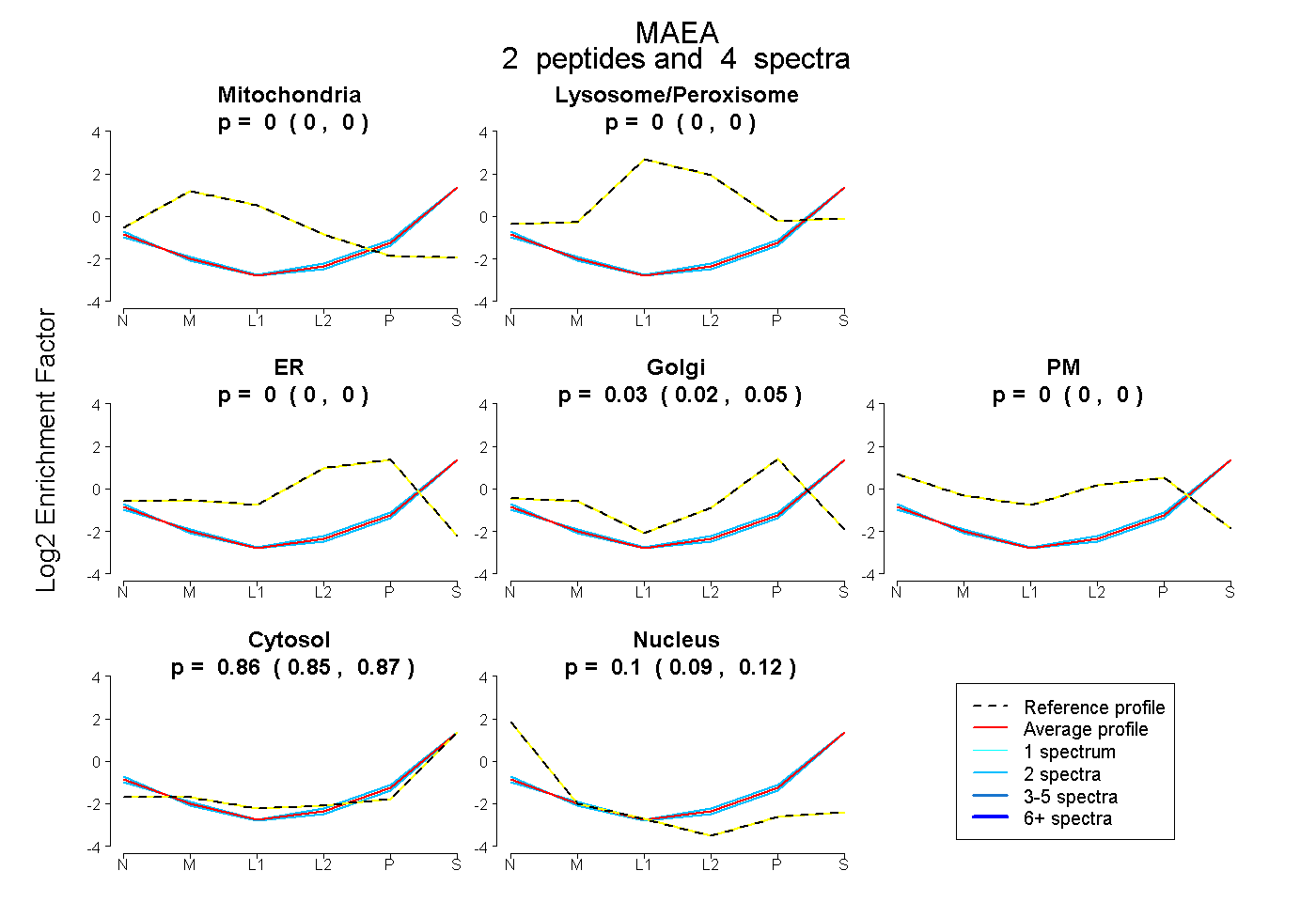 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.033 0.017 | 0.046 |
0.000 0.000 | 0.000 |
0.865 0.853 | 0.874 |
0.102 0.087 | 0.115 |