peptides
spectra
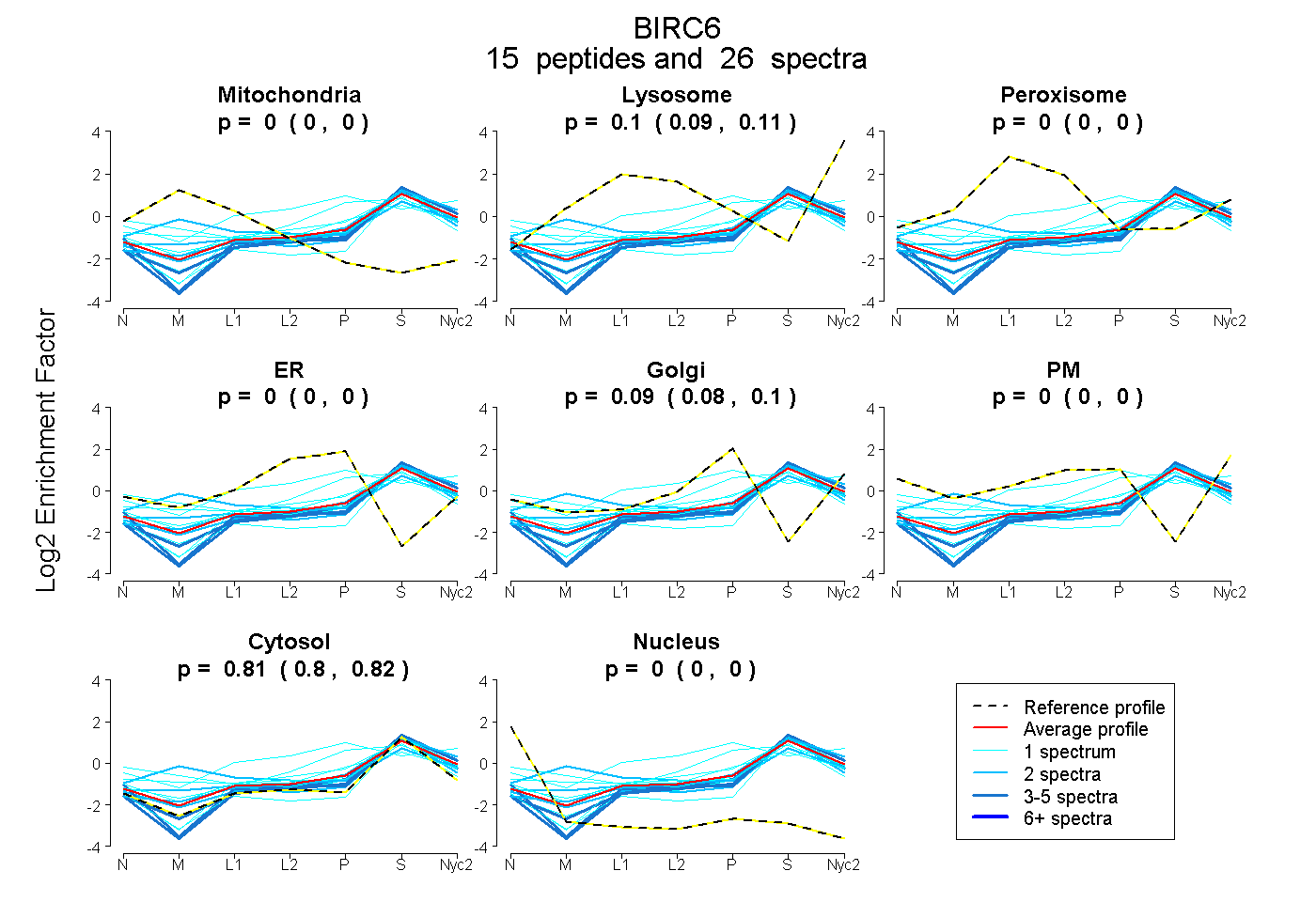
0.000 | 0.000
0.092 | 0.109
0.000 | 0.000
0.000 | 0.000
0.079 | 0.100
0.000 | 0.000
0.799 | 0.816
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
26 spectra |
 |
0.000 0.000 | 0.000 |
0.101 0.092 | 0.109 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.091 0.079 | 0.100 |
0.000 0.000 | 0.000 |
0.808 0.799 | 0.816 |
0.000 0.000 | 0.000 |
| 1 spectrum, IQALLK | 0.000 | 0.066 | 0.000 | 0.037 | 0.274 | 0.000 | 0.623 | 0.000 | ||
| 2 spectra, AVCGEMTR | 0.000 | 0.030 | 0.000 | 0.000 | 0.111 | 0.000 | 0.858 | 0.000 | ||
| 1 spectrum, TLPVLLLYSIK | 0.000 | 0.063 | 0.000 | 0.000 | 0.035 | 0.000 | 0.902 | 0.000 | ||
| 1 spectrum, VLDLSNFEILAK | 0.108 | 0.000 | 0.107 | 0.000 | 0.049 | 0.042 | 0.695 | 0.000 | ||
| 3 spectra, LIDILLR | 0.000 | 0.083 | 0.000 | 0.000 | 0.000 | 0.000 | 0.917 | 0.000 | ||
| 1 spectrum, IVTLEEEPVK | 0.000 | 0.006 | 0.000 | 0.000 | 0.000 | 0.000 | 0.994 | 0.000 | ||
| 2 spectra, TSIGWLR | 0.000 | 0.170 | 0.000 | 0.000 | 0.000 | 0.000 | 0.830 | 0.000 | ||
| 1 spectrum, DLNGILLLDTALQTPVSK | 0.000 | 0.126 | 0.196 | 0.000 | 0.339 | 0.000 | 0.339 | 0.000 | ||
| 2 spectra, ESPEIEPLPFTLAHDR | 0.223 | 0.201 | 0.000 | 0.000 | 0.000 | 0.000 | 0.576 | 0.000 | ||
| 3 spectra, LTPLEALLQTR | 0.000 | 0.026 | 0.000 | 0.000 | 0.000 | 0.000 | 0.973 | 0.000 | ||
| 2 spectra, GSLPTSGNISGFVR | 0.070 | 0.112 | 0.000 | 0.000 | 0.000 | 0.000 | 0.818 | 0.000 | ||
| 1 spectrum, TLHLPVSTTLSDVLDR | 0.110 | 0.000 | 0.000 | 0.000 | 0.034 | 0.266 | 0.590 | 0.000 | ||
| 1 spectrum, IGLQSTR | 0.000 | 0.161 | 0.000 | 0.000 | 0.108 | 0.005 | 0.725 | 0.000 | ||
| 4 spectra, AVSSTPPRPPSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.071 | 0.000 | 0.929 | 0.000 | ||
| 1 spectrum, DQLMFDLLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.050 | 0.000 | 0.950 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
13 spectra |
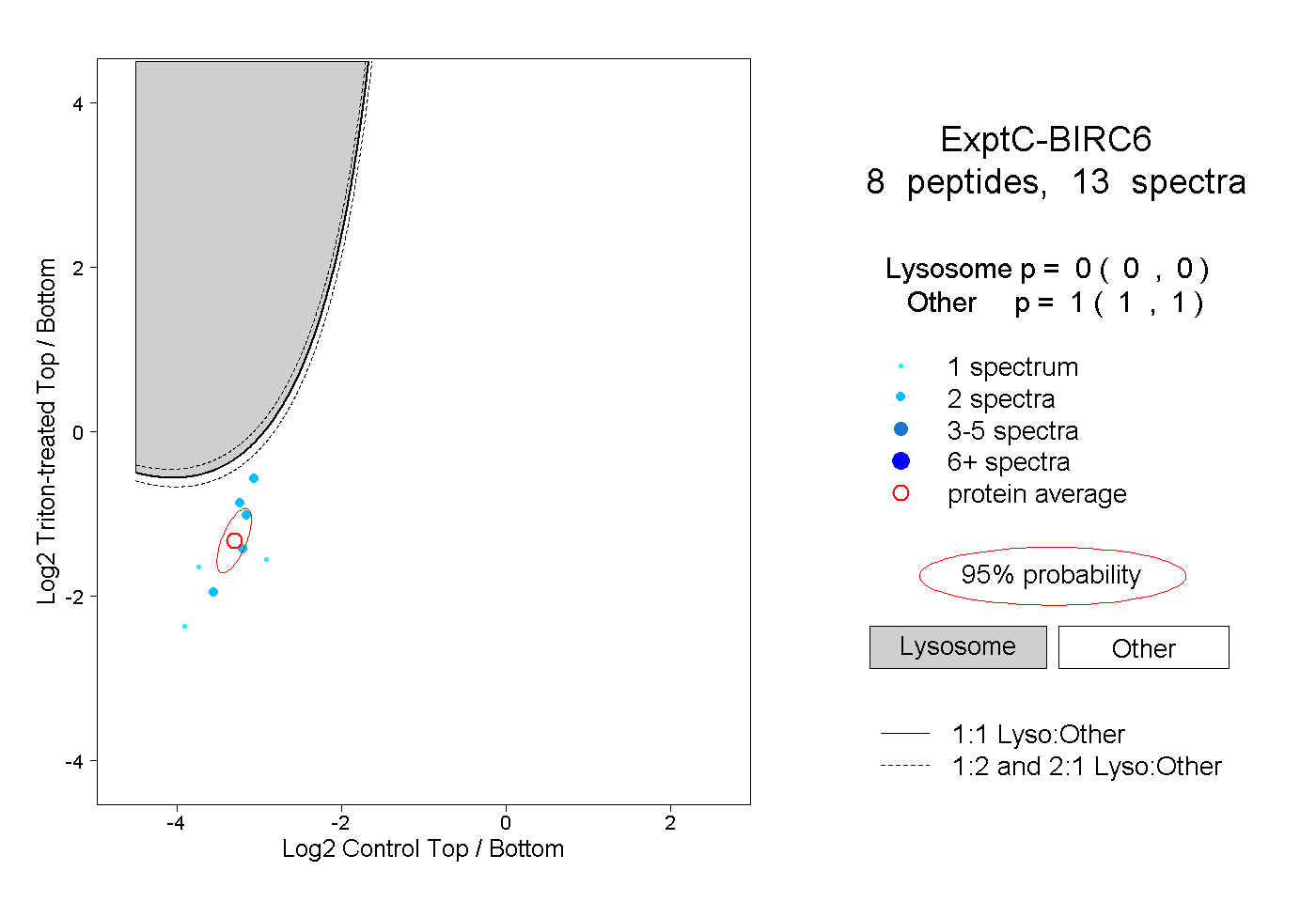 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |