peptides
spectra
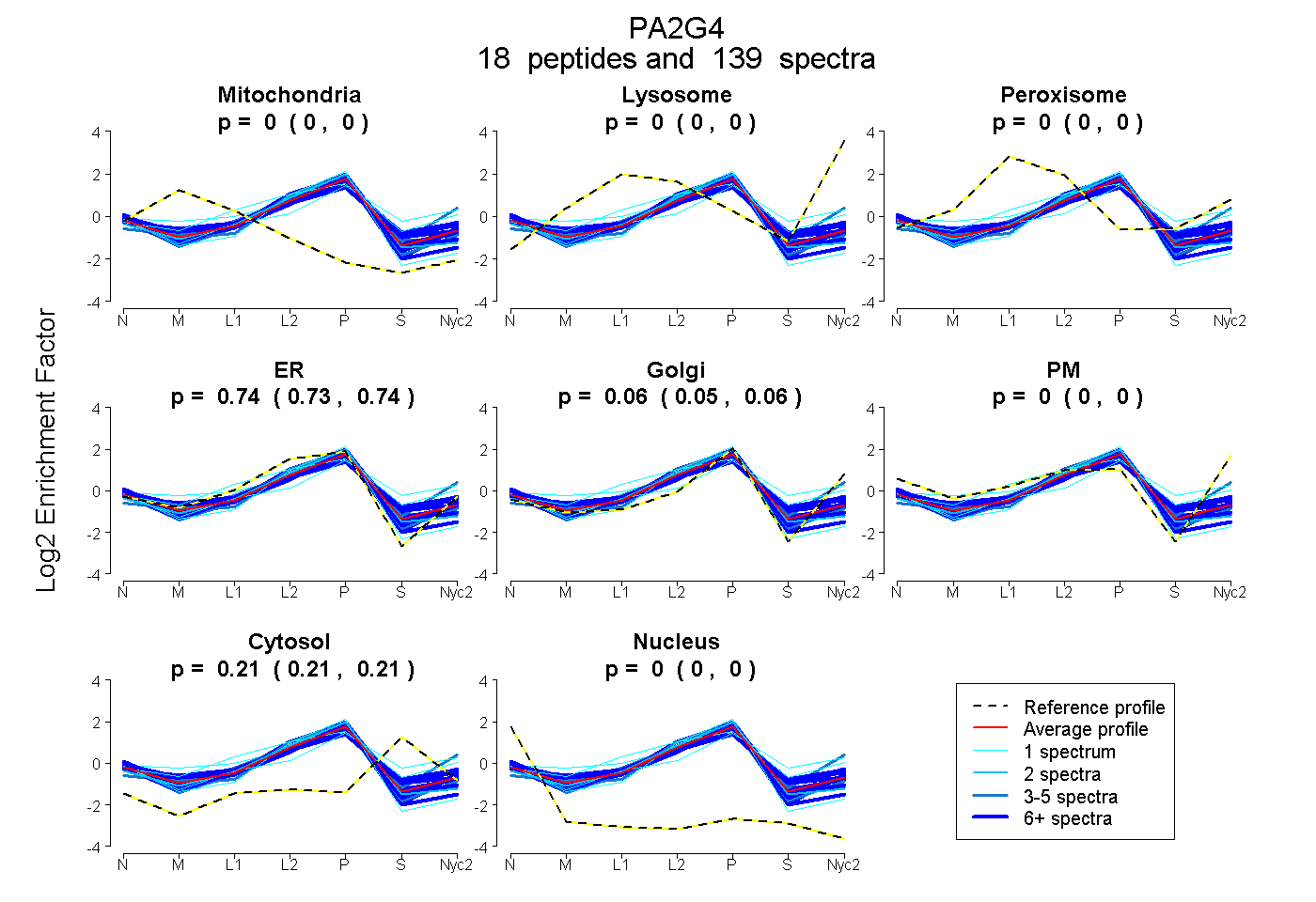
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.730 | 0.740
0.049 | 0.062
0.000 | 0.000
0.205 | 0.210
0.000 | 0.001
peptides
spectra
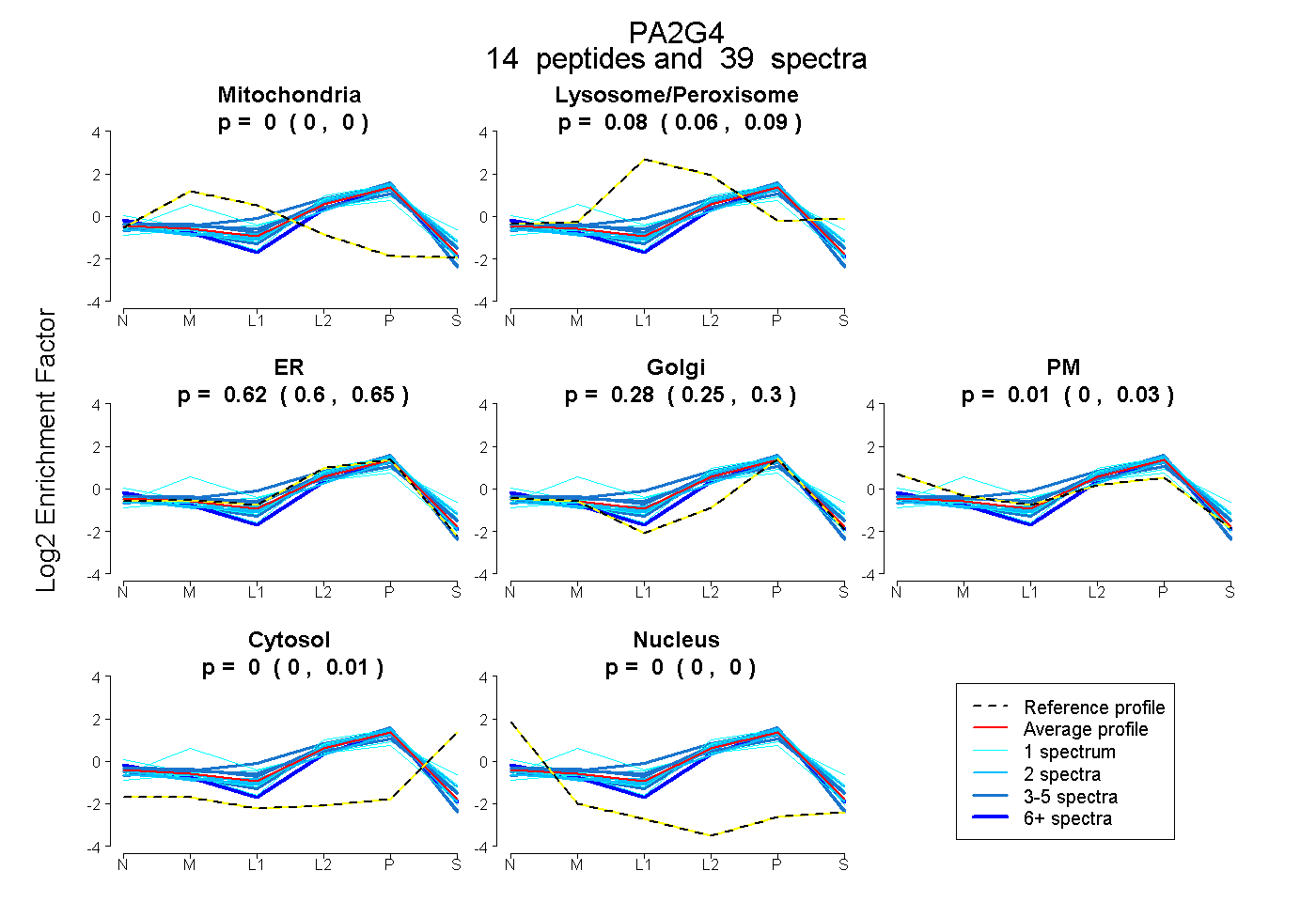
0.000 | 0.000
0.060 | 0.090
0.597 | 0.648
0.255 | 0.304
0.000 | 0.025
0.000 | 0.012
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
139 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.736 0.730 | 0.740 |
0.056 0.049 | 0.062 |
0.000 0.000 | 0.000 |
0.208 0.205 | 0.210 |
0.000 0.000 | 0.001 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
39 spectra |
 |
0.000 0.000 | 0.000 |
0.077 0.060 | 0.090 |
0.624 0.597 | 0.648 |
0.284 0.255 | 0.304 |
0.010 0.000 | 0.025 |
0.005 0.000 | 0.012 |
0.000 0.000 | 0.000 |
| 1 spectrum, FDAMPFTLR | 0.000 | 0.000 | 0.807 | 0.101 | 0.000 | 0.092 | 0.000 | |||
| 2 spectra, TTIYK | 0.000 | 0.005 | 0.805 | 0.168 | 0.000 | 0.022 | 0.000 | |||
| 1 spectrum, GDAMIMEETGK | 0.000 | 0.333 | 0.000 | 0.427 | 0.192 | 0.048 | 0.000 | |||
| 4 spectra, AFFSEVER | 0.000 | 0.000 | 0.754 | 0.246 | 0.000 | 0.000 | 0.000 | |||
| 12 spectra, ALLQSSASR | 0.000 | 0.000 | 0.452 | 0.459 | 0.089 | 0.000 | 0.000 | |||
| 1 spectrum, MGGDIANR | 0.000 | 0.027 | 0.779 | 0.068 | 0.000 | 0.125 | 0.000 | |||
| 2 spectra, SEMEVQDAELK | 0.000 | 0.155 | 0.401 | 0.370 | 0.000 | 0.075 | 0.000 | |||
| 4 spectra, HELLQPFNVLYEK | 0.000 | 0.173 | 0.472 | 0.311 | 0.044 | 0.000 | 0.000 | |||
| 3 spectra, AAHLCAEAALR | 0.010 | 0.085 | 0.905 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, EGEFVAQFK | 0.000 | 0.000 | 0.878 | 0.122 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, ITSGPFEPDLYK | 0.000 | 0.231 | 0.331 | 0.425 | 0.013 | 0.000 | 0.000 | |||
| 2 spectra, AFEDEK | 0.000 | 0.021 | 0.738 | 0.168 | 0.000 | 0.073 | 0.000 | |||
| 1 spectrum, FTVLLMPNGPMR | 0.297 | 0.000 | 0.665 | 0.038 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, TIIQNPTDQQK | 0.000 | 0.047 | 0.669 | 0.254 | 0.030 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
119 spectra |
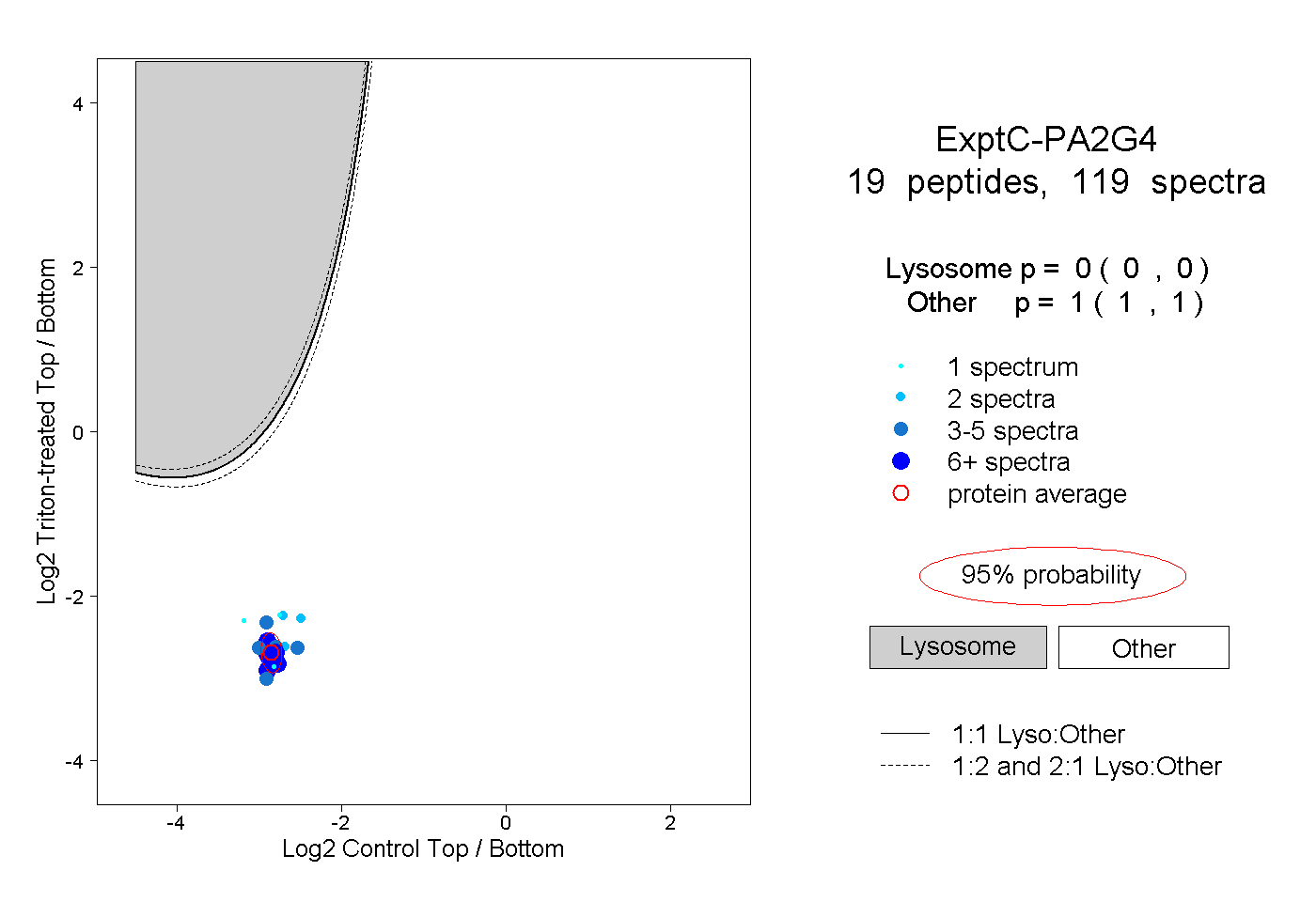 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
31 spectra |
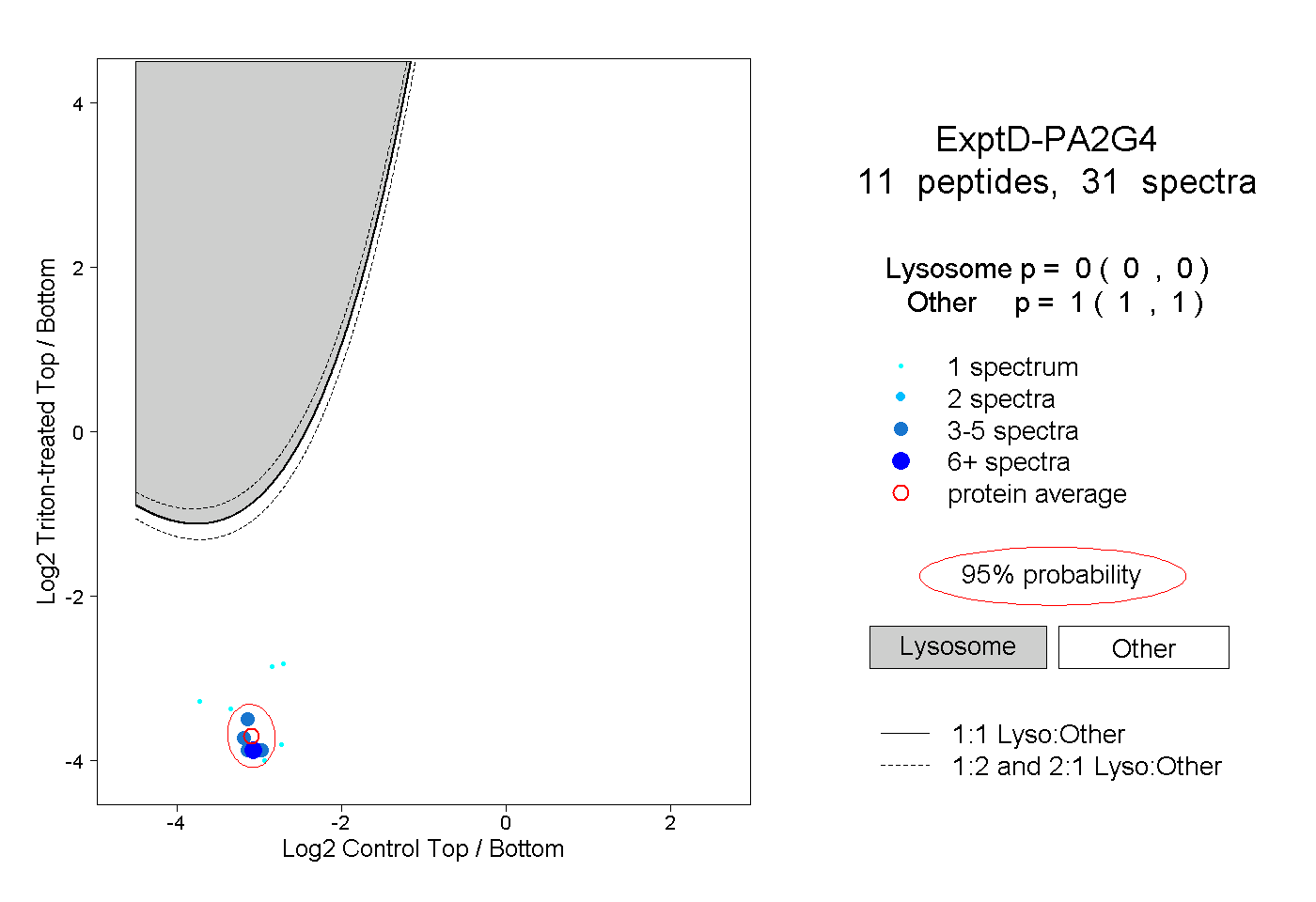 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |