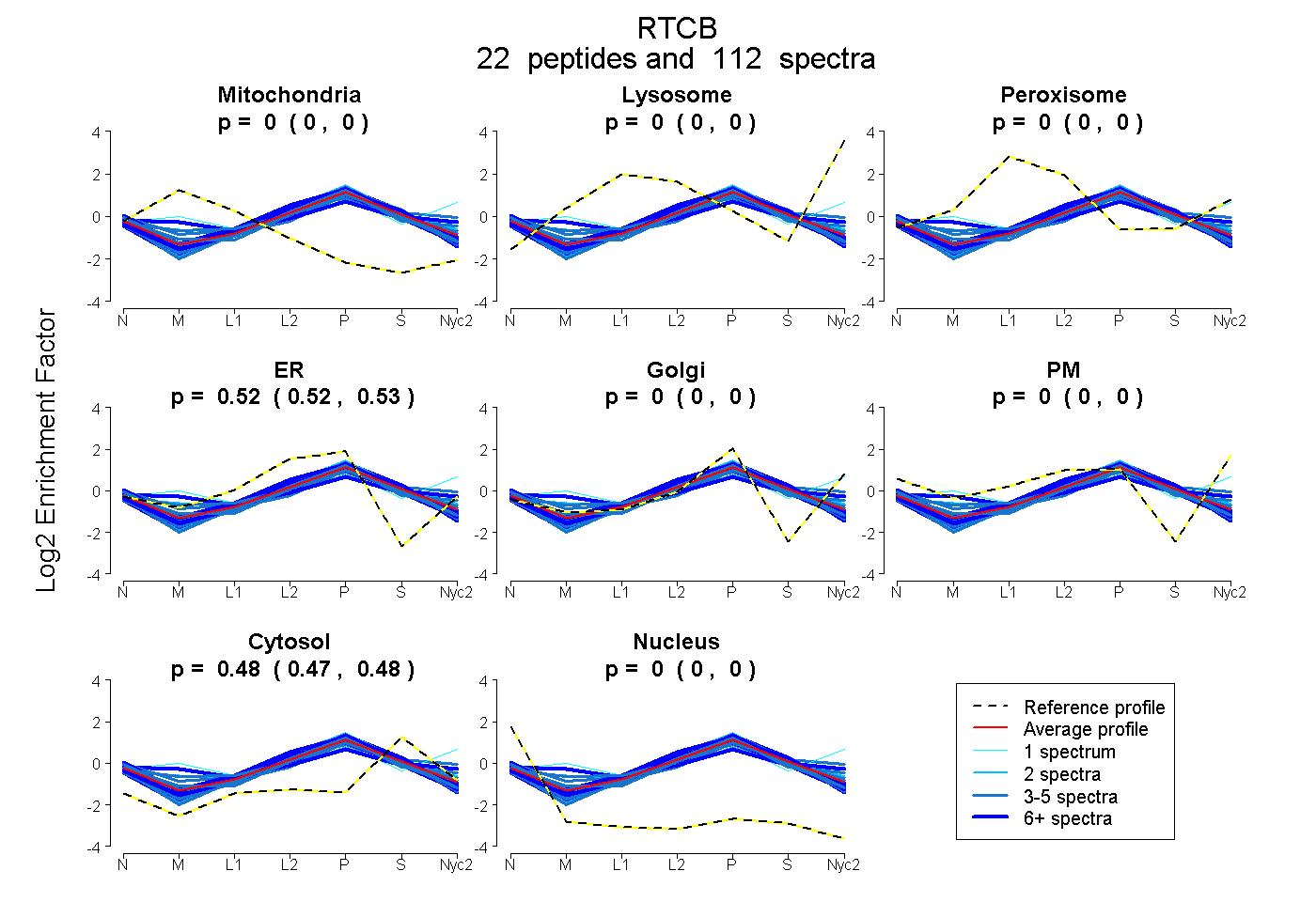
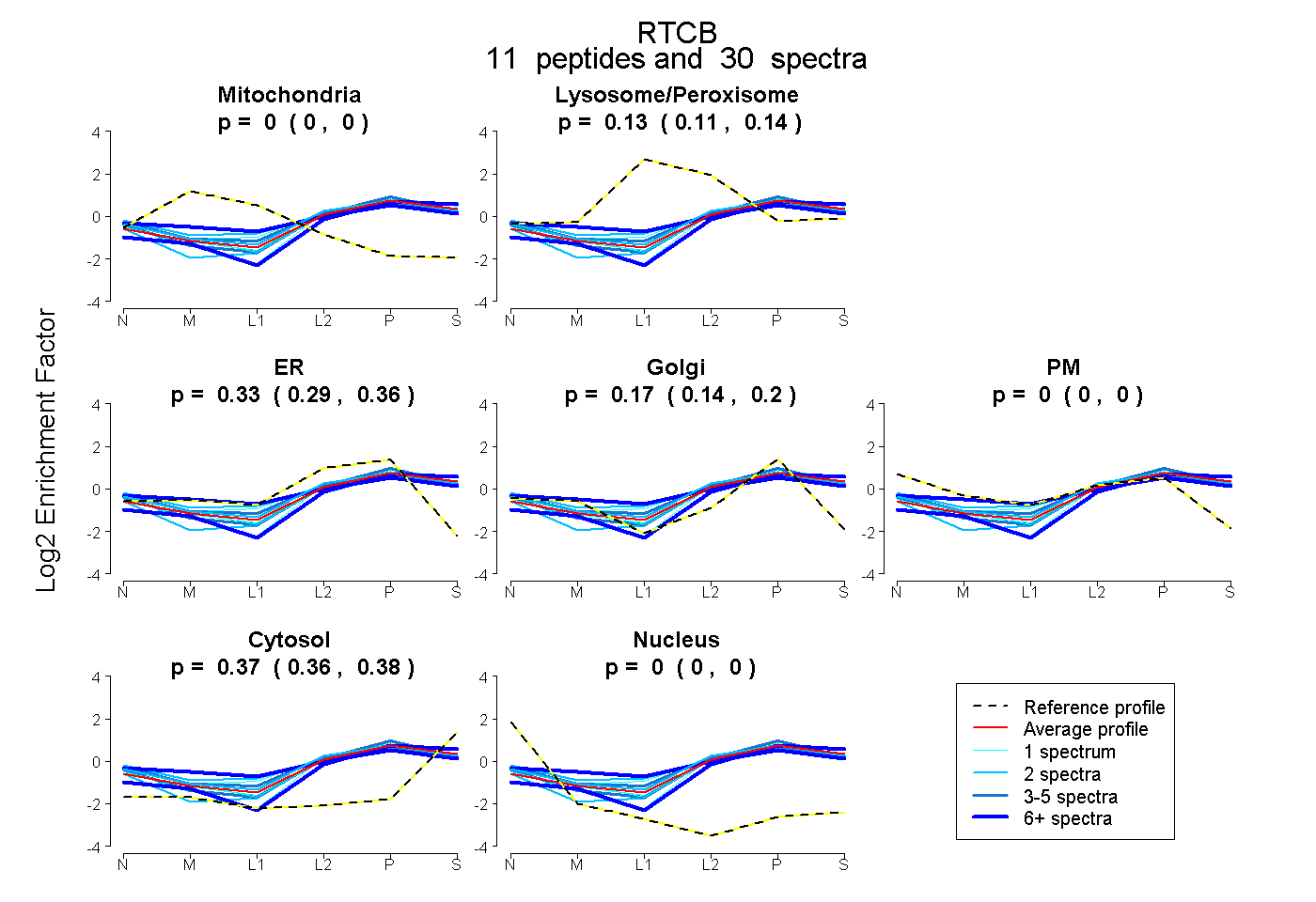
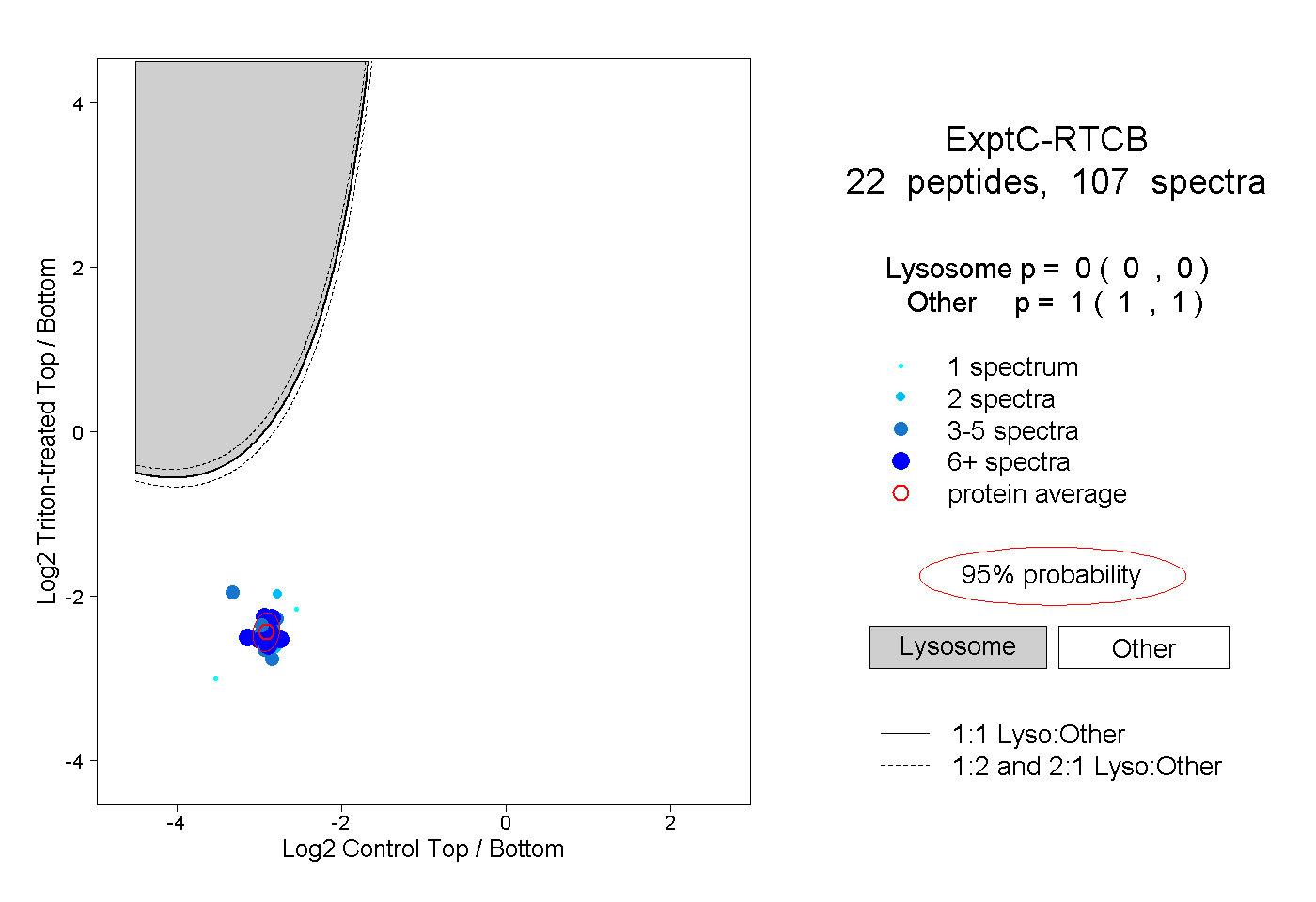
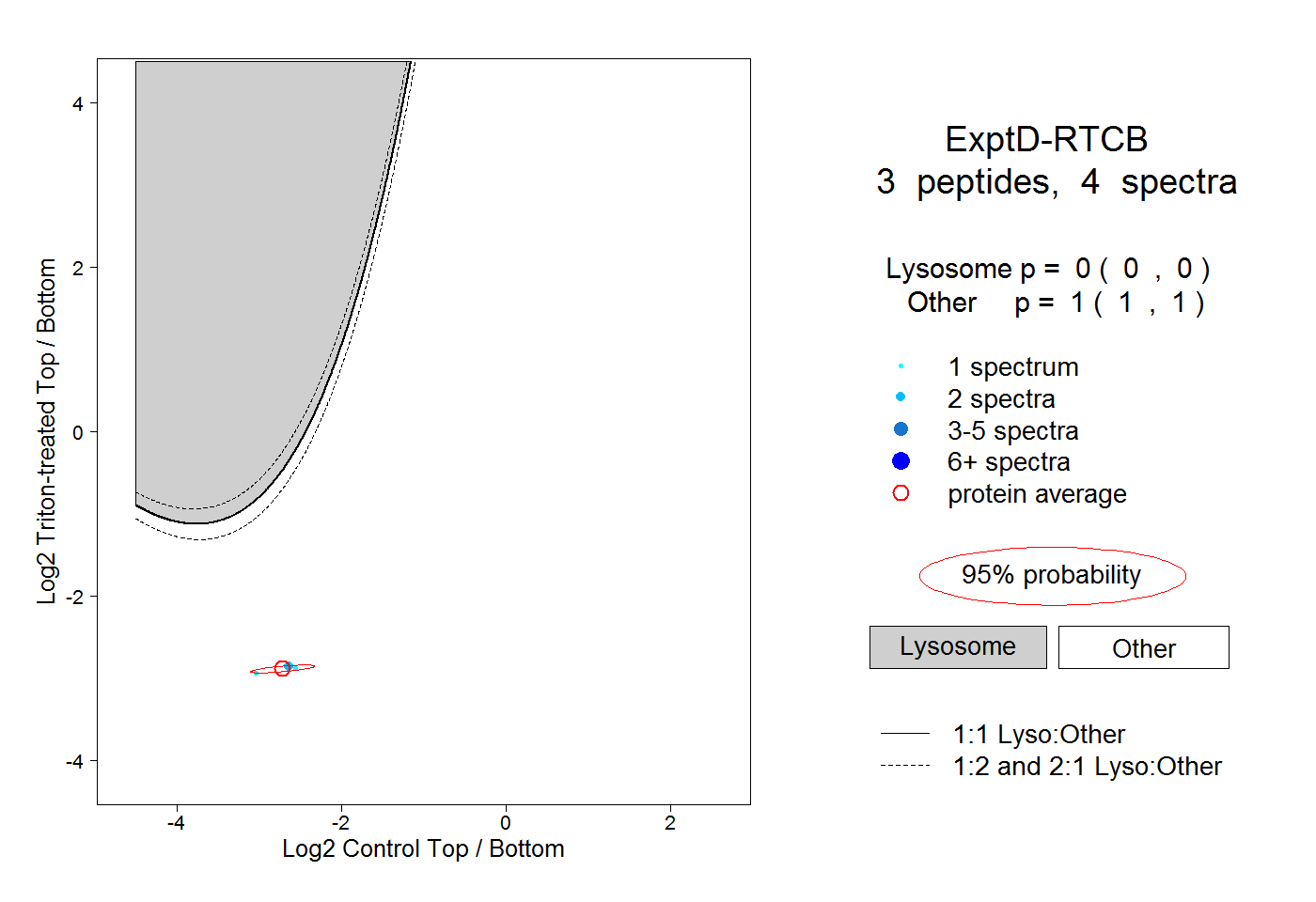
| 4 spectra, VFNTTPDDLDLHVIYDVSHNIAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, IASPEGQDYLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, GMAAAGNYAWVNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, LRPIAVIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, NLDFQDVLDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, SSMTFLTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, NVTDVVNTCHDAGISK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QLACAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GQVCVMIHSGSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QIGNVAALPGIVHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, LVMEEAPESYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, GGGVGGFLPAMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, TLLVHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, VEQHVVDGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LMFEELR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EQLAQAMFDHIPVGVGSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, IIVNDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, MLQADPNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, MGIDHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, GVIPMNAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, GLGHQVATDALVAMEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, LGDMGIAIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |